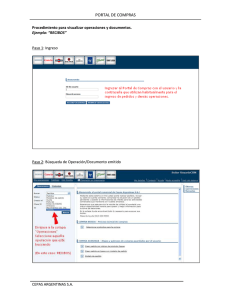
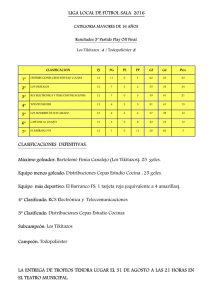
EVALUACIÓN DE LA SEGURIDAD IN VITRO DE CEPAS DE
Anuncio

UNIVERSIDAD COMPLUTENSE DE MADRID FACULTAD DE VETERINARIA MÁSTER: INVESTIGACIÓN EN CIENCIAS VETERINARIAS Trabajo de Investigación EVALUACIÓN DE LA SEGURIDAD IN VITRO DE CEPAS DE Lactococcus lactis AISLADAS DE TRUCHA ARCOÍRIS (Oncorhynchus mykiss) Y SU AMBIENTE ACUÍCOLA PARA SU APLICACIÓN COMO PROBIÓTICOS EN LA ACUICULTURA Martha Isabel Ramírez Peinado TUTOR: Luis M. Cintas Izarra CO-TUTOR: Carmen Herranz Sorribes Madrid, junio de 2013 UNIVERSIDAD COMPLUTENSE DE MADRID FACULTAD DE VETERINARIA DEPARTAMENTO DE NUTRICIÓN, BROMATOLOGÍA Y TECNOLOGÍA DE LOS ALIMENTOS EVALUACIÓN DE LA SEGURIDAD IN VITRO DE CEPAS DE Lactococcus lactis AISLADAS DE TRUCHA ARCOÍRIS (Oncorhynchus mykiss) Y SU AMBIENTE ACUÍCOLA PARA SU APLICACIÓN COMO PROBIÓTICOS EN LA ACUICULTURA Memoria que, para optar al título de Máster Universitario de Investigación en Ciencias Veterinarias, del Programa Oficial de Posgrado “Ciencias Veterinarias”, presenta la Licenciada Martha Isabel Ramírez peinado Madrid, junio de 2013 DEPARTAMENTO DE NUTRICIÓN, BROMATOLOGÍA Y TECNOLOGÍA DE LOS ALIMENTOS FACULTAD DE VETERINARIA Ciudad Universitaria, s/n. 28040 Madrid Teléfono: 91 394 3751. Fax: 91 394 37 43 LUIS M. CINTAS IZARRA, PROFESOR CONTRATADO DOCTOR DE NUTRICIÓN Y BROMATOLOGÍA DEL DEPARTAMENTO DE NUTRICIÓN, BROMATOLOGÍA Y TECNOLOGÍA DE LOS ALIMENTOS DE LA FACULTAD DE VETERINARIA DE LA UNIVERSIDAD COMPLUTENSE DE MADRID, CERTIFICA Que el trabajo de Fin de Máster titulado “Evaluación de la seguridad in vitro de cepas de lactococcus lactis aisladas de trucha arcoíris (oncorhynchus mykiss) y su ambiente acuícola para su aplicación como probióticos en la acuicultura”, del que es autora la Licenciada en Veterinaria Dña Martha Isabel Ramírez Peinado, ha sido realizado bajo su dirección en el Departamento de Nutrición, Bromatología y Tecnología de los Alimentos de la Facultad de Veterinaria de la Universidad Complutense de Madrid y cumple con las condiciones exigidas para optar al título de Máster Universitario de Investigación en Ciencias Veterinarias, del Programa Oficial de Posgrado “Ciencias Veterinarias”. Madrid, Junio de 2013 Luis M. Cintas Izarra ÍNDICE……………………………………………………………………………………….....1 RESUMEN/ABSTRACT.............................................................................................................4 I. JUSTIFICACIÓN Y OBJETIVOS DEL TRABAJO DE INVESTIGACIÓN…………6 II. MATERIAL Y MÉTODOS……………………………………………………………….16 II.1 EVALUACIÓN FENOTÍPICA DE LA PRESENCIA DE FACTORES DE VIRULENCIA DE LAS CEPAS DE Lactococcus lactis AISLADAS DE LA TRUCHA ARCOIRIS Y SU AMBIENTE ACUÍCOLA……………………………………………16 II.1.1 EVALUACIÓN DE LA ACTIVIDAD HEMOLÍTICA……………………..16 II.1.2 EVALUACIÓN DE LA ACTIVIDAD PROTEOLÍTICA…………………..16 II.1.3 EVALUACION DE LA ACTIVIDAD MUCINOLÍTICA……………..……18 II.2. EVALUACIÓN FENOTÍPICA Y GENOTÍTPICA DE LA SENSIBILIDAD/RESISTENCIA DE Lactococcus lactis A LOS PRINCIPALES ANTIBIÓTICOS EMPLEADOS EN ACUICULTURA, MEDICINA HUMANA Y VETERINARIA…………………………………………………………………………...18 II.2.1.DETERMINACIÓN MEDIANTE EL MÉTODO DE MICRODILUCIÓN EN PLACA DE LAS CONCENTRACIONES MÍNIMAS INHIBIDORAS (CMI) DE LOS ANTIBIÓTICOS……………………………………………………………18 II.2.2.DETECCIÓN MEDIANTE LA REACCIÓN EN CADENA DE LA POLIMERASA (PCR) DE GENES DE RESISTENCIA A ANTIBIÓTICOS………………………………………………………………………19 II.3. EVALUACIÓN FENOTÍPICA DE DIVERSAS ACTIVIDADES ENZIMATICAS PERJUDICIALES EN LAS CEPAS DE Lactococcus lactis…………………………...20 II.3.1.EVALUACIÓN DE LA DESCONJUGACIÓN DE LAS SALES BILIARES…………………………………………………………………………….20 3 Beneficiario COLFUTURO 2011 II.3.2.EVALUACIÓN DE LA PRODUCCIÓN DE AMINAS BIÓGENAS…………………………………………………………………………...22 II.3.2.1.Detección de la producción de aminas biógenas en medios de cultivo diferenciales………………………………………………………………………..22 II.3.2.2.Determinación mediante PCR de la presencia de los genes involucrados en la síntesis de aminas biógenas…………………………………………………23 II.3.2.2.1. Detección de la presencia del gen que codifica la histidina descarboxilasa (HDC)…………………………………………………………..23 II.3.2.2.2. Detección de la presencia del gen que codifica la tirosina descarboxilasa (TDC)…………………………………………………………..24 II.3.2.2.3. Detección de la presencia del gen que codifica la ornitina descarboxilasa (ODC)…………………………………………………………..24 II.3.2.2.4. Detección de la presencia del gen que codifica la lisina descarboxilasa (LDC)…………………………………………………………...24 III. RESULTADOS Y DISCUSIÓN…………………………………………………………..25 III.1. EVALUACIÓN FENOTÍPICA DE LA PRESENCIA DE FACTORES DE VIRULENCIA EN LAS CEPAS DE L. lactis AISLADAS DE TRUCHA ARCOÍRIS Y SU AMBIENTE ACUÍCOLA…………………………………………………………….26 III.1.1. EVALUACIÓN DE LA ACTIVIDAD HEMOLÍTICA………………...26 III.1.2. EVALUACIÓN DE LA ACTIVIDAD PROTEOLÍTICA……………...27 III.1.3. EVALUACIÓN DE LA ACTIVIDAD MUCINOLÍTICA……………...28 III.2. EVALUACIÓN FENOTÍPICA Y GENOTÍPICA DE LA SENSIBILIDAD/ RESISTENCIA DE L. lactis A LOS PRINCIPALES ANTIBIÓTICOS EMPLEADOS EN ACUICULTURA Y MEDICINA HUMANA Y VETERINARIA……………………………………………………………………….………………...29 III.2.1.DETERMINACIÓN MEDIANTE EL MÉTODO DE MICRODILUCIÓN EN PLACA DE LAS CMI DE LOS ANTIBIÓTICOS……………………………...29 4 Beneficiario COLFUTURO 2011 III.2.2.DETECCIÓN MEDIANTE PCR DE GENES DE RESISTENCIA A ANTIBIÓTICOS………………………………………………………………………33 III.3.EVALUACIÓN FENOTÍPICA DE DIVERSAS ACTIVIDADES ENZIMATICAS PERJUDICIALES EN LAS CEPAS DE Lactococcus lactis………38 III.3.1.EVALUACIÓN DE LA DESCONJUGACIÓN DE SALES BILIARES…………………………………………………………………………38 III.3.2.EVALUACIÓN DE LA PRODUCCIÓN DE AMINAS BIÓGENAS………………………………………………………………………...40 III.4. SELECCIÓN DE LAS CEPAS DE Lactococcus lactis AISLADAS DE TRUCHA ARCOIRIS Y DE SU AMBIENTE ACUICOLA POTENCIALMENTE SEGURAS PARA SU POSTERIOR CARACTERIZACIÓN COMO PROBIÓTICOS PARA EL DESARROLLO DE UNA ACUICULTURA SOSTENIBLE…………………………………………………………………………...43 IV. CONCLUSIONES…………………………………………………………………………45 V. BIBLIOGRAFÍA…………………………………………………………………………..47 VI. APÉNDICES………………………………………………………………………………61 VI.1 LISTADO DE TABLAS…………………..…………………………………...61 VI.2 LISTADO DE FIGURAS………………………..…………………………….62 5 Beneficiario COLFUTURO 2011 RESUMEN La prevención y el control de las enfermedades de los peces, especialmente las de etiología bacteriana que se producen durante las etapas larvaria y de alevinaje, representan uno de los principales retos para la moderna acuicultura. Tradicionalmente se han utilizado antibióticos como agentes terapéuticos, muchas veces de forma indiscriminada; sin embargo, cada vez existe una mayor reticencia a su empleo por sus posibles efectos perjudiciales para la salud animal y humana, la seguridad alimentaria y el medio ambiente, entre los que destaca la aparición y transferencia de (multi)resistencias a antibióticos, lo que conlleva un aumento del riesgo de epizootías. Aunque la vacunación constituye, en principio, el método ideal de control de las ictiopatologías, su aplicación está dificultada por factores como su disponibilidad, efectividad, grado de protección, estrés animal, coste económico y la problemática de su aplicación en las etapas larvarias. En consecuencia, cada vez es mayor el interés por la investigación y desarrollo de metodologías alternativas o complementarias a la quimioterapia y la vacunación que resulten eficaces, seguras, respetuosas con el medio ambiente, de aplicación sencilla y rentable económicamente. En este contexto, este trabajo se enmarca en una línea de investigación que propone, como estrategia para una acuicultura sostenible, el empleo de bacterias lácticas productoras de bacteriocinas (bacteriocinogénicas) de origen acuático como probióticos para el biocontrol de las ictiopatologías. A este respecto, el objetivo de este trabajo de investigación fue la evaluación de la seguridad in vitro de una colección de 75 cepas de Lactococcus lactis aisladas de trucha arcoíris (Oncorhynchus mykiss) y su ambiente acuícola, durante todo su ciclo biológico, y seleccionadas por su actividad antimicrobiana frente a Lactococcus garvieae y otros ictiopatógenos de relevancia para la acuicultura. Para ello, se empleó un protocolo más exhaustivo que el propuesto por la EFSA para evaluar la seguridad de las cepas de la especie L. lactis, que goza del estatus QPS (Qualified Presumption of Safety), que incluye: (i) evaluación fenotípica de la presencia de factores de virulencia (actividad hemolítica, proteolítica y mucinolítica); (ii) evaluación fenotípica y genotípica de la susceptibilidad a antibióticos empleados en acuicultura y medicina humana y veterinaria, y (iii) evaluación fenotípica y/o genotípica de actividades enzimáticas perjudiciales (desconjugación de sales biliares y producción de aminas biógenas). Los resultados obtenidos demuestran la utilidad del protocolo propuesto en este trabajo, ya que ha permitido establecer que, a pesar del estatus QPS de L. lactis, de las 75 cepas de origen acuático de esta especie evaluadas, 60 cepas (80%) deben excluirse como probióticos potenciales para la acuicultura ya que no son seguras para el hombre, los peces y/o el medio ambiente. Palabras clave: acuicultura, probióticos, Lactococcus lactis, seguridad in vitro 6 Beneficiario COLFUTURO 2011 ABSTRACT Prevention and control of fish pathologies, mainly those arising during the larval and alevine stages, represents one of the main challenges for the modern aquaculture industry. Traditionally, antibiotics have been thoroughly used as therapeutic compounds, very often indiscriminately; however, there is an overgrowing reticence for their use, due to their harmful effects for the human and animal health, the food safety and the environment, including the generation and transference of antibiotic bacterial (multi)resistances, which lead to an increased risk of epizooties. Although vaccination constitutes, in principle, the ideal control method, its application may be hampered by several factors such as availability, effectiveness, level of protection, animal stress, economic cost and problems associated to their application at the larval stages, because of the immaturity of their immune system and the handling difficulties. Therefore, there is an increasing interest of research and develop of alternative or complementary strategies to chemotherapy and vaccination not only effective but also safe, environmentally friendly, easy to apply and economically efficient. In this respect, this work is framed in a research topic dealing with the use of probiotics as bacteriocin producers (bacteriocinogenic) Lactic Acid Bacteria of aquatic origin as a strategy for the biocontrol of the most relevant icthiopathologies in a sustainable aquaculture context. With regard to this, the aim of this research work was to evaluate the in vitro safety of a collection of 75 Lactococcus lactis strains previously isolated from rainbow trout (Oncorhynchus mykiss) and their aquatic environment, during the whole fish lyfe-cycle, and selected for their antimicrobial activity against Lactococcus garvieae and other fish pathogens of relevance for the aquaculture. To achieve this goal, a more exhaustive procedure proposed by EFSA for the safety assessment of L. lactis strains, a species recognized with the QPS status (Qualified Presumpion of Safety), was carried out, including: (i) phenotypic evaluation of the presence of virulence factors (hemolytic, proteolytic and mucinolytic activities); (ii) phenotypic and genetic evaluation of bacterial susceptibility to several antibiotics used in aquaculture and human and veterinary medicine, and (iii) phenotypic and genetic evaluation of detrimental activities (deconjugation of bile salts and production of biogenic amines). The obtained results demonstrate the effectiveness of the safety assessment protocol used in this work, since, despite the QPS status of L. lactis, 60 out of the tested 75 L. lactis strains of aquatic origin (80%) should be excluded as potential probiotics for aquaculture since they are not safe for humans, fishes and/or the environment. Keywords: aquaculture, probiotics, Lactococcus lactis, in vitro safety 7 Beneficiario COLFUTURO 2011 I. JUSTIFICACIÓN Y OBJETIVOS DEL TRABAJO DE INVESTIGACIÓN La Unión Europea (UE) entiende la Acuicultura como la cría o cultivo de organismos acuáticos con técnicas encaminadas a aumentar su producción por encima de las capacidades naturales del medio. Debido a la sobreexplotación de los recursos pesqueros, la creciente demanda mundial de pescado es cubierta con dificultad por la pesca extractiva, por lo que la acuicultura se perfila como la única posibilidad de que pueda cubrirse esta demanda en un futuro próximo. A este respecto, según el informe de la FAO, Estado Mundial de la Pesca y la Acuicultura: 2012 (FAO, 2012), la acuicultura es una actividad con un alto potencial para satisfacer la creciente demanda de alimentos acuáticos, ya que es probablemente el sector productivo de más rápido ascenso, generando actualmente alrededor del 50% de la producción de pesca en el mundo. Sin embargo, para ello, la moderna acuicultura requiere disponer de metodologías eficaces y seguras que permitan incrementar la productividad animal y la calidad y seguridad de los productos que se comercializan, por lo que resulta de gran importancia la aplicación de nuevas tecnologías que, entre otros aspectos, permitan reducir el deterioro medioambiental del medio acuático y la incidencia de las enfermedades de los peces, principalmente las de etiología bacteriana que tienen lugar durante las etapas larvaria y de alevinaje, que suponen en la actualidad un importante lastre para el desarrollo de esta actividad que cada vez está adquiriendo una mayor relevancia en el sector productivo internacional. A este respecto, entre las ictiopatologías de etiología bacteriana que afectan a especies acuícolas marinas o continentales destacan las producidas por los siguientes grupos de microorganismos: (i) bacilos Gram-negativos aerobios y anaerobios facultativos, entre los que se incluyen Enterobacteriáceas como Yersinia spp. (Y. ruckeri), Vibrionáceas como Vibrio spp. (V. anguillarum, V. harvey y V. campbellii) y Photobacterium spp. (P. damselae), Aeromonadáceas como Aeromonas spp. (A. salmonicida y A. hydrophila) y Pseudomonadáceas como Pseudomonas spp. (P. fluorescens y P. anguilliseptica); (ii) cocos y bacilos Gram-positivos como Streptococcus spp., Lactococcus spp. y Renibacterium spp.; (iii) Micobacteriáceas y Nocardiáceas; y (iv) Flavobacterias (F. psychrophilum) (Padrós y Furones, 2002; Ghittino et al., 2003). Hasta hace unos años, las infecciones bacterianas en acuicultura eran debidas en su mayoría a microorganismos Gram-negativos y, en menor medida, a microorganismos Grampositivos, concretamente Renibacterium spp. y bacterias lácticas como Streptococcus spp.; sin embargo, en los últimos años se ha registrado un importante incremento de las infecciones debidas a patógenos oportunistas Gram-positivos, principalmente del género Lactococcus (L. 8 Beneficiario COLFUTURO 2011 garvieae), y, en la actualidad, estos microorganismos constituyen uno de los principales problemas para la acuicultura (Padrós y Furones, 2002; Vendrell et al., 2006). En este sentido, Renibacterium salmoninarum (R. salmoninarum) provoca la enfermedad bacteriana renal (BKD, del inglés Bacterial Kidney Disease), que afecta principalmente a salmónidos y cuyo diagnóstico y tratamiento resulta muy complicado (Wiens y Kaattari, 1999; Padrós y Furones, 2002; Ghittino et al., 2003). Por otra parte, los problemas originados por bacterias lácticas son debidos principalmente a las infecciones de la trucha por L. garvieae, Streptococcus iniae, Carnobacterium piscicola y Vagococcus salmoninarum, así como a las infecciones del rodaballo causadas por Streptococcus parauberis. Conviene destacar que en la actualidad las infecciones causadas por L. garvieae, denominadas lactococosis, son unas de las de mayor importancia para la acuicultura debido a las pérdidas que ocasionan en el cultivo de la trucha y otras especies acuícolas de agua dulce (Ghittino et al., 2003; Vendrell et al., 2006). En este sentido, aunque actualmente se están ensayando en campo diversas vacunas, el nivel y el periodo de protección que confieren son limitados (Padrós y Furones, 2002). Tradicionalmente se han empleado antibióticos como agentes terapéuticos y, en algunos casos, en los tratamientos profilácticos de las ictiopatologías citadas anteriormente; no obstante, cada vez existe una mayor reticencia a su empleo, no sólo por parte de las agencias sanitarias sino también por las propias piscifactorías y los consumidores, debido a los efectos perjudiciales derivados de su uso indiscriminado, entre los que destacan la aparición y la transferencia de resistencias microbianas, lo que conlleva un alto riesgo de incremento del número de epizootías causadas por microorganismos resistentes a estos compuestos antimicrobianos. Entre sus posibles repercusiones también se incluyen las alteraciones de las relaciones ecológicas entre bacterias, humanos, animales y su medio ambiente, las reacciones adversas de los residuos de antibióticos en los manipuladores de los alimentos, los efectos toxicológicos y tecnológicos derivados de la presencia de residuos de antibióticos en los alimentos y la contaminación medioambiental (Angulo, 2000; Defoirdt et al., 2007). En este sentido, la creciente preocupación por el empleo de antibióticos en acuicultura ha llevado a su prohibición como promotores de crecimiento en la UE y al desarrollo de regulaciones cada vez más restrictivas no sólo en la UE sino también en EE.UU., Canadá y otros países industrializados (Gatlin et al., 2007). Por lo tanto, cada vez es mayor el interés por la investigación y el desarrollo de metodologías alternativas, que no sólo resulten eficaces para el control de las ictiopatologías 9 Beneficiario COLFUTURO 2011 sino que, además, sean seguras, respetuosas con el medio ambiente y cuya aplicación resulte sencilla y rentable económicamente. En este contexto, está adquiriendo una creciente relevancia el empleo de probióticos/prebióticos, vacuna e inmunoestimulantes (e.g., ácidos orgánicos, extractos de plantas y cofactores) como sustitutos de la quimioterapia para el biocontrol de microorganismos patógenos (Gatesoupe, 1999; Verschuere et al., 2000; Irianto y Austin, 2002; Balcázar et al., 2006; Farzanfar, 2006; Gatlin et al., 2007). En lo que respecta a los probióticos, Fuller los definió en 1989 como “microorganismos vivos que en forma de suplementos alimentarios afectan beneficiosamente al hospedador animal mediante una mejora de su equilibrio intestinal” (Fuller, 1989). En una definición más amplia, los probióticos para la acuicultura se consideran como cultivos microbianos vivos que ejercen un efecto beneficioso en el hospedador mediante: (i) la modificación de su microbiota y/o la de su medio ambiente; (ii) el incremento de la eficiencia en la asimilación del alimento y/o de su valor nutritivo; (iii) la mejora de la respuesta del hospedador a las enfermedades; y/o (iv) el incremento de la calidad del medio ambiente acuático en el que se desarrolla el hospedador. Con base en esta definición, los probióticos pueden incluir cultivos microbianos que: (i) previenen la proliferación de microorganismos patógenos en el tracto intestinal de los animales acuáticos, en las superficies de las piscifactorías y en el ambiente de cultivo; (ii) aseguran un aprovechamiento óptimo del alimento mediante su ayuda a la digestión (estimulación del crecimiento); (iii) mejoran la calidad del agua; y/o (iv) estimulan el sistema inmune del hospedador (Verschuere et al., 2000). La primera aplicación de los probióticos en acuicultura se remonta a mediados de la década de los 80 del pasado siglo, no habiendo cesado desde entonces el creciente interés por su empleo (Chabrillón et al., 2007). Históricamente, los probióticos se han asociado a la ganadería y la medicina humana, limitándose su empleo a bacterias Gram-positivas, concretamente bacterias lácticas (principalmente Lactobacillus spp. y Streptococcus spp.) y Bifidobacterium spp.; sin embargo, desde hace unos años se ha propuesto la utilización en acuicultura de cultivos probióticos de bacterias Gram-positivas y Gram-negativas, bacteriófagos, levaduras y algas unicelulares (Verschuere et al., 2000; Irianto y Austin, 2002). En este contexto, la mayoría de los probióticos propuestos para su empleo en acuicultura pertenecen al grupo de las bacterias lácticas (principalmente Lactobacillus spp., Carnobacterium spp., Enterococcus spp., Lactococcus spp., Pediococcus spp. y, en menor medida, Streptococcus thermophilus) y a los géneros Bifidobacterium, Bacillus, Vibrio y Pseudomonas (Austin et al., 1995; Robertson et al., 2000; Verschuere et al., 2000; Chabrillón et al., 2007; Dimitroglou et al., 2010; Nayak, 2010; Ringø et al., 2010).A este respecto, aunque las bacterias lácticas no constituyen la microbiota 10 Beneficiario COLFUTURO 2011 intestinal predominante de los peces, que está representada por los géneros Photobacterium, Pseudomonas y Vibrio (peces marinos) y Aeromonas, Plesiomonas, Enterobacteriaceae, Bacteroides, Fusobacterium y Eubacterium (peces de agua dulce), algunos géneros de este grupo, principalmente Lactococcus, Lactobacillus, Pediococcus, Streptococcus, Enterococcus y, en menor medida, Vagococcus, Carnobacterium, Leuconostoc, Aerococcus y Weisella, forman parte de la microbiota intestinal de muchos peces cultivados, especialmente de los de agua dulce (Ringø y Gatesoupe, 1998; Ringø y Holzapfel, 2000; Ringø et al., 2000; Irianto y Austin, 2002; Austin, 2006; Campos et al., 2006; Gatesoupe, 2008; Desriac et al., 2010; Mansfield et al., 2010; Ringø et al., 2010), lo que avala su empleo como probióticos para la acuicultura (Verschuere et al., 2000; Chabrillón et al., 2007; Gatesoupe, 2008; Merrifield et al., 2010). En este contexto, numerosos estudios ponen de manifiesto la eficacia in vitro e in vivo de la aplicación de bacterias lácticas como probióticos en la acuicultura de peces y, aunque en menor medida, crustáceos y moluscos (Balcázar et al., 2006a, b; Farzanfar, 2006; Verschere et al., 2000; Vine et al., 2006; Gatesoupe, 2008; Ninawe y Selvin, 2009; Merrifield et al., 2010; Prado et al., 2010; Dimitroglou et al., 2011). En lo que respecta a la acuicultura continental y marina de peces, la mayoría de los estudios realizados hasta la fecha hacen referencia al empleo de bacterias lácticas (principalmente de los géneros Lactococcus, Lactobacillus, Pediococcus, Enterococcus, Streptococcus y Carnobacterium) como probióticos de salmónidos, entre los que se incluyen el salmón del Atlántico (Salmo salar), la trucha arcoíris (O. mykiss) y la trucha común (Salmo trutta), así como de, aunque en menor medida, otras especies de relevancia para la acuicultura mediterránea como, por ejemplo, la lubina (Dicentrarchus labrax), la dorada (Sparus aurata), el rodaballo (S. maximus), el lenguado (Solea solea y Solea senegalensis), la anguila (Anguilla anguilla) y la tilapia (Oreochromis niloticus) (para una revisión de la literatura reciente ver Balcázar et al., 2006a; Farzanfar, 2006; Verschere et al., 2000; Vine et al., 2006; Gatesoupe, 2008; Merrifield et al., 2010; Dimitroglou et al., 2011). No obstante, a pesar de los numerosos estudios realizados, conviene destacar que, hasta la fecha, en la UE sólo está autorizado (desde 2009) el empleo de un microorganismo (P. acidilactici CNCM MA18/5M, bacteria láctica registrada comercialmente como Bactocell®) como aditivo zootécnico para la acuicultura, concretamente para la mejora de la supervivencia y productividad de salmónidos y camarones. Desde hace tiempo se conoce que, además de su función tecnológica, las bacterias lácticas ejercen efectos beneficiosos para la salud de los animales y el hombre y, además, se caracterizan por su actividad antimicrobiana frente a diversos microorganismos patógenos de 11 Beneficiario COLFUTURO 2011 importancia en clínica humana y veterinaria (Rolfe, 2000¸ Cintas et al., 2001; Cleveland et al., 2001; Irianto, 2002; Deegan et al., 2006; Balcázar et al., 2004). A este respecto, sus principales mecanismos de antagonismo microbiano son la competencia por los nutrientes del sustrato y la formación de ácidos orgánicos (principalmente ácido láctico), con el consiguiente descenso del pH; no obstante, las bacterias lácticas también pueden inhibir el desarrollo de un amplio rango de microorganismos patógenos de los peces, al tener la capacidad de secretar otras sustancias antimicrobianas entre las que se incluyen el etanol, dióxido de carbono, diacetilo, diacetaldehído, peróxido de hidrógeno y otros metabolitos del oxígeno, benzoato, isómeros D de los aminoácidos, reuterina y otros compuestos no proteicos de pequeño tamaño molecular y, por último, un grupo heterogéneo de sustancias antimicrobianas (antibacterianas, principalmente frente a bacterias Gram-positivas, y, en algunos casos, antifúngicas) de naturaleza peptídica o proteica y de síntesis ribosomal denominadas bacteriocinas (Cintas et al., 2001; Fimland et al., 2005; Cotter et al., 2005). Dado que la seguridad e inocuidad de las bacterias lácticas se ha aceptado durante mucho tiempo, y en la actualidad la mayoría (e.g., Lactococcus lactis) se consideran microorganismos seguros por la EFSA (status QPS, del inglés Qualified Presumption of Safety) (EFSA, 2005a,b; EFSA, 2007), aparte de su aplicación como probióticos para el ser humano y los animales, también se ha sugerido su utilización y/o la de sus metabolitos como “bioconservantes” de los alimentos, para que, formando parte de un sistema de “barreras”, permitan garantizar su calidad higiénico-sanitaria y seguridad e incrementar su vida útil (Cintas et al., 2001; Cleveland et al., 2001; Deegan et al., 2006). De forma general, independientemente del tipo de microorganismos utilizados, los tratamientos probióticos en acuicultura pueden considerarse como: (i) métodos de biocontrol, ya que permiten la introducción de microorganismos que mediante diferentes mecanismos posibilitan que los microorganismos patógenos puedan ser eliminados o reducidos en número en el ambiente acuícola y/o (ii) probióticos sensu stricto, ya que favorecen que el hospedador se encuentre en un adecuado estado inmune para combatir al microorganismo patógeno (Chabrillón y Moriñigo, 2007). En este sentido, los principales mecanismos por los que los probióticos ejercen su efecto beneficioso incluyen los siguientes: (i) supresión de microorganismos patógenos mediante exclusión competitiva mediada por la producción de compuestos antimicrobianos bacteriostáticos o bactericidas (bacteriocinas, ácidos orgánicos, peróxido de hidrógeno, lisozima, amonio, diacetilo, etc.) y sideróforos (e.g., de hierro), por la competencia por los nutrientes y energía disponibles y/o por la competencia por los lugares de adhesión del intestino u otras superficies mucosas; (ii) mejora de la nutrición del hospedador 12 Beneficiario COLFUTURO 2011 debida al suministro de nutrientes (e.g., ácidos grasos, vitaminas y aminoácidos esenciales) y/o al favorecimiento de la digestión (e.g., producción de lipasas y proteasas); (iii) mejora de la respuesta inmune del hospedador (e.g., activación de la respuesta humoral, incremento de la actividad fagocítica, etc.), y (iv) mejora de la calidad del agua de cultivo (e.g., conversión de materia orgánica en CO2, reducción de los niveles de amonio o nitritos, etc.) (Verschuere et al., 2000; Balcázar et al., 2006). Por otra parte, la selección y el desarrollo de probióticos aplicables comercialmente en acuicultura constituye un proceso multidisciplinar que incluye diferentes etapas en las que resultan necesarias la investigación básica y la aplicada, así como diversos ensayos a escalas piloto y real y estudios de viabilidad económica (Verschuere et al., 2000). En este sentido, y de forma general, el desarrollo de probióticos seguros y eficaces incluye las siguientes fases: (i) adquisición o aislamiento de probióticos potenciales, preferentemente procedentes del hospedador en el que se pretenden emplear o del ambiente acuático en el que deben ejercer su efecto probiótico; (ii) evaluación in vitro de su actividad antimicrobiana frente a los microorganismos patógenos que se pretenden controlar mediante ensayos en medios sólidos y líquidos; (iii) identificación y filiación taxonómica; (iv) evaluación de su seguridad in vitro (ausencia de patogenicidad); (v) evaluación de su capacidad para sobrevivir en el ambiente acuático y durante el tránsito por el tracto gastrointestinal del hospedador (e.g., resistencia a las sales biliares, pH bajo y proteasas), así como de su capacidad para colonizar el intestino o una superficie externa del hospedador, mediante su adherencia a las células epiteliales y mucosas, y prevenir el establecimiento de bacterias potencialmente patógenas; (vi) evaluación in vivo de su seguridad y sus efectos probióticos en el hospedador, entre los que se incluyen su efecto en el crecimiento (estado nutricional) y la tasa de supervivencia del hospedador y en el sistema inmune, así como ensayos en los que el hospedador se infecta experimentalmente con el patógeno que se pretende controlar; (vii) evaluación de sus características tecnológicas, tales como su resistencia y viabilidad bajo condiciones de crecimiento y almacenamiento estándar y tras los procesos industriales empleados generalmente (e.g., sensibilidad al oxígeno, producción de ácido, velocidad de crecimiento, liofilización, extrusión, etc.); (viii) caracterización microbiológica y metagenómica del efecto de su empleo en la estructura y dinámica poblacional de la microbiota del hospedador al que se adicionen como probióticos y de su medio acuático, y, por último, (ix) análisis de costes y beneficios (Gómez-Gil et al., 2000; Verschuere et al., 2000; Nikoskelainen et al., 2001; Spanggaard et al., 2001; Irianto y Austin, 2002; Vine et al., 2004; Balcázar et al., 2006). Por otra parte, en los últimos años se está 13 Beneficiario COLFUTURO 2011 destacando la importancia y el interés de la evaluación del empleo de prebióticos como complementos alimenticios promotores de la salud de las especies de interés en acuicultura; sin embargo, su aplicación en este campo está aún en una fase preliminar y, hasta la fecha, ha sido poco evaluada. A este respecto el término “prebiótico” hace referencia a sustancias o productos no digeribles como, por ejemplo, fructanos de cadena larga (inulina) y corta o fructooligosacáridos (FOS), transgalacto-oligosacáridos y manano-oligosacáridos, que: (i) sirven de sustrato para bacterias beneficiosas del tracto gastrointestinal y estimulan su crecimiento o actividad metabólica; (ii) modifican favorablemente la microflora intestinal, y, por último, (iii) ejercen efectos beneficiosos en el hospedador, tanto a nivel sistémico como intestinal (Gibson y Roberfroid, 1995; Gatlin et al., 2007). Conviene destacar que la inclusión de prebióticos en la dieta de las especies de acuicultura puede llevarse a cabo de forma independiente o conjuntamente con los cultivos de bacterias probióticas, esto es, en forma de preparaciones simbióticas. De forma general, la administración de probióticos se lleva a cabo mediante su adición a los piensos comerciales, bien una vez finalizado su proceso de elaboración (dado que los microorganismos se inactivan generalmente por las condiciones de procesamiento industrial) o en el momento de suministrarse a los peces; no obstante, diversos estudios demuestran una mayor eficacia cuando se adicionan directamente al agua de cultivo de los sistemas cerrados (fases larvaria y de alevinaje) o semicerrados (fase de engorde) de recircularización empleados en las modernas piscifactorías, o cuando se incorporan al agua de cultivo del alimento vivo, suministrado generalmente durante las fases larvaria y de alevinaje (e.g., A. franciscana, A. salina y B. plicatilis), con el objetivo de encapsularlos al mismo y protegerlos de su inactivacion (bioencapsulación), favorieciendo por tanto su ingestión a dosis elevadas por las especies acuícolas a las que se suministre dicho alimento vivo “enriquecido” con la(s) especie(s) microbiana(s) de interés (Vine et al., 2006; Dimitroglou et al., 2010; Merrifield et al., 2010). A continuación, se describen los objetivos de este trabajo de investigación, que se encuadra en la línea de investigación iniciada en 2007 por el Grupo de Seguridad y Calidad de los Alimentos por Bacterias Lácticas, Bacteriocinas y Probióticos (grupo SEGABALBP), integrante del Grupo Investigador UCM-920193, Departamento de Nutrición, Bromatología y Tecnología de los Alimentos, Facultad de Veterinaria (UCM), la cual tiene como objetivo global la utilización de bacterias lácticas de origen acuático como probióticos en el contexto de una acuicultura sostenible. A este respecto, la finalidad global de esta línea de investigación es el desarrollo de una estrategia sostenible, alternativa o complementaria a la quimioterapia y la 14 Beneficiario COLFUTURO 2011 vacunación, para la prevención y el control de las ictiopatologías de mayor relevancia que se producen, especialmente durante las fases larvaria y de alevinaje, durante el cultivo intensivo de la trucha arcoíris (Oncorhynchus mykiss) y el rodaballo (Scophthalmus maximus), que representan actualmente dos de las especies acuícolas de mayor relevancia económica para la acuicultura continental y marina españolas, respectivamente. La estrategia propuesta, basada en el empleo como probióticos de bacterias lácticas productoras de bacteriocinas (bacteriocinogénicas) autóctonas de la trucha arcoíris y el rodaballo, sus ambientes acuícolas (agua y vegetación de los tanques de cultivo), el alimento vivo (en el caso del rodaballo) y los piensos comerciales (en el caso de la trucha arcoíris) empleados para su alimentación, permitiría, además, mejorar la productividad animal y la calidad y seguridad de los productos comercializados, así como minimizar el deterioro medioambiental del medio acuático de las piscifactorías. En trabajos previos (Araujo et al., 2001a,b,c), se procedió al aislamiento y filiación taxonómica de la microbiota autóctona de la trucha arcoíris durante todo su ciclo biológico; esto es, desde la eclosión de los huevos hasta la comercialización de las truchas (aprox., 1 año de vida), así como de los piensos empleados para su alimentación y de sus ambientes acuáticos (agua de salida de los tanques y vegetación). Asimismo, en estos trabajos previos se evaluó la actividad antimicrobiana de las bacterias lácticas frente a los microorganismos Gram-positivos y Gram-negativos causantes de las ictiopatologías de mayor relevancia para el cultivo intensivo de la trucha arcoíris (e.g., Streptococcus iniae, Lactococcus garvieae, Yersinia ruckerii, Vibrio campbelli y Aeromonas salmonicida). Posteriormente, se seleccionaron 75 cepas, que se identificaron como Lactococcus lactis subesp. lactis (en adelante L. lactis) y se procedió a su tipificación molecular, con el objetivo de identificar y seleccionar las más ubícuas y con un mayor y más potente espectro de acción antimicrobiana frente a L. garvieae y otros ictiopatógenos de la trucha arcoíris. Este trabajo de investigación tiene como objetivos globales la evaluación de la seguridad in vitro de la citada colección de 75 cepas de L. lactis aisladas previamente por SEGABALBP de la trucha arcoíris y su ambiente acuícola, así como la selección de las cepas potencialmente seguras para su posterior caracterización como probióticos para el desarrollo de una acuicultura sostenible de la trucha arcoíris y, probablemente, otras especies acuícolas de relevancia comercial. Conviene mencionar que aunque actualmente no existen directrices nacionales o internacionales específicas sobre la evaluación de microorganismos probióticos para su empleo en acuicultura, para la planificación y el desarrollo de los propuestos objetivos en este trabajo se 15 Beneficiario COLFUTURO 2011 han tenido en cuenta las recomendaciones internacionales generales para la evaluación del empleo de probióticos en los alimentos, como las que se recogen en el documento Guidelines for the Evaluation of Probiotics in Food, preparado por una Comisión Conjunta de Expertos de la FAO y la OMS (FAO/WHO, 2002). Asimismo, en este trabajo se han considerado diversos documentos comunitarios publicados por, entre otros, el Comité Científico de Nutrición Animal (SCAN) de la European Food Safety Authority (EFSA) acerca del concepto Qualified Presumption of Safety (QPS), de la evaluación de la seguridad de los microorganismos empleados en los alimentos y piensos, de su identificación y filiación taxonómica y de su resistencia a los antibióticos empleados en medicina humana y veterinaria (EFSA, 2005a,b,c; EFSA 2007; EFSA, 2008; EFSA, 2012). Por todo ello, los objetivos de este trabajo de investigación fueron los siguientes: Objetivo 1. Evaluación in vitro de la seguridad de las 75 cepas de L. lactis aisladas de trucha arcoíris y su ambiente acuícola. La especie L. lactis goza del estatus QPS por lo que, de acuerdo con la EFSA (EFSA, 2008, EFSA, 2012), para la evaluación de la seguridad in vitro de las cepas de esta especie que pretendan emplearse como aditivos zootécnicos únicamente es necesario evaluar su resistencia a antibióticos de relevancia en acuicultura y en medicina humana y veterinaria, con el objeto de descartar las cepas que muestren resistencias adquiridas y transmisibles; no obstante, en este trabajo se empleó un protocolo de evaluación de la seguridad más exhaustivo, desarrollado previamente por SEGABALBP (Muñoz-Atienza et al., 2012), en el que se incluyen los siguientes objetivos: Subobjetivo 1.1. Evaluación fenotípica de la presencia de factores de virulencia. Subobjetivo 1.1.1. Evaluación de la actividad hemolítica. Subobjetivo 1.1.2. Evaluación de la actividad proteolítica. Subobjetivo 1.1.3. Evaluación de la actividad mucinolítica. Subojetivo 1.2. Evaluación fenotípica y genotípica de la sensibilidad/resistencia a diversos antibióticos empleados en acuicultura y medicina humana y veterinaria. 16 Beneficiario COLFUTURO 2011 Subobjetivo 1.2.1. Determinación mediante el método de microdilución en placa de las concentraciones mínimas inhibidoras (CMI). Subobjetivo 1.2.2. Determinación mediante la reacción en cadena de la polimerasa (PCR) de la presencia de genes de resistencia. Subobjetivo 1.3. Evaluación fenotípica de diversas actividades enzimáticas perjudiciales. Subobjetivo 1.3.1. Evaluación de la desconjugación de sales biliares. Subobjetivo 1.3.2. Evaluación de la producción de aminas biógenas. Subobjetivo 1.3.2.1. Detección de la producción de aminas biógenas en medios de cultivo diferenciales. Subobjetivo 1.3.2.2. Determinación mediante PCR de la presencia de los genes involucrados en la síntesis de aminas biógenas. Objetivo 2. Selección de las cepas de L. lactis potencialmente seguras para su posterior caracterización como probióticos y/o biocontroladores para el desarrollo de una acuicultura sostenible. II. MATERIAL Y MÉTODOS 17 Beneficiario COLFUTURO 2011 II.1. EVALUACIÓN FENOTÍPICA DE LA PRESENCIA DE FACTORES DE VIRULENCIA DE LAS CEPAS DE Lactococcus lactis AISLADAS DE LA TRUCHA ARCOIRIS Y DE SU AMBIENTE ACUÍCOLA La evaluación de la seguridad in vitro de la colección de 75 cepas de L. lactis aisladas de trucha arcoíris y su ambiente acuícola (Araujo et al., 2001a,b,c) (Tabla II.1) se llevó a cabo mediante un procedimiento desarrollado previamente por SEGABALBP (Muñoz-Atienza et al., 2012), de acuerdo con la metodología que se describe a continuación. II.1.1. EVALUACIÓN DE LA ACTIVIDAD HEMOLÍTICA Para evaluar su actividad hemolítica, las 75 cepas de L. lactis aisladas de trucha arcoíris y su ambiente acuícola se inocularon en caldo MRS y se incubaron a 32ºC en aerobiosis durante 16 horas. Posteriormente, se sembraron mediante la técnica de siembra por estría en placas (20 ml) de agar Columbia (Oxoid, Ltd., Basingstoke, Reino Unido) suplementado con 5% (v/v) de sangre de caballo (Biomériux®). Después de su incubación a 37°C durante 24 h, las placas que presentaban zonas de hemólisis (hemólisis ) alrededor de las colonias fueron consideradas positivas. Como controles positivos se utilizaron las cepas Enterococcus faecalis SDP10 y P4. II.1.2. EVALUACIÓN DE LA ACTIVIDAD PROTEOLÍTICA Para evaluar su actividad proteolítica, las 75 cepas de L. lactis se inocularon en caldo MRS y se incubaron a 32ºC en aerobiosis durante 16 horas. Posteriormente, se sembraron mediante la técnica de siembra por estría en placas (20 ml) de agar Todd-Hewitt (Oxoid) con gelatina al 3% (p/v) y se incubaron a 37°C durante 24 horas. Finalizada la incubación, las placas se mantuvieron a 4°C durante 5 h. La presencia de un halo transparente (hidrólisis de la gelatina) alrededor de las estrías de inoculación se consideró indicativa de la actividad proteolítica (gelatinasa). Como controles positivos se emplearon las cepas E. faecalis SDP10 Y P4. Tabla II.1. Identificación, origen y fase de desarrollo de aislamiento de la colección de 75 cepas de L. lactis aisladas de trucha arcoíris y su ambiente acuícola. 18 Beneficiario COLFUTURO 2011 Cepas Origen Fase de desarrollo (días tras la eclosión) LT1 LT2 LT3 LT4 LT5 LT6 LT7 LT8 LT9 LT10 LT11 LT12 LT13 LT14 LT15 LT16 LT17 LT18 LT19 LT20 LT21 LT22 LT23 LT24 LT25 LT26 LT27 LT28 LT29 LT30 LT31 LT32 LT33 LT34 LT35 LT36 LT37 LT38 Intestino Intestino Intestino Intestino Intestino Intestino Vegetación Vegetación Vegetación Vegetación Vegetación Vegetación Agua Agua Agua Agua Agua Agua Vegetación Vegetación Vegetación Vegetación Vegetación Vegetación Agua Agua Agua Agua Agua Agua Intestino Intestino Intestino Intestino Intestino Intestino Agua Agua Alevín (30) Alevín (30) Alevín (30) Alevín (30) Alevín (30) Alevín (30) Alevín (30) Alevín (30) Alevín (30) Alevín (30) Alevín (30) Alevín (30) Alevín (30) Alevín (30) Alevín (30) Alevín (30) Alevín (30) Alevín (30) Alevín (90) Alevín (90) Alevín (90) Alevín (90) Alevín (90) Alevín (90) Alevín (90) Alevín (90) Alevín (90) Alevín (90) Alevín (90) Alevín (90) Alevín (240) Alevín (240) Alevín (240) Alevín (240) Alevín (240) Alevín (240) Alevín (240) Alevín (240) II.1.3. ACTIVIDAD MUCINOLÍTICA 19 Beneficiario COLFUTURO 2011 Cepas Origen Fase de desarrollo (días tras la eclosión) LT39 LT40 LT41 LT42 LT43 LT44 LT45 LT46 LT47 LT48 LT49 LT50 LT51 LT52 LT53 LT54 LT55 LT56 LT57 LT58 LT59 LT60 LT61 LT62 LT63 LT64 LT65 LT66 LT67 LT68 LT69 LT70 LT71 LT72 LT73 LT74 LT75 Agua Agua Agua Agua Vegetación Vegetación Vegetación Vegetación Vegetación Vegetación Intestino Intestino Vegetación Vegetación Vegetación Vegetación Vegetación Intestino Intestino Intestino Intestino Intestino Intestino Intestino Intestino Intestino Agua Agua Agua Agua Agua Vegetación Vegetación Vegetación Vegetación Vegetación Vegetación Alevín (240) Alevín (240) Alevín (240) Alevín (240) Alevín (240) Alevín (240) Alevín (240) Alevín (240) Alevín (240) Alevín (240) Alevín (300) Alevín (300) Alevín (300) Alevín (300) Adulto (450) Adulto (450) Adulto (450) Adulto (540) Adulto (540) Adulto (540) Adulto (540) Adulto (540) Adulto (540) Adulto (540) Adulto (540) Adulto (540) Adulto (540) Adulto (540) Adulto (540) Adulto (540) Adulto (540) Adulto (540) Adulto (540) Adulto (540) Adulto (540) Adulto (540) Adulto (540) La actividad mucinolítica de las 75 cepas de L. lactis se determinó empleando el método en placas descrito por Zhou et al. (2001). En primer lugar, estas cepas se inocularon en caldo MRS y se incubaron a 32ºC en aerobiosis durante 16 horas. Posteriormente, se sembraron 10 µl en placas (20 ml) de medio de cultivo mínimo anaeróbico (medio B) con la siguiente composición: triptona (7,5 g/l), casitona (caseína hidrolizada 7,5 g/l), extracto de levadura (30 g/l), extracto de carne (5,0 g/l), NaCl (5 g/l), KH2PO4 (0,5 g/l), MgSO4 (0,5 g/l), cisteína-HCl (0,5 g/l), resarzurina (0,002 g/l), mucina (HGM 0,5%) y agarosa (Sigma-Aldrich, tipo I-A) (1,5%, p/v); pH, 7,2. Finalizada la incubación de las placas a 37°C en anaerobiosis durante 72 h se realizó una tinción con Amido black (0,1%, p/v; Merck) en ácido acético 3,5 M durante 30 min. A continuación, las placas se lavaron con ácido acético 1,2 M para, en el caso de que existiera actividad mucinolítica, visualizar la aparición de un halo de decoloración (lisis de la mucina) alrededor de las estrías de inoculación. Como control positivo se empleó un homogeneizado de heces frescas de caballo, perro y gato. II.2. EVALUACIÓN FENOTÍPICA Y GENOTÍPICA DE LA SENSIBILIDAD/ RESISTENCIA DE Lactococcus lactis FRENTE A LOS PRINCIPALES ANTIBIÓTICOS EMPLEADOS EN ACUICULTURA, MEDICINA HUMANA Y VETERINARIA II.2.1. DETERMINACIÓN MEDIANTE EL MÉTODO DE MICRODILUCIÓN EN PLACA DE LAS CONCENTRACIONES MÍNIMAS INHIBITORIAS (CMI) La Concentración Mínima Inhibidora (CMI) de los antibióticos establecidos por la EFSA (Tabla II.2) (EFSA, 2008b y 2012) se determinó mediante el método de microdilución en placa, considerando en todos los ensayos las disposiciones y los puntos de corte o breakpoints establecidos por la EFSA (2008b y 2012). Para la realización de estos ensayos, se resuspendieron un número variable de colonias individuales de las 75 cepas de L. lactis, desarrolladas previamente en agar MRS a 32ºC durante 32 h, en solución salina (0.85% NaCl, p/v) estéril hasta una turbidez de 1 según la escala McFarland (aprox., 3 × 108 ufc/ml). A continuación, las suspensiones bacterianas se diluyeron (1/1.000) en caldo LSM (90% IST; 10% MRS) (Klare et al., 2007) y, seguidamente, se adicionaron 50 ó 100 μl de las suspensiones bacterianas a cada pocillo de las placas microtituladoras de 96 pocillos de fondo redondo (Nunclon™ surface, Nunc™, Dinamarca). Estas placas se sellaron con una lámina de plástico y se incubaron a 37°C durante 24 horas. Finalizadas las incubaciones, se determinaron las CMI 20 Beneficiario COLFUTURO 2011 como la menor concentración de antibiótico que inhibía el crecimiento bacteriano, determinándose que una cepa es resistente cuando esta CMI es superior a la establecida como punto de corte por la EFSA, y sensible cuando este valor es igual o inferior (EFSA, 2008b) (Tabla II.1). Tabla II.2. Puntos de corte o breakpoints (mg/l) establecidos para determinar la susceptibilidad (sensibilidad/resistencia) de L. lactis frente a diversos antibióticosª. Fuente: EFSA (2008b, 2012). L. lactis AMP VAN GEN STR ERY CHL TET KAN CLI Q+D 2 4 32 32 1 8 4 64 1 4 ªAbreviaturas: AMP, ampicilina; VAN, vancomicina; GEN, gentamicina; STR, estreptomicina; ERY, eritromicina; CHL, cloranfenicol; TET, tetraciclina; KAN, kanamicina; CLI, clindamicina; Q+D, quinupristina+dalfopristina. II.2.2. DETECCIÓN MEDIANTE LA REACCIÓN EN CADENA DE LA POLIMERASA (PCR) DE GENES DE RESISTENCIA A ANTIBIÓTICOS En las cepas en las que se detectaron resistencias adquiridas mediante el método de microdilución en placa (CMI mayor que el punto de corte establecido por la EFSA), así como en aquéllas en las que los valores de CMI resultaron iguales a los correspondientes puntos de corte, se evaluó también la presencia de los determinantes genéticos que confieren resistencia transmisible a los antibióticos respectivos, empleando para ello la técnica de la reacción en cadena de la polimerasa (PCR). De forma general, las reacciones de PCR se realizaron en mezclas de reacción de 25 ó 50 l utilizando 150-250 ng de ADN genómico purificado (InstaGene Matrix, Biorad™), desoxinucleótidos (0,2 mM), cebadores (0,7 M) y 1 U de la enzima MyTaq™ Mix (Bioline). Con el objetivo de optimizar las condiciones de las reacciones de PCR, se emplearon primero termocicladores de gradiente (MJ MiniTM Personal Thermal Cycler, Bio-Rad Laboratories) y, posteriormente, termocicladores “convencionales” (Techgene, Techne Ltd.). En todas las experiencias, las muestras se sometieron a un ciclo inicial de desnaturalización (97°C, 2 min), seguido de 30 ciclos de desnaturalización, hibridación y elongación a los tiempos y temperaturas apropiados en cada caso, seguido de una elongación final de los productos amplificados (72°C, 7 min) (Tabla II.3). 21 Beneficiario COLFUTURO 2011 En la Tabla II.3 se muestran las cepas empleadas como control positivo para cada reacción de PCR, empleándose en todos los caso las cepa L. lactis BB24 como control negativo. Las parejas de oligonucleótidos específicos de los genes que codifican resistencia transmisible a kanamicina (acc y aph3”), estreptomicina (aad), tetraciclina (tetK, tetL, tetM, tetB/P, tetO, tetQ, tetS, tetT, tetW), vancomicina (vanA, vanB, vanC1, vanC2/C3), quinupristina+dalfopristina (vatD) y clindamincina (lnuA, lnuB) se muestran en la Tabla II.3. Los productos de amplificación obtenidos (amplicones) se sometieron a electroforesis en geles de agarosa (1-2%, p/v; D1 Low EEO Agarose, Pronadisa) a 90 V durante 60 min, empleando, como agente de tinción no tóxico (en sustitución del bromuro de etidio), GelRed (Biotium), y se analizaron empleando el equipo Gel-Doc 2000, con el soporte informático de análisis de imagen Quantity One (Bio-Rad Laboratories). II.3. EVALUACIÓN FENOTÍPICA DE DIVERSAS ACTIVIDADES ENZIMATICAS PERJUDICIALES EN LAS CEPAS DE Lactococcus lactis II.3.1. EVALUACIÓN DE LA DESCONJUGACIÓN DE SALES BILIARES La capacidad de las 75 cepas de L. lactis para desconjugar las sales biliares (taurodeoxicolato) se determinó empleando la metodología descrita por Noriega et al. (2006). En primer lugar, estas cepas se inocularon en caldo MRS y se incubaron a 37ºC en aerobiosis durante 16 horas. Posteriormente, se inocularon 10l de los cultivos en placas de MRS suplementado con L-cisteína (0.05%, p/v; Merck) y taurodeoxicolato (0,5%, p/v; SigmaAldrich). Finalizadas las incubaciones de las placas a 37°C en anaerobiosis durante 72 h, la aparición de halos opacos (por precipitación de los ácidos biliares) alrededor de las colonias se consideró como un resultado positivo. Como controles positivos se utilizaron homogeneizados de heces frescas de gato, perro y ternero. 22 Beneficiario COLFUTURO 2011 Tabla II.3. Condiciones de PCR y oligonucleótidos específicos para la detección de los determinantes genéticos transmisibles que confieren resistencia a diversos antibióticos de relevancia en acuicultura y medicina humana y veterinaria. Antibiótico Gen Cebadores acc aacF aacR Kanamicina aph3" Estreptomicina aad(E) tet(K) tet(L) tet(M) tetB(P) Tetraciclina tet(O) tet(Q) tet(S) tet(T) tet(W) vanA vanB Vancomicina vanC1 vanC2/C3 QuinupristinaDalfopristina vatD lnuA Clindamicina Secuencia del cebador 5´-3´ GAGCAATAAGGGCATACCAAAAATC 95 °C ,30s; 55 °C ,20s; 72 °C, 2min. CCGTGCATTTGTCTTAAAAAACTGG Referencia CC9 Donabedian et al. (2003) 95 °C ,30s; 60 °C ,20s; 72 °C , 2min. 292 CC9 Liu et al. (2009) GCAGAACAGGATGAACGTATTCG 95 °C ,30s; 55 °C ,20s; 72 °C, 2min. ATCAGTCGGAACTATGTCCC 369 CC9 Klare et al. (2007) 95 °C ,30s; 50 °C ,20s; 72 °C , 2min. 352 C1570 95 °C , 30s; 53 °C, 20s; 72 °C , 2min. 385 CC9 95 °C , 30s; 55 °C, 20s; 72 °C ,2min. 401 CC9 95 °C por 30s, 46 °C, 20s; 72 °C , 2min. 169 - GCCGATGTGGATTGCGAAAA aph-3"R GCTTGATCCCCAGTAAGTCA aad E I Tamaño cepa control amplicón (pb) 500 aph-3"F aad EII Condiciones de PCR tet KI CAATACCTACGATATCTA tet KII TTGACGTGTCTTTGGTTCA tet LI TGGTCCTATCTTCTACTCATTC tet LII TTCCGATTTCGGCAGTAC tet MI GGTGAACATCATAGACACGC tet MII tetB (P)- Fw CTTGTTCGAGTTCCAATGC AAAACTTATTATATTATAGTG tetB (P)- Rv TGGAGTATCAATAATATTCAC tet OI AGCGTCAAAGGGGAATCACTATCC tet OII CGGCGGGGTTGGCAAATA tetQ- Fw AGAATCTGCTGTTTGCCAGTG tetQ- Rv CGGAGTGTCAATGATATTGCA tetS- Fw ATCAAGATATTAAGGAC tetS- Rv TTCTCTATGTGGTAATC tetT- Fw AAGGTTTATTATATAAAAGTG tetT- Rv AGGTGTATCTATGATATTTAC tetW- Fw GAGAGCCTGCTATATGCCAGC tetW- Rv GGGCGTATCCACAATGTTAAC vanA-36F TTGCTCAGAGGAGCATGACG vanA-992R TCGGGAAGTGCAATACCTGC vanB-23F TTA TCT TCG GCG GTT GCT CG vanB-1016R GC5C AAT GTA ATC AGG CTG TC C1 CCTACCTATTGTTTGTGGAA C2 CTTCCGCCATCATAGCT D1 CTCCTACGATTCTCTTG D2 CGAGCAAGACCTTTAAG vatD1 GCTCAATAGGACCAGGTGTA vatD2 TCCAGCTAACATGTATGGCG Klare et al . (2007) 95 °C ,30s;55 °C , 20s,72 °C, 2min. 1.723 - 95 °C ,30s; 63 °C ,20s; 72 °C ,2min. 169 - 95 °C , 30s;55 °C ,20s; 72 °C x 2min. 573 - 95 °C , 30s; 46 °C , 20s; 72 °C ,2min. 169 - 95 °C, 30s; 64 °C ,20s; 72 °c , 2min. 1187 - 95 °C ,30s; 65 °C , 20s; 72 °C ,2min. 957 RC714 95 °C , 30s; 62 °C, 20s; 72 °C ,2min. 994 RC714 95 °C, 30s; 51 °C ,20s; 72 °C , 2min. 822 CM65; CM66 Liu et al . (2009) 95 °C ,30s; 49 °C, 20s; 72 °C, 2min. 439 CM65; CM66 95 °C , 30s; 60 °C , 20s; 72 °C , 2min. 272 - lnuA1 GGTGGCTGGGGGGTAGATGTATTAACTGG 95 °C , 30s; 57 °C , lnuA2 GCTTCTTTTGAAATACATGGTATTTTTCGA 20s; 72 °C , 2min. 323 C1570 Lina et al . (1999) CCTACCTATTGTTTGTGGAA 95 °C ,30s; 54 °C, 20s; Bozdogan et al . 941 72 °C , 2min. (1999) lnuB2 ATAACGTTACTCTCCTATTTC Cepas control: Cepa Complejo Clonal asociado a hospital (CC9), E. faecium 3Er1; E. faecalis C1570; E. faecium RC714; E. caseiflavus CM65 y CM66 lnuB lnuB1 Aminov et al. (2001) 23 Beneficiario COLFUTURO 2011 II.3.2. EVALUACIÓN DE LA PRODUCCIÓN DE AMINAS BIÓGENAS. En las 75 cepas con potencial probiótico se evaluó la producción de aminas biógenas empleando dos metodologías: (1) desarrollo de las cepas bacterianas en un medio de cultivo diferencial (Bover-Cid, Holzapfel, 1999) para estimular la descarboxilación y el consiguiente viraje de color del medio debido al cambio de pH , y (2) determinación mediante PCR de la presencia de los genes involucrados en la síntesis de aminas biógenas en las cepas que mostraron un resultado positivo en las pruebas fenotípicas. II.3.2.1. Detección de la producción de aminas biógenas en medios de cultivo diferenciales La capacidad de las 75 cepas de L. lactis de producir aminas biógenas (histidina, tiramina, putrescina y/o cadaverina) se determinó, en primer lugar, según el procedimiento descrito por Bover-Cid y Holzapfel (1999), basado en su desarrollo en medios de cultivo diferenciales semisólidos que contienen bromocresol púrpura como indicador del pH y el aminoácido precursor de la amina biógena a evaluar (histidina, tirosina, ornitina o lisina, respectivamente) (Sigma). En primer lugar, con el objeto de estimular la actividad enzimática, las cepas se inocularon en medio MRS (Oxoid) con 0,1% del aminoácido precursor y 0,005% de piridoxal5-fosfato (Sigma) y se desarrollaron a 37ºC durante 24h. Una vez inducida la actividad enzimática tras 5 transferencias consecutivas en este medio, los cultivos se sembraron por agotamiento en un medio semisólido compuesto por triptona (0,5%) (Sigma), extracto de levadura (0,5%) (Pronadisa), extracto de carne (0,5%) (Merck), cloruro sódico (0,25%) (Merck), glucosa (0,05%) (Panreac), Tween 80® (0,1%) (Panreac), MgSO4 (0,02%) (Merck), MnSO4 (0,005%) (Merck), FeSO4 (0,004%) (Applichem), citrato amónico (0,2%) (Merck), tiamina (0,001%) (Fluka), K2PO4 (0,2%) (Merck), CaCO3 (0,01%) (Fluka), piridoxal-5-fosfato (0,005%) (Sigma), aminoácido (1%), bromocresol (0,006%) (Sigma) y agar (2%) (Pronadisa), con el pH ajustado a 5.3. Paralelamente, se prepararon placas control que no contenían el aminoácido precursor. Las placas problema y control inoculadas se incubaron a 37ºC en aerobiosis y anaerobiosis durante 4 días. Finalizadas las incubaciones, la producción de aminas biógenas se detectó por el viraje del color del medio de amarillo a violeta debido a su alcalinización como consecuencia de la descarboxilación del correspondiente aminoácido precursor. Como control positivo de la producción de histamina, putrescina y cadaverina se utilizó la cepa Lactobacillus sp. ATCC30a (Colección Americana de Cultivos Tipo) y, como controles de la producción de tiramina, se emplearon las cepas E. faecium GM29 y NV52. 24 Beneficiario COLFUTURO 2011 II.3.2.2. Determinación mediante PCR de la presencia de los genes involucrados en la síntesis de aminas biógenas La técnica de PCR (sección II.2.2) se empleó para evaluar la presencia en las 75 cepas de L. lactis de los genes que codifican las enzimas responsables de la producción de aminas biógenas (histidina descarboxilasa, hdc; tirosina descarboxilasa, tdc; ornitina descarboxilasa, odc, y lisina descarboxilasa, ldc), empleando las condiciones de reacción descritas por Landete et al. (2007) y las parejas de cebadores específicos para cada gen (Tabla II.4). Tabla II.4. Condiciones de PCR y oligonucleótidos degenerados para la detección de los determinantes genéticos que codifican la histidina descarboxilasa (HDC), tirosina descarboxilasa (TDC), ornitina descarboxilasa (ODC) y lisina descarboxilasa (LDC). tamaño (pb) Condiciones de PCR Primer secuencia (5´-3´) Referencia CL1 CCWGGWAAWATWGGWAATGGWTA 94 °C, 30 s; 48 °C, 30 s; Le Jeune et al. hdc 458 JV17HC AGACCATACACCATAACCTTG 72 °C, 2 min (1995) TD5 CAAATGGAAGAAGAAGTAGG 95 °C, 45 s; 48 °C, 45 s; tdc 1.100 Coton et al. (2004) TD2 ACATAGTCAACCATRTTGAA 72 °C, 1 min 3 GTNTTYAAYGCNGAYAARACNTAYTTYGT 95 °C, 30 s; 52 °C, 30 s; Marcobal et al. odc 1.446 16 TACRCARAATACTCCNGGNGGRTANGG 72 °C, 2 min (2004) CAD1-F TTYGAYWCNGCNTGGGTNCCNTAYAC 1.098 95 °C, 30 s; 53 °C, 30 s; De las Rivas et al. CAD1-R CCRTGDATRTCNGTYTCRAANCCNGG ldc 72 °C, 2 min (2006) CAD2-F CAYRTNCCNGGNCAYAA 1.185 CAD2-R GGDATNCCNGGNGGRTA *Símbolos de los nucleótidos incluidos en las posiciones con degeneración: K (G o T), R (A o G), W (A o T), Y (C o T), S (C o G), M (A o C), D (A, G o T) e I (A, G, C o T). Gen II.3.2.2.1. Detección de la presencia del gen que codifica la histidina descarboxilasa (HDC). La histamina es el producto de la descarboxilación de la histidina por la enzima histidina descarboxilasa (HDC), codificada por el gen hdc, que se amplificó empleando la pareja de cebadores CL1-JV17HC (Le Jeune et al., 1995) (Tabla II.4). Como control positivo de amplificación se empleó la cepa Lactobacillus sp. ATCC30a. II.3.2.2.2. Detección de la presencia del gen que codifica la tirosina descarboxilasa (TDC). 25 Beneficiario COLFUTURO 2011 La tiramina es el producto de la descarboxilación de la tirosina por la enzima tirosina descarboxilasa (TDC), codificada por el gen tdc, que se amplificó empleando la pareja de cebadores TD5-TD2 (Coton et al., 2004) (Tabla II.4). Como controles positivos de amplificación se emplearon Enterococcus faecium GM29 y NV52. II.3.2.2.3. Detección de la presencia del gen que codifica la ornitina descarboxilasa (ODC). La putrescina es el producto de la descarboxilación de la ornitina por la enzima ornitina descarboxilasa (ODC), codificada por el gen odc, que se amplificó empleando la pareja de cebadores 3-16 (Marcobal et al., 2004) (Tabla II.4). Como control positivo de amplificación se empleó la cepa Lactobacillus sp. ATCC30a. II.3.2.2.4. Detección de la presencia del gen que codifica la lisina descarboxilasa (LDC). La cadaverina es el producto de la descarboxilación de la lisina por la enzima lisina descarboxilasa (LDC), codificada por el gen ldc, que se amplificó empleando las parejas de cebadores CAD2-F-CAD2-R y CAD2-F-CAD2-R (De las Rivas et al., 2006) (Tabla II.4). Como control positivo de amplificación se empleó la cepa Lactobacillus sp. ATCC30a. III. RESULTADOS Y DISCUSIÓN 26 Beneficiario COLFUTURO 2011 La seguridad de los probióticos es un aspecto de gran relevancia que preocupa tanto a los autoridades competentes como a los consumidores (Franz et al., 2010; Sanders et al., 2010; Salminen y von Wright, 2012), A este respecto, la EFSA ha elaborado y actualizado recientemente una lista de los microorganismos con estatus QPS, entre los que se incluyen la especie L. lactis, proporcionando así un sistema genérico de asesoramiento de la seguridad de los microorganismos introducidos deliberadamente en la alimentación, no sólo animal sino también humana. Este calificativo se establece principalmente con base en cuatro pilares: (i) establecimiento de la identidad taxonómica; (ii) cuerpo de conocimiento; (iii) posible patogenicidad, y (iv) empleo final, lo que permite que cualquier microorganismo cuya identidad se pueda determinar inequívocamente, y se garantice su pertenencia a un grupo QPS, se pueda emplear como aditivo zootécnico con el único requerimiento de demostrar la ausencia de determinantes genéticos transmisibles de resistencia a antibióticos (EFSA, 2005a, 2005b, 2007, 2008, 2011; Franz et al., 2010; Donohue y Gueimonde, 2012; Salminen y von Wright, 2012). A este respecto, en trabajos previos se procedió a la identificación y filiación taxonómica inequívocas de las 75 cepas de L. lactis aisladas de trucha arcoíris y su ambiente acuícola (Araujo et al., 2001a,b,c) evaluadas en este trabajo para determinar su seguridad in vitro. Conviene destacar que aunque los lactococos, principalmente L. lactis subesp. lactis y L. lactis subesp. cremoris, han sido consumidos durante mucho tiempo por el hombre a través de los productos lácteos, y, por lo tanto, tienen una larga historia de consumo seguro, se han descrito en la literatura algunos casos de endocarditis, septicemia, neumonitis necrotizante artritis séptica y abscesos cerebrales y hepáticos cutos agentes etiológicos se identificaron como L. lactis (Casalta y Montel, 2008; Salminen y von Wright, 2012; von Wright, 2012). A este respecto, resulta relevante mencionar que, en la práctica totalidad de los casos descritos, los pacientes afectados tenían factores de predisposición como enfermedad subyacente, sistema inmune inmunocomprometido y elevada edad; asimismo, considerando la baja incidencia de las infecciones causadas por L. lactis, teniendo además en cuenta las elevadas dosis a las que se ingieren en los productos lácteos, los extremadamente raros casos indivduales descritos no deben considerarse como una indicación de la patogenicidad de L. lactis. Además, no puede descartarse que en muchas de estas infecciones el agente causal no fuese L. lactis sino L. garvieae, que es una especie que puede resultar patógena no sólo para el hombre sino también para los peces y otros animales (Casalta y Montel, 2008; Salminen y von Wright, 2012; von Wright, 2012). Por otra parte, se ha sugerido que L. lactis pudo ser el agente causal de la muerte 27 Beneficiario COLFUTURO 2011 masiva de más de 3.000 aves acuáticas en el sur de España durante el periodo septiembrenoviembre de 1998 (Goyache et al., 2001); no obstante, en este estudio no se pudo demostrar inequívocamente la involucración de L. lactis en este brote, aunque se sugirió que estos animales podrían actuar como reservorios de estos microorganismos. Considerando lo anteriormente expuesto, en este trabajo se evaluó la seguridad in vitro de la citada colección de 75 cepas de L. lactis aisladas de trucha arcoíris y su ambiente acuícola, empleando para ello un protocolo de evaluación de la seguridad, desarrollado previamente por SEGABALBP (MuñozAtienza et al., 20132), que es más exhaustivo que el propuesto por la EFSA para las cepas de L. lactis (EFSA, 2005, 2007, 2008, 2011, 2012) III.1. EVALUACIÓN FENOTÍPICA DE LA PRESENCIA DE FACTORES DE VIRULENCIA DE LAS CEPAS DE Lactococcus lactis AISLADAS DE LA TRUCHA ARCOÍRIS Y SU AMBIENTE ACUÍCOLA III.1.1 EVALUACIÓN DE LA ACTIVIDAD HEMOLÍTICA Las bacterias patógenas tienen la capacidad de producir una gran variedad de proteínas que contribuyen a su capacidad para colonizar y causar enfermedades en el hospedador, entre las que destacan las hemolisinas (alfa, beta, gamma y delta), que pueden degradar sus tejidos locales para convertirlos en nutrientes para las bacterias (Howe et al., 1996). Aunque se han descrito cepas de bacterias lácticas, principalmente de los géneros Enterococcus y Streptococcus, así como de las especies L. lactis y L. garvieae que poseen actividad hemolítica (Chow et al., 1993; Gilmore et al., 1994; Bolotin et al., 1999; Eaton y Gasson, 2001; Ogier y Serror, 2008; Franz et al., 2010), conviene destacar que ninguna de las 75 cepas de L. lactis aisladas de trucha arcoíris y su ambiente acuícola evaluadas en este trabajo mostró este fenotipo asociado a la patogenicidad bacteriana mediante el ensayo de hemólisis en placa (Figura 3.1). Aunque esta prueba resulta ser útil, económica y de gran fiabilidad, resulta conveniente determinar por PCR, especialmente en las cepas positivas, la presencia de los determinantes génicos cylL y cylB que, entre otros, están involucrados en síntesis de la citolisina/hemolisina (Chow et al., 1993). 28 Beneficiario COLFUTURO 2011 C+1 c- 1 C+2 Figura 3.1. Determinación fenotípica de la actividad hemolítica de cultivos de L. lactis LT75 (1) en placas de agar sangre. Como controles positivos (C+) (zona transparente por la lisis de los eritrocitos) se emplearon E. faecalis P4 (C+1) y E. faecalis SDP10 (C+2) y, como control negativo (C-), se utilizó E. faecalis P36. III.1.2 EVALUACIÓN DE LA ACTIVIDAD PROTEOLÍTICA La gelatinasa es una metaloendopeptidasa extracelular capaz de degradar sustratos como la gelatina, los fragmentos insolubles del colágeno, la cadena β de la insulina, la hemoglobina, la sustancia vasoconstrictora endotelina-1, la fibrina polimerizada y otros péptidos bioactivos de los tejidos del hospedador, mejorando así la migración y difusión bacteriana por los tejidos dañados (Waters et al., 2003). Además, la gelatinasa provee de nutrientes a la bacteria degradando el tejido del hospedador y presenta algún tipo de función en la formación de biopelículas. A este respecto, conviene destacar que ninguna de las 75 cepas de L. lactis aisladas de trucha arcoíris y su ambiente acuícola mostró actividad proteolítica (gelatinasa) (Figura 3.2), que representa uno de los factores de virulencia característicos del género Enterococcus y que, hasta la fecha, no ha sido descrito en L. lactis. 29 Beneficiario COLFUTURO 2011 c+ c- 4 3 1 2 Figura 3.2. Determinación fenotípica de la actividad proteolítica de L. lactis LT71 (1), LT72 (2), LT74 (3) y LT75 (4) en placas de Todd-Hewit con gelatina. Como control positivo (C+) (zona de turbidez por hidrólisis de la gelatina) se empleó E. faecalis P4 y, como control negativo (C-), se utilizó L. lactis BB24. III.1.3. ACTIVIDAD MUCINOLÍTICA Una de las barreras intestinales es el epitelio gastrointestinal, que está recubierto de una capa de mucus compuesta por mucinas (glicoconjugados compuestos de un núcleo de proteína unido a cadenas de hidratos de carbono) que desempeña un importante papel al evitar que las bacterias patógenas se adhieran al tracto gastrointestinal. Algunas bacterias tienen una actividad proteolítica que provoca la degradación de la mucina y, por tanto, les permite adherirse más fácilmente a la mucosa intestinal produciendo enfermedad, por lo que para la selección de un microorganismo probiótico debe tenerse en cuenta que no tenga actividad mucinolítica. A este respecto, es importante destacar que ninguna de las 75 cepas de L. lactis aisladas de trucha arcoíris y su ambiente acuícola evaluadas en este trabajo mostró actividad mucinolítica (Figura 3.3). 30 Beneficiario COLFUTURO 2011 c+ 1 Figura 3.3. Determinación fenotípica de la actividad mucinolítica de L. lactis LT46 (1) en placas de agar B con mucina. Como control positivo (C+) (zona transparente por hidrólisis de la mucina) se empleó un homogeneizado de heces frescas de gato. III.2. EVALUACIÓN FENOTÍPICA Y GENOTÍPICA DE LA SENSIBILIDAD/RESISTENCIA DE L. lactis A LOS PRINCIPALES ANTIBIÓTICOS EMPLEADOS EN ACUICULTURA Y MEDICINA HUMANA Y VETERINARIA En los últimos años, la resistencia a uno o varios antibióticos (multi-resistencia) en las bacterias lácticas ha motivado un gran interés y preocupación, ya que estos microorganismos, incluidos los lactococos, pueden actuar como reservorios de genes de resistencia a antibióticos, que, posteriormente, pueden transferirse a otras bacterias, tanto ambientales como comensales y/o patógenas del hombre y/o los peces y otros animales (Bernardeau et al., 2008; Casalta y Montel, 2008). En este contexto, queda destacar que existen dos tipos de resistencia a antibióticos: la intrínseca y la adquirida. La resistencia intrínseca (también denominada resistencia natural) es inherente a cada especie bacteriana; sin embargo, la resistencia adquirida aparece cuando una cepa sensible a un determinado antibiótico se convierte en resistente debido a, por ejemplo, una mutación cromosómica (resistencia adquirida no transmisible) o a la adquisición de un gen de resistencia que puede propagarse a otras cepas de la misma o diferente especie mediante transferencia horizontal (resistencia adquirida transmisible). A este respecto, como se mencionó anteriormente, la EFSA ha actualizado recientemente los criterios utilizados para la evaluación de microorganismos resistentes a antibióticos de importancia clínica y 31 Beneficiario COLFUTURO 2011 veterinaria (EFSA, 2008b, 2011, 2012), estableciendo la obligatoriedad de que, antes de comercializar como probiótico una cepa perteneciente a una especie con el estatus QPS, resulta necesario demostrar la ausencia de genes de resistencia a antibióticos (resistencia transmisible). III.2.1. DETERMINACIÓN MEDIANTE EL MÉTODO DE MICRODILUCIÓN EN PLACA DE LAS CMI DE LOS ANTIBIÓTICOS En la Tabla III.1 y Figura 3.4 se muestran los resultados de la susceptibilidad (sensibilidad/resistencia) de las 75 cepas de L. lactis aisladas de trucha arcoíris y su ambiente acuícola, determinada por el método de microdilución en placa para los 11 antibióticos estipulados por la EFSA (2008, 2012). Tabla III.1 Sensibilidad/resistencia de 75 cepas de Lactococcus lactis frente a los principales antibióticos empleados en acuicultura, medicina humana y veterinariaa. Cepas LT1 LT2 LT3 LT4 LT5 LT6 LT7 LT8 LT9 LT10 LT11 LT12 LT13 LT14 LT15 LT16 LT17 LT18 LT19 LT20 LT21 LT22 LT23 LT24 AMP 1 0.25 ≤0,125 1 0.25 0.5 0.25 1 0.5 0.5 1 0.5 1 0.5 1 0.25 0.25 0.5 0.5 0.5 1 0.5 1 0.25 VAN 1 ≤0,5 ≤0,5 ≤0,5 ≤0,5 ≤0,5 ≤0,5 ≤0,5 ≤0,5 ≤0,5 ≤0,5 ≤0,5 ≤0,5 ≤0,5 ≤0,5 ≤0,5 ≤0,5 ≤0,5 ≤0,5 ≤0,5 >32 ≤0,5 >32 >32 GEN 8 ≤2 16 8 4 ≤2 16 64 8 32 64 16 64 32 64 32 16 16 32 16 16 16 8 16 STR 64 ≤4 8 64 32 32 16 64 8 32 64 16 64 32 64 32 16 16 32 16 16 16 8 16 ERY 1 ≤0,125 0.5 1 ≤0,125 ≤0,125 ≤0,125 1 ≤0,125 ≤0,125 1 ≤0,125 1 ≤0,125 1 ≤0,125 ≤0,125 ≤0,125 ≤0,125 ≤0,125 ≤0,125 ≤0,125 ≤0,125 ≤0,125 32 Beneficiario COLFUTURO 2011 CHL 4 2 2 4 2 2 2 4-2 4-2 4 ≤1 2 4-2 ≤1 2 2 2 2 2 2 2 2 2 2 TET ≤0,5 ≤0,5 ≤0,5 ≤0,5 ≤0,5 ≤0,5 ≤0,5 ≤0,5 ≤0,5 ≤0,5 ≤0,5 ≤0,5 ≤0,5 ≤0,5 ≤0,5 ≤0,5 ≤0,5 ≤0,5 ≤0,5 ≤0,5 2 ≤0,5 2 1 KAN 128 ≤4 8 128 16 16 8 64 ≤4 8 128 ≤4 128 8 128 16 ≤4 ≤4 ≤4 ≤4 16 ≤4 16 ≤4 CLIN Q+D 2 2 ≤0,25 ≤0,25 0.5 1 2 1 0.5 2 ≤0,25 1 ≤0,25 1 1 2 ≤0,25 1 ≤0,25 1 2 2 ≤0,25 0.5 1 1 1 1 ≤0,25 1 ≤0,25 2 ≤0,25 1 ≤0,25 1 ≤0,25 1 ≤0,25 1 ≤0,25 1 ≤0,25 1 ≤0,25 1 ≤0,25 1 Tabla III.1 (continuación) Ce pas LT25 LT26 LT27 LT28 LT29 LT30 LT31 LT32 LT33 LT34 LT35 LT36 LT37 LT38 LT39 LT40 LT41 LT43 LT44 LT45 LT46 LT47 LT48 LT49 LT50 LT51 LT52 LT53 LT54 LT55 LT56 LT57 LT58 LT59 LT60 LT61 LT62 LT63 LT64 LT65 LT66 LT67 LT68 LT69 LT70 LT71 LT72 LT73 LT74 LT75 AMP 0,5 0,25 0,5 0,5 0,25 0,5 0,5 0,5 0,5 0,5 0,5 0,5 0,5 1 0,5 0,5 0,5 0,5 0,5 0,25 0,5 0,5 0,5 0,5 0,5 0,5 0,5 0,5 0,5 0,25 0,5 0,5 0,25 0,25 0,25 0,5 1 0,25 0,5 0,25 0,25 0,5 0,25 0,25 1 0,5 0,5 0,25 1 0,25 VAN ≤0,5 ≤0,5 ≤0,5 ≤0,5 ≤0,5 ≤0,5 ≤0,5 ≤0,5 ≤0,5 ≤0,5 ≤0,5 ≤0,5 ≤0,5 ≤0,5 ≤0,5 ≤0,5 ≤0,5 ≤0,5 ≤0,5 ≤0,5 ≤0,5 ≤0,5 ≤0,5 ≤0,5 ≤0,5 ≤0,5 ≤0,5 ≤0,5 1 ≤0,5 ≤0,5 ≤0,5 ≤0,5 ≤0,5 ≤0,5 ≤0,5 1 ≤0,5 ≤0,5 ≤0,5 ≤0,5 ≤0,5 ≤0,5 ≤0,5 1 ≤0,5 ≤0,5 ≤0,5 ≤0,5 ≤0,5 GEN 32 32 16 16 32 16 32 32 16 32 32 16 16 64 32 16 16 16 16 32 16 16 4 ≤2 4 4 ≤2 8 8 ≤2 ≤2 ≤2 ≤2 ≤2 ≤2 >128 16 ≤2 ≤2 ≤2 ≤2 8 8 8 8 ≤2 ≤2 ≤2 8 8 STR 32 32 16 16 32 16 32 32 16 32 32 16 16 64 32 16 16 16 16 32 16 16 16 16 16 32 32 16 16 8 32 32 16 16 8 32 64 16 16 8 8 32 16 32 64 16 16 32 64 64 ERY ≤0,125 ≤0,125 ≤0,125 ≤0,125 ≤0,125 ≤0,125 ≤0,125 ≤0,125 ≤0,125 ≤0,125 ≤0,125 ≤0,125 ≤0,125 1 ≤0,125 0,25 0,25 0,25 0,25 ≤0,125 0,25 ≤0,125 ≤0,125 ≤0,125 ≤0,125 ≤0,125 ≤0,125 ≤0,125 0,25 ≤0,125 ≤0,125 ≤0,125 ≤0,125 ≤0,125 ≤0,125 ≤0,125 1 ≤0,125 ≤0,125 ≤0,125 ≤0,125 ≤0,125 ≤0,125 ≤0,125 1 ≤0,125 ≤0,125 ≤0,125 1 ≤0,125 CHL 2 2 2 2 2 2 2 2 2 2 2 ≤1 2 2 2 2 2 2 2 2 2 2 2 2 2 2 2 2 2 ≤1 2 2 2 ≤1 2 2 4 2 2 ≤1 2 2 2 2 2 2 2 2 2 2 TET ≤0,5 ≤0,5 ≤0,5 ≤0,5 ≤0,5 ≤0,5 ≤0,5 ≤0,5 ≤0,5 ≤0,5 ≤0,5 ≤0,5 ≤0,5 >32 ≤0,5 >32 >32 >32 >32 >32 >32 ≤0,5 ≤0,5 ≤0,5 ≤0,5 ≤0,5 ≤0,5 >32 4 ≤0,5 ≤0,5 ≤0,5 >32 ≥32 >32 ≤0,5 ≤0,5 >32 ≤0,5 ≤0,5 >32 ≤0,5 >32 ≤0,5 >32 ≤0,5 ≤0,5 ≤0,5 ≤0,5 ≤0,5 KAN ≤4 ≤4 ≤4 ≤4 32 ≤4 8 16 8 ≤4 8 ≤4 8 128-64 16 ≤4 8 16 8 8 8 ≤4 16 16 8 16 16 4 ≤4 ≤4 8 8 8 ≤4 ≤4 ≤4 128 ≤4 8 ≤4 8 16 8 32 128 8 16 8 64 16 CLIN Q+D ≤0,25 1 ≤0,25 1 ≤0,25 1 ≤0,25 1 ≤0,25 2 ≤0,25 1 ≤0,25 1 ≤0,25 1 ≤0,25 1 ≤0,25 1 ≤0,25 2 ≤0,25 1 ≤0,25 1 2 2 ≤0,25 2 ≤0,25 2 ≤0,25 2 ≤0,25 2 ≤0,25 2 ≤0,25 2 ≤0,25 2 ≤0,25 2 ≤0,25 4 ≤0,25 1 ≤0,25 2 ≤0,25 2 ≤0,25 2 ≤0,25 4 ≤0,25 4 ≤0,25 1 ≤0,25 2 ≤0,25 2 ≤0,25 4 ≤0,25 2-1 ≤0,25 2 ≤0,25 2 2 2 ≤0,25 2 ≤0,25 2 ≤0,25 1 ≤0,25 2 ≤0,25 1 ≤0,25 2 ≤0,25 2 2 2 0,5 1 ≤0,25 1 ≤0,25 1 1 1 ≤0,25 1 ͣLos valores de CMI destacados en color rojo son superiores a los puntos de corte establecidos por la EFSA (2008b, 2012), mientras que los señalados en amarillo se encuentran en el punto de corte . 33 Beneficiario COLFUTURO 2011 De los resultados obtenidos se dedujo lo siguiente (Tabla III.1): 30 de las 75 cepas de L. lactis (40,0%) mostraron resistencia adquirida a uno o más antibióticos. 9 de las 75 cepas de L. lactis (12,0%) presentaron multi-resistencia adquirida (a dos o más antibióticos). 14 de las 75 cepas de L. lactis (21,3%) mostraron resistencia adquirida a la tetraciclina. 11 de las 75 cepas de L. lactis (14,7%) mostraron resistencia adquirida a la estreptomicina. 8 de las 75 cepas de L. lactis (10,7%) mostraron resistencia adquirida a la kanamicina. 6 de las 75 cepas de L. lactis (8,0%) mostraron resistencia adquirida a la clindamicina. 6 de las 75 cepas de L. lactis (8,0%) mostraron resistencia adquirida a la gentamicina. 3 de las 75 cepas de L. lactis (4,0%) mostraron resistencia adquirida a la vancomicina. Ninguna de las 75 cepas de L. lactis presentó resistencia adquirida a la ampicilina, eritromicina, el cloranfenicol y la quinupristina+dalfopistrina. Figura 3.4. Porcentajes de sensibilidad/resistencia de las 75 cepas de L. lactis frente a los principales antibióticos empleados en acuicultura y medicina humana y veterinaria. Otros antibióticos incluyen la ampicilina, la eritromicina, el cloranfenicol y la quinupristina+dalfopistrina. 34 Beneficiario COLFUTURO 2011 Uno de los inconvenientes del método de microdilución en placa empleado para la determinación de las CMI a los antibióticos es que no existe una cepa reconocida como control positivo estándar. Asimismo, la elección del medio de crecimiento constituye uno de los puntos críticos para la fiabilidad de los resultados de estos ensayos (Hummel et al., 2007; Klare et al., 2007); a este respecto, L. lactis tiende a ser exigente en cuanto a las condiciones atmosféricas, de temperatura, acidez y de suplementación de nutrientes (principalmente hidratos de carbono) requeridos para su crecimiento. Conviene destacar que el medio de cultivo LSM y las condiciones de crecimiento empleadas en este trabajo para la determinación de las CMI resultaron ser adecuados, ya que permitieron el crecimiento de las 75 cepas de L. lactis a evaluar y, por tanto, la determinación de su susceptibilidad a los antibióticos analizados. Aunque, como se mencionó anteriormente, el género Lactococcus tiene una larga historia de consumo seguro para el ser humano y de no mostrar patogenicidad (status QPS), se ha descrito que algunas cepas de lactococos pueden contener plásmidos movilizables y, por lo tanto, realizar intercambio de material genético mediante conjugación intra e inter-genéricos (Hummel et al., 2007); por lo tanto, existe el potencial de propagación horizontal de la resistencia a los antibióticos. En consecuencia, y teniendo en cuenta que la determinación de las CMI no es suficiente para distinguir entre resistencias adquiridas transmisibles y no transmisibles (EFSA, 2008b), en el caso de las cepas en las que se encontraron resistencias adquiridas (a vancomicina, gentamicina, estreptomicina, tetraciclina, kanamicina y/o clindamicina) por el método de microdilución en placa (Tabla III.1), se realizaron, además, diversas experiencias de PCR para determinar la presencia de los correspondientes genes de resistencia. Asimismo, para las cepas en las que su CMI coincidió con el punto de corte para el correspondiente antibiótico, también se empleó la técnica de PCR con el objeto de asegurar, presuntivamente, la ausencia de los respectivos genes de resistencia. III.2.2. DETECCIÓN MEDIANTE PCR DE GENES DE RESISTENCIA A ANTIBIÓTICOS Con el objeto de identificar las cepas con resistencia adquirida transmisible a la kanamicina, se determinó mediante PCR la presencia de los genes acc y aph 3”. Las cepas evaluadas fueron L. lactis LT1, LT4, LT8, LT11, LT13, LT15, LT38, LT62, LT70 y LT74, empleando, como control positivo, E. faecium 3Er1 CC9 (Complejo Clonal Asociado a Hospital), y, como control 35 Beneficiario COLFUTURO 2011 negativo, L. lactis BB24. Ninguna de las cepas evaluadas amplificó los dos genes evaluados (no se muestran los resultados). En lo que respecta a la resistencia adquirida transmisible a la estreptomicina, se determinó mediante PCR la presencia del gen add. Las cepas evaluadas fueron L. lactis LT1, LT4, LT8, LT11, LT13, LT15, LT38, LT64, LT70, LT74 y LT75, utilizando como control positivo E. faecium 3Er1 CC9 (Complejo Clonal Asociado a Hospital), y, como control negativo, L. lactis BB24. Ninguna de las cepas evaluadas amplificó el gen add (no se muestran los resultados). La evaluación de la resistencia a la vancomicina se realizó mediante la amplificación por PCR de los genes vanA, vanB, vanC1 y vanC2/C3. Las cepas evaluadas por PCR fueron L. lactis LT21, LT23 y LT24, empleando como control positivo para la amplificación de vanA, E. faecium RC714 y para el gen vanC2/C3 las cepas Enterococcus casseliflavus CM65 y CM66. Debido a la falta de disponibilidad, no se empleó ningún control positivo para la amplificación de vanB y vanC1, y, en todos los casos, se utilizó como control negativo L. lactis BB24. La cepa LT23 fue la única que amplificó el gen vanB (Figura 3.5). Ninguna de las cepas evaluadas amplificó los genes vanA, vanC1 y vanC2/C3 (no se muestran los resultados). M 994 pb 1 2 3 C+ C- Figura 3.5. Electroforesis en gel de agarosa del producto de PCR (994 pb) correspondiente al gen vanB que codifica la resistencia a la vancomicina empleando el ADN genómico de las cepas L. lactis LT21 (1), LT23 (2) y LT24 (3). Como control positivo (C+) se empleó el ADN genómico de E. faecium RC714 y, como control negativo (C-), se utilizó L. lactis BB24. M, marcador de tamaño molecular 2000-bp Hyperladder II (Bioline). Para la determinación de la resistencia adquirida transmisible a la quinupristina+dalfopristina, se evaluó mediante PCR la presencia del gen vatD. Las cepas 36 Beneficiario COLFUTURO 2011 evaluadas fueron L. lactis LT48, LT53, LT54 y LT58. Debido a la falta de disponibilidad, no se empleó ninguna cepa como control positivo, y, como control negativo, se utilizó L. lactis BB24. Ninguna de las cepas evaluadas amplificó el gen vatD (no se muestran los resultados). Con el objeto de identificar las cepas con resistencia adquirida transmisible a la clindamicina se se evaluó mediante PCR la presencia de los genes lnuA y lnuB. Las cepas evualuadas fueron L. lactis LT1, LT4, LT11, LT38, LT62 y LT70. Debido a la falta de disponibilidad, no se empleó ninguna cepa como control positivo, y, en ambos caso, se utilizó como control negativo L. lactis BB24. Ninguna de las cepas evaluadas amplificó el gen vatD (no se muestran los resultados). En lo que respecta a la resistencia adquirida transmisible a la estreptomicina, se determinó mediante PCR la presencia de los genes tetK, tetL, tetM, tetB/P, tetQ, tetT y tetO (Tabla III.2; Figuras 3.6, 3.7, 3.8 y 3.9). Las cepas evaluadas fueron L. lactis LT38, LT40, LT41, LT42, LT43, LT44, LT45, LT46, LT53, LT54, LT58, LT59, LT60, LT63, LT66, LT68, LT70, LT76. Las cepas empleadas como control positivo fueron E. faecalis C1570 (tetK+) y E. faecium CC9 (tetL+ y tetM+). Debido a la falta de disponibilidad, no se empleó ninguna cepa como control positivo para tetB/P, tetQ, tetT y tetO, y, en todos los casos, se utilizó como control negativo L. lactis BB24. Tabla III.2. Evaluación mediante PCR de la presencia de genes de resistencia a la tetraciclina (tetK, tetL, tetM, tetB/P,tetQ, tetT y tetO ) en las 18 cepas de L. lactis que mostraron resistencia a este antibiótico mediante el método de microdilución en placa (CMI). Gen LT38 LT40 LT41 LT42 LT43 LT44 LT45 LT46 LT53 LT54 LT58 LT59 LT60 LT63 LT66 LT68 LT70 LT76 tetK + + + + + + + + + + + + + telL + tetM tetB/P tetQ tetT + + + + + + + + + + + + tetO + + + + + + + + + + + + + - En las cepas L. lactis LT38, LT41, LT42, LT43, LT44, LT46, LT53, LT54, LT58, LT59, LT60, LT63 y LT68 se detectó la presencia de tetK. En la cepa LT53 se amplificó tetL. En las cepas LT38, LT41, LT42, LT43, LT44, LT46, LT53, LT54, LT59, LT60, LT63 y LT66 se demostró la presencia de tetT. Las cepas LT38, LT40, LT41, LT42, LT43, LT44, LT46, LT53, LT54, LT59, LT60, LT63 y LT66 amplificaron tetO. En ninguna de las cepas evaluadas se detectó la presencia de los genes de resistencia tetM, tet B/P y tetQ. 37 Beneficiario COLFUTURO 2011 M 1 2 3 4 5 6 7 8 9 10 11 12 13 14 15 16 17 C+ 352 pb Figura 3.6. Electroforesis en gel de agarosa del producto de PCR (352 pb) correspondiente al gen tetK que codifica la resistencia a la tetraciclina empleando el ADN genómico de las cepas L. lactis LT38 (1), LT40 (2), LT41 (3), LT42 (4), LT43 (5), LT44 (6), LT45 (7), LT46 (8), LT53 (9), LT54 (10), LT58 (11), LT59 (12), LT60 (13), LT63 (14), LT66 (15), LT68 (16) y LT70 (17). Como control positivo (C+) se empleó el ADN genómico de E. faecalis C1570 y, como control negativo (C-), se utilizó L. lactis BB24. M, marcador de tamaño molecular 2000-bp Hyperladder II (Bioline). M 1 2 3 4 5 6 7 8 9 10 11 12 13 14 15 16 17 C+ C- 385 pb Figura 3.7. Electroforesis en gel de agarosa del producto de PCR (385 pb) correspondiente al gen tetL que codifica la resistencia a la tetraciclina empleando el ADN genómico de las cepas L. lactis LT38 (1), LT40 (2), LT41 (3), LT42 (4), LT43 (5), LT44 (6), LT45 (7), LT46 (8), LT53 (9), LT54 (10), LT58 (11), LT59 (12), LT60 (13), LT63 (14), LT66 (15), LT68 (16) y LT70 (17). Como control positivo (C+) se empleó el ADN genómico de Cepa Complejo Clonal asociado a hospital (CC9) E. faecium 3Erl y, como control negativo (C-), se utilizó L. lactis BB24. M, marcador de tamaño molecular 2000-bp Hyperladder II (Bioline). 38 Beneficiario COLFUTURO 2011 1 M 2 3 4 5 6 7 8 9 10 11 12 13 14 15 16 17 C- 169 pb Figura 3.8. Electroforesis en gel de agarosa del producto de PCR (169 pb) correspondiente al gen tetT que codifica la resistencia a la tetraciclina empleando el ADN genómico de las cepas L. lactis LT38 (1), LT40 (2), LT41(3), LT42 (4), LT43 (5), LT44 (6), LT45 (7), LT46 (8), LT53 (9), LT54 (10), LT58 (11), LT59 (12), LT60 (13), LT63 (14), LT66 (15), LT68 (16) y LT70 (17). En estos ensayos, debido a la falta de disponibilidad, no se empleó ninguna cepa como control positivo y, como control negativo (C-), se utilizó el ADN genómico de L. lactis BB24. M, marcador de tamaño molecular 2000-bp Hyperladder II (Bioline) M 1 2 3 4 5 6 7 8 9 10 11 12 13 14 15 16 17 C- 1723 pb Figura 3.9. Electroforesis en gel de agarosa del producto de PCR (1723 pb) correspondiente al gen tetO que codifica la resistencia a la tetraciclina empleando el ADN genómico de L. lactis LT38 (1), LT40 (2), LT41(3), LT42 (4), LT43 (5), LT44 (6), LT45 (7), LT46 (8), LT53 (9), LT54 (10), LT58 (11), LT59 (12), LT60 (13), LT63 (14), LT66 (15), LT68 (16) y LT70 (17). En estos ensayos, debido a la falta de disponibilidad, no se empleó ninguna cepa como control positivo y, como control negativo (C-), se utilizó el ADN genómico de L. lactis BB24. M, marcador de tamaño molecular 2000-bp Hyperladder II (Bioline). 39 Beneficiario COLFUTURO 2011 Conviene destacar que las bacterias lácticas albergan frecuentemente plásmidos de diversos tamaños, habiéndose descrito que algunos de ellos codifican los determinantes genéticos que confieren resistencia a diversos antibióticos en L. lactis, Lactobacillus spp. y Enterococcus spp. (Gevers et al., 2003). A este respecto, la mayoría de los estudios se han realizado con Enterococcus spp., dado que estas bacterias causan numerosas y graves infecciones en el ser humano (Hummel et al., 2007; Ogier y Serror, 2008; Franz et al., 2010). No obstante, diversos estudios han descrito la presencia en L. lactis de resistencias adquiridas transmisibles a diversos antibióticos, entre los que se incluyen la tetraciclina, cloranfenicol, clindamicina estreptomicina, estreptograminas y lincosamidas (Flórez et al., 2008; Walther et al., 2008). Conviene destacar que, en este trabajo, sólo se detectaron resistencias adquiridas transmisibles a la vancomicina (vanB; L. lactis LT23) y a la tetraciclina (tetK, tetL, tetT y/o tetO). A este respecto, en 15 de las 18 cepas de L. lactis (83,3%) evaluadas por mostrar resistencia adquirida frente a la tetraciclina, mediante el método de microdilución en placa (CMI) (Tabla III.1) se detectó la presencia de uno o varios de estos genes (Tabla III.2; Figs. 3.6. a 3.9). Asimismo, resulta relevante mencionar que, de estas 15 cepas, todas a excepción de tres amplificaron dos o más de los genes de resistencia a la tetraciclina descritos hasta la fecha (tetT y tetO, 1 cepa; tetK, tetT y tetO, 10 cepas; tetK, tetT, tetO y tetL; 1 cepa). Conviene destacar que sólo se detectaron genes de resistencia a antibióticos (tetK, tetT y tetO) en una de las cepas (L. lactis LT54) evaluadas por presentar valores de CMI iguales a los puntos de corte establecidos por la EFSA (2008b, 2012). III.3. EVALUACIÓN FENOTÍPICA DE DIVERSAS ACTIVIDADES ENZIMATICAS PERJUDICIALES EN LAS CEPAS DE Lactococcus lactis III.3.1. EVALUACIÓN DE LA DESCONJUGACIÓN DE SALES BILIARES Uno de los efectos deseados en un probiótico es la habilidad de resistir a las sales biliares del intestino, lo que puede depender de su capacidad para hidrolizar las sales biliares (actividad hidrolasa de las sales biliares, BSH). Las sales biliares son sintetizadas en el hígado, a partir del colesterol, y se secretan en forma conjugada con la glicina o la taurina al duodeno, donde facilitan la absorción de las grasas para su posterior entrada en la circulación entero-hepática. Durante este proceso, las sales biliares pueden experimentar dos modificaciones importantes llevadas a cabo por la microbiota intestinal: (i) la desconjugacion de las sales biliares primarias por las enzimas hidrolasas-BSH, lo que resulta en la liberación de residuos aminoácidos, y (ii) 40 Beneficiario COLFUTURO 2011 la formación de ácidos biliares desconjugados (principalmente ácidos cólico y quenodeoxicólico), que, posteriormente, pueden ser dehidroxilados a ácidos biliares secundarios (deoxicólico y litocólico, respectivamente) (Noriega et al, 2006). Por este motivo, la presencia de enzimas hidrolasas-BSH en los probióticos hace que éstos sean más tolerantes a las sales biliares, lo que también ayuda a reducir los niveles de colesterol sanguíneo en el hospedador. La desconjugación de las sales biliares ha sido incluida hace algún tiempo por la Organización Mundial de la Salud como una de las principales actividades que debe tener un microorganismo probiótico humano (FAO/WHO, 2002). Con el fin de que las bacterias utilizadas como probióticos tengan un efecto beneficioso para la salud, éstos deben superar barreras biológicas en el tracto gastrointestinal, tales como los ácidos del estómago y la bilis del intestino (Lankaputhra y Shah, 1995¸ Nikoskelainen et al. 2001, Kimoto et al., 2002; Balcazar et al., 2008). Asimismo, la adaptación a altas concentraciones de ácidos biliares podría ser una herramienta valiosa para incrementar la habilidad de los microorganismos probióticos para sobrevivir en el tracto gastrointestinal (Patel et al., 2010). A este respecto, Kimoto et al., (2002) estudiaron la tolerancia a la bilis de Lacotococcus spp. demostrando que algunas de las cepas evaluadas mostraban tolerancia a elevadas concentraciones de bilis, por lo que se seleccionaron como probióticos potenciales. 3 2 4 1 Figura 3.10. Determinación fenotípica de la desconjugación de las sales biliares por L. lactis LT7 (1), LT9 (2), LT10 (3) y LT11 (4) en placas de MRS suplementado con L-cisteína y taurodeoxicolato. Como controles positivos se emplearon heces frescas de perro (C1+) y gato (C2+). 41 Beneficiario COLFUTURO 2011 Conviene destacar que ninguna de las 75 cepas de L. lactis aisladas de trucha arcoíris y su ambiente acuícola evaluadas en este trabajo mostró capacidad para desconjugar las sales biliares evaluadas en este trabajo (taurodeoxicolato) (figura 3.10). Sin embargo, esto no quiere decir que en las pruebas in vivo las cepas de L. lactis seleccionadas no sean capaces de sobrevivir en el tracto gastrointestinal de la trucha arcoíris, ya que se ha demostrado que los resultados de los ensayos in vitro e in vivo pueden ser contradictorios (Burbank et al., 2012). III.3.2. EVALUACIÓN DE LA PRODUCCIÓN DE AMINAS BIÓGENAS 1 2 Las aminas biógenas son bases orgánicas de bajo tamaño molecular que aparecen en diversos alimentos como el pescado, el queso, el vino, los embutidos curados y otros productos fermentados, y que ejercen efectos fisiológicos moderadamente graves que se manifiestan como cuadros alérgicos (Coton, et al., 2010). La presencia de estos compuestos en los alimentos puede ser debida a la descarboxilación de los aminoácidos por enzimas microbianas, producidas por bacterias lácticas u otros microorganismos, y en alimentos no fermentados (principalmente el pescado) son producidas por microrganismos indeseables y son indicativas de su deterioro (Halász et al., 1994; ten Brink et al., 1990). La histamina y la tiramina han sido muy estudiadas debido a sus efectos tóxicos derivados de sus propiedades vasoactivas y psicoactivas. A este respecto, la histamina ha sido reconocida como la causa de la intoxicación por escómbridos (intoxicación histamínica), mientras que la tiramina está relacionada con migrañas y crisis hipertensivas en pacientes tratados con el inhibidor de la enzima monoamino-oxidasa (MAO). En lo que respecta a la putrescina y la cadaverina, su problemática radica en que potencian los efectos de otras aminas biógenas (especialmente histamina y tiramina) y/o dificultan su detoxificación en el organismo (Vidal-Carou, 1990; Silla, 1996; Landete et al., 2007). La capacidad de los microorganismos para descarboxilar los aminoácidos precursores de estas aminas biógenas ha sido descrita principalmente en Enterobacteriaceae, Pseudomonas spp., enterococos y algunas otras bacterias lácticas, entre las que se incluyen L. lactis y otros lactococos (Landete et al., 2007; Bunková et al., 2009; Ladero et al., 2011)). Por lo tanto, resulta conveniente proceder a la detección de las cepas productoras de estas sustancias con el objeto de descartarlas para su empleo como probióticos. A este respecto, actualmente se dispone de diversas metodologías cualitativas y cuantitativas, tanto fenotípicas como genotípicas, para la determinación de la producción de aminas biógenas, entre las que se incluyen los ensayos en 42 Beneficiario COLFUTURO 2011 placas de cultivo, la cromatografía líquida de alta presión (HPLC, del inglés High Pressure Liquid Chromatography), la cromatografía gas-líquido y la cromatografía en capa fina (TLC, del inglés Thin-Layer Chromatography) y la técnica de PCR (García-Moruno et al., 2005). En este trabajo se compararon dos metodologías: (1) un ensayo fenotípico (medios de cultivo diferenciales), y (2) un ensayo genotípico (PCR), con el objetivo de evaluar para las 75 cepas de L. lactis aisladas de trucha arcoíris y su ambiente acuícola la producción de aminas biógenas (histamina, tiramina, putrescina y cadaverina) y la presencia de los genes que codifican la síntesis de las correspondientes enzimas descarboxilasas, respectivamente. En lo que respecta a la evaluación fenotípica de la producción de histamina, tiramina, putrescina y cadaverina por las 75 cepas de L. lactis, se obtuvieron los siguientes resultados: 18 de las las 75 cepas de L. lactis (24%) produjeron, presumiblemente, una de las aminas biógenas evaluadas. 7 de las 75 cepas de L. lactis (9,3%) produjeron presumiblemente tiramina (Figura 3.11). 7 de las 75 cepas de L. lactis (9,3%) produjeron presumiblemente cadaverina (no se muestran los resultados). 3 de las 75 cepas de L. lactis (4,0%) produjeron presumiblemente histamina (no se muestran los resultados). 1 de las 75 cepas de L. lactis (1,3%) produjeron presumiblemente putrescina (no se muestran los resultados). Ninguna de las 75 cepas de L. lactis (0%) produjeron dos o más aminas biógenas. 43 Beneficiario COLFUTURO 2011 1 4 2 5 3 6 9 8 10 C- C+ 7 Figura 3.11. Determinación fenotípica de la producción de tiramina por las cepas L. lactis LT24 (1), LT25 (2), LT26 (3), LT29 (4), LT10 (5), LT18 (6), LT37 (7), LT33 (8), LT39 (9) y LT36 (10). Como control positivo (C+) (viraje del color del medio de amarillo a violeta) se empleó E. faecium GM29 (C+) y, como control negativo (C-), se empleó Lactobacillus sp ATCC30a. En cuanto a la evaluación fenotípica de la producción de aminas biógenas producidas por bacterias se puede decir que las técnicas convencionales de cultivo tienen la desventaja de ser tediosas y, además, poco fiables ya que pueden dar resultados falsos positivos (Landete et al., 2007), debido a la formación de otros compuestos alcalinos (Bover-Cid et al., 1999). Por este motivo, en este trabajo también se realizó la evaluación por PCR de la presencia de los genes que codifican las enzimas descarboxilasas que dan lugar a la producción de las aminas biógenas evaluadas. La técnica de PCR tiene varias ventajas, como la rapidez, sensibilidad, simplicidad, así como la detección de los genes específicos, por lo que, en principio, los resultados son más fiables que los obtenidos con los métodos tradicionales de cultivo. A este respecto, conviene destacar que, sorprendentemente, de las 18 cepas que mostraron capacidad de producir alguna de las aminas biógenas evaluadas en este trabajo, tan sólo una cepa (L. lactis LT12) amplificó uno de los genes que codifican las enzimas descarboxilasas, concretamente el gen tdc que codifica la tirosina descarboxilasa (TDC) (Figura 3.12). 44 Beneficiario COLFUTURO 2011 M 1 2 3 4 5 6 7 8 9 10 11 12 13 14 15 16 C+1 C+2 C1100 pb Figura 3.12. Electroforesis en gel de agarosa del producto de PCR (1100 pb) correspondiente al gen que codifica la enzima tirosina descarboxilasa (tdc), empleando los cebadores TD5/TD2 y el ADN genómico de L. lactis LT3 (1), LT10 (2), LT11 (3), LT12 (4), LT14 (5), LT33 (6), LT54 (7) y otras cepas de L. lactis no incluidas en este estudio (8, 9, 10, 11, 12, 13, 14, 15 y 16). Como controles positivos se empleó ADN genómico de las cepas E. faecium GM29 (C+1) y E. faecium NV52 (C+2) y, como control negativo (C-), se utilizó Lactobacillus sp ATCC30a. Considerando estos resultados, es necesario proceder a la realización de estudios complementarios para determinar si se trata realmente de falsos positivos de la técnica fenotípica basada en el empleo de medios de cultivo diferenciales, o, por el contrario, son realemnete cepas productoras de estas aminas biógenas que presentan mutaciones en la secuencia nucleotídica de los correspondientes genes, lo que impide su amplificación por PCR empleando los oligonucleótidos descritos en este trabajo, que no son específicos para L. lactis. III.4. SELECCIÓN DE LAS CEPAS DE Lactococcus lactis AISLADAS DE TRUCHA ARCOIRIS Y SU AMBIENTE ACUICOLA POTENCIALMENTE SEGURAS PARA SU POSTERIOR CARACTERIZACIÓN COMO PROBIÓTICOS PARA EL DESARROLLO DE UNA ACUICULTURA SOSTENIBLE Con base en los resultados de la evaluación de la seguridad in vitro de las 75 cepas de L. lactis aisladas de trucha arcoíris y su ambiente acuícola, seleccionadas por su espectro de actividad antimicrobiana frente a L. garviae y otros ictiopatógenos de relevancia para el cultivo intensivo de esta especie acuícola, solamente 15 cepas (Tabla III.3), lo que representa un 20% de las cepas evaluadas, pueden considerarse potencialmente seguras para el hombre, los peces y otros animales y el medio ambiente, ya que no mostraron actividad hemolítica, proteolítica o mucinolítica, no desconjugaron las sales biliares (taurodeoxicolato), no produjeron aminas biógenas y no presentaron resistencia adquirida (transmisible o no transmisible) a ninguno de los antibióticos de relevancia para la acuicultura, medicina humana y veterinaria evaluados en 45 Beneficiario COLFUTURO 2011 este trabajo y especificados por la EFSA. No obstante, resulta necesario completar la evaluación de su seguridad in vitro, así como demostrar fehacientemente la ausencia de patogenicidad in vivo frente a diversas líneas celulares y las especies animales en las que se pretenden emplear como probióticos para el desarrollo de una acuicultura sostenible. Conviene destacar que las 15 cepas de L. lactis consideradas potencialmente seguras con base en los resultados obtenidos en este trabajose aislaron de intestino de trucha arcoíris y vegetación y agua de salida de los tanques de cultivo durante todo el ciclo biológico de esta especie acuícola (desde alevines a ejemplares adultos). Finalmente, los resultados obtenidos demuestran la utilidad del protocolo de evaluación de la seguridad in vitro propuesto, ya que, a pesar del estatus QPS de la especie L. lactis, la mayoría de las cepas aisladas de trucha arcoíris y su ambiente acuícola durante todo su ciclo biológicono pueden considerarse seguras para su aplicación como probióticos en la acuicultura. Asimismo, este protocolo podría resultar de validez para la evaluación de la seguridad in vitro del empleo como probióticos de otras especies de bacterias lácticas de relevancia para la acuicultura, tanto continental como marina. Tabla III.3. Identificación, origen y fase de desarrollo de las 15 cepas de L. lactis aisladas de trucha arcoíris y su ambiente acuícola seleccionadas por su seguridad in vitro. Cepas Origen Fase de desarrollo (días tras la eclosión) LT2 LT7 LT9 LT18 LT27 LT28 LT30 Intestino Vegetación Vegetación Agua Agua Agua Agua Alevín (30) Alevín (30) Alevín (30) Alevín (30) Alevín (30) Alevín (30) Alevín (30) LT36 LT37 LT47 Intestino Agua Vegetación Alevín (240) Alevín (240) Alevín (240) LT49 Intestino Alevín (300) LT55 LT64 LT65 LT72 Beneficiario COLFUTURO 2011 Vegetación Intestino Agua 46 Vegetación Adulto (450) Adulto (450) Adulto (450) Adulto (450) IV. CONCLUSIONES PRIMERA. Ninguna de las 75 cepas de Lactococcus lactis aisladas de trucha arcoíris y su ambiente acuícola evaluadas en este trabajo mostró actividad hemolítica, proteolítica o mucinolítica, ni tampoco capacidad para la desconjugación de sales biliares (taurodeoxicolato). SEGUNDA. 30 de las las 75 cepas de L. lactis (40,0%) mostraron resistencia adquirida a uno o más antibióticos, y, de éstas, 9 cepas (12,0%) presentaron multirresistencia adquirida (a dos o más antibióticos). En lo que respecta a las resistencias identificadas en este trabajo, las más frecuentes fueron a tetraciclina (16 cepas; 21,3%) y, en menor medida, estreptomicina (11 cepas; 14,7%), kanamicina (8 cepas; 10,7%), clindamicina (6 cepas; 8,0%), gentamicina (6 cepas; 8,0%) y, por último, vancomicina (3 cepas, 4,0%). Ninguna de las 75 cepas de L. lactis presentó resistencia adquirida a ampicilina, eritromicina, cloranfenicol y quinupristina+ dalfopistrina. TERCERA. Únicamente se detectaron resistencias adquiridas transmisibles a la vancomicina (vanB; L. lactis LT23) y a la tetraciclina (tetK, tetL, tetT y/o tetO). En 15 de las 18 cepas de L. lactis (83,3%) evaluadas por mostrar resistencia adquirida frente a la tetraciclina mediante el método de microdilución en placa (CMI) se detectó la presencia de uno o varios de estos genes. De estas 15 cepas, todas a excepción de tres amplificaron dos o más de los genes de resistencia a la tetraciclina descritos hasta la fecha (tetT y tetO, 1 cepa; tetK, tetT y tetO, 10 cepas; tetK, tetT, tetO y tetL; 1 cepa). Tan sólo se detectaron genes de resistencia a antibióticos (tetK, tetT y tetO) en una de las cepas (L. lactis LT54) evaluadas por presentar valores de CMI iguales a los puntos de corte establecidos por la EFSA. CUARTA. 18 de las 75 cepas de L. lactis (24%) produjeron, presumiblemente, una o más aminas biógenas, y, de éstas, ninguna cepa produjo, dos o más aminas biógenas. En lo que respecta a la producción de cada amina biógena, las más frecuentes fueron tiramina (7cepas; 9,3%), cadaverina (7cepas; 9,3%), histamina (3 cepas; 4,0%), y, por último, putrescina (1 cepa; 1,3%). Sorprendentemente, de las 18 cepas que mostraron capacidad de producir alguna de las aminas biógenas evaluadas en este trabajo, tan sólo una cepa (L. lactis LT12) amplificó uno de los genes que codifican las enzimas descarboxilasas, concretamente el gen tdc que codifica la tirosina descarboxilasa (TDC). 47 Beneficiario COLFUTURO 2011 QUINTA. De las 75 cepas de L. lactis aisladas de trucha arcoíris y su ambiente acuícola evaluadas en este trabajo, seleccionadas por su espectro de actividad antimicrobiana frente a L. garviae y otros ictiopatógenos de relevancia para el cultivo intensivo de esta especie acuícola, solamente 15 cepas (20%) pueden considerarse potencialmente seguras para el hombre, los peces, otros animales y el medio ambiente, ya que no mostraron actividad hemolítica, proteolítica o mucinolítica, no desconjugaron las sales biliares (taurodeoxicolato), no produjeron aminas biógenas y no mostraron resistencia adquirida (transmisible o no transmisible) a ninguno de los antibióticos de relevancia para la acuicultura, medicina humana y veterinaria evaluados en este trabajo y especificados por la EFSA. No obstante, resulta necesario completar la evaluación de su seguridad in vitro, así como demostrar fehacientemente la ausencia de patogenicidad in vivo frente a diversas líneas celulares y las especies animales en las que se pretenden emplear como probióticos para el desarrollo de una acuicultura sostenible. SEXTA. Los resultados obtenidos demuestran la utilidad del protocolo de evaluación de la seguridad in vitro propuesto, ya que, a pesar del estatus QPS de la especie L. lactis, la mayoría de las cepas aisladas de trucha arcoíris y su ambiente acuícola durante todo su ciclo biológico no pueden considerarse seguras para su aplicación como probióticos para la acuicultura. 48 Beneficiario COLFUTURO 2011 V. BIBLIOGRAFIA 1. Aminov, R.I., Garrigues-Jeanjean N., and Mackie R.I. 2001. Molecular ecology of tetracycline resistance: development and validation of primers for detection of tetracycline resistance genes encoding ribosomal protection proteins. Applied Environmental Microbiology. 67: 22–32. 2. Angulo, F. 2000. Antimicrobial agents in aquaculture: Potential impact on public health. APUA Newsletter, 18: 4-5. 3. Araújo, C., Muñoz-Atienza E., Gómez-Sala B., del Campo R., Muñoz R., Igrejas G., Poeta P., Hernández P. E., Herranz C., and Cintas L. M. 2011a. Lactic acid bacteria (LAB) of aquatic origin as probiotics for a sustainable aquaculture. 4th Congress of European Microbiologists FEMS 2011. Ginebra, Suiza, 26-30 de junio. 4. Araújo, C., Muñoz-Atienza E., Igrejas G., Poeta P., Hernández P. E., Herranz C., and Cintas L. M. 2011b. Aislamiento e identificación de bacterias lácticas con potencial probiótico de la trucha arco-iris (Onchorrynchus mykiss) y su ambiente acuícola. VI Jornadas Complutenses-V Congreso Nacional de Investigación para Alumnos de Pregrado en Ciencias de la Salud-X Congreso de Ciencias Veterinarias y Biomédicas. Comunicaciones, formato digital. Madrid, 7-9 de abril. 5. Araújo, C., Muñoz-Atienza E., and Nahuelquín Y, Campanero C., Poeta P., Igrejas G., Hernández P. E., Herranz C., and Cintas L. M. 2011c. Identification and characterization of the microbiota from rainbow trout (Oncorhynchus mykiss Walbaum) and its aquatic environment as potential probiotics for a sustainable aquaculture. 4th International Conference on Environmental, Industrial and Applied MicrobiologyBioMicroWorld 2011. Abstracts p. 146. Málaga, September 14-16. 6. Austin, B., Stuckey L.F., Robertson P. A. W., Effendi I., and Griffith D. R. W. 1995. A probiotic strain of Vibrio alginolyticus effective in reducing diseases caused by Aeromonas salmonicida, Vagococcus anguillarum and V. ordalii. Journal of Fish Diseases, 18: 93-96. 7. Austin, B. 2006. The bacterial microflora of fish, revised. Sc World J, 6:45-931. 8. Balcázar, J.L., de Blas I., Ruiz-Zarzuela I., Vendrell D., and Muzquiz J.L. 2004. Probiotics: a tool for the future of fish and shellfish health management. Journal of aquaculture in the tropics, 19: 239-242. 49 Beneficiario COLFUTURO 2011 9. Balcázar, J.L., de Blas I., Ruiz-Zarzuela I., Vendrell D., Cunningham D., and Muzquiz J.L. 2006a. The role of probiotics in aquaculture. Veterinary Microbiology, 114: 173-186. 10. Balcázar, J. L., de Blas I., Ruiz-Zarzuela I, Vendrell D., Evora M.D., and Múzquiz J. L. 2006b. Growth inhibition of Aeromonas species by lactic acid bacteria isolated from salmonids. Microbial Ecology in Health and Disease, 18: 61-63. 11. Balcázar, J. L., de Blas I., Ruiz-Zarzuela I., Calvo A. C., Márquez I., Gironés O., and Múzquiz J. L. 2007a. Changes in intestinal microbiota and humoral immune response following probiotic administration in brown trout (Salmo trutta). British Journal of Nutrition, 97: 522-552. 12. Balcázar, J. L., de Blas I., Ruiz-Zarzuela I., Vendrell D., Calvo A. C., Márquez I., Gironés O., and Múzquiz J. L. 2007b. Enhancement of the immune response and protection induced by probiotic lactic acid bacteria against furunculosis in rainbow trout (Oncorhynchus mykiss). FEMS Immunology and Medicine Microbiology, 51: 185-193. 13. Balcazar, J.L., Vendrell D., De Blas I., Ruiz-Zarzuela I., Muzquiz J.L., and Girones O. 2008. Characterization of probiotics properties of Lactic acid bacteria isolated from intestinal microbiota of fish. Aquaculture, 278: 188-191. 14. Bernardeau, M., Vernoux J. P., Henri-Dubernet S., and Gueguen M. 2008. Safety assessment of dairy microorganisms: the Lactobacillus genus. Int. J. Food Microbiol. 126: 278−285. 15. Bover-Cid, S., and Holzapfel W.H. 1999. Improved screening procedure for biogenic amine production by lactic acid bacteria. International Journal Food Microbiology, 53:33-41. 16. Bozdogan, B., Berrezouga L., Kuo Ming-Shang, Yurek D., Farley K., Stockman B., and Leclercq R. 1999. A New Resistance Gene, linB, Conferring Resistance to Lincosamides by Nucleotidylation in Enterococcus faecium HM1025. Antimicrob. Agents Chemotherapy, 925: 4-43. 17. Bradford, M. M. 1976. A rapid and sensitive method for the quantitation of microgram quantities of protein utilizing the principle of protein-dye binding. Analytical Biochemistry, 72: 248-54. 50 Beneficiario COLFUTURO 2011 18. Buňková, L., Buňka F., Hlobilová M., Vaňátková Z., Nováková D., and Drab V. 2009. Tyramine production of technological important strains of Lactobacillus, Lactococcus and Streptococcus. European Food Research Technology, 229:533-538. 19. Burbank, D.R., LaPatra S. E., Fornshell G., and Cain1 K.D. 2012. Isolation of bacterial probiotics candidates from the gastrointestinal tract of rainbow trout Oncorhynchus mykiss (Walbaum), and screening for inhibitory activity against Flavobacterium psychrophilum. Journal of Fish Diseases, 35: 809-816. 20. Burr, G., and Gatlin D. 2005. Microbial ecology of the gastrointestinal tract of fish and the potential application of prebiotics and probiotics in finfish aquaculture. Journal of the World Aquaculture Society, 36: 425-436. 21. Brunt, J., Newaj-Fyzul A., and Austin B. 2007. The development of probiotics for the control of multiple bacterial diseases of rainbow trout, Oncorhynchus mykiss (Walbaum). Journal of Fish Diseases, 30: 573-579. 22. Cabello, F. C. 2006. Heavy use of prophylactic antibiotics in aquaculture: a growing problem for human and animal health and for the environment. Environmental Microbiology, 8: 1137-1144. 23. Campos, C., Rodríguez O., Calo-Mata P., Prado M., and Barros-Velázquez J. 2006. Preliminary characterization of bacteriocins from Lactococcus lactis, Enterococcus faecium and Enterococcus mundtii strains isolated from turbot (Psetta maxima). Food Research International, 39: 356-364. 24. Casalta, E., and Montel M.C. 2008. Safety assessment of dairy microorganisms: the Lactococcus genus. Int. J. Food Microbiol., 126: 271-273. 25. Cintas, L.M., Casaus P., Herranz C., Nes I.F., and Hernández P.E. 2001. Bacteriocins of lactic acid bacteria. Food Science and Technology International, 7: 281305. 26. Chabrillón, M., and M. A. Moriñigo M. A. 2007. ¿Pueden los peces comer yogur? Disponible en la dirección de internet http://www. encuentros. uma.es/ encuentros 89/peces.htm. 27. Chabrillón, M., Díaz-Rosales P., Balebona M.C., and Moriñigo M.A. 2007. Application of Lactic Acid Bacteria (LAB) as probiotics in fish farming. Panorama Acuícola Magazine, marzo/abril: 28-34. 51 Beneficiario COLFUTURO 2011 28. Chow, J.W., Thal, L.A., Perri, M.B., Vazquez, J.A., Donabedian, S.M., Clewell, D.B., and Zervos, M.J. 1993. Plasmid associated hemolysin and aggregation substance production contribute to virulence in experimental enterococcal endocarditis. Antimicrobial Agents Chemotherapy. 37: 2474-2477. 29. Cleveland, J., Montville T.J., Nes I.F., and Chikindas M.L. 2001. Bacteriocins: safe, natural antimicrobials for food preservation. International Journal of Food Microbiology, 71: 1-20. 30. Clinical and Laboratory Standards Institute. 2006. Methods for dilution antimicrobial susceptibility tests for bacteria that grow aerobically. Approved standard M7–A7. Clinical and Laboratory Standards Institute, Wayne, Philadelphia, USA. 31. Coton, M., Coton E., Lucas, P., and Lonvaud, A. 2004. Identification of the gene encoding a putative tyrosine decarboxylase of Carnobacterium divergens 508. Development of molecular tools for the detection of tyramine-producing bacteria. Food Microbiology, 21: 125-130. 32. Coton, M., Romano A., Spano G., Ziegler K., Vetrana C., Desmarais C., LonvaudFunel A., Lucas P., and Coton E. 2010. Occurrence of biogenic amine-forming lactic acid bacteria in wine and cider. Food Microbiology, 27: 1078-1085. 33. Cotter, P. D., Hill C., and Ross P. 2005. Bacteriocins: developing innate immunity for food. Nature Reviews Microbiology, 3: 777-788. 34. Das, S., Ward L., and Burke C. 2008. Prospects of using marine actinobacteria as probiotics in aquaculture. Applied Microbiology Biotechnology, 81: 419-429. 35. de Las Rivas, B., Marcobal A., Carrascosa, A., and Muñoz, R. 2006. PCR detection of foodborne bacteria producing the biogenic amines histamine, tyramine, putrescine, and cadaverine. Journal of Food Protection, 69: 2509-2514. 36. Deegan, L. H., Cotter P.D., Hill C., and Ross P. 2006. Bacteriocins: biological tools for bio-preservation and shelf-life extension. International Dairy Journal, 16: 10581071. 37. del Cerro, A., Marquez I., and Prieto J.M. 2010. Genetic diversity and antimicrobial resistance of Flavobacterium psychrophilum isolated from cultured rainbow trout, Oncorhynchus mykiss (Walbaum), in Spain. Journal of Fish Diseases, 33: 285-291. 52 Beneficiario COLFUTURO 2011 38. Defoirdt, T., Boon N., Sorgeloos P., Verstraete W., and Bossier P. 2007. Alternatives to antibiotics to control bacterial infections: luminiscent vibriosis in aqualculture as an example. Trends in Biotechnology, 25: 472-479. 39. Dimitroglou, A., Merrifiel D. L., Carnevali O., Picchietti S., Avella M., Daniels C., Güroy D., and Davies S. J. 2011. Microbial manipulations to improve fish health and production-A Mediterranean perspective. Fish and Shellfish Immunology, 30: 1-16. 40. Donabedian, S. M., Thal L. A., Hershberger E., Perri M. B., Chow J.W., Bartlett P., Jones R., Joyce K., Rossiter S., and Gay K. 2003. Molecular characterization of gentamicin-resistant Enterococci in the United States: evidence of spread from animals to humans through food. Journal Clinic Microbiology, 41: 1109–1113. 41. Donohue, D. C., and Gueimonde M.. 2012. Some considerations for the safety of novel probiotics bacteria. En: “Lactic acid bacteria: microbiological and functional aspects”, 4ª edición. Lahtinen, S., Ouwehand A. C., Salminen S. and Von Wright A. (eds). CRC Press, Taylor y Francis Group, Boca Ratón, Florida, USA, pp. 423-438. 42. Dutka-Malen, S., Evers S., and Courvalin P. 1995. Detection of glycopeptide resistance genotypes and identification to the species level of clinically relevant enterococci by PCR. Journal Clinic Microbiology,. 33:1-24. 43. Eaton, T.J., and Gasson, M.J. 2001. Molecular screening of Enterococcus virulence determinants and potential for genetic exchange between food and medical isolates. Applied Environmental Microbiology. 67: 1628-1635. 44. EFSA (European Food Safety Authority). 2004. EFSA Scientific Colloquium Summary Report. QPS: qualified presumption of safety of microorganisms in food and feed. European Food Safety Authority, Brussels, Belgium. 45. EFSA. 2005a. Opinion of the Scientific Committee on a request from EFSA related to a generic approach to the safety assessment by EFSA of microorganisms used in food/feed and the production of food/feed additives. The EFSA Journal, 226:1-12. 46. EFSA. 2005b. QPS-Qualified Presumption of Safety micro-organisms in food and feed. EFSA Scientific Colloquium, Summary Report, October 2005. 47. EFSA. 2005c. Opinion of the Scientific Panel on Additives and Products or Substances used in animal feed on the updating of criteria used in the assessment of bacteria for 53 Beneficiario COLFUTURO 2011 resistance to antibiotics of human or veterinary importance. The EFSA Journal, 223:112. 48. EFSA. 2007. Opinion of the Scientific Committee on a request from EFSA on the introduction of a Qualified Presumption of Safety (QPS) approach for assessment of selected microorganisms referred to EFSA. The EFSA Journal, 587:1-16. 49. EFSA. 2008a. Scientific report of EFSA prepared by Working Group on trout welfare on animal welfare aspects of husbandry for farmed trout. Annex I to The EFSA Journal, 796:1-97.ç 50. EFSA. 2008b. Update of the criteria used in the assessment of bacterial resistance to antibiotics of human or veterinary importance; prepared by the Panel on Additives and Products or Substances used in Animal Feed (FEEDAP). The EFSA Journal, 732: 1-15. 51. EFSA. 2012. Opinion guidance on the assessment of bacterial susceptibility to antimicrobials of human and veterinary importance; prepared by the panel on Additives and products or Substances used in Animal Feed (FEEDAP). The EFSA Journal, 10(6): 2740. 52. FAO/WHO (Food and Agriculture Organization of the United Nations/World Health Organization). 2002. Joint FAO/WHO Working Group Report on drafting guidelines for the evaluation of probiotics in food. London; Ontario, Canada; April 30 and May 1, 2002. Food and Agriculture Organization of the United Nations, World Health Organization, 2002. 53. FAO. 2012. Estado Mundial de la Pesca y la Acuicultura: 2012. Roma, Italia. 54. Farzanfar, A. 2006. The use of probiotics in shrimp aquaculture. FEMS Immunological and Medical Microbiology, 48: 149-158. 55. Fimlnad, G., Johnsen L., Dalhus B., and Nissen-Meyer J. 2005. Pediocin-like antimicrobial peptides (class IIa bacteriocins) and their immunity proteins: biosynthesis, structure, and mode of action. Journal of Peptide Science, 11: 688-696. 56. Flórez, A. B., Ammor M. S., and Mayo B. 2008. Identification of tet(M) in two Lactococcus lactis strains isolated from a Spanish traditional starter-free cheese made of raw milk and conjugative transfer of tetracycline resistance to lactococci and enterococci. International Journal of Food Microbiology, 121:189-194. 54 Beneficiario COLFUTURO 2011 57. Franz, C. M. A. P., Cho G.-S., Holzapfel W. H., and A. Gálvez. 2010. Safety of lactic acid bacteria. En: “Biotechnology of lactic acid bacteria: novel applications”, 1ª edición. Mozzi, F., Raya R. R., and Vignolo G. M. (eds.). Wiley-Blackwell, Oxford, Reino Unido, pp. 341-359. 58. Fuller, R. 1989. Probiotics in man and animals. Journal of Applied Bacteriology, 66: 365-378. 59. García-Moruno, E., Carrascosa A., and Muñoz R. 2005. A rapid and inexpensive method for the determination of biogenic amines from bacterial cultures by thin-layer chromatography. J Food Prot, 68: 625-9. 60. Gatesoupe, F. J. 1999. The use of probiotics in aquaculture. Aquaculture, 180: 147165. 61. Gatesoupe, F. J. 2008. Updating the importance of Lactic Acid Bacteria in Fish Farming: Natural Occurrence and Probiotic Treatments. Journal Molecular Microbiology Biotechnology, 14: 107–114. 62. Gatlin, D. M., Li P., Wang X., Burr G.S., Castille F., and Lawrence L. 2007. Potential application of prebiotics in aquaculture. Panorama Acuícola Magazine, 5: 1014. 63. Gevers, D., Huys G., and Swings J. 2003. In vitro conjugal transfer of tetracycline resistance from Lactobacillus isolates to other gram-positive bacteria. FEMS Microbiology Letters, 225: 125-130. 64. Gibson, G. R., and Roberfroid G.R. 1995. Dietary modulation of the human colonic microbiota: introducing the concept of prebiotics. The Journal of Nutrition, 125: 140112. 65. Gilmore, M.S., Segarra, R.A., Booth, M.C., Bogie, C.P., Hall, L.R., and Clewell, D.B. 1994. Genetic structure of Enterococcus faecalis plasmid pAD1-encoded cytolytic toxin system and its relationship to lantibiotic determinants. Journal Bacteriology, 176: 7335-7344. 66. Ghittino, C., Latini M., Agnetti F., Panzieri C., Lauro L., Ciappelloni R., and Petracca G. 2003. Emerging pathologies in aquaculture: effects on production and food safety. Veterinary Research Communications, 27: 471-479. 55 Beneficiario COLFUTURO 2011 67. Gómez-Gil, B., Roque A., and Turnbull J.F. 2000. The use and selection of probiotic bacteria for use in the culture of larval aquatic organisms. Aquaculture, 191: 159-270. 68. Goyache, J., Vela A. I., Gibello A., Blanco M. M., Briones V., Gónzales S., Téllez S., Ballesteros C., Domínguez L., and Fernández-Garayzabal J. F. 2001. Lactococcus lactis subsp. lactis Infection in Waterfowl: First Confirmation in Animals. Emerging Infectious diseases, 7: 884-886. 69. Gram, L., Melchiorsen J., Spanggaard B., Huber I., and Nielsen, T.F. 1999. Inhibition of Vibrio anguillarum by Pseudomonas fluorescens AH2, a possible probiotic treatment of fish. Applied and Environmental Microbiology, 65: 969-973. 70. Halász, A., Barath A., Simon-Sarkadi L., and Holzapfel, W. 1994. Biogenic amines and their production by microorganisms in food. Trends in Food Science and Technology, 5:42-49. 71. Hansen, G.H., and Olafsen J.A. 1989. Bacterial colonization of cod (Gadus morhua L.) and halibut (Hippoglossus hippoglossus) eggs in marine aquaculture. Appl. Environ. Microbiology, 55: 1435-1446. 72. Howe, R.A., Brown N.M., and Spencer R.C. 1996. The new threats of Gram positive pathogens: re-emergence of things past. Journal Clinical Pathology, 49: 444-9. 73. Hummel, A., Hertel C., Holzapfel W., and Franz C. 2007. Antibiotic Resistances of Starter and Probiotic Strains of Lactic Acid Bacteria. Appl. Environmental Microbiology, 73:3-730. 74. Irianto, A., and Austin B. 2002. Probiotics in aquaculture. Journal of fish diseases, 25:1-10. 75. Kesarcodi-Watson, A., Kaspar H., Lategan M.J., and Gibson L. 2008. Probiotics in aquaculture: the need, principles and mechanisms of action and screening processes. Aquaculture, 274: 1-14. 76. Kim, D.H., and Austin B. 2006. Innate immune responses in rainbow trout (Oncorhynchus mykiss) induced by probiotics. Fish and Shellfish Immunology, 21: 513524. 77. Kimoto, H., Ohmomo S., and Okamoto T. 2002. Enhancement of bile tolerance in Lactococci by tween 80. Journal of Applied Microbiology, 92: 41-46. 56 Beneficiario COLFUTURO 2011 78. Klare, I., Konstabel1 C., Werner1 G., Huys G., Vankerckhoven V., Kahlmeter G., Hildebrandt B., Muller-Bertling S., Witte W., and Goossens H. 2007. Antimicrobial susceptibilities of Lactobacillus, Pediococcus and Lactococcus human isolates and cultures intended for probiotic or nutritional use. Journal of Antimicrobial Chemotherapy, 59: 900-912. 79. Ladero, V., Rattray F. P., Mayo B., Martín M. C., Fernández M., and Alvarez M. A. 2011. Sequencing and transcriptional analysis of the biosinthesis gene cluster of putrescine-producing Lactococcus lactis. Applied and Environmental Microbiology, 77: 6409-6418. 80. Lankaputhra, W. E. V., and Shah N. P. 1995. Survival of Lactobacillus acidophilus and Bifidobacterium spp in the presence of acid and bile salts. Cultured Dairy Products Journal, 30: 2-7. 81. Landete, J. M., De Las Rivas B., Marcobal A., and Muñoz R. 2007. Molecular methods for the detection of biogenic amine-producing bacteria on foods. International Journal of Food Microbiology, 117: 258-269. 82. Le Jeune, C., Lonvaud-Funel A., Ten Brink H., and Van der Vossen J.M.B.M. 1995. Development of a detection system for histidine decarboxylating lactic acid bacteria on DNA probes, PCR and activity test. Journal of Applied Bacteriology, 78: 316-326. 83. Leeds, T.D., Silverstein J.T., Weber G.M., Vallejo R.L., Palti Y., Rexroad C.E., Evenhuis J., Hadidi S., Welch T.J., and Wiens G.D. 2010. Response to selection for bacterial coldwater disease resistance in rainbow trout. Journal of Animal Science, 88:1936–1946. 84. Lilly, D.M., and Stillwell R.H. 1965. `Probiotics: Growth Promoting Factors Produced by Microorganisms'. Science, 147: 747-748. 85. Lina, G., Quaglia A., Reverdy M. E., Leclercq R., Vandenesch F., and Etienne J. 1999. Distribution of genes encoding resistance to macrolides, lincosamides, and streptogramins among staphylococci. Antimicrobial Agents Chemotherapy, 43: 10621066. 86. Mansfield, G., Desai A. R., Nilson S. A., Van Kessel A. G., and Drew M. D. 2010. Characterization of rainbow trout (Oncorhynchus mykiss) intestinal microbiota and 57 Beneficiario COLFUTURO 2011 inflammatory marker gene expression in a recirculating aquaculture system. Aquaculture, 307: 95-104. 87. Marcobal, A., de las Rivas B., Moreno-Arribas M. V., and Muñoz R. 2004. Identification of the ornithine decarboxylase gene in the putrescine-producer Oenococcus oeni BIFI-83. FEMS Microbology Letters, 239: 213-220. 88. Marcobal, A., de las Rivas B., Moreno-Arribas M. V., and Muñoz R. 2005. Multiplex PCR method for the simultaneous detection of histamine, tyramine and putrescine producing lactic acid bacteria in foods. Journal of Food Protection, 68: 874878. 89. Merrifield, D. L., Dimitroglou A., Foey A., Davies S.J., Baker R.T.M., Bøgwald J.,Castex M., and Ringø E. 2010. The current status and future focus of probiotic and prebiotic applications for salmonids. Aquaculture, 302:1-18. 90. Moriarty, D. 1998. Control of luminous Vibrio species in penaeid aquaculture ponds. Aquaculture, 164: 351-358. 91. Mounir, F., Jacques Frère, K. M., and Mohamed M. 2001. Lactococcin MMFII, a novel class IIa bacteriocin produced by Lactococcus Lactis MMSII, isolated from a Tunisian dairy product. FEMS Microbiology Letters, 205: 49-55. 92. Muñoz-Atienza, E., Gómez-Sala B., Araújo C., Campanero C., del Campo R., Hernández P. E., Herranz C., and Cintas L. M. 2013. Antimicrobial activity, antibiotic susceptibility and virulence factors of lactic acid bacteria of aquatic origin intended for use as probiotics in aquaculture. BMC Microbiology, 13: 15. 93. Nayak, S. K. 2010. Probiotics and immunity: a fish perspective. Fish and Shellfish Immunology, 29: 2-14. 94. Nikoskelainen, S., Salminen S., Bylund G., and Ouwehand A. C. 2001. Characterization of the properties of human- and dairy-derived probiotics for prevention of infectious diseases in fish. Applied and Environmental Microbiology, 67: 2430-2435. 95. Nikoskelainen, S., Owehand A., Salminem S., and Bylund G. 2001. Protection of rainbow trout (Oncorhynchus mykiss) from furunculosis by Lactobacillus rhamnosus. Aquaculture, 198:229-236. 96. Ninawe, A.S., and Selvin J. 2009. Probiotics in shrimp aquaculture: avenues and challenges. Critical Reviews in Microbiology, 35: 43-66. 58 Beneficiario COLFUTURO 2011 97. Noriega, L., Cuevas I., Margolles A., and de los Reyes-Gavilán C. 2006. Deconjugation and bile salts hydrolase activity by Bifidobacterium strains with acquired resistance to bile. International Dairy Journal, 16: 850–855. 98. Ogier, J. C., and Serror P. 2008. Safety assessment of dairy microorganisms: the Enterococcus genus. International Journal of Food Microbiology, 126: 291-301. 99. Onarheim, A.M., Wiik R., Burghardt J., and Stackebrandt E. 1994. Characterization and identification of two Vibrio species indigenous to the intestine of fish in cold sea water; description of Vibrio iliopiscarius sp. nov. System Applied Microbiology, 17: 370-379. 100. Padrós, F., y Furones M.D. 2002. Patología bacteriana en piscicultura. Actualidad SEM, 34: 13-21. 101. Patel, Anil K., Singhania Reeta R., Pandey Ashok C., and Sudhir B. 2010. Probiotic bile salt hydrolase: current developments and perspectives. Applied biochemistry and biotechnology, 162:166-180. 102. Prado S., Romalde J. L., and Barja J. L. 2010. Review of probiotics for use in bivalve hatcheries. Veterinary Microbiology, 145: 187-97. 103. RingØ, E., and Gatesoupe. 1998. Lactic acid bacteria in fish: a review. Aquaculture, 160: 177-203. 104. RingØ, E., and Holzapfel W. 2000. Identification and characterization of carnobacteria associated with the gills of Atlantic Salmon (Salmo salar L.). System Applied Microbology, 23: 523-7. 105. RingØ, E., Bendiksen, H., Wesmajervi M., Olsen R., Jansen P., and Mikkelsen H. 2000. Lactic acid bacteria associated with the digestive tract of Atlantic salmon (Salmo salar L.). System Applied Microbology, 89: 317-22. 106. Ringø, E., Løvmo L., Kristiansen M., Bakken Y., Salinas I., Myklebust R., Olsen R. E., and Mayhew T. M. 2010. Lactic acid bacteria vs. pathogens in the gastrointestinal tract of fish: a review. Aquaculture Research, 41: 451-467. 107. Robertson, P. A. W., O’Dowd C., Burrels C., Williams P., and Austin B. 2000. Use of Carnobacterium sp. as a probiotic for Atlantic salmon (Salmo salar L.) and rainbow trout (Oncorhyncus mykiss, Walbaum). Aquaculture, 185: 235-243. 59 Beneficiario COLFUTURO 2011 108. Rolfe, R.D. 2000. The role of probiotic cultures in the control of gastrointestinal health. Journal of Nutrition, 130: 396S-402S. 109. Sakata, T. 1990. Microflora in the digestive tract of fish and shell-fish. In: Lesel, R. (Ed.), Microbiology in Poecilotherms. Elsevier, pp. 171–176. 110. Sahu, M.K., Swarnakumar N.S, and Sivakumar K. 2008. Probiotics in aquaculture: importance and future perspective, review. Indian J. Microbiol, 48: 299308. 111. Salminen, S., and A. von Wright. 2012. Probiotics: safety and efficacy. En: “Lactic acid bacteria: microbiological and functional aspects”, 4ª edición. Lahtinen, S., A. C. Ouwehand, S. Salminen y A. von Wright (eds). CRC Press, Taylor y Francis Group, Boca Ratón, Florida, USA, pp. 509−524. 112. Sameer, E., Hamilton N., Boyd D., and Mulvey M. 2001. Improved Primer Design for Multiplex PCR Analysis of vancomycin-resistant Enterococcus spp. Journal of Clinical Microbiology, 2367: 39-6. 113. Sanders, M. E., Akkermans L. M., Haller D., Hammerman C., Heimbach J., Hörmannsperger G., Huys G., Levy D. D., Lutgendorff F., Mack D., Phothirath P., Solano-Aguilar G., and Vaughan E. 2010. Safety assessment of probiotics for human use. Gut Microbes. 1: 164-185. 114. Shalini, M., and Rameshwar S. 2005. Antibiotic resistance in food lactic acid bacteria—a review. International Journal of Food Microbiology, 105: 281-295. 115. Silla, M.H. 1996. Biogenic amines: Their importance in foods. International Journal of Food Microbiology, 29: 213-231. 116. Spanggaard, B., Huber I., Nielsen J., Sick E.B., Pipper C.B., Martinussen T., Slieredrecht W.J., and Gram L. 2001. The probiotic potential against vibriosis of the indigenous microflora of rainbow trout. Environmental Microbiology, 3: 755-765. 117. Ringø, E., Strøm E., and Tabacheck J. 1995. Intestinal microflora of salmonids: a review. Aquaculture Research, 26: 773-789. 118. Saarela, M., Mogensen G., Fondén R., Mättö J., and Mattila-Sandholm T. 2000. Probiotic bacteria: safety, functional and technological properties, review. Journal of Biotechnology, 84: 197-215. 60 Beneficiario COLFUTURO 2011 119. Salminen, S., and A. von Wright. 2012. Probiotics: safety and efficacy. En: “Lactic acid bacteria: microbiological and functional aspects”, pp. 509 524, 4ª edición. Lahtinen, S., A. C. Ouwehand, S. Salminen y A. von Wright (eds). CRC Press, Taylor y Francis Group, Boca Ratón, Florida, USA. 120. Ten, Brink B., Damink C., Joosten H.M.J.L., and Huis In´t Veld. 1990. Ocurrence and formation of biologically acrive amines in foods. International Journal of Food Microbiology, 11: 73-84. 121. Vendrell, D., Balcázar J.L., Ruiz-Zarzuela I., De Blas I., Gironés O., and Múzquiz J.L. 2006. Lactococcus garvieae in fish: a review. Comparative Immunology, Microbiology & Infectious Diseases, 29: 177-198. 122. Verschuere, L., Rombaut G., Sorgeloos P., and Verstraete W. 2000. Probiotic Bacteria as Biological Agents in Aquaculture. Microbiology and Molecular Biology Reviews, 64: 655-671. 123. Vidal-Carou, M.H., Izquierdo-Pulido M., Martín-Morro M., and Mariné-Font A. 1990. Histamine and tyramine in meat products: relationship with meat spoilage. Food Chemistry, 37: 239-349. 124. Vine, N. G., Leukes W.D., and Kaiser H. 2004. In vitro growth characteristics of five candidate aquaculture probiotics and two fish pathogens grown in fish intestinal mucus. FEMS Microbiology Letters, 231: 145-152. 125. Vine, N. G., Leukes W. D., and Kaiser H. 2006. Probiotics in marine larviculture. FEMS Microbiology Reviews, 30: 404-27. 126. Von Wright. 2012. Genus Lactococcus. In: “Lactic acid bacteria: microbiological and functional aspects”, 4ª edición. Lahtinen, S., A. C. Ouwehand, S. Salminen y A. von Wright (eds). CRC Press, Taylor y Francis Group, Boca Ratón, Florida, USA. pp. 63-76. 127. Walther, C., Rossano A., Thomann A., and Perreten V. 2008. Antibiotic resistance in Lactococcus species from bovine milk: Presence of a mutated multidrug transporter mdt(A) gene in susceptible Lactococcus garviae strains. Veterinary Microbiology, 131: 348-357. 128. Waters, C.M., Antiporta M.H., Murray B.E., and Dunny G.M. 2003. Role of the Enterococcus faecalis GelE protease in determination of cellular chain length, supernatant 61 Beneficiario COLFUTURO 2011 pheromone levels, and degradation of fibrin and misfolded surface proteins. Journal Bacteriology, 185: 3613-3623. 129. Wiens, G. D., and Kaatari S.L. 1999. Bacterial Kidney Disease (Renibacterium salmoninarum). Fish Diseases and Disorders, 3: 269-301. 130. Zhou, J.S., Gopal P.K., and Gill P.K. 2001. Potential probiotic lactic acid bacteria Lactobacillus rhamnosus (HN001), Lactobacillus acidophilus (HN017) and Bifidobacterium lactis (HN019) do not degrade gastric mucin in vitro. International Journal of Food Microbiology, 63: 81-90. 62 Beneficiario COLFUTURO 2011 VI. APÉNDICES VI.1. LISTADO DE TABLAS Tabla II.1. Identificación, origen y fase de desarrollo de aislamiento de la colección de 75 cepas de L. lactis aisladas de trucha arcoíris y su ambiente acuícola…………………………..17 Tabla II.2. Puntos de corte o breakpoints (mg/l) establecidos para determinar la susceptibilidad (sensibilidad/resistencia) de Lactococcus lactis frente a diversos antibióticos…………………………………………….………………………………………..19 Tabla II.3. Condiciones de PCR y oligonucleótidos específicos para la detección de los determinantes genéticos transmisibles que confieren resistencia a diversos antibióticos de relevancia en acuicultura y medicina humana y veterinaria…………………………………....21 Tabla II.4. Condiciones de PCR y oligonucleótidos degenerados para la detección de los determinantes genéticos que codifican la histidina descarboxilasa (HDC), tirosina descarboxilasa (TDC), ornitina descarboxilasa (ODC) y lisina descarboxilasa (LDC)…………………………………………………………………………………………...23 Tabla III.1. Sensibilidad/resistencia de 75 cepas de Lactococcus lactis frente a los principales antibióticos empleados en acuicultura, medicina humana y veterinaria………………………..30 Tabla III.2. Evaluación mediante PCR de la presencia de genes de resistencia a la tetraciclina (poner genes) en las 18 cepas de L. lactis que mostraron resistencia a este antibiótico mediante el método de microdilución en placa (CMI)……………………………………………………35 Tabla III.3. Identificación, origen y fase de desarrollo de las 15 cepas de L. lactis aisladas de trucha arcoíris y su ambiente acuícola seleccionadas por su seguridad in vitro………………..44 63 Beneficiario COLFUTURO 2011 VI.2. LISTADO DE FIGURAS Figura 3.1. Determinación fenotípica de la actividad hemolítica de cultivos de Lactococcus lactis LT75 (1) en placas de agar sangre………………………………………………………..27 Figura 3.2. Determinación de la actividad proteolítica de Lactococcus lactis LT71 (1), LT72 (2), LT73 (3), LT74 (4) y LT75 (5)..............................................................................................28 Figura 3.3. Determinación fenotípica de la actividad mucinolítica de L. lactis LT46 (1) en placas de agar B con mucina……………………………………………………………………29 Figura 3.4. Porcentajes de sensibilidad/resistencia de las 75 cepas de cepas Lactococcus lactis frente a los principales antibióticos empleados en acuicultura y medicina humana y veterinaria.....................................................................................................................................33 Figura 3.5. Electroforesis en gel de agarosa del producto de PCR (994bp) correspondiente al gen vanB que codifica la resistencia a la vancomicina, empleando el ADN genómico de Lactococcus lactis LT21 (1), LT23 (2) y LT24 (3)……………………………………………..34 Figura 3.6. Electroforesis en gel de agarosa del producto de PCR correspondiente al gen tetK que codifica la resistencia a la tetraciclina, empleando el ADN genómico de las cepas de Lactococcus lactis LT38 (1), LT40 (2), LT41 (3), LT42 (4), LT43 (5), LT44 (6), LT45 (7), LT46 (8), LT53 (9), LT54 (10), LT58 (11), LT59 (12), LT60 (13), LT63 (14), LT66 (15), LT68 (16) y LT70 (17)………………………………………………………………………………………..36 Figura 3.7. Electroforesis en gel de agarosa del producto de PCR correspondiente al gen tetL que codifica la resistencia a la tetraciclina empleando el ADN genómico de las cepas de Lactococcus lactis LT38 (1), LT40 (2), LT41 (3), LT42 (4), LT43 (5), LT44 (6), LT45 (7), LT46 (8), LT53 (9), LT54 (10), LT58 (11), LT59 (12), LT60 (13), LT63 (14), LT66 (15), LT68 (16) y LT70 (17)……………………………………………………………………………………………...36 64 Beneficiario COLFUTURO 2011 Figura 3.8. Electroforesis en gel de agarosa del producto de PCR correspondiente al gen tetT que codifica la resistencia a la tetraciclina empleando el ADN genómico de las cepas de Lactococcus lactis LT38 (1), LT40 (2), LT41 (3), LT42 (4), LT43 (5), LT44 (6), LT45 (7), LT46 (8), LT53 (9), LT54 (10), LT58 (11), LT59 (12), LT60 (13), LT63 (14), LT66 (15), LT68 (16) y LT70 (17)………………………………………………………………………………………..37 Figura 3.9. . Electroforesis en gel de agarosa del producto de PCR correspondiente al gen tetO que codifica la resistencia a la tetraciclina empleando el ADN genómico de las cepas de Lactococcus lactis LT38 (1), LT40 (2), LT41 (3), LT42 (4), LT43 (5), LT44 (6), LT45 (7), LT46 (8), LT53 (9), LT54 (10), LT58 (11), LT59 (12), LT60 (13), LT63 (14), LT66 (15), LT68 (16) y LT70 (17)……………………………………………………………………………………….37 Figura 3.10. Determinación fenotípica de la desconjugación de las sales biliares en L. lactis LT7 (1), LT9 (2), LT10 (3) y LT11 (4) en placas de MRS suplementado con L-cisteína y taurodeoxicolato………………………………………………………………………………...39 Figura 3.11. Determinación fenotípica de la producción de tiramina por cepas de Lactococcus lactis LT24 (1), LT25 (2), LT26 (3), LT29 (4), LT10 (5), LT18 (6), LT37 (7), LT33 (8), LT39 (9) y LT36 (10).............................................................................................................................41 Figura 3.12. Electroforesis en gel de agarosa del producto de PCR correspondiente al gen que codifica la enzima tirosina descarboxilasa (tdc), empleando los cebadores TD5/TD2 y el ADN genómico de Lactococcus lactis LT3 (1), LT10 (2), LT11 (3), LT12 (4) LT14 (5), LT33 (6), LT54 (7) y otras cepas de L. lactis no incluidas en este estudio (8, 9, 10, 11, 12, 13, 14, 15 y 16)……………………………………………………………………………………………….42 65 Beneficiario COLFUTURO 2011