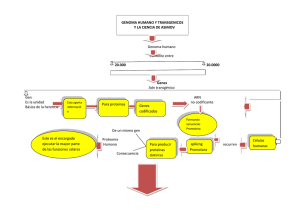
Descarga de la revista completa en formato pdf
Anuncio

! ! ! Volumen 7 ¦ Número 150 Monografía 2-2014 " MONOGRAFÍA CAZADORES DE GENOMAS ! ! "! #! $! ! ! ! #! %! $! %! #! %! #! $! #! %! #! ! ! ! ! ! $! #! "! %! "! %! #! #! $! #! %! #! $! #! ! "! "! $! "! "! %! #! ! #! ! ! ! ! ! ! ! ! ! ! ! #! #! #! %! $! #! #! "! %! $! #! "! $! %! "! ! $! $! $! #! #! $! %! %! #! $! %! #! %! "! #! Autor de la ilustración: Moisés Donoso Revista de divulgación científica open-access Equipo Editorial y Créditos Co-Editores: José María Pérez Pomares [email protected] Biología del desarrollo y cardiovascular Coordinación general- Editoriales- Entrevistas Miguel Ángel Medina Torres [email protected] Biología Molecular y de Sistemas-BiofísicaBioquímica Coordinación general- Editoriales- MonitorMaquetación Encuentros en la Biología Revista de divulgación científica (Indexada en Dialnet) Edición electrónica: www.encuentros.uma.es Correspondencia a: Miguel Ángel Medina Torres Departamento de Biología Molecular y Bioquímica Facultad de Ciencias Universidad de Málaga 29071 Málaga [email protected] [email protected] ! Entidad editora: Universidad de Málaga Editado SIN FINANCIACIÓN INSTITUCIONAL Depósito Legal: MA-1.133/94 ISSN (versión electrónica): 2254-0296 ISSN (versión impresa): 1134-8496 Diseño: Raúl Montañez Martínez [email protected] Periodicidad: Comité editorial ejecutivo: Alicia Rivera [email protected] Neurobiología Enfermedades neurodegenerativas Ana Grande [email protected] Genética-Virología, Patogénesis virales Rincón del doctorando Antonio Diéguez [email protected] Filosofía de la Ciencia A Debate-Recensiones Carmen González [email protected] Biblioteconomía Calidad y difusión Enrique Viguera [email protected] Genética- Genómica Monográficos-Eventos especiales Héctor Valverde Pareja [email protected] Biología evolutiva molecular Coordinación de espacios Web José Carlos Dávila [email protected] Biología Celular -Neurobiología ¿Cómo funciona? Juan Carlos Aledo [email protected] Bioquímica-Biología Molecular, Energética de procesos biológicos Vida y obra Juan Carlos Codina [email protected] Microbiología, Educación Secundaria Ciencias en el Bachillerato Luis Rodríguez Caso [email protected] Técnicas de Laboratorio Calidad y difusión Ramón Muñoz-Chápuli [email protected] Biología del desarrollo y cardiovascular Coordinación de edición electrónica- Foros de la Ciencia ! Comité editorial asociado: Alberto Martínez [email protected] Educación Ambiental, E. para el Empleo Alejandro Pérez García [email protected] Microbiología, Interacción planta-patógeno Enrique Moreno Ostos [email protected] Ecología- Limnología Félix López Figueroa [email protected] Ecología-Fotobiología, Cambio climático Francisco Cánovas [email protected] Fisiología Molecular Vegetal, Bioquímica y Biología Molecular Jesús Olivero [email protected] Zoogeografía, Biodiversidad animal Juan Antonio Pérez Claros [email protected] Paleontología Margarita Pérez Martín [email protected] Fisiología Animal Neurogénesis Encuentros en la Biología publica 4 números ordinarios (uno por trimestre) y al menos 1 número extraordinario monográfico al año. María del Carmen Alonso [email protected] Microbiología de aguas, Patología vírica de peces María Jesús García Sánchez [email protected] Fisiología Vegetal, Nutrición mineral María Jesús Perlés [email protected] Geomorfología, Riesgos medioambientales M. Gonzalo Claros [email protected] Bioquímica-Biología Molecular y Bioinformática Raquel Carmona [email protected] Ecofisiología, Biorremediación Salvador Guirado [email protected] Biología Celular-Neurobiología Trinidad Carrión [email protected] Ciencias de la Salud, E-Salud El equipo editorial de esta publicación no se hace responsable de las opiniones vertidas por los autores colaboradores. Vol.7 ¦ Nº 150-Monográfico MONOGRAFÍA CAZADORES DE GENOMAS! ! Monografía 2-2014 ! EDITORIAL Encuentros en la Biología alcanza su número 150. Para celebrar esta pequeña efemérides de gran importancia para quienes mantenemos este proyecto editorial, este número “especial” se torna monográfico alrededor de la temática Cazadores de genomas. El editor invitado para esta manografía es Luis Rodríguez Caso, componente del Comité Editorial Ejecutivo de esta revista y uno de los responsables de su área de “Calidad y difusión”. En un empeño personal, Luis ha conseguido la participación de los más destacados científicos españoles implicados en proyectos genoma. Es un orgullo para el equipo editorial de Encuentros en la Biología contar con la colaboración de c i e n t í fi c o s d e l a t a l l a y reconocimiento internacional de los doctores, Carles Lalueza Fox, Carlos López Otín o Pere Puigdomenech. Ellos, como el resto de colaboradores lo han hecho de forma completamente altruista, “robando” un poco de su preciado tiempo para atender amablemente a la invitación que se les hizo a participar en este número monográfico. Al primer genoma mesolítico, los genomas y el cáncer y el genoma del melón, comentados por estos tres autores, se unen otras contribuciones relevantes sobre el genoma del tomate, el del lince ibér ico, los de dos tortugas, el genoma de los geminivirus y el genoma de B u c h n e ra a p h i d i co l a ( q u e representó el primer proyecto genoma made in Spain). El monográfico se completa con una exhaustiva contribución sobre el ensamblaje de genomas, que incluimos dentro de la sección Cómo funciona. A pesar de su carácter monográfico, en el presente número 150 de Encuentros en la Biología no faltan los Foros de la ciencia, La imagen comentada y la sección Monitor y aparece una nueva entrega de la sección Los premios dedicada a glosar los premios Nobel de Química y Medicina o Fisiología de 2014 . !Los co-editores Índice Editorial 117 Foros de la Ciencia 118 La imagen comentada 119 Monitor 120 Editorial invitado: Presentación del número monográfico 121 Primer genoma mesolítico europeo 123 Cáncer, genes y genomas 127 Abriendo el genoma del melón 131 Genoma del tomate 133 La genómica al rescate del lince ibérico 136 La secuenciación de los genomas de dos tortugas 139 Primer genoma made in Spain 143 Premio Nobel de Química 2014 146 Genomas de geminivirus 147 Ensamblaje de genomas 151 Premio Nobel de Medicina o Fisiología 2014 157 Apéndice: Perfil de los autores 159 Vol.7 ¦ Nº 150-Monográfico 117 ! Foros de la ciencia Científicos desnudos: No, esto no tiene nada que ver con los recortes en los presupuestos de investigación. Los científicos desnudos son un grupo de jóvenes investigadores y periodistas de la Universidad de Cambridge que utilizan la radio convencional y la Red para divulgar la ciencia a todos los niveles, con simpatía pero también con rigor. Su lema es "Ayudar a la gente a disfrutar de la ciencia tanto como ellos y, al mismo tiempo, divertirse". Los científicos desnudos tienen un programa en la BBC los domingos por la tarde (no a altas horas de la madrugada, como es habitual en los programas de divulgación científica en España) 118 q u e a l c a n z a u n a a u d i e n c i a potencial de seis millones de personas en Inglaterra y que es seguido por muchos millones de personas más a través de Internet, ya que se edita como podcast. Desde 2007 han registrado 40 millones de descargas de sus podcasts. Este programa y su labor de divulgación les ha merecido varios premios nacionales e internacionales, como el Premio a la Comunicación Científica de la Federación de Biociencias en 2006, el Premio Kohn de la Royal Society en 2008, El Premio Europeo al mejor podcast no comercial y el Premio a la Comunicación Científica de la Sociedad de Biología en 2012. El grupo también organiza un ciclo de conferencias (Naked Science at Borders) que imparten algunos de l o s m á s c é l e b r e s c i e n t í fi c o s británicos. Os recomendamos de forma especial su web ( http:// www.thenakedscientists.com ) desde la que os podéis descargar los podcasts de los programas de radio, los vídeos de las conferencias, leer artículos de actualidad o participar en los foros científicos, en los que se generan debates en todos los campos de la ciencia. ¡Sólo en los foros de Ciencias de la Vida hay registrados más de 60.000 entradas! Otras secciones interesantes son las de preguntas científicas, a la que es posible suscribirse, y "Ciencia en la cocina", que enseña a hacer experimentos en casa (como construir una lámpara de lava o un motor eléctrico, ilusiones ópticas, o la ciencia de las palomitas de maíz). Recomendamos especialmente este foro a nuestros estudiantes por una razón más. Los nuevos títulos de graduado en ciencias exigen un cierto nivel de inglés, que de todas formas ya se ha vuelto necesario para el mundo actual. Los científicos desnudos, a través de sus podcasts os proporcionan una excelente opor tunidad para practicar la comprensión del inglés científico, co n e l a ñ a d i d o d e l a p u l i d a pronunciación de la Universidad de Cambridge. ! Ramón Muñoz-Chápuli [email protected] Instrucciones para los autores !"#$%&'()"#!"#$%"&'()*%"*+,*-.(+(/0,#%(#*+"#,*-.'/"/'0+#1*%#,$%)%+2%#2'3*+2'$4#2%#35$6"#"6%+"#7#"//%('-.%4#."(#8.96"(#+5&%2"2%(#/'%+:;/"(#1*%# ,*%2"+#'+)%$%("$#)"+)5#"#%()*2'"+)%(#/565#"#,$53%(5$%(#2%#)52"(#."(#<$%"(#2%#."#-'5.5=>"?#@2%6<(#2%#."#&%$('0+#'6,$%("4#."#$%&'()"#)"6-'A+#(%# ,*%2%# /5+(*.)"$# %+# .>+%"# %+# BC,DEEFFF?%+/*%+)$5(?*6"?%(E?# 1$,+2$.%'* 3%')(",* 3$%4%* 3$5+.#,'* %"* %++,# ('%6,$%# 1*%# /*6,."# ."(# ('=*'%+)%( normas a la hora de elaborar sus originales: G525(#.5(#6"+*(/$')5(#2%-%$<+#(%$#'+A2')5(#5#/5+)"$<+#/5+#."#"*)5$'H"/'0+#%I,$%("#2%.#5$="+'(65#1*%#,5(%"#.5(#2%$%/B5(#2%#$%,$52*//'0+?# @2%6<(4#2%-%+#)%+%$#".=*+"#$%."/'0+#/5+#%.#5-J%9&5#2%#."#$%&'()"#K.5(#1*%#('6,.%6%+)%#$%L%J%+#5,'+'5+%(#(%#$%/B"H"$<+#2'$%/)"6%+)%K?# M.#35$6")5#2%.#25/*6%+)5#,*%2%#(%$#NGO4#PQRESTG#US,%+SV/%W#5#TSX#UY'/$5(5Z#R5$2W?#T%-'25#"#."(#$%()$'//'5+%(#2%#%(,"/'54#."#%I)%+('0+# 2%# .5(# 6'(65(# +5# 2%-%# (*,%$"$# ."(# [\]]# ,"."-$"(^# %+# /"(5# /5+)$"$'54# %.# %2')5$# (%# $%(%$&"# %.# 2%$%/B5# 2%# 2'&'2'$.5# %+# &"$'"(# ,"$)%(# 1*%# ","$%/%$<+#%+#+86%$5(#2'(9+)5(?# X"2"#/5+)$'-*/'0+#/5+()"$<#2%#*+#:)*.54#"*)5$#5#"*)5$%(4#7#(*#;.'"/'0+#U(')*"/'0+#"/"2A6'/"^#'+(9)*/'0+#*#5$="+'(65#2%#";.'"/'0+^#2'$%//'0+# ,5()".#/56,.%)"^#/5$$%5#%.%/)$0+'/5^#)%.A35+5W?# _"$"#2'3%$%+/'"$#."#";.'"/'0+#2%#2'3%$%+)%(#"*)5$%(#*9.'/%#(>6-5.5(#U`4#a4#b4#c4#dW#2%(,*A(#2%.# +56-$%#2%#/"2"#"*)5$?## !5(#+56-$%(#2%#."(#,$5)%>+"(#(%#%(/$'-'$<+#%+#6"78(/*."(#7#$%25+2'.."#U@eX#5#@-/W?#!5(#2%#.5(#=%+%(#7#."(#%(,%/'%(#","$%/%$<+#%+#/*$('&"#U!"#4# $%&%'()*+,-(W?#G"6-'A+#(%#,5+2$<+#%+#/*$('&"#"1*%..5(#)A$6'+5(#1*%#(%#/')%+#%+#*+#'2'56"#1*%#+5#(%"#%.#/"()%.."+5?# M+# %()"# +*%&"# %)","4# /5+)%6,."65(# "/%,)"$# 1*%# "1*%..5(# "*)5$%(# 1*%# +5# )%+="+# %.# /"()%.."+5# /565# .%+=*"# 6")%$+"# ,*%2"+# $%6'9$# (*(# 6"+*(/$')5(#%+#'+=.A(?#f+"#&%H#"/%,)"254#*+#$%(*6%+#2%.#6'(65#%+#/"()%.."+5#(%$>"#%."-5$"25#,5$#%.#,$5,'5#%1*',5#%2')5$'".?## !"(# )"-."(4# ;=*$"(4# 2'-*J5(# 7# 2%6<(# %.%6%+)5(# =$<;/5(4# %+# -."+/5# 7# +%=$5# ,*$5(4# %(/"."(# 2%# =$'(%(# 5# /5.5$4# 2%-%$<+# "2J*+)"$(%# %+# ;/B%$5(# '+2%,%+2'%+)%(?#!"(#;=*$"(4#."(#30$6*."(#7#."(#)"-."(#2%-%$<+#%+&'"$(%#%+#35$6")5(#GgOO4#hgO#5#i_h4#"#*+"#$%(5.*/'0+#2%#j]]#2,'#7#".#6%+5(#k# -')(#2%#,$53*+2'2"2?# X*"+25#(%"+#+%/%("$'"(4#."(#$%3%$%+/'"(#-'-.'5=$<;/"(#U#$,&'(#"#.5#(*65W#(%#/')"$<+#+*6%$"2"(#,5$#5$2%+#2%#","$'/'0+#%+)$%#,"$A+)%('(#2%+)$5# 2%.#,$5,'5#)%I)5?#@.#;+".#2%.#6'(654#(%#'+/.*'$<#."#(%//'0+#2%#e'-.'5=$"l"#2%#"/*%$25#/5+#%.#%(9.5#2%.#('=*'%+)%#%J%6,.5D# M'+()%'+# m4# mF%()%'+# T4# TN%'()%'+# n4# n'%$()%'+# O4# P)?# _'%$$%# M?# P",9".# '+)%=$"95+# '+# )B%# )%6,5$".# /5$)%I?# N%(# _$5/# o%*$5,B('5.# O"+"9/# P5/# [D# pqrqs4#[tup?# M+#/"(5#2%#/')"$#*+#.'-$54#)$"(#%.#:)*.5#2%-%+#'+2'/"$(%#."#%2')5$'".4#."#/'*2"2#2%#%2'/'0+#7#%.#"v5?# P'#%.#)%I)5#,$'+/',".#+5#'+/.*7%#$%3%$%+/'"(#-'-.'5=$<;/"(4#(%#$*%="#"#.5(#"*)5$%(#1*%#",5$)%+#jrp#$%3%$%+/'"(#=%+%$".%(#w,"$"#("-%$#6<(w#5#w,"$"# 6<(#'+35$6"/'0+w?# @1*%..5(# 1*%# 1*'%$"+# /5+)$'-*'$# "# ."# (%//'0+# !"# $%"&'(# )*%'(+","# 2%-%$<+# $%6'9$# *+"# .6,/%"* ('./.",+# %+# 35$6")5# %.%/)$0+'/5# /5+# *+"# $%(5.*/'0+# 6>+'6"# 2%# j]]# 2,'# 74# %+# 25/*6%+)5# ","$)%4# *+# -$%&%# /56%+)"$'5# U2%# +5# 6<(# 2%# 788* ,"."-$"(W# 2%# ."# 6'(6"?# T'/B5# /56%+)"$'5# 2%(/$'-'$<#."#'6"=%+4#2%()"/"$<#."#'+35$6"/'0+#$%.%&"+)%#1*%#",5$)"#7E5#%(,%/';/"$<#.(5#,$5/%2'6'%+)5(#)A/+'/5(#,5$#.5(#1*%#(%#/5+('=*'0?# !5(#/5r%2')5$%(#/5+('2%$"$<+#/*".%(1*'%$"#5)$"(#/5+)$'-*/'5+%(#,"$"#."(#2'3%$%+)%(#(%//'5+%(#2%#."#$%&'()"?# M+&>5#2%#/5+)$'-*/'5+%(D#%.#5$'='+".#(%#%+&'"$<#,5$#/5$$%5#%.%/)$0+'/5#"#.5(#/5r%2')5$%(#U6%2'+"x*6"?%(4#J6,%$%H,x*6"?%(W#5#"#/*".1*'%$#5)$5# 6'%6-$5#2%.#/56')A#%2')5$'".#1*%#/5+('2%$%+#6<(#"l+#".#/5+)%+'25#2%#(*#/5+)$'-*/'0+?#@*+1*%#.5#2%("/5+(%J"65(4#)"6-'A+#(%#,*%2%+#%+&'"$# ,5$#/5$$%5#5$2'+"$'5#UY'=*%.#y+=%.#Y%2'+"4#T%,"$)"6%+)5#2%#e'5.5=>"#Y5.%/*."$#7#e'51*>6'/"4#f+'&%$('2"2#2%#Y<."="4#st]u[#Y<."="4#M(,"v"W# "/56,"v"25(#2%#*+#XT?#o5#(%#2%&5.&%$<#+'+=8+#5$'='+".#"#.5(#"*)5$%(?# Vol.7 ¦ Nº 150-Monográfico MONOGRAFÍA CAZADORES DE GENOMAS! " Monografía 2-2014 ! LA IMAGEN COMENTADA 119 Caracterización de la interacción de la enzima histidina descarboxilasa con su inhibidor EGCG. La enzima L-histidina descarboxilasa (HDC) es responsable de la síntesis de histamina a partir del aminoácido histidina. La histamina es un mediador de procesos inflamatorios y alérgicos, y el desarrollo de compuestos antihistamínicos es un importante campo de investigación farmacológica. La epigalocatequina-3-galato (EGCG), una catequina muy abundante en el té verde, que ha demostrado ejercer diversas funciones como antiinflamarorio, antitumoral y antiangiogénico, es capaz de inhibir la actividad HDC, proporcionando un mecanismo para modular la producción de histamina. El mecanismo de inhibición se estudió in silico mediante técnicas de acoplamiento molecular (docking) y dinámica molecular. Estos estudios demostraron que el EGCG es capaz de interactuar con varios residuos claves para la actividad enzimática situados en el centro activo, así como de bloquear físicamente el canal de acceso al sitio de unión del sustrato. En la imagen se observa la estructura tridimensional de la HDC en interacción con el compuesto EGCG situado en el centro activo. Cada uno de los monómeros idénticos que conforman la enzima activa se han representado en color azul, mostrando el monómero B con transparencia para permitir observar al compuesto inhibidor (en verde) situado en el bolsillo catalítico. ! Información adicional: Jankun, J., Selman, S.H., Swiercz, R., Skrzypczak-Jankun, E. 1997. Why drinking green tea could prevent cancer. Nature, 387, 561. Pino-Angeles, A., Reyes-Palomares, A., Melgarejo, E., Sanchez-Jimenez, F. 2012. Histamine: an undercover agent in multiple rare diseases? J.Cell.Mol.Med., 16, 1947-1960. Rodriguez-Caso, C., Rodriguez-Agudo, D., Sanchez-Jimenez, F., Medina, M.A. 2003. Green tea epigallocatechin-3-gallate is an inhibitor of mammalian histidine decarboxylase. Cell Mol.Life Sci., 60, 1760-1763. Ruiz-Pérez MV, Pino-Ángeles A, Medina MA, Sánchez-Jiménez F, Moya-García A. 2012. Structural perspective on the direct inhibition mechanism of EGCG on mammalian histidine decarboxylase and dopa decarboxylase. J. Chem. Inf. Model. 52(1): 113-119. María Victoria Ruiz Pérez Investigadora postdoctoral del Departamento de Biología Molecular y Bioquímica, Universidad de Málaga. [email protected] Vol.7 ¦ Nº 150-Monográfico MONOGRAFÍA CAZADORES DE GENOMAS! # M !! onitor Las 50 estrellas de la ciencia en Twitter: Cada vez es mayor el impacto de la divulgación de la ciencia a través de las redes sociales. Recientemente, la Cada año desde revista científica Science ha publicado 1945, los premios Lasker la lista de los 50 científicos con mayor reconocen a investigadores número de seguidores en Twitter con individuales que han hecho indicación de su cuenta en dicha red grandes contribuciones a la social, su número de seguidores, el biomedicina. El pasado 8 de número de citas, su índice K y el Septiembre se ha hecho públicos la número total de tweets. El primero en nómina de premiados en la la lista es el astrofísico Neil deGrasse convocatoria 2014 del premio Lasker Tyson, con más de dos millones en cada una de sus tres categorías. cuatrocientos mil seguidores en El premio Lasker de investigación Twitter, superando en casi un millón biomédica básica ha sido concedido de seguidores al segundo de la lista, a los doctores Kazutoshi Mori el físico Brian Cox. El primer biólogo (Universidad de Kioto, Japón) y Peter aparece en tercera posición. No Walter (Universidad de California en resulta sorprendente que se trate del www.nature.com/focus/Lasker/ San Francisco, Estados Unidos) por polémico (y polemista) Richard 2014/index.html sus descubrimientos sobre la Dawkins, quien cuenta con más de denominada unfolded un millón de seguidores. Ningún otro proteína response, un sistema científico supera la barrera del millón de control de calidad (ni siquiera, la del medio millón) de endocelular que detecta seguidores en Twitter. Del resto de proteínas mal plegadas en el científicos incluidos dentro de esta retículo endoplásmico y lista, 23 de ellos son especialistas en licita vías de señalización algún área de las ciencias biológicas. que promueven en el núcleo Enlace: http://http:// la puesta en acción de news.sciencemag.org/scientificmedidas correctivas. community/2014/09/top-50-scienceEl premio Laskerstars-twitter DeBakey de investigación médica clínica ha sido concedido a los doctores Mahlon R. DeLong (Colegio Médico Universitario de Emory, Estados Unidos) por el desarrollo de un sistema de estimulación cerebral profunda del núcleo subtalámico, una técnica quirúrgica que reduce los temblores y restaura la función motora de pacientes con enfermedad de Parkinson avanzada. El premio LaskerKoshland por logros especiales en ciencias médicas ha sido concedido a la doctora Mary-Claire King (Universidad de Washington, Seattle, Estados Unidos) por diversas contribuciones imaginativas e importantes a las ciencias médicas y los derechos humanos. Ella Premios Lasker 2014: 120 descubrió el locus génico BRCA1 ligado al cáncer de mama hereditario y desarrolló estrategias técnicas basadas en el DNA que ha permitido el reencuentro de personas desaparecidas o sus restos con sus familiares. Como viene siendo habitual en los últimos años, el número de octubre de la revista Nature Medicine dedica una sección especial a estos galardones. La información en este caso incluye una editorial un artículo de presentación escrito por el Nobel Jospeh Goldstein y entrevistas a cada uno de los cinco galardonados. Toda esta información está libremente disponible en la URL de la revista. Enlace: http://http:// ! Miguel Ángel Medina [email protected] Vol.7 ¦ Nº 150-Monográfico MONOGRAFÍA CAZADORES DE GENOMAS! Monografía 2- 2014 EDITORIAL INVITADO: UN PRODIGIO EN EL LIBRO DE LA VIDA-PRESENTACIÓN DEL NÚMERO MONOGRÁFICO " " " " Desde la creación del Premio Nobel tan solo cuatro investigadores han conseguido por segunda vez hacerse con este preciado galardón. Ocho proezas que guardan algunos de los logros tecnológicos que más amplitud y desarrollo han tenido en la era moderna: dos para la radiactividad [M. Curie; Physics 1903, Chemistry 1911], y dos para los semiconductores [J. Bardeen; Physics 1956, Physics 1972], uno sobre la naturaleza del enlace químico y su configuración en la estructura de moléculas complejas y otro por la paz, precisamente contra el desarrollo de armamento nuclear [L. Pauling; Chemistry 1954, Peace 1 9 6 2 ] y fi n a l m e n t e d o s galardones que fueron otorgados al desarrollo y avance de la secuenciación de proteínas y ácidos nucleicos, en el primer caso con la determinación de la secuencia aminoacídica de la insulina [FredericK Sanger; Chemistry 1958] y en el segundo (de forma compartida con Walter Gilbert) por su contribución en la secuenciación de ácidos n u c l e i c o s . [ F. S a n g e r ; Chemistry 1980]. En la lectura del segundo premio Sanger también nombró a los galardonados en 1959 con el Nobel en Fisiología o Medicina [Arthur Korgberg y Severo Ochoa] por su contribución en la descripción de la síntesis enzimática del ADN y ARN respectivamente. Posiblemente la comunidad científica tomara buena nota por aquel entonces de lo que precisamente Linus Pauling ya había avanzado diez años antes [L Pauling; Science 1949]: un cambio conformacional en una proteína, en este caso la hemoglobina modificada en enfermos con anemia falciforme, podía ser producido por un cambio alélico en un único gen implicado en su síntesis. Lo cierto es que se hacía necesario conocer el valor de la información que se transmite en la herencia desde el ADN hasta las proteínas, ya que nuestra salud podía ir en ello. " A principio de los 70 Frederick Sanger ya trabajaba en el desarrollo de un método para la determinación de secuencias de nucleótidos de ADN. El método fue primeramente aplicado a la determinación de la secuencia del DNA del bacteriofago ΦX174. El molde fue el ADN circular de cadena simple (6000 nc) del fago y su cebador el octanucleótido ACCATCCA. La reacción de síntesis fue llevada a cabo por la DNA polimerasa I de E coli, en presencia de manganeso y nucleosidostrifosfatos; al menos uno de los cuatro ! radiactivamente " con marcado 32P y sustituyendo uno de los desoxinucleótidostrifosfatos (dGTP o dCTP) por su r i b o n u c l e ó t i d o correspondiente, de manera que fuera posible su separación mediante el uso de ribonucleasas específicas y su posterior identificación en un gel de electroforesis. En 1976 publicó el artículo A Rapid Method for Determining Sequences in DNA [Sanger F et al. J. Mol. Biol, 1976] y en 1977 tras haber reemplazado el método de sustitución de ribonucleótidos por el de finalización de la secuencia de elongación mediante el uso de 2’3’ dideoxnucleótidos trifosfato [Sanger F et al. Proc. Nati. Acad. Sci. USA, 1977] p u b l i c a fi n a l m e n t e l a secuencia completa del bacteriófago ΦX174 [Sanger F et al. Nature, 1977], lo cual determinará sin lugar a dudas su camino hacia su segundo Nobel. " Pocos años bastaron para automatizar el método de secuenciación desarrollado p o r Fr e d e r i c k S a n g e r y aproximadamente dos décadas para la publicación de las secuencias genómicas de muchos de los principales organismos modelo: bacteria: H. influenzae; Fleischmann RD et al. Science 1995, levadura: S. cerevisiae; Goffeau A et al. Nature 1997, Nematodo: C. elegans; The C. elegans Sequencing Consortium. Science 1998, Mosca del vinagre: D. melanogaster; Myers EW et al. Science 2000, Pl a nt a : A , t h a l i a n a; Th e Arabidopsis Genome Initiative; Vol.7 ¦ Nº 150-Monográfico 121 " MONOGRAFÍA CAZADORES DE GENOMAS! Humano: H. sapiens; International Human Genome Sequencing Consortium. Nature 2001 & Venter JC et al Science 2001, Ratón: M. musculus; Mouse Genome Sequencing Consortium. Nature 2002, y Rata: R. norvegicus; Rat Genome Sequencing Consortium. Nature 2004, por destacar algunos. La carrera para el desarrollo de la siguiente generación tecnológica para la secuenciación genómica estaba así en marcha y a partir de entonces cualquier grupo con recursos suficientes, en muchos casos consorcios, tiene ya capacidad para abordar la secuenciación de un organismo vivo o extinto, y desarrollar en el intento una tecnológica analítica y computacional impensable hasta la fecha. En la actualidad existen varias bases de datos que recogen información detallada sobre los diferentes proyectos de secuenciación realizados o en fase de realización tanto de genomas completos o parte de ellos, exomas, transcriptomas o patologías como el cancer: NCBI [Genome database of Nacional Center for Biotechnology Information], GOLD [Genomes Online Database of DOE Joint Genome Institute ] o The Wellcome Trust Sanger Institute databases, entre otras. " 122 La repercusión de este hecho en el conocimiento humano marca un antes y un después, que ya es posible apreciar hoy en día: una de las consultoras globales con más prestigio e influencia internacional publicó recientemente un interesante informe sobre el potencial económico que alcanzarán en 2025 los avances tecnológicos que transformaran la vida y la economía global del mundo [McKinsey & Company; Disruptive Technologies 2013]. Guardando las distancias sobre lo que nos deparará el futuro dentro de aproximadamente 3 ó 4 proyectos de investigación, lo interesante es que el séptimo lugar se llama Next-generation genomics, posición señalada por su bajo coste tecnológico y rapidez alcanzada en la secuenciación de genes, su gran valor analítico y su influencia en el área de la biología sintética, en la agricultura, en el desarrollo de compuestos con alto potencial productivo como los biocombustibles y por supuesto en el área de la medicina; gracias al tratamiento personalizado con base genética y, esto es aun más llamativo, no esencialmente como hasta ahora; mediante ensayo y error, sino a través de la comparación sistemática de variaciones genéticas entre poblaciones. Visto desde hoy, un prodigio en el libro de la vida. " A continuación Encuentros en la Biología presenta una mirada monográfica a la aportación que han tenido y tienen en este importante campo científico y tecnológico los investigadores españoles, discutiendo la posición de sus trabajos en el campo de la genómica y su percepción acerca del futuro de sus descubrimientos. Conoceremos de la mano de sus autores la importancia que tiene la búsqueda y descripción de los pequeños genomas de virus, el significado vital y evolutivo del concepto de genoma mínimo, y de lo que supone a nivel productivo hacerse con el genoma del melón y del tomate, sabremos lo que significa a nivel de especie dilucidar el genoma de la tortuga, del lince ibérico y de nuestros antepasados, tendremos nuestro propio manual para el ensamblaje de genomas y sabremos mucho más sobre la genómica del cáncer. " He de agradecer, por último, la generosidad con la que todos los autores han participado en la realización de este número especial. Muchos de los lectores podrán reconocer en este número el recordado título Cazadores de Microbios, de Paul de Kruif, publicado en 1986 dentro de la colección Biblioteca Científica Salvat. Con todo ello he querido dejar aquí mi particular homenaje al reconocido trabajo y labor pionera de los que a continuación conoceremos con el título de Cazadores de Genomas (en España). " Editor invitado de este número monográfico: Luis Rodríguez Caso Vol.6 ¦ Nº 150-Monográfico MONOGRAFÍA CAZADORES DE GENOMAS! Monografía 2- 2014 El primer genoma mesolítico europeo: cuando éramos cazadores-­‐ recolectores Carles Lalueza-Fox Instituto de Biología Evolutiva, CSIC-Universitat Pompeu Fabra, Barcelona [email protected] ! Estamos acostumbrados a ver documentales donde aparecen grupos de cazadores-­‐recolectores en ambientes como desiertos o selvas que para nosotros son exó9cos; sin embargo, hace apenas 8.000 años todos los habitantes de Europa eran también cazadores-­‐recolectores. Este modo de vida desapare-­‐ ció con la llegada del neolí9co, que se había originado en el Próximo Oriente unos dos mil años antes. El neolí9co e caracteriza por la domes9cación de plantas y animales y por la consiguiente sedentariza-­‐ ción de las poblaciones. Estos factores favorecen un incremento demográfico y permiten que las pobla-­‐ ciones agricultoras se expandan rápidamente por áreas climá9cas favorables a este modo de producción, reemplazando o mezclándose con las poblaciones locales de cazadores-­‐recolectores. Al cabo de pocos miles de años, todos los europeos son agricultores y ganaderos. Es evidente que el cambio de vida con-­‐ lleva adaptaciones que 9enen que verse reflejadas a nivel gené9co. La dieta es menos proteica y en al-­‐ gunos casos se basa casi exclusivamente en cereales; aparecen con el 9empo nuevos recursos alimen9-­‐ cios como los lácteos, obtenidos de los animales domes9cados. Estos mismos animales nos transmiten una serie de enfermedades infecciosas que son algunas de las más comunes que nos afligen en la actua-­‐ lidad. Las epidemias se hacen frecuentes debido también a que las poblaciones son más grandes y se-­‐ dentarias. Quizás también se seleccionan rasgos cogni9vos relacionados con la estructuración social, y no solo se domes9can algunos animales sino también los humanos. En defini9va, nuestro modo de vida actual 9ene que haber comportado cambios metabólicos, dietarios e inmunológicos que 9enen que ver-­‐ se reflejados en los genomas de los europeos actuales. Nosotros somos primariamente los descendientes de dichos neolí9cos. Nuestros genomas son, en buena medida, los genomas de aquellos que hace miles de años sobrevivieron a las primeras epidemias. Pero es evidente que no se trata de una subs9tución completa: algunos no podemos digerir la leche y otros 9enen problemas con el gluten de los cereales. Es por todo esto que a priori resultaba interesante poder analizar un genoma europeo de antes del neolí9co, para saber qué había cambiado con la llegada de la agricultura. En 2013, el único genoma prehistórico europeo que disponíamos era el genoma de Ötzi, el llamado Hombre del Hielo. Se trata del cuerpo de un hombre de la Edad del Cobre (hace unos 5.300 años) hallado en 1991 en los Alpes del Tirol y conservado de forma espectacular en el hielo. Era lógico que, dadas las condiciones de conservación (ya que el frío ayuda a preservar el ADN), se intentara recuperar primero este genoma. Pero Ötzi es un individuo del neolí9co tardío, y sigue sin informarnos de cómo eran los europeos antes de la transición mesolí9co-­‐neolí9co. Unos años antes, en 2006, unos espeleólogos exploraron una pequeña cavidad situada en la cordillera cantábrica, cerca de los municipios leoneses de La Braña-­‐Arintero. Después de adentrarse una treintena de metros por un estrecho pasadizo, encontraron un esqueleto casi completo depositado en conexión anatómica en una pequeña repisa. A escasos metros, en el fondo de un pequeño pozo ver9cal, había otro esqueleto. Ambos correspondían a varones de edad adulta. Algunos detalles, como una estalagmita que había crecido sobre algunos de los huesos, les hicieron pensar que podrían ser bastante an9guos. La difusión de la no9cia en los medios locales llevó a la Junta de Cas9lla y León a organizar la dibcil excava-­‐ ción de los dos esqueletos (que fueron bau9zados como La Braña 1 y 2, o más informalmente, por los periodistas locales como Ataúlfo y Wenceslao), dirigida por Julio Manuel Vidal Encinas. Al re9rar los res-­‐ tos del segundo individuo aparecieron numerosos caninos atróficos de ciervo perforados. Estos dientes son un ornamento fpico de los cazadores mesolí9cos, quienes los llevaban cosidos a las ves9mentas. La posterior datación por carbono-­‐14, que dio fechas cercanas a los 7.000 años antes del presente, confir-­‐ mó esta atribución. 123 ! Vol.7 ¦ Nº 150-Monográfico MONOGRAFÍA CAZADORES DE GENOMAS! 124 Figura : Los esqueletos de La Braña 1 (superior) y La Braña 2 (inferior) tal como fueron descubiertos en 2006. Autor de las fotos: Julio Manuel Vidal Encina. ! Vol.7 ¦ Nº 150-Monográfico MONOGRAFÍA CAZADORES DE GENOMAS! ! Monografía 2- 2014 En aquellos momentos las nuevas tecnologías de secuenciación masiva en paralelo (también denomi-­‐ nadas “second genera9on sequencing”) todavía se estaban implementando y con una aproximación clá-­‐ sica basada en la reacción en cadena de la polimerasa (o PCR) solo era posible recuperar pequeños fragmentos del ADN mitocondrial de estos individuos. Exisfan ya algunas secuencias mesolí9cas del cen-­‐ tro y norte de Europa, que mostraban una notable uniformidad gené9ca: todas eran de los linajes mito-­‐ condriales U4 o U5; entre estos úl9mos, muchos tenían sorprendentemente el mismo haplo9po U5b2. Esto indicaba que, con toda probabilidad, los mesolí9cos europeos eran muy uniformes gené9camente, y esto sólo era posible si imaginábamos poblaciones muy móviles a lo largo de una gran área geográfica. En el año 2013 empezamos a probar diversas muestras del individuo de La Braña 1 con la intención de secuenciarlo completamente, y conseguimos localizar una librería genómica, construida a par9r de las raíces dentales del tercer molar superior derecho, que tenía un contenido de ADN cercano al 50%. Es decir, de cada cien secuencias que generábamos con la plataforma de Illumina, cerca de la mitad eran humanas (el resto, como ocurre en todas las muestras an9guas, era mayoritariamente secuencias bacte-­‐ rianas). Esta elevada eficiencia es muy inusual en muestras an9guas de una edad similar (e incluso más recientes), y sólo puede atribuirse a que las excepcionales condiciones del yacimiento, asociadas a la al-­‐ tura, la estabilidad térmica y la baja temperatura, han contribuido a conservar el material gené9co en-­‐ dógeno. Después de varias reacciones de secuenciación con la plataforma Illumina conseguimos recupe-­‐ rar el genoma con una cobertura de 3,4x. Es una cobertura baja pero suficiente para llevar a cabo diver-­‐ sos 9pos de análisis evolu9vos. Empezamos mirando un listado de genes que habían sido descritos como el producto de selección reciente en europeos actuales. Nuestra intención era ver si el individuo de La Braña tenía los alelos an-­‐ cestrales (es decir, idén9cos a las poblaciones africanas) o los derivados (idén9cos a los europeos). Entre estos úl9mos, sorprendentemente, aparecían diversos genes del sistema inmunitario que se habían aso-­‐ ciado con resistencia a patógenos. Claramente, gran parte de los desabos inmunológicos que habían modelado el genoma de los europeos actuales eran anteriores a la llegada del neolí9co. Esto significaba también que si estamos interesados en estudiar los cambios adapta9vos producidos por la transmisión de patógenos desde los animales domes9cados a los humanos, debemos de buscarlos entre aquellos genes alelos ancestrales presentes en las muestras de La Breña. Entre este 9po de genes con el alelo ancestral en La Braña aparecían, sorprendentemente, los dos genes (SLC45A2 y SLC24A5) que 9enen un papel esencial en la pigmentación clara de los europeos. Las variantes derivadas estan esencialmente fijadas en los europeos actuales . Ampliamos la lista a otros ge-­‐ nes de pigmentación que intervienen en el cabello y de forma minoritaria en la piel y descubrimos que este individuo mesolí9co seguía presentando en muchos de ellos las variantes africanas. Con toda pro-­‐ babilidad, y en contra de lo que se creía hasta el momento, la pigmentación clara todavía no exisfa o no se había generalizado en el mesolí9co. Las sorpresas no habían terminado allí: descubrimos que al mis-­‐ mo 9empo La Braña poseía las variantes gené9cas en los genes HERC2/OCA2 que en los humanos actua-­‐ les producen los ojos azules. Es decir, nuestro individuo tenía la piel oscura y los ojos azu-­‐ les, en un background gené9co que por otra parte era inequívocamente europeo (en rigor, más cercano a los norte-­‐europeos que a cualquier otra población actual). No es posible saber el grado exacto del tono de la piel, pero claramente tenía que ser más oscuro que los europeos actuales pero quizás no tan oscuro como los africanos sud-­‐ saharianos. En todo caso, se trata de un feno9po que ya no existe en las poblaciones europeas actuales. Los resultados del análisis de este primer genoma mesolí9co podrán confirmarse con la secuenciación de más muestras en el futuro, pero ahora mismo ofrecen una idea de la potencialidad que 9enen los estudios paleogenómicos para reconstruir los procesos migratorios y adapta9vos de las poblaciones humanas, incluyendo la euro-­‐ pea. 125 ! Bibliografía para saber más: Olalde, I., Allentoft, ME., Sánchez-Quinto, F., Santpere, G., Chiang, CWK., DeGiorgio, M., Prado-Martínez J Rodríguez, JA., Rasmussen S., Quilez, J., Ramírez, O., Marigorta, U.M., Fernández, M., Prada, ME., Vidal Encinas, JM., Nielsen, R., Netea, MG, Novembre, J., Sturm, RA., Sabeti, P., MarquèsBonet, T., Navarro, A., Willerslev, E., Lalueza-Fox, C. (2014). Derived Immune and Ancestral Pigmentation Alleles in a 7,000-Year-old Mesolithic European. Nature. Doi:10.1038/nature12960 Vol.7 ¦ Nº 150-Monográfico MONOGRAFÍA CAZADORES DE GENOMAS! 126 Vol.7 ¦ Nº 150-Monográfico MONOGRAFÍA CAZADORES DE GENOMAS! Monografía 2- 2014 Cáncer, genes y genomas Carlos López-Otín Departamento de Bioquímica, Facultad de Medicina Instituto Universitario de Oncología, Universidad de Oviedo, 33006-Oviedo [email protected] El cáncer es una enfermedad cuya capacidad para hacernos sentir vulnerables parece aumentar cada día. Las previsiones de la Organización Mundial de la Salud para el año 2020 hablan de 16 millones de nuevos diagnósticos y 10 millones de víctimas mortales. Sin embargo, pese a estos números abrumadores que casi asemejan el cáncer a una epidemia moderna, no estamos ante una patología reciente, basta recordar su origen para convencernos de ello. En efecto, tras la formación de las primeras células hace más de tres mil millones de años, la vida en nuestro planeta transcurrió en un ámbito exclusivamente unicelular. Milenio tras milenio, la vida unicelular dominó la Tierra hasta que hace unos 800 millones de años, una de estas células primigenias compartió con éxito su vida con otras semejantes, iniciando el proceso que las condujo a construir organismos multicelulares. Fue también en ese momento cuando comenzaron a gestarse las primeras vías que más tarde conducirían al cáncer. !! !El origen del cáncer !La adquisición de la pluricelularidad fue un indudable logro evolutivo al que debemos nuestra propia vida. Sin embargo, el proceso de generación de seres pluricelulares dejó necesariamente algunas deficiencias moleculares que nos proporcionaron ventajas evolutivas, pero que simultáneamente nos abocaron a la posibilidad de desarrollar procesos tumorales. El cáncer surge cuando una sola de los billones de células que cons- truyen nuestro cuerpo se transforma, pierde su sentido altruista y se multiplica sin control intentando destruir al organismo al que hasta entonces contribuyó a modelar. Entre las deficiencias mecanísticas intrínsecas a nuestra propia naturaleza pluricelular podemos señalar la falta de fidelidad en los mecanismos de replicación y reparación del ADN, la existencia de una compleja red de señalización inter- e intracelular susceptible de sufrir múltiples alteraciones y el mantenimiento en nuestros órganos y tejidos de un cierto número de células -incluyendo las células madre adultas- con gran potencial proliferativo o invasivo. Estas células son necesarias para afrontar procesos fisiológicos fundamentales como el desarrollo embrionario y además, participan activamente en el mantenimiento y defensa del organismo. La pérdida de los controles que permiten que la función de estas células se mantenga siempre en unos límites apropiados, conlleva la adquisición de las propiedades mitogénicas e invasivas características de las células transformadas que conforman los tumores malignos. !Afortunadamente, nuestro progreso evo- 127 lutivo también nos ha proporcionado una serie de mecanismos biológicos para tratar de minimizar el potencial tumoral derivado de estas deficiencias surgidas de la pluricelularidad. Entre ellos podemos citar la capacidad replicativa finita de las células, la cuantiosa inversión en sistemas de reparación del daño genético, los programas de apoptosis o la eficacia de nuestro sistema inmune antitumoral. Pese a ello, es una realidad el hecho de que los organismos pluricelulares desarrollan tumores malignos, y en el caso de nuestra especie, con una frecuencia que ha venido aumentando en las últimas décadas. ¿Por qué sucede esto? Muy probablemente porque hemos ido adquiriendo una gran capacidad de interferir con nuestra propia naturaleza biológica a través de cambios en la dieta, exposición a agentes cancerígenos, o simplemente, por un incremento Vol.7 ¦ Nº 150-Monográfico MONOGRAFÍA CAZADORES DE GENOMAS! notable en la esperanza de vida en buena parte de las sociedades actuales. !En suma, el cáncer es un proceso muy an- 128 tiguo que surge como consecuencia inevitable de nuestra propia evolución. Aunque sólo podemos aventurar los mecanismos moleculares que generaron los primeros tumores, parece claro que el cáncer nos ha acompañado desde el principio de nuestra historia como especie. Más aún, los paleopatólogos han encontrado indicios de tumores óseos malignos en vértebras de dinosaurios del periodo Mesozoico, avalando la idea de la antigüedad de los procesos tumorales. También desde el principio, la búsqueda de soluciones frente al problema del cáncer ha sido amplia y diversa. Así, la cirugía, y después la quimioterapia y la radioterapia, aportaron respuestas precisas y evitaron que las palabras cáncer y muerte fuesen términos inseparables dentro de la misma ecuación, de forma que hoy muchos tumores malignos pueden curarse. Las últimas estadísticas indican que más del 50% de los pacientes con cáncer sobreviven a la enfermedad. Sin embargo, todos tenemos la triste certeza de que la curación de otros tumores nos obliga necesariamente a la exploración de soluciones adicionales. !! !Cáncer y Biología Molecular !Hace poco más de tres décadas, destaca- dos científicos intuyeron que la Biología Molecular también podía aportar nuevas respuestas al problema del cáncer. En efecto, los avances en esta disciplina han contribuido a desvelar secretos importantes de los procesos tumorales y nos han mostrado que, esencialmente, el cáncer es el resultado de la acumulación de daño genético o epigenético en oncogenes, genes supresores y genes de mantenimiento de la integridad del ADN. También hemos aprendido que este daño se hereda de nuestros progenitores en un pequeño porcentaje de casos, pero que en la mayoría de las ocasiones se adquiere a lo largo de la vida por agresiones externas como las radiaciones solares, el tabaco, algunos virus, o simplemente por azar. Además, varias décadas de investigación molecular en Biología tumoral nos han enseñado que, tras la impresionante variabilidad clínica y biológica de los tumores malignos, hay una serie de características bioquímicas adquiriVol.7 ¦ Nº 150-Monográfico das por las células transformadas y compartidas por la mayoría de los tumores. Entre ellas podemos citar la adquisición de mecanismos autónomos de proliferación, la insensibilidad a las señales de inhibición del crecimiento celular, la generación de estrategias de resistencia a la apoptosis, la reprogramación metabólica, la deficiente o exagerada respuesta inmune a las células tumorales, la superación de la barrera de la mortalidad por reactivación de la telomerasa, el desarrollo de programas de angiogénesis que aporten el oxígeno y los nutrientes requeridos para la progresión tumoral y finalmente, la adquisición de una capacidad letal de invadir otros territorios corporales y generar metástasis. En efecto, una vez que las células tumorales alcanzan el torrente sanguíneo y se extienden por el cuerpo, la progresión tumoral se torna prácticamente irreversible. !Tras esta información biológica básica so- bre los mecanismos de progresión del cáncer, subyace el deseo de encontrar respuestas clínicas para tratar aquellos tumores para los que la Medicina todavía no ha encontrado respuestas. La resolución de la estructura tridimensional de las distintas proteínas asociadas al cáncer, la exploración de estrategias de letalidad sintética para diseñar terapias combinadas, el diseño de chips genéticos que permiten el análisis global de los cambios en la actividad génica durante la progresión de la enfermedad y la creación de animales transgénicos humanizados en los que se pueden examinar los mecanismos de desarrollo del cáncer y los efectos de nuevos fármacos antitumorales, constituyen aspectos que han dirigido muchos estudios recientes en el campo de la investigación oncológica. Sin embargo, la extraordinaria complejidad del cáncer nos obliga a ampliar nuestra mirada científica más allá de todas las aproximaciones actuales. En este sentido, el nuevo proyecto de los genomas del cáncer, constituye un hito fundamental en la investigación oncológica. El proyecto pretende determinar la secuencia completa de nucleótidos de al menos 500 genomas tumorales de pacientes con cada uno de los MONOGRAFÍA CAZADORES DE GENOMAS! tipos de cáncer más frecuentes, incluyendo enfermos con leucemia linfática crónica que es el proyecto que se está realizando en España bajo la dirección del Dr. E. Campo en el Hospital Clínico de Barcelona y de nuestro propio grupo en la Universidad de Oviedo. !! ! El paisaje genético de la leucemia linfática crónica !La leucemia linfática crónica (LLC) es el tipo de neoplasia hematológica más frecuente en adultos y provoca la acumulación de linfocitos B en la sangre, la médula ósea, los nódulos linfáticos y el bazo. Los avances en el conocimiento de la biología molecular del cáncer durante las últimas décadas han permitido determinar que se trata de una enfermedad producida por la acumulación de daños genéticos en las células normales, pero hasta ahora la identificación de dichos cambios era un proceso lento y laborioso. Sin embargo, gracias a las nuevas tecnologías de secuenciación de ácidos nucleicos este proceso se ha acelerado de manera extraordinaria y nos ha permitido determinar la secuencia completa del genoma de las células tumorales de diversos pacientes con LLC y su comparación con la secuencia del genoma de las células sanas de los mismos individuos. Esta aproximación nos ha permitido comprobar que cada tumor ha sufrido más de mil mutaciones en su genoma. El posterior análisis de los genes mutados en un grupo de más de 300 pacientes con LLC nos ha llevado a identificar la existencia de varias mutaciones recurrentes, de forma que los mismos genes se encuentran dañados en distintos pacientes. Además, en algunos casos se han detectado exactamente las mismas mutaciones en pacientes distintos, lo cual es realmente extraordinario si recordamos que nuestro genoma posee 3.000 millones de nucleótidos y cualquiera de ellos podría ser susceptible de ser dañado. Entre los genes recurrentemente mutados hemos identificado los denominados NOTCH1, SF3B1, POT1, MYD88, XPO1 y SI, alguno Monografía 2- 2014 de los cuales no se habían encontrado alterados previamente en ningún tipo de cáncer, avalando así la relevancia de estas nuevas estrategias genómicas no dirigidas por hipótesis pero capaces de generarlas una vez analizados cuidadosamente los múltiples datos generados. Además, es importante resaltar que estudios paralelos nos han permitido definir las alteraciones epigenéticas más significativas de los pacientes con LLC, destacando fundamentalmente el hallazgo de la existencia de una reprogramación epigenética masiva en las células tumorales de estos enfermos que conduce a una hipometilación general en regiones no-promotoras de numerosos genes. !Finalmente, y pese al escaso tiempo transcurrido desde el inicio de este proyecto, debemos enfatizar que ya han comenzado a vislumbrarse sus importantes aplicaciones clínicas. Así, los resultados del proyecto genoma LLC, sumados a los de proyectos equivalentes sobre otros tumores, han permitido abrir una nueva vía hacia la identificación de los genes mutantes a los que los tumores se vuelven adictos, los cuales se están convirtiendo así en dianas preferentes de intervención terapéutica. Además, se han podido descubrir nuevos procesos, nuevos mecanismos y nuevas interacciones génicas que probablemente conducirán a nuevos tratamientos cuyas raíces surgirán de este viaje de exploración científica al minúsculo mundo nuclear en el que habitan los genomas. La investigación del cáncer entra así en una nueva era que promete la adquisición de un nuevo y profundo nivel de conocimiento científico pero que no oculta el largo camino que todavía debe recorrerse. Por ello, hay que entender que el desciframiento del genoma de los tumores malignos no va a representar la curación rápida y definitiva de todos los tipos de cáncer que hoy nos afectan, sino la posibilidad de ofrecer a los oncólogos toda la información biológica y molecular posible acerca de cada tumor, que facilite la futura instauración de los tratamientos más adecuados para cada paciente. Para lograr este objetivo todavía deberán superarse una serie de barreras científicas, técnicas y económicas que limitan las posibilidades actuales de estos proyectos. Además, esta mirada genómica global a la biografía del cáncer deberá completarse con complejos estudios funcionales que permitan definir cuáles son las mutaciones impulsoras o conductoras de la transformación maligna y cuáVol.7 ¦ Nº 150-Monográfico 129 MONOGRAFÍA CAZADORES DE GENOMAS! les son las denominadas pasajeras que actúan únicamente como meras acompañantes del proceso tumoral. En cualquier caso, y pese a estas incertidumbres que no son nunca ajenas al avance de la Ciencia, esperamos que el enorme progreso que se pretende alcanzar a través del estudio de los genomas del cáncer, llegue a ofrecer nuevas ! respuestas a las numerosas cuestiones todavía abiertas en torno a una enfermedad que hace sentir muy de cerca la vulnerabilidad humana, pero que puede abordarse con una nueva perspectiva en esta fascinante era genómica que hemos comenzado a vivir. !! 130 Lecturas recomendadas para saber más: Kulis M et al “Epigenetic analysis detects widespread gene-body DNA hypomethylation in chronic lymphocytic leukemia” Nature Genetics 44: 1236-1242 (2012) Puente XS and López-Otín C “The evolutionary biography of chronic lymphocytic leukemia” Nature Genetics 44: 1236-1242 (2012) Puente XS et al "Whole-genome sequencing identifies recurrent mutations in chronic lymphocytic leukemia” Nature 475: 101-105 (2011) Quesada V et al “Exome sequencing identifies recurrent mutations of the splicing factor SF3B1 gene in chronic lymphocytic leukemia” Nature Genetics 44: 47-52 (2012) Ramsay AJ, Quesada V, Foronda M, Conde L, Martínez-Trillos A, Villamor D, Rodríguez D, Kwarciak A, Garabaya C, Gallardo M, López-Guerra M, López-Guillermo A, Puente XS, Blasco MA, Campo E, and López-Otín C. “POT1 mutations cause telomere dysfunction in chronic lymphocytic leukemia” Nature Genetics 45: 526-530 (2013) Vol.7 ¦ Nº 150-Monográfico MONOGRAFÍA CAZADORES DE GENOMAS! Monografía 2-2014 ! !"#$%&'()%*)+%&(,-)'%*),%*.&) Pere Puigdomènech i Rosell Centre de Recerca en Agrigenómica (CRAG), CSIC-IRTA-UAB-UB Campus de la Universidad Autónoma de Barcelona, 08193 Bellaterra [email protected] Desde que Mendel formuló sus leyes en 1865 sabemos que la información que se transmite de padres a hijos, que nos hace iguales entre los individuos de una especie y que también nos hace diferentes unos de otros puede analizarse con unas leyes sencillas. Desde principios del siglo XX llamamos genes a las unidades de información hereditaria. Desde justo después de la Segunda Guerra Mundial sabemos que los genes están escritos en el DNA y en su famosa doble hélice. Desde principios de los 70 sabemos aislar los genes, amplificarlos y modificarlos. Todo este proceso nos ha permitido acumular una cantidad de información muy precisa sobre qué son los genes, cuántos tenemos, cómo expresan su información para convertirla en aquello que da lugar a un organismo vivo y por qué a veces no funcionan y producen enfermedades. Hasta hace pocos años íbamos conociendo gen a gen, descubriendo su estructura y cómo interviene en el funcionamiento de un ser vivo. Era cómo entrar en una mina con una luz muy fina, descubrir una piedra preciosa y admirarla con detalle. Pero ahora ha ocurrido que hemos desarrollado posibilidades para observar todos los genes de prácticamente cualquier organismo. Es como entrar en esta mina y encender una luz que la ilumina toda entera. El resplandor es extraordinario, pero ahora nuestro trabajo es entender este conjunto y utilizarlo en beneficio de todos. El desarrollo de los proyectos genoma ha seguido el desarrollo de las tecnologías de secuenciación de los ácidos nucleicos. Desde que se supo que la información genética estaba escrita en las cuatro letras que representan los componentes del DNA, el interés por conocer la secuencia de éste fue creciendo. La secuencia es el listado de los cuatro componentes del DNA (A, C, T y G) que de forma ordenada y lineal almacenan lo que define los genes de cualquier organismo. En la década de los 80 las técnicas de secuenciación fueron haciéndose más sencillas hasta automatizarse. En los 90 ya se conoció la secuencia de un virus y se planteó la secuencia, primero de una bacteria y más tarde de la levadura, que se publicó en 1996. Pronto se emprendió la secuenciación del genoma de un vegetal, la planta modelo Arabidopsis thaliana y del genoma humano, proyectos que en su momento habían parecido inabordables. Siguieron los genomas de las especies animales y vegetales de mayor interés. Es en este entorno que se planteó abordar el proyecto de secuenciar el genoma del melón, el primer proyecto de esta naturaleza que se ha llevado a cabo en España. Las razones para plantearse secuenciar el genoma del melón son múltiples y se basan en cuestiones de índole científica, económica y técnica. El melón es una especie que ha sido estudiada desde el punto de vista genético incluso antes de Mendel. En las Cucurbitáceas se definieron algunos de los conceptos clave para la Genética gracias a la variabilidad que se observa en estas especies. Existe una buena información sobre las bases genética de caracteres interesantes y se habían desarrollado ya herramientas útiles como un mapa genético. Pero además el melón es un cultivo importante en el mundo y en España. Las Cucurbitáceas (melón, sandía, pepino, calabazas) son el segundo grupo de especies hortícolas en importancia tras las Solanáceas (tomate, pimiento, berenjena, además de la patata). España es el quinto productor mundial de melón y el primer exportador. Su semilla es híbrida y tiene un alto valor comercial, por tanto el interés industrial en la especies es alto. Finalmente se sabía que es un genoma de tamaño medio (unas 450 megabases) y por tanto abordable con las técnicas de que se disponía en aquel momento. El proyecto se emprendió en el marco de una iniciativa que coordinó y financió en casi un 50% la Fundación Genoma, el resto de financiación la aportaron cinco Comunidades Autónomas (Andalucía, Castilla-la Mancha, Cataluña, Madrid y Murcia) y cinco empresas (Semillas Fitó, Syngenta, Sistemas Genómicos, Savia Biotech y Roche). Lo realizaron 14 grupos de investigación de distintos centros y universidades españolas con el apoyo inicial de grupos americanos que aportaron tecnología no publicada en el tratamiento de secuencias. La tecnología que se utilizó en la secuenciación del genoma del melón está basada en el uso de las nuevas técnicas de secuenciación masiva. En éstas se producen centenares de miles o millones de secuencias relativamente cortas y el trabajo consiste en ensamblar el conjunto del genoma. Para ayudar el trabajo se decidió utilizar una variedad denominada diplohaploide que no contiene las variaciones genéticas que se producen en los cruces entre dos progenitores. 131 Vol.7 ¦ Nº 150-Monográfico MONOGRAFÍA CAZADORES DE GENOMAS! 132 El uso de las técnicas de secuenciación masiva permite conseguir el resultado de forma mucho más rápida y más económica, por lo que el resultado final se consiguió publicar dentro de la duración del proyecto y además de la secuencia de referencia se obtuvieron otras seis secuencias de variedades distintas, lo cual permite explorar la variabilidad que existe en la especie. Una vez se obtiene la secuencia de un genoma termina una etapa del trabajo de secuenciación propiamente dicho pero comienza el trabajo para extraer la información que interesa. De hecho estos proyectos tienen como objetivo construir una base datos de la que extraer la información que queramos para la investigación biológica o para la mejora de la especie. En primer lugar hay que encontrar los genes que se hallan en la secuencia. Para ello hay programas informáticos que predicen donde hay un gen y si se conocen genes parecidos en otras especies. En el caso del melón se han encontrado unos 26000 genes, un número muy parecido a otras especies de plantas y similar también al número de genes que tiene el genoma de la especie humana. Este bajo número de genes en especies complejas como la nuestra es una de las sorpresas que han dado estos proyectos. En las bases de datos se presentan los genes predichos y se anotan con la información que esté disponible de ellos. En realidad éste es un trabajo que tiene que ir rehaciéndose ya que la calidad de las secuencias puede siempre mejorar y la información que se dispone de los genes va creciendo continuamente. Desde luego si se hace este trabajo es para sacar partido de él. Un genoma de buena calidad y bien anotado es útil en muy diferentes direcciones. Desde un punto de vista del conocimiento nos permite, por ejemplo, comparar genomas entre sí. En el caso de las Cucurbitáceas se dispone ahora de dos genomas completos el del pepino y el del melón. El primero (de 350 Mbases) es más pequeño que el segundo (de 450 Mbases). Su comparación permite observar como se forman los genomas y se expanden por diferentes mecanismos. Si además podemos comparar genomas de variedades dentro de una misma especie, esto nos permite examinar con detalle como varían las especies casi en tiempo real. Pero si el estudio de genomas interesa a los científicos también las empresas invierten en ellos y esto debe ser porque el conocimiento de los genomas les da una ventaja competitiva. La razón de ello es que la agricultura moderna se basa en variedades que para el agricultor tienen la garantía de que son resistentes a enfermedades, de que van a producir granos o frutos de las características que esperan los consumidores o de que van a tener los rendimientos adecuados. Estos son caracteres genéticos más o menos fáciles de interpretar en términos genómicos. Disponer de la secuencia del genoma proporciona unas herramientas que para el productor de semillas permite avanzar en la obtención de aquellas que el agricultor desea de forma más rápida y dirigida. Esta es la razón del interés industrial en los genomas de las plantas de mayor cultivo. En el caso del melón los caracteres que interesan al agricultor son por una parte caracteres de calidad como la forma, el tamaño, los aromas, el sabor, que en general dependen de un número relativamente grande de genes. Pero interesan también los genes de resistencia a enfermedades. El melón sufre del ataque de virus, hongos o bacterias que es posible evitar si las variedades son resistentes a ellas. Una de las sorpresas de la secuenciación del genoma del melón es el bajo número de genes de resistencia comparando con otras especies que pueden tener genomas incluso menores. Ello indica que estas especies tienen una estrategia específica para defenderse de las enfermedades y del ataque de los predadores. Es obvio que esta estrategia tiene éxito ya que se trata de especies que han sobrevivido en entornos muy diversos. El genoma de que se dispone permite diseñar experimentos para analizar estas características. La era de los genomas nos da una herramienta poderosa par conocer la bases moleculares del funcionamiento de los organismos, incluyéndonos a nosotros mismos. Pero también para conocer las especies en las que basamos nuestra alimentación y para proseguir el proceso de mejora en que se basa nuestra agricultura. Nuestra sociedad se basa en el cultivo de un reducido grupo de especies que identificamos hace 10000 años y que hemos transformado hasta dar lugar a las especies productivas en que basamos nuestra alimentación. El conocimiento que nos da la genómica constituye una esperanza de que podamos afrontar los retos complejos como el aumento de la población, el cambio climático, etc, que se nos van a plantear en los años que se avecinan. Con esta nueva herramienta podemos abordar la mejora de las especies de las que nos alimentamos de forma más dirigida y rápida. Por ello un nuevo genoma es una puerta abierta al descubrimiento de las bases de biológicas de los fenómenos que controlan el crecimiento de las especies cultivadas y también al desarrollo de nuevas variedades que respondan a las necesidades de nuestra agricultura. Vol.7 ¦ Nº 150-Monográfico MONOGRAFÍA CAZADORES DE GENOMAS! Monografía 2-2014 !"#$"%&'('$"(')*#+,$"-./"#+*#+/#$%.0+(&.#1+# ,+(2+*('"(')*#1+/#&.3"&+#0#1+#,2#$"%'+*&+# 34,#$%)5'3.#!"#$%&$%'())%*+)%,&# Antonio Granell Richart Instituto de Biología Molecular y Celular de Plantas de Valencia, Universidad Politécnica de Valencia [email protected] ! Este creo que ha sido el primer genoma de planta de cultivo en cuya secuenciación nuestro país ha participado significativamente; ha sido un camino largo y tortuoso, pero lo importante es que hemos obtenido un recurso importante para la comunidad científica y además fue portada en la revista “Nature”. Nos comprometimos a participar en el proyecto internacional de secuenciación del genoma del tomate en el 2003. Siendo España a la sazón el principal exportador europeo de tomate en fresco era natural pesar en su inclusión. Y también influyó claro, el que relacionado con su importancia estratégica existieran en nuestro país grupos de investigación reconocidos que utilizaban el tomate como sistema modelo. El proyecto de secuenciación nació tras una reunión que tuvo lugar en Washington ese mismo año y en la que científicos representantes de una serie de países consideramos de interés el obtener una secuencia de calidad del genoma del tomate que sirviera como referencia para ésta y otras Solanáceas entre las que se incluyen plantas de claro interés agrícola como el pimiento, la berenjena, la petunia, etc. Lograrlo se consideraba como fundamental para entender la diversidad y adaptación de las Solanáceas a ambientes muy diversos que van desde los desiertos como el Atacama a la pluviselva y del litoral hacia alturas superiores a los 4000 m, y también para entender las bases genéticas de los caracteres de interés agronómico. Todo ello permitiría mejorar la calidad y tolerancia de los cultivos de Solanáceas en unas condiciones de clima cambiantes. La secuenciación pues se planteó desde el principio como un proyecto de alto interés científico que podría tener importante repercusiones económicas y que permitiría acelerar y dirigir los programas de mejora. A pesar de las reticencias iniciales por parte de algunos socios, se acordó que no solo la secuenciación tenía que ser una tarea consorciada, sino que además la información tenía que ser liberada al dominio público tan pronto como su calidad fuera contrastada. La idea era generar un recurso que estuviera disponible a toda la comunidad: ese recurso tenía que ser fácilmente accesible, sin restricciones y de alta calidad para ser realmente útil. Para ello se habilitó un portal web donde se iban depositando las secuencias, y que se iba actualizando y refinando con anotaciones de forma continuada. [http://solgenomics.net/]. La secuenciación se realizó inicialmente utilizando tecnología de Sanger que permitía lecturas largas de alta calidad sobre colecciones de BACs que representaban el genoma del tomate de la variedad Heinz en fragmentos de unas 130kb. Esta estrategia respondía a que las regiones ricas en genes se localizan, en el caso del tomate, en regiones eucromáticas distales de los cromosomas, las cuales están bastante delimitadas de las heterocromáticas pericentrométricas, por lo que se propuso secuenciar solo los BACs que mapeaban en las regiones eucromáticas ricas en genes. El método consistía pues en identificar para cada cromosoma de los 12 del tomate una serie de BACs distribuidos a lo largo de las regiones eucromáticas e ir irradiando a partir de esos BACs semillas a los siguientes, basándose en una serie de técnicas como fingerprints, secuencias de los extremos de BACs, etc, para elegir el BAC contiguo con mínimo solapamiento. Esa forma de hacer las cosas era la clásica en el momento inicial del proyecto, producía secuencias de alta calidad pera era muy costosa y lenta. Nuestro grupo fue encargado de la secuenciación del cromosoma 9 y nos pusimos a seleccionar, confirmar y secuenciar los BACs correspondientes a este cromosoma con la participación de una empresa española de secuenciación. Con la incorporación de las nuevas tecnologías de secuenciación masiva 454, Illumina, etc., que suponen un abaratamiento en la secuenciación y un incremento en el cantidad de secuencias, propusimos tomar un cambio de estrategia. 133 " Vol.7 ¦ Nº 150-Monográfico MONOGRAFÍA CAZADORES DE GENOMAS! ! 134 En 2009 un pequeño consorcio formado por grupos de Holanda, Italia, Francia, EEUU y España decidimos secuenciar no solo las regiones eucromáticas sino todo el genoma utilizando las nuevas tecnología de secuenciación de nueva generación. Nos dividimos las tareas y cada grupo construyó librerías de DNA de tamaño diferente, desde shotgun de pequeño tamaño hasta librerías de tamaños grandes para cada una de las tecnología disponibles, 454, Illumina y SOLID. Nuestro grupo se encargó de generar genotecas de 6kb para secuenciación SOLID. Cada una de las genotecas obtenidas por el consorcio se secuenció hasta que no generaban información nueva y se generaron lecturas con cada una de esas tecnologías que en global representaban 250 veces el genoma del tomate. Lo importante no era disponer de tal profundidad en la secuencia (en promedio cualquier posición debería de haberse leído pues 250 veces aunque eso no es estrictamente así), sino que las lecturas de cada tipo de librería llevaba información que facilita el ensamblado, como por ejemplo en algunos casos se obtenían lecturas apareadas correspondientes a cada uno de los extremos de cada fragmento de DNA del cual teníamos además información de la distancia entre ellas por el tamaño de la librería. Esa información es relevante ya que permite ensamblar trozos distantes cuyos huecos se irán llenando posteriormente con más lecturas. La estrategia consistió en unir primero las lecturas largas generadas por 454 y utilizar las lecturas más cortas de Illumina y SOLID para confirmar y verificar la secuencias y su posicionamiento. Dos grupos fundamentalmente en Holanda y Francia llevaron a cabo el ensamblaje global de las secuencias generadas por los diferentes participantes utilizando los ensambladores Newbler y Cabog respectivamente. El 90 % de los 950 millones de pares de bases (una tercera parte del tamaño del genoma humano) está representado en la versión actual en aproximadamente 80 contigs de secuencia continua (el ensamblaje optimo sería 24 seudo moléculas correspondientes a los 12 cromosomas con dos brazos cada uno). La tasa de error es inferior a 1 en 10000 y la mayor parte de la secuencia no ensamblada, como ocurre con otros genomas incluido el humano, el de Arabidopsis o el del arroz corresponde a secuencias altamente repetidas con pocos o ningún gen y por lo tanto en principio no muy interesante. Para que la secuencia del genoma sea útil, es necesario alinearlas con los mapas físico y genéticos y nuestro grupo del IBMCP en colaboración con el de la ISHM y otros grupos en EEUU y Italia contribuimos a ello desde nuestra experiencia con poblaciones de líneas consanguíneas y de introgresión que teníamos ampliamente genotipadas. Esto junto con localización in situ mediante FISH permitió confirmar y orientar algunos ensamblajes dudosos. La secuencia del genoma es poco útil sin una anotación adecuada que indique donde se localizan los genes, si hay indicaciones que se expresen y donde, etc. y eso fue la tarea de entre otros grupos españoles especializados localizados en el CRG y en los centros de análisis genómico y de supercomputación de Barcelona. " " " " Vol.7 ¦ Nº 150-Monográfico MONOGRAFÍA CAZADORES DE GENOMAS! Monografía 2-2014 135 A grandes rasgos la secuencia del tomate y su comparación con otros genomas secuenciados incluido uva ha permitido averiguar que el tomate ha sufrido varios eventos de triplicación y que durante el tiempo evolutivo algunos de los genes han sido seleccionados y adaptados para dotar al fruto de algunas de sus características como maduración controlada por etileno, su regulación por la luz y la acumulación de carotenoides en el fruto. De forma similar la comparación del tomate con su pariente silvestre más próximo, ha permitido averiguar que hay varios centenares de genes que producirían proteínas truncadas, seguramente no viables y que seguramente son responsables de parte de los cambios fenotípicos que se observan entre el tomate cultivado y los de S pimpinellifolium. La información de la secuencia y la anotación así como un “buscador” dotado de diferentes herramientas de búsqueda están disponibles de forma libre y sin ataduras para la comunidad científica internacional a través del portal antes indicado. Un aspecto a destacar es que fruto de este consorcio formado alrededor de la secuenciación se organizan anualmente reuniones de la comunidad de solanceas (SOL meetings), se han implementado plataformas de genotipado y analisis de expresión génica y se ha facilitado la formulación de proyectos de secuenciación de otras especies relacionadas de interés, incluida la secuenciación de numerosas otras solanaceas SOL 100, o 100 variedades para 100 cultivos. Todos estos proyectos y otros que se están planteando nos permitirán reconstruir el proceso de domesticación e identificar de forma más eficiente las bases genéticas de los caracteres de interés. En ese sentido la obtención de la secuencia ha facilitado en este ultimo año la identificación de una serie de mutaciones que afectan la calidad como por ejemplo la mutación “y” que produce mutantes de fruto rosa muy apreciados en el mercado asiático y del “uniform fruit ripening” o “u” que afecta la calidad del fruto. Estos y otros avances recientes están demostrando que el esfuerzo conjunto realizado es útil a la comunidad científica y es de esperar que aumente la precisión y acelere el ritmo de producción de nuevas variedades de mayor calidad y mejor adaptadas a las condiciones de cultivo y que satisfagan las necesidades de consumidores y productores. " Vol.7 ¦ Nº 150-Monográfico MONOGRAFÍA CAZADORES DE GENOMAS! !"#"$%&'()'*($&+"'%(',$'-"#"%&./' )"'*($0+1-"'")'.(2-"3('%()')1$-(' 145.1-&' José A. Godoy Estación Biológica Doñana, CSIC. C/ Américo Vespucio, s/n. 41092 Sevilla [email protected] ! 136 !"#"$"%&'&()#*+#,"-#.+')/,/01"-#*+#-+'2+)'&"'&()#*+#)2+3"#0+)+%"'&()#4"#"5$,&"*/#-2-.")'&",5+).+# .")./#+,#%")0/#*+#+-$+'&+-#62+#$2+*+)#-+%#'"%"'.+%&7"*"-#"#2)#)&3+,#0+)(5&'/#'/5/#+,#*+#$%/8,+5"-#"# ,/-#62+#"$,&'"%#+-./-#)2+3/-#%+'2%-/-9#:+-$2;-#*+#62+#-+#'2,5&)"-+#+,#0%")#4&./#*+#,"#-+'2+)'&"'&()#*+# 0+)/5"# 425")/<# 62+# %+62&%&(# '/,/-",+-# +-=2+%7/-# ># 2)"# 0%")# &)3+%-&()# +'/)(5&'"# '/)# ,"-# .+')/,/01"-# +?&-.+).+-#+)#+-"#;$/'"<#,"#-+'2+)'&"'&()#*+#0+)/5"-#'/5$,+./-#=2+#+?.+)*&;)*/-+#,+)."5+).+#"#/%0"@ )&-5/-#5/*+,/#$"%"#,"#&)3+-A0"'&()#B+909#%".()<#5/-'"#*+,#3&)"0%+C#>#",02)/-#/%0")&-5/-#'/)#",0D)#&).+@ %;-#+'/)(5&'/#B'2,A3/-<#0")"*/<#EC9#F+%/#'/)#,"-#.+')/,/01"-#"'.2",+-<#,"#-+'2+)'&"'&()#*+#2)#0+)/5"# )2+3/#$"%A+)*/#*+#'+%/#$2+*+#'/-."%#$/'/#5G-#*+#'&+)#5&,#+2%/-#>#,"#%+@-+'2+)'&"'&()#*+#0+)/5"-#>"# '"%"'.+%&7"*/-# %/)*"# ,/-# $/'/-# 5&,+-# *+# +2%/-9# F/%# +,,/<# "4/%"# +5$&+7")# "# 4"'+%-+# ="'A8,+-# +5$%+-"-# 62+#").+-#%+-2,."8")#&5$/-&8,+-<#'/5/#,"#-+'2+)'&"'&()#*+#0+)/5"-#&)*&3&*2",+-#$"%"#5+*&'&)"#$+%-/@ )",&7"*"<#/#,"#-+'2+)'&"'&()#*+#*&+7#5&,#0+)/5"-#*+#3+%.+8%"*/-#$"%"#'/)/'+%#+,#/%&0+)#*+#,"-#="-'&)")@ .+-#"*"$."'&/)+-#62+#4")#+3/,2'&/)"*/#+)#+-./-#/%0")&-5/-#BH"2--,+%#+.#",9#IJJKC9#L2)#"-1<#)/#*+M"#*+# -+%#,,"5"A3/#62+#,"#$%&5+%"#+-$+'&+#*+#3+%.+8%"*/#+)#3+%#-2#0+)/5"#-+'2+)'&"*/#+)#N-$"O"#)/#+-#2)# 5/*+,/#*+#&)3+-A0"'&()#8&/5;*&'"#>#'"%+'+#"$"%+).+5+).+#*+#&).+%;-#+'/)(5&'/P#+,#,&)'+#&8;%&'/<!"#$%! &'()*$+,9## !"# 3+%*"*# +-# 62+# )&)02)"# *+# ,"-# */-# "Q%5"'&/)+-# ").+%&/%+-# +-# ./.",5+).+# '&+%."P# +,# ,&)'+# A+)+# 2)# +)/%5+# 3",/%# +'/,(0&'/# ># -&58(,&'/<# ># '/)-A.2>+# 2)# 82+)# 5/*+,/# *+# &)3+-A0"'&()# +)# +,# G58&./# *+# ,"# 8&/,/01"#*+#,"#'/)-+%3"'&()9#N,#,&)'+#&8;%&'/#+-#2)"#+-$+'&+#',"3+#*+,#+'/-&-.+5"#+)#62+#4"8&."<#+,#5/).+# 5+*&.+%%G)+/<#>#-2#$%+-+)'&"#"O"*+#3",/%#+'/,(0&'/#",#+)./%)/#>#'/).%&82>+#*+#5")+%"#=2)*"5+).",#"#-2# '/)-+%3"'&()9#F+)-")*/#+)#"-$+'./-#52>#*&%+'."5+).+#%+,"'&/)"*/-#'/)#"'A3&*"*+-#425")"-#'/5/#,"# '"7"<#+,#,&)'+#5")A+)+#"#%">"#"#/.%/-#*+$%+*"*/%+-#5G-#*"O&)/-#$"%"#+,#4/58%+#'/5/#+,#7/%%/#/#+,#5+@ ,/)'&,,/<#$/%#,/#62+#4"#*+#3+%-+#5G-#'/5/#2)#",&"*/#62+#'/5/#2)#'/5$+A*/%#+)#+-.+#G58&./9#N-#2)/#*+# ,/-#5D,A$,+-#+)*+5&-5/-#*+#,"#$+)1)-2,"#&8;%&'"<#62+#-+#4"#*&=+%+)'&"*/#*+#-2-#4+%5")/-#,/-#,&)'+-#8/@ %+",+-#B"#$%!-#$%C#+)#-2#"*"$."'&()#",#',&5"#5+*&.+%%G)+/#>#-2#+-$+'&",&7"'&()#+)#+,#'/)-25/#*+#'/)+M/-9# N-# 52># '/5$,&'"*/# R># ",0/# "%%&+-0"*/@# +-."8,+'+%# 2)# 3",/%# +'/)(5&'/# '/)'%+./# "# ,"# +?&-.+)'&"# *+# 2)"# +-$+'&+<#$+%/#+,#,&)'+#&8;%&'/#+-#-&)#*2*"#2)#$".%&5/)&/#*+#)2+-.%"#*&3+%-&*"*#)".2%",<#$"%"#,"#62+#-+#4"# '/)3+%A*/#+)#-158/,/#>#+-.")*"%.+9#S#+-.+#$".%&5/)&/#+-.G#+)#0%"3+#%&+-0/#*+#$+%*+%-+9# N,#,&)'+#&8;%&'/#+-#+,#=+,&)/#5G-#"5+)"7"*/#*+,#$,")+."#>#2)/#*+#,"-#'&)'/#+-$+'&+-#*+#5"51=+%/-#+2@ %/$+/-#'".",/0"*/-#'/5/#+)#$+,&0%/#'%1A'/#$/%#,"#T)&()#U).+%)"'&/)",#$"%"#,"#V/)-+%3"'&()#*+#,"#W".2%"@ ,+7"#BUTVWC9#!"#+-$+'&+#4"#-2=%&*/#2)#&).+)-/#*+',&3+#*2%").+#,"#D,A5"#5&."*#*+,#-&0,/#XX<#*+8&*/#"#,"#*+-@ .%2''&()#*+#-2#4G8&.".#)".2%",<#+,#5/).+#5+*&.+%%G)+/<#>#,"#&).+)-"#$+%-+'2'&()#*&%+'."#"#,"#62+#=2+%/)# -/5+A*/-#,/-#$%+*"*/%+-<#&)',2-/#'/)#&)'+)A3/-#+'/)(5&'/-#*+#$%/0%"5"-#+-.".",+-#$"%"#+,#'/).%/,#*+# Y",&5"O"-Z9#L#+-."-#'"2-"-<#62+#4")#"=+'."*/#."58&;)#"#52'4"-#/.%"-#+-$+'&+-<#-+#4"#-25"*/#+)#+,#'"-/# *+,#,&)'+#,"#%+*2''&()#*+#-2#$%+-"#$%&)'&$",<#+,#'/)+M/<#$/%#-2'+-&3"-#+$&*+5&"-#3&%",+-9#!"#"''&()#'/58&@ )"*"#*+#+-./-#="'./%+-#%+,+0(#,"#+-$+'&+#"#-(,/#*/-#$/8,"'&/)+-#"&-,"*"-#B:/O")"#>#L)*DM"%C#'/)#5+)/-# *+#[JJ#&)*&3&*2/-#+)#./.",#+)#IJJI9#!/-#+-=2+%7/-#*+#'/)-+%3"'&()#&)&'&"*/-#+)#+-"#;$/'"<#Q)")'&"*/-# $/%# ,"# T)&()# N2%/$+"# "# .%"3;-# *+# -2'+-&3/-# $%/>+'./-# !U\N<# 4")# '/)-+02&*/# +3&."%# ,"# +?A)'&()# $/%# +,# 5/5+)./<# +-."8&,&7")*/# +)# $%&5+%"# &)-.")'&"# ,"-# */-# $/8,"'&/)+-# %+5")+).+-# +# &)'%+5+).")*/# $/-.+@ %&/%5+).+#+,#'+)-/#0,/8",#4"-."#-2$+%"%#,/-#]JJ#+M+5$,"%+-#+)#,&8+%."*#+)#IJ[[#B^&5/)#+.#",9#IJ[IC9#L,# 5&-5/# A+5$/<# -+# 4"# '/)-+02&*/# +-."8,+'+%# 2)"# $/8,"'&()# '"2A3"# 62+# -2$/)+# 2)"# -",3"02"%*"# *+# ,"# +-$+'&+#>#62+#+-.G#"$/%.")*/#+M+5$,"%+-#$"%"#+,#%+=2+%7/#*+#,"-#$/8,"'&/)+-#-&,3+-.%+-#>#$"%"#"'.2"'&/@ )+-#*+#%+&).%/*2''&()#+)#G%+"-#*+#$%+-+)'&"#4&-.(%&'"#B_"%0"-#+.#",9#IJJKC9#N-."-#>"#4")#'/5+)7"*/#+)# L)*",2'1"#B`2",5+,,"./<#V(%*/8"<# #>#`2"%%&7"-<#a"+)C#>#+-.G)#$%/0%"5"*"-#+)#,/-#$%(?&5/-#"O/-#+)#N?@ .%+5"*2%"<#V"-A,,"@!"#b")'4"<#b2%'&"#>#F/%.20",#8"M/#+,#)2+3/#$%/>+'./#!U\N#YU8+%,&)'+Z#B4c$Pddeee9,&@ =+,&)'+9/%0C9## Vol.7 ¦ Nº 150-Monográfico ! MONOGRAFÍA CAZADORES DE GENOMAS! Monografía 2- 2014 " N,# ;?&./# *+# ,/-# +-=2+%7/-# 62+# -+# +-.G)# %+",&7")*/# $"%"# ,"# '/)-+%3"'&()# *+,# ,&)'+# &8;%&'/# $2+*+)<# -&)# +58"%0/<#62+*"%#'/5$%/5+A*/-#$/%#,"#"5+)"7"#/'2,."#*+#,"#+%/-&()#0+);A'"9#!"-#$/8,"'&/)+-#62+#-+# 4"'+)#$+62+O"-#>#-+#"1-,")#*+#/.%"-#$/8,"'&/)+-#$&+%*+)#*&3+%-&*"*#0+);A'"<#"'252,")#0+)+-#*+=+'.2/@ -/-<#>#-+#4"'+)#+)*/0G5&'"-9#N,#%+-2,."*/#+-#62+#+-."-#$/8,"'&/)+-#3+)#%+*2'&*"#-2#3&"8&,&*"*<#",#62+*"%# "=+'."*"-# )+0"A3"5+).+# ,"# -2$+%3&3+)'&"# ># ,"# %+$%/*2''&()<# ># -2# '"$"'&*"*# $"%"# "*"$."%-+# "# '"58&/-# "58&+).",+-9#N-./-#'"58&/-#0+);A'/-#-/8%+3+)&*/-#$2+*+)#$%+'&$&."%#,"#+?A)'&()#*+#,"#+-$+'&+<#&)',2-/# '2")*/#,"-#'"2-"-#D,A5"-#*+,#*+',&3+#4">")#*+-"$"%+'&*/<#*+8&*/#"#,"#%+.%/",&5+)."'&()#$/-&A3"#62+#-+# +-."8,+'+#+).%+#+,#*+.+%&/%/#*+5/0%GQ'/#>#*+.+%&/%/#0+);A'/<#2)"#*&)G5&'"#62+#-+#4"#*+-'%&./#'/5/#Y+,# 3(%A'+#*+#,"#+?A)'&()Z#BL,,+)*/%=#+.#",9#IJ[If#\%")g4"5#+.#",9#IJ[JC9#S#+-./#+-#,/#62+#$2+*+#+-."%#-2'+@ *&+)*/# '/)# +,# ,&)'+# &8;%&'/9# !"-# */-# $/8,"'&/)+-# *+# ,&)'+# 62+# 4")# -/8%+3&3&*/# 4"-."# ,"# =+'4"# 52+-.%")# -&0)/-#*+#+%/-&()#0+);A'"#>#3"%&/-#&)*&'&/-#"$2).")#"#62+#$2+*+#+-."%#'/5$%/5+A*"#,"#%+$%/*2''&()#># ,"#-2$+%3&3+)'&"<#-/8%+#./*/#+)#:/O")"#BV"-"-@b"%'+#+.#",9#IJ[]f#F",/5"%+-#+.#",9#IJ[If#h2&7@!/$+7#+.#",9# IJ[IC9# W/# +-# =G'&,# '2")AQ'"%# +,# ,"-.%+# 62+# ,"# 0+);A'"# -2$/)+# $"%"# ,"# %+'2$+%"'&()# *+# ,"# +-$+'&+<# $+%/# +-.+#$2+*+#-+%#+3",2"*/#5+*&").+#+-.2*&/-#0+);A'/-#>#5&)&5&7"*/#'/)#2)"#"*+'2"*"#0+-A()#0+);A'"9# F"%"# +-./<# ,/-# 5"%'"*/%+-# 5/,+'2,"%+-# '/5/# ,/-# 5&'%/-".;,&.+-# 4")# -&*/# 4"-."# "4/%"# ,"-# 4+%%"5&+)."-# 8G-&'"-#B`/*/>#IJJKC<#$+%/#,/-#)2+3/-#+)=/62+-#*+#,"#0+)(5&'"#$%/5+.+)#2)#-",./#'2",&."A3/#+)#,"#5"@ )+%"#*+#+-.2*&"%#,"#0+);A'"#*+#,"-#+-$+'&+-#"5+)"7"*"-9#N,#-",./#*+#2)/-#$/'/-#"#5"%'"*/%+-#)+2.%",+-# "#5&,+-#*+#3"%&").+-#'/)#$/-&'&()#>#+=+'./-#=2)'&/)",+-#'/)/'&*/-#)/#-(,/#"25+)."%G#*+#5")+%"#+-$+'@ ."'2,"%#,"#$%+'&-&()#>#%+-/,2'&()#*+#,/-#")G,&-&-<#-&)/#62+#*"%G#"''+-/#"#,"#4"-."#"4/%"#&)+?$,/%"*"#=%"'@ '&()#=2)'&/)",#*+,#0+)/5"#BL,,+)*/%=#+.#",9#IJ[JC9# :+#+-./-#").+'+*+).+-#-2%0&(#,"#$%/$2+-."#*+,#$%/>+'./#Y./,0/-'$)1!/-!2/$13'!)/-!-*$4/!*56(*41Z<#Q@ )")'&"*"# $/%# ,"# \2)*"'&()# `+)+%",# V^UV<# '/)# 2)"# '/).%&82'&()# +-$+'&",# *+,# i")'/# *+# ^").")*+%<# +)# -2# '/)3/'"./%&"# *+# F%/>+'./-# V+%/# -/8%+# YN-$+'&+-# L5+)"7"*"-Z# *+,# "O/# IJ[J# B`"8",*()# IJ[If# `/*/># IJ[JC#B4c$Pddeee9,>)?0+)/5&'-9+-C9#!"#-/,&'&.2*#&)&'&",#=2+#&5$2,-"*"#$/%#'2".%/#&)-A.2./-#*+#.%+-#&)-A@ .2'&/)+-# *&-A)."-P# ,"# N-."'&()# i&/,(0&'"# :/O")"# ># +,# V+).%/# *+# U)3+-A0"'&/)+-# i&/,(0&'"-<# "58/-# *+,# V^UV<#+,#V+).%/#W"'&/)",#*+#L)G,&-&-#`+)(5&'/<#+,#V+).%/#*+#h+02,"'&()#`+)(5&'"9#N,#/8M+A3/#0+)+%",#*+,# $%/>+'./#+-#+,#*+#0+)+%"%#%+'2%-/-#0+)(5&'/-#$"%"#,"#&)3+-A0"'&()#>#,"#'/)-+%3"'&()#*+#,"#+-$+'&+#>#+,# "$%/3+'4"5&+)./#*+#+-./-#%+'2%-/-#$"%"#+-.2*&"%#,"#+3/,2'&()#>#,"#4&-./%&"#*+5/0%GQ'"#*+#,"#+-$+'&+<#"-1# '/5/#$"%"#+3",2"%#+,#&5$"'./#*+,#*+',&3+#-/8%+#-2#3"%&"'&()#0+)(5&'"9#L#'/)A)2"'&()#-+#%+-25+)#,/-# /8M+A3/-#$"%A'2,"%+-#*+,#$%/>+'./#>#,/-#%+-2,."*/-#4"-."#,"#=+'4"P# ^+'2+)'&"'&()#>#+)-"58,"M+#*+#2)#0+)/5"#*+#%+=+%+)'&"9#T)#$%&5+%#/8M+A3/#*+,#$%/>+'./# +-#+,#*+#0+)+%"%#+,#0+)/5"#*+#%+=+%+)'&"#*+#,"#+-$+'&+9#N,#/8M+A3/#+-#%+'/)-.%2&%#,"#-+'2+)'&"#*+,#'/)M2)@ ./#*+,#0+)/5"<#*+#./*/-#>#'"*"#2)/#*+#,/-#'%/5/-/5"-<#*+#,"#5")+%"#5G-#'/5$,+."#>#'/)A02"#$/-&8,+9# N,#2-/#*+#.+')/,/01"-#*+#-+'2+)'&"'&()#*+#-+02)*"#0+)+%"'&()#-2$/)+#2)"#3+)."M"#+3&*+).+#*+8&*/#"#-2# ",."# $%/*2'A3&*"*# ># -2# 8"M/# '/-.+# $/%# 8"-+# -+'2+)'&"*"<# $+%/# ,"-# -+'2+)'&"-# -+# /8A+)+)# +)# $"%+-# *+# 8,/62+-#*+#[JJ#8"-+-#'/)A02"-#$%/3+)&+).+-#*+#'2",62&+%#,20"%#",#"7"%#*+,#0+)/5"#>#62+#-+#+)'2+).%")# -+$"%"*"-#$/%#2)"#*&-.")'&"#'/)/'&*"9#N)-"58,"%#+-."-#-+'2+)'&"-#+)#=%"05+)./-#5">/%+-#"$%/3+'4")@ */#,/-#-/,"$"5&+)./-#+).%+#+-."-#,+'.2%"-#'/%."-#+-#./*/#2)#%+./#62+#+?&0+#+Q'&+).+-#",0/%&.5/-#5".+@ 5GA'/-#>#$/.+).+-#/%*+)"*/%+-9#F"%"#"-&-A%#+)#+-."#."%+"<#+,#$%/>+'./#4"#/$."*/#$/%#,"#0+)+%"'&()#*+# $"%+-# *+# -+'2+)'&"-# -+$"%"*"-# +).%+# -&# $/%# *&-A)."-# *&-.")'&"-# BjJJ<# k9JJJ<# l9JJJ<# kJ9JJJ# 8"-+-C<# 2)"# +-.%".+0&"#4"8&.2",#+)#,"#-+'2+)'&"'&()#*+#)/3/#*+#0+)/5"-9#L*+5G-<#4+5/-#2-"*/#2)"#+-.%".+0&"#'/5@ $,+5+)."%&"#'/)-&-.+).+#+)#%+*2'&%#,"#'/5$,+M&*"*#*+,#$%/8,+5"<#-+'2+)'&")*/#>#+)-"58,")*/#2)"#$+@ 62+O"# =%"''&()# *+,# 0+)/5"# '"*"# 3+79# F"%"# +,,/# -+# 4")# 0+)+%"*/# '/,+''&/)+-# *+# =%"05+)./-# *+# kJ<JJJ# 8"-+-#&)-+%."*/-#+)#3+'./%+-#*+#',/)"'&()#B=(-5&*/-C#62+#-/)#$%/$"0"*/-#+)#8"'.+%&"-f#-+#4")#-+'2+)@ '&"*/# ># +)-"58,"*/# Km# '/)M2)./-# ",+"./%&/-# &)*+$+)*&+).+-# '/)# [9IJJ# *+# +-./-# =%"05+)./-# '"*"# 2)/9# F/%#D,A5/<#-+#4"#"$%/3+'4"*/#,"#&)=/%5"'&()#/8.+)&*"#*+#,"#-+'2+)'&"'&()#*+#hWL-#>#,"#-+'2+)'&"#0+@ )(5&'"#*+,#0"./#*/5;-A'/#$"%"#0+)+%"%#2)#8/%%"*/%#'/)#2)"#,/)0&.2*#./.",#*+#'"9#I<j#0&0"8"-+-#B,"#,/)@ 0&.2*#+-A5"*"#*+,#0+)/5"#*+,#,&)'+#+-#*+#"$%/?&5"*"5+).+#I<l#0&0"8"-+-C<#+)#+,#62+#5G-#*+#,"#5&."*# *+,#0+)/5"#+-.G#%+$%+-+)."*/#+)#=%"05+)./-#'/)A02/-#*+#5G-#*+#[<j#5+0"8"-+-9#N-./-#%+-2,."*/-#-+# '/)-&*+%")#8"-.").+#82+)/-<#+-$+'&",5+).+#'2")*/#-+#'/)-&*+%"#,"#5/*+%"*"#&)3+%-&()#%+",&7"*"#+)#,"# 0+)+%"'&()#*+#*"./-<#,/#62+#-20&+%+#62+#,"#+-.%".+0&"#*+#-+'2+)'&"'&()#*+#'/)M2)./-#",+"./%&/-#*+#=(-5&@ */-#$2+*+#'/)3+%A%-+#+)#2)"#+-.%".+0&"#3+)."M/-"#$"%"#,"#-+'2+)'&"'&()#*+#0+)/5"-#'/5$,+M/-9# L)/."'&()#*+,#0+)/5"9#N,#+)-"58,"M+#$%/$/%'&/)"#2)#5"$"#52*/#*+,#0+)/5"#",#62+<#$"%"#62+# -+"#%+",5+).+#DA,<#4">#62+#"O"*&%#,+>+)*"-#62+#&*+)AQ62+)#,"#,/'",&7"'&()#*+#0+)+-#>#/.%/-#+,+5+)./-# =2)'&/)",+-#>#+-.%2'.2%",+-9#!/-#0+)+-#-+#%+'/)/'+)#2A,&7")*/#.%+-#+-.%".+0&"-#*&-A)."-P#&C#&*+)AQ'")*/# $".%/)+-#*+#-+'2+)'&"#'"%"'.+%1-A'/-#*+#,/-#0+)+-#B$%+*&''&()#"8#&)&A/C<#&&C#$/%#-2-#-&5&,&.2*+-#'/)#0+)+-# &*+)AQ'"*/-# +)# /.%"-# +-$+'&+-# ># &&&C# $/%# '/&)'&*&%# '/)# ,"-# -+'2+)'&"-# /8.+)&*"-# *+# hWL-<# ,"-# 5/,;'2,"-# &).+%5+*&"%&"-# +)# ,"# +?$%+-&()# *+# ,/-# 0+)+-9# !"# "$,&'"'&()# *+# +-."-# +-.%".+0&"-# 4"# $+%5&A*/# &*+)AQ'"%# ",0/#5G-#*+#3+&).+#5&,#0+)+-#$2."A3/-9#N,#.%"8"M/#+)#'2%-/#$%+.+)*+#&*+)AQ'"%#,"#=2)'&()#*+#'"*"#2)/# *+#+-./-#0+)+-#>#"-&0)"%,+-#".%&82./-#=2)'&/)",+-#'/5/#,/-#$%/'+-/-#'+,2,"%+-#+)#,/-#62+#$"%A'&$"<#,"#,/@ '",&7"'&()#&).%"'+,2,"%#*+#-2#$%/*2'./#/#-2#=2)'&()#5/,+'2,"%#B&9+9#/)./,/01"#0;)&'"C9# 137 ! Vol.7 ¦ Nº 150-Monográfico MONOGRAFÍA CAZADORES DE GENOMAS! 138 `+)(5&'"# '/5$"%"*"9# !"# '/5$"%"'&()# *+,# 0+)/5"# *+,# ,&)'+# '/)# +,# *+,# 0"./# */5;-A'/<# +,# $+%%/# ># /.%/-# 5"51=+%/-# 5G-# ,+M")"5+).+# +5$"%+)."*/-<# $+%5&A%G# &*+)AQ'"%# ,"-# '"%"'.+%1-A'"-# '/5$"%A*"-# $/%# *&-A)."-#+-$+'&+-#>#"62+,,"-#62+#-/)#+?',2-&3"-#*+#2)"#+-$+'&+#+)#$"%A'2,"%9#N-.+#")G,&-&-#$2+*+#%+3+,"%#$/%# .")./# ,/-# '"58&/-# +3/,2A3/-# 62+# -28>"'+)# "# ,"-# $+'2,&"%&*"*+-# ># "*"$."'&/)+-# '"%"'.+%1-A'"-# 62+# 4")# &*/# *&=+%+)'&")*/#2)"-#+-$+'&+-#*+#/.%"-#><#+)#$"%A'2,"%<#,"-#62+#*+Q)+)#",#,&)'+#&8;%&'/#'/5/#+-$+'&+9#N)#+-.+# $%/'+-/#-+#&*+)AQ'")#,/-#0+)+-#62+#4")#+-."*/#-/5+A*/-#"#2)"#-+,+''&()#)".2%",#&).+)-"#+)#,"#+-$+'&+<#"-1# '/5/#,"-#="5&,&"-#0;)&'"-#62+#4")#-2=%&*/#+?$")-&()#/#'/).%"''&()#+)#+,#,&)"M+#*+#,/-#,&)'+-9# # `+)(5&'"#$/8,"'&/)",9#N,#$%/>+'./#4"#-+'2+)'&"*/#'/)#2)"#5+)/%#'/8+%.2%"#*&+7#&)*&3&*2/-#*+#,&)'+# &8;%&'/#"*&'&/)",+-#>#2)#,&)'+#8/%+",<#,"#+-$+'&+#5G-#'+%'")"#",#,&)'+#&8;%&'/9#L#$"%A%#*+#+-./-#*"./-#-+#4")# &*+)AQ'"*/#5G-#*+#2)#5&,,()#*+#3"%&").+-#*+#-+'2+)'&"#62+#+-.G)#-+0%+0")*/#+)#,"-#$/8,"'&/)+-#*+#,&)'+<# &)',2>+)*/#$/,&5/%Q-5/-#*+#2)#-/,/#)2',+(A*/#B^&)0,+#W2',+/A*+#F/,>5/%$4&-5-<#^WF-C<#&)-+%'&/)+-#>#*+@ ,+'&/)+-#>#/.%"-#3"%&").+-#'/5$,+M"-9#N,#")G,&-&-#*+#+-./-#*"./-#"$/%."%G#2)"#&5"0+)#*+#52>#",."#%+-/,2'&()#*+# ,/-# $".%/)+-# 0+)(5&'/-# '/).+5$/%G)+/-# ># +-A5"-# $%+'&-"-# *+# *&3+%-&*"*# 0+);A'"<# '/)-")02&)&*"*# ># *&=+@ %+)'&"'&()#+).%+#$/8,"'&/)+-9#!/-#%+-2,."*/-#'/)Q%5")#,/-#/8.+)&*/-#'/)#2)/-#'2")./-#5"%'"*/%+-#5/,+'2@ ,"%+-<#",#&)*&'"%#2)"#&5$/%.").+#+%/-&()#0+);A'"#+)#,"-#$/8,"'&/)+-#*+#,&)'+9#F+%/#,/#62+#+-#5G-#&5$/%.").+<# ."58&;)# %+3+,"%G)# 62;# %+0&/)+-# 0+)(5&'"-# ># =2)'&/)+-# 0;)&'"-# 4")# 62+*"*/# 5G-# "=+'."*"-# ># ">2*"%G)# "# &*+)AQ'"%#,"#8"-+#0+);A'"#%+-$/)-"8,+#*+#'"%"'.+%+-#*+,+.;%+/-#62+#$2+*+)#-+%#%+-$/)-"8,+-#*+#,"#$;%*&*"# *+#3&"8&,&*"*#62+#'/5&+)7"#"#*/'25+)."%-+#+)#,"#+-$+'&+9#L*+5G-<#"#$"%A%#*+#,/-#*"./-#/8.+)&*/-#*+#0+)/@ 5"-#&)*&3&*2",+-#-+#$/*%G)#%+'/)-.%2&%#,/-#'"58&/-#*+5/0%GQ'/-#-2=%&*/-#$/%#,"#+-$+'&+#"#,/#,"%0/#*+#-2#4&-@ ./%&"#>#+-A5"%#'2G)*/#>#'(5/#-+#-+$"%(#*+,#,&)'+#8/%+",9#N)#2)#"-$+'./#5G-#"$,&'"*/<#'"*"#2)"#*+#,"-#3"%&")@ .+-#+)'/).%"*"-#"$/%."#2)#5"%'"*/%#0+);A'/#$"%"#+,#-+02&5&+)./#*+#&)*&3&*2/-#>#$/8,"'&/)+-#>#$"%"#,"#0+-@ A()#0+);A'"#*+#,"#+-$+'&+9#N,#$%/>+'./#-+,+''&/)"%G#[jJJ#*+#+-./-#5"%'"*/%+-#$"%"#'"%"'.+%&7"%#+,#'/)M2)./# *+#,"#$/8,"'&()#'"2A3"#>#52+-.%"-#%+$%+-+)."A3"-#*+#,"-#$/8,"'&/)+-#-&,3+-.%+-9# N,# *+,# ,&)'+# &8;%&'/# -+# '/)3&+%.+# "-1# +)# +,# $%&5+%# 0+)/5"# ")&5",# '/5$,+M/# +)# -+%#-+'2+)'&"*/#1).+0%"5+).+#+)#N-$"O"#>#2)/#*+#,/-#$%&5+%/-#0+)/5"-#*+#+-@ $+'&+-# "5+)"7"*"-# +)# -+%# -+'2+)'&"*/# +)# +,# 52)*/9# !/-# %+'2%-/-# 0+)+%"*/-# -+%G)#=2)*"5+).",+-#$"%"#,"#&)3+-A0"'&()#*+#,"#+-$+'&+#>#,/-#")G,&-&-#%+",&7"*/-# "%%/M"%G)#,27#-/8%+#-2#/%&0+)<#-2#+3/,2'&()#>#-2#4&-./%&"#*+5/0%GQ'"9#!/#62+#+-# 5G-# &5$/%.").+<# )/-# $+%5&A%G)# '"%"'.+%&7"%<# '/)# 2)# )&3+,# *+# *+.",,+# ").+-# &)&5"0&)"8,+<#,/-#'"58&/-#0+);A'/-#62+#,"#+-$+'&+#4"#-2=%&*/#'/5/#'/)-+'2+)@ '&"# *+,# *+',&3+# $/8,"'&/)",9# N-# *+# +-$+%"%# 62+# +-."# &)=/%5"'&()# '/).%&82>"# *+# 5")+%"#-&0)&Q'"A3"#"#,"#'/)-+%3"'&()#*+#2)"#+-$+'&+#62+#+-#+58,+5"#*+#,"#8&/@ *&3+%-&*"*# +)# N-$"O"# ># +)# N2%/$"9# L*+5G-<# ,/# 62+# "$%+)*"5/-# -+%G# %+,+3").+# $"%"#,"#'/)-+%3"'&()#*+#,"-#)25+%/-"-#+-$+'&+-#62+#-+#+)'2+).%")#+)#2)"#-&.2"@ '&()#-&5&,"%#>#,"#+?$+%&+)'&"#"'252,"*"#-+%G#-&)#*2*"#DA,#$"%"#,"#'"%"'.+%&7"'&()# *+# )2+3/-# 0+)/5"-9# N,# /8M+A3/# *+# -",3"%# ,"# 8&/*&3+%-&*"*# %+62&+%+# +-=2+%7/-# +)/%5+-# ># ,"# '/).%&82'&()# *+# 5D,A$,+-# G%+"-# *+# '/)/'&5&+)./<# $+%/# +)# +-."# +5$%+-"#'/)."5/-#"4/%"#'/)#,"#0+)(5&'"#'/5/#2)#)2+3/#>#$/*+%/-/#",&"*/9# Bibliografía citada: Allendorf FW, Hohenlohe PA, Luikart G (2010) Genomics and the future of conservation genetics. Nature Reviews Genetics 11, 697-709. Allendorf FW, Luikart G, Aitken SN, ebrary Inc (2012) Conservation and the genetics of populations. In: E-Libro, pp. xviii, 602, [608] p. John Wiley & Sons, Chichester, West Sussex. Casas-Marce M, Soriano L, López-bao JV, Godoy JA (2013) Genetics at the verge of extinction: insights from the Iberian lynx. Molecular Ecology, n/a-n/a. Frankham R, Ballou JD, Briscoe DA (2010) Introduction to conservation genetics, 2nd ed edn. Cambridge University Press, Cambridge ; New York. Gabaldón T (2012) El lince ibérico entra en la era de la genómica. Lychnos, 14-19. Godoy JA (2009) La genética, los marcadores moleculares y la conservación de especies. Ecosistemas 18, 23-33. Godoy JA (2010) La genómica y la conservación del lince ibérico. Lychnos, 14-18. Haussler D, O'Brien SJ, Ryder OA, et al. (2009) Genome 10K: A Proposal to Obtain Whole-Genome Sequence for 10 000 Vertebrate Species. Journal of Heredity 100, 659-674. Palomares F, Godoy JA, Lopez-Bao JV, et al. (2012) Possible Extinction Vortex for a Population of Iberian Lynx on the Verge of Extirpation. Conservation Biology 26, 689-697. Ruiz-Lopez MJ, Ganan N, Godoy JA, et al. (2012) Heterozygosity-Fitness Correlations and Inbreeding Depression in Two Critically Endangered Mammals. Conservation Biology 26, 1121-1129. Simon MA, Gil-Sanchez JM, Ruiz G, et al. (2012) Reverse of the Decline of the Endangered Iberian Lynx. Conservation Biology 26, 731-736. Vargas A, Breitenmoser C, Breitenmoser U (2009) Iberian Lynx Ex situ Conservation: An Interdisciplinary Approach, p. 556. Fundación Biodiversidad in collaboration with: International Union for Conservation of Nature, Species Survival Commission (IUCN /SSC ) Cat Specialist Group, Madrid. Vol.7 ¦ Nº 150-Monográfico MONOGRAFÍA CAZADORES DE GENOMAS! ! Monografía 2-2014 !"#$%&'%(&)"&)*(#+%#,-$#.%(-/"$#+%# +-$#0-10'."$2#!"#$%&'()'*'&+"+'&'#3# ,-"#$+&.*/0%.'# Juan Pascual Anaya Investigador científico contratado. Laboratory for Evolutionary Morphology, RIKEN Center for Developmental Biology. Minatojima-minami, 3-2-2, 650-0047 Kobe, Japan [email protected] En el año 2010, justo acabada la tesis doctoral en la Universitat de Barcelona (a la que me mudé tras licenciarme en Biología por la Universidad de Málaga), empecé mi estancia post-doctoral en el Centro de Biología del Desarrollo del RIKEN, en el laboratorio del Dr. Shigeru Kuratani, probablemente el investigador más destacado de la última década en Japón en el campo de la evolución del desarrollo, y uno de los más importantes del mundo en el campo de la embriología comparada. El laboratorio del Dr. Kuratani estudia los cambios morfológicos que se han producido durante la evolución de los vertebrados, prestando especial atención a aquellas innovaciones que suponen unos cambios drásticos en el bauplan de estos. Por ejemplo, la aparición de la mandíbula, el origen de la cabeza (y al mismo tiempo estructuras clave relacionadas como la cadera anterior y el cuello) y, sobre todo, el origen del caparazón de la tortuga han sido algunos de los ejemplos estudiados en profundidad en su laboratorio. Como es bien sabido, la evolución consiste en descendencia con modificación, lo cual implica un hecho muy importante en el marco evolutivo: que todo lo nuevo deriva de algo viejo. Sin embargo, esto no está tan claro para ciertas estructuras, las que se denominan innovaciones verdaderas; es decir, que no aparecen claramente a partir de la modificación de una estructura que estaba presente anteriormente. Una de estas estructuras es el caparazón de la tortuga. En el año 2005, el laboratorio del Dr. Kuratani publicó un trabajo sobre genes que se expresan específicamente en la cresta ectodérmica del caparazón (CR, del inglés carapacial ridge), la estructura embrionaria que derivará en el caparazón, descubriendo la implicación de genes clave como LEF1, un factor de transcripción que se activa al final de la vía de señalización de WNT [1]. La expresión de estos genes, junto con la similitud histológica entre la CR y la cresta apical ectodérmica de los primordios de las extremidades llevaron a pensar que el origen de la CR se encuentra asociado a la co-opción de redes génicas ya establecidas en el desarrollo de las extremidades [2]. Sin embargo, este trabajo estaba limitado a la poca cantidad de información genética que se tenía entonces sobre las tortugas. Y este fue el principal motivo que llevó al grupo a plantearse un proyecto de secuenciación de genoma, bajo la coordinación del Dr. Naoki Irie, de la tortuga china de caparazón blando (Pelodiscus sinensis), modelo con el que trabajamos. El trabajo ha sido recientemente publicado en Nature Genetics, y es de acceso libre [3], y en los siguientes párrafos explicaré brevemente la historia del proyecto, los resultados más importantes y, sobre todo, mi participación científica en él. En el año 2010 el proyecto empezó mediante la concesión de financiación para su realización por parte del gobierno japonés. Tras varios contactos con algunos proveedores, llegamos a la conclusión de que aunque las nuevas técnicas de secuenciación han abaratado mucho los proyectos de genómica, el presupuesto no llegaba para hacer todo lo que queríamos solos. Así pues, en enero de 2011 fuimos a la XIX conferencia internacional “Plant and Animal Genome” en San Diego, California (EEUU). Y fue allí donde entablamos los contactos para asociarnos al Beijing Genome Institute (BGI) de China y al Instituto Europeo de Bioinformática (EBI, de sus siglas en inglés). El enorme esfuerzo que supone la secuenciación de un genoma de novo (no la secuenciación de genomas de individuos para los que existe ya un genoma de referencia, como el caso del ser humano), no sólo económico, sino de recursos humanos, hizo que el número de instituciones participantes aumentara durante los siguientes seis meses, englobando finalmente a nueve centros de investigación en total. 139 " Vol.7 ¦ Nº 150-Monográfico MONOGRAFÍA CAZADORES DE GENOMAS! ! 140 Además, dentro del BGI ya había otro grupo que había empezado a secuenciar el genoma de la tortuga verde marina (Chelonia mydas) y decidimos unir esfuerzos con el objetivo de presentar un trabajo más completo con dos genomas que diera ideas sobre el grupo de las tortugas en general y no solo sobre una especie en particular. Queda de manifiesto por tanto la importancia de establecer fructíferas colaboraciones para la realización de proyectos de esta envergadura. Así pues, el trabajo a realizar quedó repartido principalmente entre el RIKEN, el BGI y el EBI de la siguiente manera: el BGI se encargaría de la secuenciación y ensamblaje del genoma, así como de la realización de una anotación (descripción estructural del genoma: coordenadas génicas de los diferentes elementos génicos: genes, elementos repetitivos, RNAs no codificantes, etc…) preliminar; el EBI se encargaría de la realización de una página web donde se daría un soporte gráfico para análisis así como de una anotación más profunda utilizando RNA-seq (secuencias de RNA producidas mediante técnicas de última generación de secuenciación a partir del RNA mensajero que producen millones de “lecturas” que luego se alinean frente al genoma para establecer así el origen genómico de los tránscritos); y en el RIKEN nos encargaríamos de un análisis funcional del genoma. Entre los diferentes análisis a realizar, el más importante era aprovechar la ingente cantidad de información que puede proporcionar un genoma para establecer definitivamente la posición filogenética de las tortugas, posición que siempre ha sido dudosa usando tanto datos morfológicos como moleculares. Las tortugas han sido clasificadas como (i) una rama temprana de los reptiles (anápsidos) colocándolos a la base de los diápsidos, (ii) como grupo hermano de arcosaurios (cocodrilos y aves) o (iii) como grupo hermano de lepidosaurios (lagartos, serpientes y tuataras), y no sólo basándose en aspectos morfológicos, sino también moleculares (genes que codifican para proteínas, microRNAs o incluso elementos no codificantes conservados). En nuestro caso usamos la secuencia encadenada de 1113 genes de las dos tortugas estudiadas así como de otros diez genomas de vertebrados secuenciados (pollo, diamante mandarín, cocodrilo marino, aligátor americano, lagarto anoles, perro, humano, ornitorrinco, la rana Xenopus tropicalis y el medaka común). Los diferentes análisis filogenéticos usando este set de datos, el mayor hasta la fecha, emplazan inequívocamente a las tortugas como grupo hermano de arcosaurios (Figura 1). El tiempo de divergencia estimado para las tortugas, ajustado mediante el uso de fósiles, es de aproximadamente 260 millones de año. Este periodo coincide con el final del Pérmico y el inicio del Triásico, momento que en el que se produce una gran extinción y que podría estar asociado con la aparición y éxito posterior de las tortugas. " Figura 1: Posición filogenética y tiempo de divergencia de las tortugas respecto a otros vertebrados, usando la secuencia encadenada de 1113 genes. Imagen cedida por el Dr. Naoki Irie, coordinador del proyecto. Vol.7 ¦ Nº 150-Monográfico " MONOGRAFÍA CAZADORES DE GENOMAS! Monografía 2-2014 Como objetivos del proyecto se encontraban además identificar rasgos genómicos específicos de las tortugas, por un lado, e intentar aprovechar la excelente herramienta que supone un genoma para identificar elementos moleculares del desarrollo embrionario específicos para la tortuga. Respecto al primer objetivo, es reseñable la expansión de genes que codifican para receptores de odorantes que ha ocurrido en tortugas, especialmente en P. sinensis que llega hasta niveles similares o incluso superiores a los de mamíferos. Esta expansión es específica e independiente de tortugas (sobre todo de receptores tipo α) y queda mejor reflejado en el gráfico de la figura 2. " " 141 Figura 2: Gráfico que muestra la expansión de los genes que codifican para los receptores de odorantes en diferentes genomas de vertebrados. En azul, receptores tipo ; en verde, receptores tipo ; en rojo, receptores tipo . Imagen cedida por el Dr. Naoki Irie, coordinador del proyecto " !! " " " " Vol.7 ¦ Nº 150-Monográfico MONOGRAFÍA CAZADORES DE GENOMAS! 142 En el segundo objetivo es donde se enmarcó mi función dentro del proyecto. Mi participación se basó en identificar los aspectos moleculares relacionados con el desarrollo del caparazón. Como he explicado antes, en un trabajo anterior se había identificado un posible papel de la vía de señalización WNT en el desarrollo del caparazón, pero sin embargo no se había identificado hasta la fecha la expresión asociada de ningún ligando WNT. Así pues, decidí buscar todos los genes que codifican para ligandos WNT en el genoma de las tortugas, y analizar su expresión durante el desarrollo. En total pude anotar 20 genes que codifican para WNT, incluyendo WNT10B, que parece haberse perdido en el linaje de las aves, y WNT11B, perdido en mamíferos. Tras analizar la expresión de los 20 genes, observamos que WNT5A era el único expresado en la CR. Sorprendentemente, WNT5A también se encuentra activo en el desarrollo de las extremidades, lo que da fuerza a las hipótesis anteriores que sugieren una coopción de las redes génicas de las extremidades a la CR. Por otro lado, decidí también investigar el papel de un tipo de moléculas cuyo rol en el desarrollo embrionario es aún bastante desconocido: los microRNAs. Los microRNAs son unas moléculas de RNA pequeñas, de entre 21-23 nucleótidos que regulan la traducción de los genes a proteínas mediante mecanismos de represión en los que no entraré en detalle. Se separó la fase de RNAs pequeños de una extracción de RNAs de tres tejidos diferentes (la CR, las extremidades y la pared lateral del cuerpo) de embriones en el estadio en el que la CR empieza a desarrollarse. Luego, esta fase de RNAs pequeños fue secuenciada masivamente por técnicas de small RNA-seq (igual al RNA-seq, pero con las moléculas pequeñas), y por último, mediantes técnicas de bioinformática pude predecir, usando los resultados del small RNA-seq y el genoma, microRNAs que posiblemente están expresados en estos tejidos. Finalmente, comparando la presencia o ausencia de microRNAs entre los tres tejidos, se pueden identificar microRNAs específicamente detectados en un tejido y no en los demás. En total, pude identificar la presencia de 212 microRNAs específicos de la CR, y que podrían tener algún papel en su desarrollo. " En conclusión, lo que es más valioso de este trabajo es la obtención de unas herramientas tan importantes como los genomas de dos tortugas: una muy utilizada en estudios de desarrollo, P. sinensis, y la otra que es primordial en programas de conservación de la bioesfera, como es la tortuga verde marina, C. mydas, en peligro de extinción. Aunque en nuestro trabajo ya presentamos algunos resultados sorprendentes y que podrían estar relacionados con algunos de los rasgos más llamativos de las tortugas como el caparazón, estoy seguro que los resultados más importantes en el campo están aún por llegar y en ellos la utilización de estos genomas jugarán un papel fundamental. " " " " Bibliografía citada: 1. Kuraku S, Usuda R, & Kuratani S (2005) Comprehensive survey of carapacial ridge-specific genes in turtle implies co-option of some regulatory genes in carapace evolution. Evolution & Development 7(1):3-17. 2. Burke A (1989) Development of the turtle carapace: implications for the evolution of a novel bauplan. J Morphol 199:363-378. 3. Wang Z, et al. (2013) The draft genomes of soft-shell turtle and green sea turtle yield insights into the development and evolution of the turtle-specific body plan. Nature Genetics. Vol.7 ¦ Nº 150-Monográfico MONOGRAFÍA CAZADORES DE GENOMAS! Monografía 2-2014 ! !"#$%&'()(*$+,+#-.(!"#$%&'$" (')*&+"/(,&)+%)0*(+%" Enrique Viguera Mínguez Profesor Titular del Área de Genética, Departamento de Biología Celular, Genética y Fisiología. Universidad de Málaga [email protected] En mayo de 2001, tras cerca de cinco años de estancia postdoctoral en París estudiando mecanismos básicos de replicación y recombinación en bacterias, me incorporé a un atractivo proyecto: se empezaban a poner los cimientos del Centro de Astrobiología (CAB), un centro mixto del Instituto Nacional de Tecnología Aeroespacial (INTA) y el Consejo Superior de Investigaciones Científicas (CSIC), asociado al NASA Astrobiology Institute [NAI]. Liderado por el visionario Dr. Juan Pérez-Mercader, el CAB iba a estar dedicado al estudio del origen y evolución de la vida con un claro enfoque transdisciplinar en el que trabajarían juntos biólogos, químicos, geólogos astrofísicos, informáticos e ingenieros. Embarcarse en un proyecto nuevo con tales objetivos, con investigadores en plena ebullición de ideas resultaba lo suficientemente atractivo como para decidir que era el momento de volver a España. ¡Quién iba a decirnos que once años más tarde algunos de estos investigadores iban a estar colaborando codo con codo con investigadores del Jet Propulsion Laboratory (California Institute of Technology-NASA), colaborando en la misión Mars Science Laboratory que lleva por primera vez en la historia un instrumento de diseño y fabricación española: REMS. 143 "En los inicios del CAB se puso en evidencia la necesidad de desarrollar un proyecto emblemático que supusiera un reto a la altura del centro de investigación que se diseñaba. En este punto el Dr. Andrés Moya, en aquel momento tutor o asesor científico del centro, sugirió la posibilidad de secuenciar íntegramente el genoma de una bacteria endosimbionte en la que llevaba varios años trabajando junto con la Dra. Amparo Latorre y el Dr. Francisco Silva en su laboratorio del Instituto Cavanilles de Biodiversidad y Biología Evolutiva, en Valencia. Este trabajo iba a suponer la introducción de la genómica bacteriana en España. El candidato era Buchnera aphidicola, una bacteria que vive en el interior de unas células especializadas del pulgón Baizongia pistaciae denominadas bacteriocitos. De hecho, esta relación de simbiosis entre bacteria e insecto no es infrecuente en la naturaleza: se estima que al menos un 20% de todas las especies de insectos han desarrollado relaciones obligadas con microorganismos y suelen establecerse como consecuencia de una dieta limitada del hospedador en la que la bacteria aporta los nutrientes de los que éste carece. Así el pulgón, que se alimenta de la savia de las plantas, muy rico en azúcares pero pobre en compuestos nitrogenados, completa su dieta con aminoácidos esenciales que le aporta Buchnera. En otras relaciones insectos-bacteria, como por ejemplo en las moscas tse-tse, el insecto se alimenta de la sangre de los vertebrados, rico en aminoácidos en su dieta, por lo que la bacteria Wigglesworthia glossinidia le aporta vitaminas. En este ambiente, el insecto le proporciona a la bacteria un ambiente protegido y estable. Sin embargo, una característica fundamental de las bacterias endosimbiontes es la reducción genómica como consecuencia de la adaptación a la vida intracelular en insectos: en un ambiente estable que le proporciona todos los recursos que necesita se produce una pérdida de genes. Así, B. aphidicola con un genoma de unas 650 Kb, sufrió una reducción de siete veces su tamaño con respecto a Escherichia coli, su pariente de vida libre más próximo conocido. Por tanto, el estudio del genoma de una bacteria endosimbionte como Buchnera suponía también el aproximarse a conocer cuál sería el componente génico mínimo para mantener una vida endosimbiótica y, al compararlo con los genomas de bacterias de vida libre, inferir cuál sería el número mínimo de genes necesario para mantener un organismo con organización celular. " Vol.7 ¦ Nº 150-Monográfico MONOGRAFÍA CAZADORES DE GENOMAS! ! Sin embargo el estudio de un genoma endosimbionte presentaba una dificultad técnica importante: B. aphidicola no es una bacteria cultivable, por lo que las muestras debían tomarse a partir de los áfidos recolectados directamente de la naturaleza. Se trataba, por tanto, de uno de los primeros proyectos de genómica ambiental desarrollados hasta la fecha en el que varios genotipos iban a ser secuenciados a la vez. Uno de los primeros problemas de hecho, consistía en prevenir la contaminación de la muestra de DNA bacteriano con DNA nuclear o mitocondrial del pulgón. Esta dificultad se solventó tras someter los extractos celulares de los pulgones recolectados a sucesivas filtraciones para eliminar las células del insecto y a centrifugación suave para eliminar las bacterias intactas de las mitocondrias. La estrategia utilizada para la secuenciación del DNA bacteriano fue la de “random shotgun”, en la que el DNA genómico se fragmentó al azar mecánicamente por sonicación y los fragmentos obtenidos, del orden de 1,5-2 kb, se aislaron por Electroforesis en Campo Pulsante [Pulsed-field Electrophoresis-PFGE] y se clonaron en el plásmido pUC18 para generar la genoteca correspondiente. la secuenciación se realizó por secuenciación Sanger y se utilizó el robot de manejo de líquidos MultiPROBE II (Perkin Elmer), toda una novedad en aquel momento. 144 "Me gustaría sin embargo, detallar las condiciones en que realmente se secuenció este primer genoma, que visto en la lejanía del tiempo no deja de ser anecdótico, pero en aquel momento suponía un handicap severo habida cuenta de que estábamos compitiendo con otros laboratorios extranjeros que perseguían los mismos objetivos. No hay que olvidar que las instalaciones del Centro de Astrobiología se inauguraron en enero de 2003 y en el momento del desarrollo del proyecto de secuenciación de B. aphidicola, ¡todavía se veían excavadoras preparando el terreno! Afortunadamente, el INTA cedió uno de sus hangares para acoger a la avanzadilla de investigadores que comenzó el proyecto, dirigido en el CAB por el Dr. Roeland Van Ham, brillante investigador –hoy día vicepresidente y director de Bioinformática en Keygene - y asistido en la parte técnica por las meticulosas manos de Judith Kamerbeek. Así, en un laboratorio improvisado de apenas 10 metros cuadrados se obtuvo el que iba a ser el primer genoma que se secuenciaba íntegramente en España, si bien es cierto que para arrancar el proyecto, una parte de la secuenciación tuvo que realizarse en la Universidad de Valencia. "Tras el ensamblaje y cierre de gaps hasta obtener un único contig de cerca de 620.000 nucleótidos, comenzó la fase de anotación funcional mediante búsquedas BLAST en las bases de datos no redundantes de proteínas y DNA del NCBI. Los resultados indicaron que el endosimbionte B. aphidicola era capaz de vivir con escasos 500 genes codificantes de proteínas, un número similar al que posee el genoma de Mycoplasma genitalium pero muy alejado de los aproximadamente 4150 genes que contiene el genoma de E. coli con la que comparte un mismo ancestro. De hecho, B. aphidicola no ha ganado ninguna función nueva dado que no posee ningún gen que no contenga E. coli, debido a que en este ambiente intracelular, en el que Buchnera es transmitida vía materna a través de los huevos, no se produce intercambio de genes por transferencia génica horizontal. La comparación del genoma de B. aphidicola con los genomas de otras dos Buchneras de diferentes especies de áfidos sugirió que la mayoría de la reducción genómica ocurrió justo después del establecimiento de la relación de endosimbiosis, pero antes de la diversificación de las principales líneas de áfidos. No hay que olvidar que al tratarse de una muestra ambiental, el estudio nos permitió además, determinar la variación intrapoblacional. La identificación de polimorfismos que afectaban al marco abierto de lectura de algunos genes nos proporcionaba además, una fotografía del proceso por el que se iban inactivando los genes. Precisamente, el impacto mayor en la reducción genómica se observó en el conjunto de genes dedicados a replicación, recombinación y reparación del DNA (3R): Buchnera había perdido la mayoría de los genes implicados en la vía de reparación por recombinación, por lo que propusimos que en ausencia del gen recA, el complejo recBCD tendría una función general de exonucleasa de reparación. " Vol.7 ¦ Nº 150-Monográfico MONOGRAFÍA CAZADORES DE GENOMAS! Monografía 2-2014 Además otros componentes del sistema de reparación de daño oxidativo del DNA y componentes del reensamblaje de horquillas de replicación bloqueadas se habían perdido como consecuencia del proceso de reducción genómica. Quizá las pérdidas de genes más llamativas afectan al complejo de replicación: B. aphidicola carece de la subunidad Tau, implicada en la replicación coordinada de las hebras líder y retrasada. polA, codificante para la DNA polimerasa I había conservado únicamente el dominio 5’-3’ exonucleasa, implicada en la eliminación de cebadores RNA durante la replicación, siendo por tanto Pol III la única DNA polimerasa presente en su genoma. Por tanto, concluimos que la reducción de las maquinarias 3R contribuyó notablemente a la inactivación génica en B. aphidicola. "Por otro lado, uno de los firmantes del trabajo, el Dr. Ugo Bastolla, hoy día científico titular del CSIC en el centro de Biología Molecular Severo Ochoa [CBMSO], realizó un anális que concluía que el sesgo mutacional hacia AT en bacterias con una relación de endosimbiosis obligada como Buchnera, generaba una disminución de la estabilidad termodinámica de las proteínas sintetizadas y por lo tanto, en el plegamiento correcto de las proteínas. Dado que la chaperona GroELS se expresa abundantemente en Buchnera, ésta actuaría como un mecanismo compensatorio para contrarrestar la acumulación de sustituciones de aminoácidos que desestabilizan las proteínas de Buchnera. "En síntesis, los datos obtenidos mostraban la existencia de un sesgo mutacional, pér- 145 dida de los sistemas reguladores (genes y secuencias reguladoras), acumulación de mutaciones que afectan a la estabilidad de proteínas, formación de pseudogenes y pérdida de genes en todas las categorías funcionales, un sesgo de inactivación de genes hacia la región del término de replicación y una reducción continua de los genes 3R. Por comparación con otros genomas podíamos identificar genes específicos de simbiosis, siendo este contenido dependiente del modo de vida de cada endosimbionte. Sin embargo, este estudio permitió identificar también el número mínimo de genes o dominios de proteínas esenciales implicados en los procesos básicos de mantenimiento de la célula: replicación, transcripción y traducción, así como rutas biosintéticas mínimas, proporcionando una valiosa información en los estudios de biología sintética. "Las conclusiones que planteamos fue que la evolución de B. aphidicola sería un caso de evolución degenerativa, más que adaptativa y el destino final sería la extinción. Años más tarde el grupo de la Dra. Amparo Latorre publicaría la existencia de endosimbiontes secundarios, Serratia, que sustituirían a Buchnera, lo que permitió obtener una visión global del proceso de endosimbiosis, reducción genómica, degeneración y sustitución de un endosimbionte por otro. "El trabajo fue aceptado para su publicación en PNAS a finales de 2002, siendo editado por el mismísimo Craig Venter. Previamente había sido rechazado en Science por la editora por “cuestiones de espacio” a pesar de la opinión favorable y unánime de los tres referees! Esa limitación de espacio pareció no afectar a la posterior publicación en esta misma revista del trabajo de nuestros competidores a pesar de que el genoma que analizábamos había divergido de éste unos 100 millones de años antes. Esto nos permitió incluir en nuestro trabajo la comparación de los contenidos génicos de los tres genomas de Buchnera secuenciados y obtener conclusiones más profundas sobre contenido génico mínimo y el proceso de reducción de genomas. Prueba de ello son las más de 750 citas que acumula esta publicación. La continuación de esta línea de investigación en el Instituto Cavanilles de Valencia liderada por los Dres. Amparo Latorre y Andrés Moya ha sido una de las más productivas en España en los últimos diez años, con numerosas publicaciones incluyendo revistas de primer nivel como Science o PNAS. Este trabajo permitiría más tarde a este grupo liderar un proyecto europeo sobre biología sintética y comenzar estudios de metagenómica sobre el microbioma humano, poniendo una vez más de relieve la importancia de realizar y financiar la investigación básica. " Vol.7 ¦ Nº 150-Monográfico Premio Nobel de Química 2014 146 Fuente: Comunicado de prensa de la Asamblea Nobel del Instituto Karolinska informando de la concesión del Premio Nobel de Química 2014. Vol.7 ¦ Nº 150-Monográfico MONOGRAFÍA CAZADORES DE GENOMAS! Monografía 2- 2014 Genomas de geminivirus: pequeños pero matones Jesús Navas Castillo Laboratorio de Virología, Instituto de Hortofruticultura Subtropical y Mediterránea "La Mayora", Universidad de Málaga - Consejo Superior de Investigaciones Científicas (IHSM-UMS-CSIC), Estación Experimental "La Mayora", 29750 Algarrobo-Costa, Málaga [email protected] !! Todos los organismos vivos poseen un genoma, constituido por ácido nucleico, que codifica las proteínas necesarias para completar su ciclo vital e interaccionar con el medio ambiente. Sin entrar en la disquisición más o menos filosófica de si los virus son o no organismos vivos, lo que sí puede afirmarse es que la vida en la Tierra no puede imaginarse sin la existencia de estos "sencillos" organismos. Los virus poseen un genoma de ácido desoxirribonucleico (ADN) o ácido ribonucleico (ARN) que suele encapsidarse en una cubierta proteica más o menos compleja que en ocasiones contiene componentes lipídicos. El tamaño del genoma viral varía enormemente entre especies. Así, entre los genomas virales de menor tamaño están aquellos de los circovirus, que apenas contienen dos mil nucleótidos y codifican sólo dos proteínas. En el extremo opuesto, los recientemente descubiertos pandoravirus, con un genoma de más de 2.500.000 nucleótidos, codifican más de dos mil proteínas [16]. En general, los virus de RNA poseen genomas de menor tamaño que los de DNA, en parte debido a que su mayor tasa de error al replicarse los limita a un tamaño máximo por encima del cual la acumulación de mutaciones impediría su replicación o los volvería poco competitivos. Para compensar este fenómeno, muchos virus de RNA poseen genomas segmentados, reduciendo así la probabilidad de que una mutación en un componente genómico sea letal para el genoma completo. En contraste, los genomas de los virus de ADN suelen poseer un mayor tamaño, asociado con una mayor fidelidad en su replicación. Sin embargo, algunos virus de ADN escapan a esta regla y poseen un genoma de pequeño tamaño, como numerosos virus con genoma de ADN de cadena sencilla (ADN-cs). ! !! La necesidad práctica de compartimentar el mundo viral en entidades que puedan ser distinguibles entre sí, sobre las que exista un consenso por parte de los virólogos, justifica el desarrollo de un sistema de clasificación viral. La última taxonomía oficial publicada, que incluye a todos los virus que infectan animales, plantas, hongos, bacterias y arqueas, así como a los viroides, recoge 2284 especies de virus y viroides distribuidos en 349 géneros y 87 familias [8]. Una de estas familias, Geminiviridae, contiene virus con genoma circular de ADN-cs encapsidado en viriones geminados formados por la unión de dos icosaedros incompletos. Existen siete géneros dentro de esta familia, de los cuales el género Begomovirus es el mayor con diferencia, con más de 200 especies virales. La mayoría de los begomovirus poseen un genoma bipartito, compuesto por dos componentes, ADN-A y ADN-B, de alrededor de 2700 nucleótidos cada uno. El único componente de los begomovirus monopartitos es homólogo al ADNA. El pequeño tamaño del genoma de estos virus es un paradigma de la economía utilizada por los virus en general en cuanto a maximizar la información genética utilizable a partir de la secuencia disponible. Así, varios de los genes codificados en el genoma de los begomovirus están solapados, es decir, una misma secuencia puede codificar distintas proteínas funcionales dependiendo del marco de lectura escogido. Numerosos begomovirus causan graves enfermedades emergentes que afectan a numerosos cultivos de enorme importancia económica como el tomate, la mandioca o el algodón [15]. Los begomovirus se transmiten en la naturaleza por la mosca blanca (orden Hemiptera, familia Aleyrodidae) Bemisia tabaci de forma persistente y la mayor parte de ellos están limitados al floema de las plantas infectadas. En los últimos años, el Laboratorio de Virología del IHSM-UMA-CSIC ha estado involucrado en una serie de proyectos conducentes a caracterizar nuevos begomovirus presentes tanto en España como en distintos países de Latinoamérica. La estrategia utilizada en la mayor parte de los casos se ha basado en la técnica denominada amplificación por círculo rodante (rolling cirVol.7 ¦ Nº 150-Monográfico 147 MONOGRAFÍA CAZADORES DE GENOMAS! 148 cle amplification, RCA) utilizando la ADN polimerasa del fago F29 (Figura 1). Al contrario de otras técnicas de amplificación de ácidos nucleicos, como la reacción en cadena de la polimerasa (polymerase chain reaction, PCR), la aplicación de la RCA no necesita de un conocimiento previo de la secuencia viral y además amplifica específicamente moléculas circulares de ADN-sc. Como resultado de este trabajo, hemos logrado clonar y secuenciar aislados pertenecientes a numerosas nuevas especies de begomovirus, que incluyen: i) dos begomovirus monopartitos originados como resultado de la recombinación entre especies del complejo del rizado amarillo del tomate (virus de la cuchara) previamente presentes en el sur peninsular, ii) cuatro sweepovirus (un grupo particular de begomovirus monopartitos que infecta batata y Vol.7 ¦ Nº 150-Monográfico especies afines) en España y en Brasil, iii) cuatro begomovirus bipartitos que producen graves enfermedades en tomate, pimiento y judía en Perú, Uruguay y Venezuela y iv) cinco begomovirus bipartitos que infectan especies silvestres en Cuba y Venezuela. Para algunos de estos nuevos virus hemos obtenido clones infectivos que han permitido demostrar los postulados de Koch para las enfermedades observadas en campo. La Tabla 1 recoge los nombres de estos virus así como los huéspedes donde fueron encontrados. Los resultados, conclusiones e implicaciones de estos proyectos de secuenciación de nuevos geminivirus pueden resumirse en los puntos que se resumen a continuación. • El objetivo final de la línea de investigación de nuestro laboratorio es el control de MONOGRAFÍA CAZADORES DE GENOMAS! Monografía 2- 2014 enfermedades virales, fundamentalmente aquellas transmitidas por mosca blanca, que causan daños cuantiosos a la producción hortícola en nuestro país y muchos otros de las zonas cálidas y templadas del mundo. Conocer al enemigo y determinar las armas con las que cuenta es un paso inicial imprescindible para tener éxito en su control eficiente y duradero. La caracterización del genoma viral es básico para alcanzar este objetivo. • La abundancia y diversidad de begomovirus presentes en especies silvestres subrayan el papel de la flora silvestre como huésped alternativo para virus que pueden atacar asimismo a especies cultivadas. Se conocen numerosos casos de begomovirus originarios de especies silvestres que han colonizado cultivos como el tomate en América y Asia o la mandioca en África. Éste puede ser el caso para algunos de los nuevos begomovirus encontrados en especies silvestres. de ADN-sc. La mayor parte de estos genomas muestran huellas genéticas de intercambio de fragmentos genómicos ocurridos en el pasado y, en algunos casos, hemos demostrado que los nuevos genomas poseen características patológicas distintas de los virus parentales. También hemos detectado posibles fenómenos de transferencia horizontal de genes (horizontal gene transfer, HGT) entre el genoma viral y el genoma del huésped. • Nuestros resultados, junto con estudios recientes de metagenómica ponen de manifiesto que la diversidad de genomas que estamos observando es sólo la punta del iceberg. Así, en muy diversos ambientes se han amplificado genomas virales de ADN-sc, unos totalmente desconocidos hasta el momento y otros con cierta relación con los geminivirus. Estos ambientes incluyen algunas zonas que en principio son poco favorables para la vida, como algunos lagos de la Antártida [9]. Sin duda, el número de • La caracterización de nuevos genomas ha confirmado la extraordinaria frecuencia con la que tiene lugar el fenómeno de recombinación en el mundo viral, sobre todo en los virus especies/géneros/familias de virus con genoma circular de ADNsc que queda por descubrir es muy elevado. Vol.7 ¦ Nº 150-Monográfico 149 MONOGRAFÍA CAZADORES DE GENOMAS! • Se conoce un buen número de begomovirus monopartitos que se asocian con moléculas de ADN-sc que dependen de dichos virus para su replicación y/o transmisión, denominados betasatélites y alfasatélites. Estas entidades subvirales, con la mitad de tamaño de los componentes genómicos virales, codifican para una proteína y en algunos casos modifican la sintomatología causada por el virus ayudante. En nuestra búsqueda de genomas de begomovirus en Latinoamérica hemos descubierto una nueva clase de satélites más pequeños aún, con la mitad de tamaño de los betasatélites y los alfasatélites, sin capacidad codificante [4]. Que- ! 150 Bibliografía citada: da por determinar la posible influencia que estos pequeños satélites, auténticos parásitos de parásitos, puedan tener sobre la acumulación viral o su papel como determinantes de patogenicidad. !! !! !! ! 1. Albuquerque LC, Inoue-Nagata AK, Pinheiro B, Ribeiro SG, Resende RO, Moriones E, Navas-Castillo J (2011) A novel monopartite begomovirus infecting sweet potato in Brazil. Archives of Virology 156: 1291-1294. 2. Fiallo-Olivé E, Chirinos DT, Geraud-Pouey F, Moriones E, Navas-Castillo J (2013a) Complete genome sequences of two begomoviruses infecting weeds in Venezuela. Archives of Virology 158: 277-280. 3. Fiallo-Olivé E, Márquez-Martín B, Hassan I, Chirinos DT, Geraud-Pouey F, Navas-Castillo J, Moriones E (2013b) Complete genome sequences of two novel begomoviruses infecting common bean in Venezuela. Archives of Virology 158: 723–727. 4. Fiallo-Olivé E, Martínez-Zubiaur Y, Moriones E, Navas-Castillo J (2012a) A novel class of DNA satellites associated with New World begomoviruses. Virology 426: 1-6. 5. Fiallo-Olivé E, Navas-Castillo J, Moriones E, Martínez-Zubiaur Y (2010) Two novel begomoviruses belonging to different lineages infecting Rhynchosia minima. Archives of Virology 155: 2053-2058. 6. Fiallo-Olivé E, Navas-Castillo J, Moriones E, Martínez-Zubiaur Y (2012b) Begomoviruses infecting weeds in Cuba: increased host range and a novel virus infecting Sida rhombifolia. Archives of Virology 157: 141-146. 7. García-Andrés S, Monci F, Navas-Castillo J, Moriones E (2006) Begomovirus genetic diversity in the native plant reservoir Solanum nigrum: evidence for the presence of a new virus species of recombinant nature. Virology 350: 433-442. 8. King AMQ, Adams MJ, Carstens EB, Lefkowitz EJ (2012) Virus Taxonomy. Ninth Report of the International Committee on Taxonomy of Viruses. Elsevier, Academic Press. 9. López-Bueno A, Tamames J, Velázquez D, Moya A, Quesada A, Alcamí A (2009) High diversity of the viral community from an Antarctic lake. Science 326: 858-861. 10.Lozano G, Trenado HP, Valverde RA, Navas-Castillo J (2009) Novel begomovirus species of recombinant nature in sweet potato (Ipomoea batatas) and Ipomoea indica: taxonomic and phylogenetic implications. Journal of General Virology 90: 2550-2562. 11.Márquez-Martín B, Aragón-Caballero L, Fiallo-Olivé E, Navas-Castillo J, Moriones E (2011) Tomato leaf deformation virus, a novel begomovirus associated with a severe disease of tomato in Peru. European Journal of Plant Pathology 129: 1-7. 12.Márquez-Martín B, Maeso D, Martínez-Ayala A, Bernal R, Federici MT, Vincelli P, Navas-Castillo J, Moriones E (2012) Diverse population of a novel bipartite begomovirus infecting tomato crops in Uruguay. Archives of Virology 157: 1137–1142. 13.Martínez-Ayala A, Sánchez-Campos S, Cáceres F, Aragón-Caballero L, Navas-Castillo J, Moriones E (2013). Characterization and genetic diversity of pepper leafroll virus, a new bipartite begomovirus infecting pepper, bean and tomato in Peru. Annals of Applied Biology (en prensa) 14.Monci F, Sánchez-Campos S, Navas-Castillo J, Moriones E (2002) A natural recombinant between the geminiviruses Tomato yellow leaf curl Sardinia virus and Tomato yellow leaf curl virus exhibits a novel pathogenic phenotype and is becoming prevalent in Spanish populations. Virology 303: 317-326. 15.Navas-Castillo J, Fiallo-Olivé E, Sánchez-Campos S (2011) Emerging virus diseases transmitted by whiteflies. Annual Review of Phytopathology 49: 219–248. 16.Philippe N, Legendre M, Doutre G, Couté Y, Poirot O, Lescot M, Arslan D, Seltzer V, Bertaux L, Bruley C, Garin J, Claverie JM, Abergel C (2013). Pandoraviruses: amoeba viruses with genomes up to 2.5 Mb reaching that of parasitic eukaryotes. Science 341: 281-286. Vol.7 ¦ Nº 150-Monográfico MONOGRAFÍA CAZADORES DE GENOMAS! ! ¿CÓMO FUNCIONA? ! Monografía 2- 2014 Genomas y rompecabezas: una visión sobre el ensamblaje de genomas Aureliano Bombarely Gómez Investigador Asociado, Department of Plant Biology, Cornell University, Ithaca, Estados Unidos [email protected] !"#$%"&' El desarrollo nuevas tecnologías de secuenciación ha revolucionado el análisis de genomas. Los grandes proyectos de secuenciación se han ido sustituyendo por aproximaciones más modestas, tanto en personal como en costes. Actualmente es posible secuenciar, ensamblar y analizar un genoma vegetal de tamaño medio con una cantidad limitada de recursos, si bien todavía estamos lejos de poder ensamblar cualquier genoma. Genomas de gran tamaño, con un gran contenido en repeticiones, poliploides, o genomas con una elevada heterocigosidad pueden ser un problema de difícil solución. ! '("#)"'"*'+,-%",'.-,$#'/0#10'*0'+,-%"2' ,0'+*0&10'+3*-+*3-)"' La secuenciación de genomas nace en 1976 con el genoma del Bacteriófago MS2 1. No más grande que muchos tránscritos eucariotas (3,568 nucleótidos), fue secuenciado mediante nucleótidos marcados con 32P, digeridos con la ribonucleasa T1 y separados en un gel de poliacrilamida, en una época donde todavía no se había desarrollado la reacción en cadena de la polimerasa 2 y donde los ordenadores portátiles pesaban 25 kilos y tenían 64 Kb de memoria RAM (como el modelo IBM 5100). El desarrollo de los secuenciadores automáticos de ADN mediante el método de Sanger por parte de Applied Biosystems en 1987 supuso un salto cuantitativo. El primer genoma bacteriano, Haemophilus influenzae con un tamaño de 1.83 Mb, fue secuenciado en 1995 por Craig Venter mediante la metodología de Whole Genome Shotgun (WGS) usando 14 secuenciadores AB373 durante 3 meses. Las lecturas se ensamblaron con TIGR ASSEMBLER 3, un programa desarrollado por The Institute for Genomic Research (TIGR) que se basaba en el solapamiento de secuencias alineadas mediante una versión modificada del algoritmo Smith-Waterman. Se tardó 30 horas en un equipo con un solo procesador y 512 Mb de memoria RAM 4. Le seguirían la secuenciación del primer genoma eucariota (con un tamaño de 12.1 Mb), Saccharomyces cerevisiae 5; el del primer animal multicelular (con un tamaño de 100 Mb), Caenorhabditis elegans 6; el de la primera planta (con un tamaño de 157 Mb), Arabidopsis thaliana 7; el borrador del genoma del ser humano (con un tamaño de 3.2 Gb) 8,9; el genoma del primer vertebrado tras el ser humano (con un tamaño de 390 Mb), Fugu rubripes 10y el del primer mamífero tras el ser humano (con un tamaño de 2.5 Gb), Mus musculus 11. Para todos estos proyectos se utilizó la misma tecnología de secuenciación, y generalmente eran el fruto del esfuerzo de muchos grupos de investigación durante varios años. Exceptuando en los proyectos donde se utilizó la metodología de BAC-by-BAC como en Arabidopsis, los programas utilizados para el ensamblaje de (Arachne 12, WGA assembler 13) no diferían mucho en su planteamiento del desarrollado por TIGR años atrás basado en el solapamiento de secuencias, si bien eran programas mejor estructurados (con diferentes fases durante el ensamblaje) y que aprovechaban ciertos recursos computacionales como el uso de grupo de servidores (server farm) para usar cientos de procesadores. Por ejemplo en el proyecto del genoma humano dirigido por Craig Venter se utilizó un sistema con 40 servidores (con 4 procesadores y 4 Gb de memoria RAM cada uno) trabajando en paralelo durante 5 días. El ritmo de secuenciación de genomas eucariotas durante los primeros años del nuevo milenio ha sido de aproximadamente dos o tres genomas por año en el mejor de los casos pero actualmente dicho ritmo se ha disparado. En el año 2012, solo en el área de plantas se han publicado más de una docena de genomas14-27. Este cambio se debe a dos factores: El desarrollo de las nuevas tecnologías de secuenciación (Next Generation Sequencing, NGS) que han permitido el abaratamiento del coste de la secuenciación y el uso de nuevos programas de ensamblaje más rápidos y eficientes. En el año 2005 se publicó la primera de las nuevas metodologías de secuenciación basada en una reacción de pirólisis sobre una matriz sólida con millones de puntos, cada uno representado un secuencia 28. 454 (que más tarde sería comprada por Roche) sacó al mercado un nuevo sistema de secuenciación capaz de producir millones de lecturas por proceso. Al pirosecuenciamiento de 454 le han seguido la secuenciación basada en terminadores de química reversible de Illumina (2005) 29, la secuenciación por ligamiento de SOLiD (2007) 30, la secuenciación por iones semiconductores de Ion Torrent Biosystems (2011) 31 y la secuenciación de una sola molécula en tiempo real de Pacific Vol.7 ¦ Nº 150-Monográfico 151 MONOGRAFÍA CAZADORES DE GENOMAS! Monografía 2- 2014 Biosciences (2012) 32 entre otros, aunque sin duda alguna, la más popular es Illumina. Actualmente puede producir 600 Gb de lecturas por proceso, 200 veces el tamaño del genoma humano en tan solo 11 días haciendo posible la secuenciación de genomas de tamaño similares en cortos periodos de tiempo. creación de una secuencia consenso para cada alelo en las regiones con más variabilidad, lo que se traduce en burbujas de ensamblaje y que a menudo suelen ser difícil de incluir en la reconstrucción del genoma. Lo que es más, la cobertura efectiva (cuantas veces está representado el genoma en el set de secuencias) disminuye dificultando el ensamblaje. ! !" Eventos de duplicación. Una gran mayoría de organismos eucariotas presentan algún evento de duplicación genómica (Whole Genome Duplication, WGD) en su historia. Este fenómeno es especialmente representativo en plantas donde los eventos de duplicaciones son relativamente comunes. Por ejemplo existen dos eventos de duplicación (datados alrededor de 319 y 192 Ma respectivamente) comunes para todas las angioespermas 34. En el caso de Arabidopsis existen otros 3 eventos de duplicación que han dado forma al genoma que se conoce hoy día (el primero producido tras la separación de monocotiledóneas y dicotiledóneas, y el segundo y tercero durante de la formación de las brasicáceas 35,36) aunque no han influenciado de forma notable el ensamblaje de su genoma. Distinto es el caso de la soja (Glycine max) con dos eventos de duplicación, el más reciente con una antigüedad de 13 Ma y con un gran elevado contenido de repeticiones 37. !" Repeticiones. Genomas con un elevado contenido en repeticiones pueden ser difíciles de ensamblar. A fin de facilitar el proceso de ensamblaje, estos programas filtran las lecturas extremadamente representadas pudiendo producir genomas muy fragmentados en caso de que las repeticiones se encuentren uniformemente distribuidas a lo largo de todo el genoma. Es conveniente realizar estudios preliminares sobre el contenido en repeticiones usando una secuenciación de baja cobertura 38y/o análisis citogenéticos mediante FISH (Fluorescent InSitu Hybridization) 39. Si los resultados preliminares revelan un alto contenido en elementos repetitivos uniformemente distribuidos en la eucromatina puede que el uso de la metodología de WGS sin el apoyo de secuenciación de BACs sea inviable. (-#"40&)3'$&'+,35"613')"'#"6$"&6-06-7&' 152 Antes de embarcarse en un proyecto de secuenciación de un genoma es crítico tener un diseño experimental adecuado. La aproximación puede ser totalmente distinta incluso entre individuos de la misma especie dependiendo de algunas diferencias genéticas como el grado de heterocigosidad del individuo en cuestión. Cada uno de ellos tienen distintas características que pueden hacer totalmente inadecuadas algunas metodologías. Por otro lado el presupuesto y tiempo disponible pueden limitar el uso de algunas metodologías como el uso de cromosomas artificiales bacterianos (BAC), que si bien son más seguras y exactas, pueden disparar el coste de procesamiento y secuenciación varios órdenes de magnitud. 1- Conoce a tu enemigo: Que secuenciar. Unos de los primeros pasos para enfrentarse a un proyecto de secuenciación es el de conocer algunas características del genoma a secuenciar tales como: !" Tamaño de genoma. Existen algunas bases de datos que pueden dar una información orientativa del tamaño del genoma a través de estudios citogenéticos. Un buen ejemplo de ello es la base de datos de Plant DNA C-values 33 donde pueden encontrarse medidas de tamaños para más de 1,200 genomas vegetales. !" Poliploidía. Al igual que en el caso anterior, estudios citogenéticos previos pueden facilitar este tipo de información. El ensamblaje de una especie poliploide tiene el gran problema de que una gran parte de las regiones homoeólogas (provenientes de uno o varios progenitores, en el caso de auto- y alo-poliploides respectivamente) van a colapsar en una misma secuencia consenso 23. Existen distintas opciones para minimizar este problema como el uso de la información de pares para crear una fase para las regiones homoeólogas aunque por el momento la aproximación más usada es la de la secuenciación de uno de los progenitores diploides para su uso como referencia 27. !" Heterocigozidad. De forma parecida a la autopoliploidía, una baja heterocigosidad de la muestra puede conducir al colapso de dos alelos, aunque en este caso es un efecto deseable. Por otro lado una elevada heterocigosidad puede traducirse en la ! De esta manera es importante que en la medida de lo posible se simplifique el proyecto de secuenciación seleccionando variedades con una baja heterocigosidad, dobles haploides si la especie es de forma natural un autopoliploide o secuenciando los progenitores diploides si la especie es un alopoliploide y generando estudios preliminares sobre el contenido en repeticiones antes de comenzar a secuenciar. 2- Estima la cantidad de datos necesaria: Cómo y cuánto secuenciar. Vol.7 ¦ Nº 150-Monográfico MONOGRAFÍA CAZADORES DE GENOMAS! El siguiente paso es decidir que tecnología usar y cuanto secuenciar. Para secuenciaciones mediante WGS (Whole Genome Shotgun) es esencial, independientemente de la tecnología utilizada, el uso de pares (Pair Ends y Mate Pairs)40,41. Estos sirven para relacionar las secuencias consenso (contigs) entre sí y crear así estructuras de mayor tamaño (scaffolds) con una estimación aproximada de la distancia entre contigs. Es importante el uso de combinaciones de librerías de pares con insertos de varios tamaños, por ejemplo una o dos librerías con insertos de tamaños entre 170 y 800 pb y dos o tres librerías con insertos entre 2 y 20 Kb. La longitud de las lecturas utilizadas dependerá de la tecnología de secuenciación seleccionada, pero es aconsejable secuenciar con la máxima longitud disponible siempre y cuando no tenga un efecto drástico en la calidad de las secuencias (actualmente 500 pb para 454 y 150 pb para Illumina HiSeq y 250 pb para Illumina MiSeq). Finalmente queda decidir cuanto ha de secuenciarse, y de nuevo dependerá de la tecnología de secuenciación usada. Para 454 es recomendable usar al menos 10X (es decir 10 veces el tamaño del genoma a secuenciar), si bien se obtienen buenos resultados a partir de 30X. Para Illumina la comunidad se ha puesto de acuerdo para recomendar coberturas en torno a 100X. De esta manera significa que, por ejemplo, si se quisiera secuenciar una especie como el olivo (Olea europaea) con un tamaño estimado de 1.9 Gb se necesitarían al menos 57 Gb o 190 Gb de lecturas procesadas, producidas por 454 o Illumina respectivamente (sin contar posibles problemas inherentes a esta especie como su elevada heterocigosidad). 3- Se consciente de que no sólo es un problema de secuencias: ¿qué recursos computacionales y genéticos son necesarios? Otro factor a tener en cuenta son los recursos computacionales disponibles ya que los ensambladores utilizan una gran cantidad de memoria RAM. Por ejemplo, el genoma de Nicotiana benthamiana (con un tamaño estimado de 3 Gb, secuenciado con una cobertura de 63X, 229.2 Gb de lecturas 23) no pudo ensamblarse en un servidor de 512 Gb de memoria RAM, y tuvo que crearse un subset de datos con 2/3 del set original para ajustarse a los recursos disponibles a partir del cual se creó el ensamblaje base. Los gaps fueron completados con el set completo de datos en una operación que necesitó menos recursos computaciones. Respecto al software utilizado para el ensamblaje, dependerá en gran medida de la tecnología de secuenciación y la metodología utilizada, pero los más populares son AllPath_LG 42 y SOAPdenovo 43. Una vez el genoma está ensamblado es conveniente mapear las lecturas y llamar SNPs para valorar la heterocigosidad del genoma, o en caso de poliploides, estimar el porcentaje de colapso entre regiones homoeólogas. Una vez se ha conseguido un ensamblaje, el siguiente paso es asignar los contigs y scaffolds producidos a diferentes cromosomas usando mapas genéticos y marcadores moleculares. A este proceso se le denomina anclaje de secuencias en pseudo- Monografía 2- 2014 moléculas. Para este proceso es importante tener mapas genéticos de alta densidad con un gran número de marcadores. El número necesario de marcadores para anclar un ensamblaje dependerá de la calidad de este. Por ejemplo, el ensamblaje de N. benthamiana posee un valor de N90=30,261 (es decir que el 90% del ensamblaje está representado por 30,261 secuencias) de manera que el anclaje del 90% del ensamblaje requeriría al menos de 60,522 marcadores (dos marcadores por secuencia para poder orientarlas). Si bien el uso de NGS puede generar cientos de miles de marcadores, su uso para la creación de un mapa dependerá del tamaño de la población utilizada y del numero de eventos de recombinación producidos al generar la población de mapeo. El uso de Genotyping-By-Sequencing (GBS) 44 y microarrays de genotipado 45ha permitido impulsar la creación de mapas varios órdenes de magnitud hasta miles de marcadores. En el caso de N. benthamiana se necesitaría mejorar el ensamblaje al menos un orden de magnitud (N50 ~ 6,000) antes de abordar un anclaje con un mapa de alta densidad. Ensamblajes con scaffolds de mayor tamaño disminuyen el número de marcadores necesarios para anclar el ensamblaje. Por ejemplo para la versión 2.40 de S. lycopersicum donde el 95% del ensamblaje está contenido en 72 scaffolds de al menos 1.96 Mb se usaron dos mapas físicos y un mapa genético. En total se ancló un 97% del ensamblaje 16. 4- Buscando el ensamblaje útil: cómo anotar un ensamblaje Independientemente de que se haya o no anclado una gran parte del genoma, un paso determinante en un proyecto de secuenciación de un genoma es la anotación estructural del mismo. Existen dos anotaciones estructurales que comúnmente se utilizan sobre cualquier ensamblaje: Repeticiones y genes: !" Para la anotación de repeticiones se analiza el número de ocurrencias de distintos fragmentos del genoma y se compara con bases de datos de repeticiones como RepBase 46. La herramienta más utilizada es RepeatModeler como pipeline que integra RepeatScout 47. !" La anotación de genes es algo más compleja. Se combinan dos tipos de metodologías: Predicciones de-novo y creación de modelos de genes basados en alineamientos con tránscritos. En el primer caso un programa analiza la secuencia producida en el ensamblaje en busca de marcos de lectura (ORF). Los programas más usados son Augustus 48, SNAP 49 o GeneMark 50. En el segundo caso se necesita una buena representación del transcriptoma lo que implica el uso de diferentes librerías de ESTs (Expressed Sequence Tags) ensambladas en unigenes o diferentes sets de datos de RNAseq. Por ejemplo en la anotación del genoma de N. benthamiana se usó librerías de RNAseq de hoja, raíz, flores y distintos estreses bióticos y abióticos a fin de capturar la Vol.7 ¦ Nº 150-Monográfico 153 ! 154 MONOGRAFÍA CAZADORES DE GENOMAS! Monografía 2- 2014 máxima diversidad transcriptómica. Como programas se usan Exonerate para unigenes 51o Tophat para RNAseq 52. Otra alternativa es el uso de la secuencia de la proteína tal y como hace GeneWise 53. Todos estos programas suelen usarse en una pipeline de análisis que integra los resultados de las predicciones de novo y de las predicciones basadas en alineamientos con tránscritos. La más popular es Maker 54. Al igual que los ensamblajes, que requieren de un buen poder computacional, la anotación de genomas requiere del uso de sistemas multinúcleo o granjas de computadores con sistemas MPI o Sun Grid Engine a fin de realizar la anotación en una cantidad razonable de tiempo. Por ejemplo, la anotación del genoma de N. benthamiana se realizó en un servidor con 64 núcleos y 512 Gb de memoria RAM (aunque en este caso no llegó a usarse más de 32 Gb) durante aproximadamente 20 días. Una vez se ha generado una anotación estructural es conveniente visualizar los resultados usando un navegador genómico (Genome Browser). Si bien los más populares son UCSC Genome Browser 55y Gbrowse 56, son navegadores difíciles de instalar generalmente orientados a ser usados por una base de datos. Es más adecuado el uso de programas orientados a una instalación local. Un buen ejemplo es IGV (Integrative Genome Viewer) que permite además cargar otro tipo de datos (como mapas de secuencias) sobre la anotación estructural 57. La anotación estructural no asigna posibles funciones a cada uno de los genes producidos durante el proceso de anotación. Para ello es necesario efectuar una anotación funcional de los mismos comparando las secuencias de CDS o proteínas predecidas con las bases de datos existentes. Generalmente se utilizan dos aproximaciones complementarias: La primera, la búsqueda de genes homólogos a través de alineamientos de estas secuencias con las secuencias de distintas bases de datos usando el algoritmo de Smith-Waterman. La herramienta más utilizada es Blast 58y las bases de datos más comunes son GenBank 59, SwissProt y TrEmbl 60. También se suelen comparar con los modelos de las especies más conocidas dentro del clase de estudio, por ejemplo, en plantas suele utilizarse arabidopsis (Arabidopsis thaliana) y arroz (Oryza sativa) como modelo para dicotiledóneas y monocotiledóneas respectivamente. La segunda es la búsqueda de homología de los dominios funcionales de las proteínas predecidas. La herramienta usada para ello es InterProScan y la base de datos usada InterPro, compuesta a su vez por diferentes bases de datos de dominios como Pfam o Panther 61. La anotación funcional de dominios lleva asociada la asignación de términos basados en categorías de vocabulario controlado procedentes de las ontologías de genes (Gene Ontology, GO terms) 62. 8"&7%-60' 63%+0,01-.09' :;#' 0**;' )"' $&' <"&3%0' El proceso de ensamblaje y anotación puede resumirse en varios ficheros fasta con las secuencias producidas durante el ensamblaje y la anotación (contigs, scaffolds, pseudomoléculas, genes, ARNm, secuencias codificantes, proteínas y repeticiones) y .gff3 con la información de mapeado (cómo se integran los contigs en los scaffolds o cómo se integran éstos en las pseudomoléculas, o cómo son las relaciones estructurales entre los distintos elementos de la anotación como genes y exones)63. Pero es justo en este momento cuando comienza el verdadero análisis, cuando se puede buscar sentido a los datos obtenidos generalmente a través de la comparación con otras especies secuenciadas anteriormente. Los análisis más comunes son: !" Análisis de familias de genes. Los genes producidos se agrupan con genes de otras especies basados en porcentajes de homología entre proteínas. El programa más utilizado es Ortho-MCL 64. Este análisis también permite filtrar aquellos genes provenientes de múltiples repeticiones de transposones ya que generalmente se agrupan en familias con una enorme cantidad de genes de la misma especie. !" Análisis de enriquecimiento de términos GO. También es común la agrupación de genes por categorías funcionales y su comparación con otras especies. Para ello se aplican tests estadísticos como el análisis de enriquecimiento 65a fin de discernir si existen categorías funcionales sobrerrepresentadas en la especie analizada. !" Análisis de sintenia con otras especies. Consiste en comparar el orden lineal de los genes entre especies distintas a fin de descubrir el grado de conservación de dicho orden. En especies más cercanas desde un punto de vista filogenético cabe esperar una mayor conservación en el orden de los genes. Existen varias herramientas diseñadas para el estudio de sintenia entre especies. Destacan SyMap 66por su uso sencillo y MCScanX 67por su capacidad de computar los valores de Ks (ratio de sustituciones sinónimas) a fin de estimar la edad de divergencia entre bloques de sintenia. Este tipo de análisis pueden utilizarse para el estudio de WGD (Whole Genome Duplications) a través de los bloques sintenia internos del genoma en cuestión. =",#+"61-.0#'+0,0'$&'>$1$,3'?&%")-013' El desarrollo de nuevas metodologías y aplicaciones en el campo de la secuenciación es un proceso continuo y rápido. Desde que se diseña un proyecto de secuenciación hasta que finalmente llega la financiación ocurren cambios en tecnologías conocidas o aparecen nuevas aplicaciones que pueden modificar parte del plan original. Son comunes la disminución en los precios de secuenciación o la generación de lecturas de mayor longitud por el mismo precio. Otros cambios interesanVol.7 ¦ Nº 150-Monográfico MONOGRAFÍA CAZADORES DE GENOMAS! tes son el desarrollo de nuevos protocolos y reactivos para crear librerías de pares con insertos de mayor tamaño como Nextera® 68 o NxSeq® 40 Kb librerías 69. También está por ver si el desarrollo de métodos como el de Moleculo® para secuenciar fragmentos únicos de 10 Kb 70 o el uso de la tecnología de fragmentos largos (Long Fragment Read, LFR)71solventará parte de los problemas derivados de genomas poliploides o de una elevada heterocigosidad. Desde un punto de vista computacional existe un continuo avance en el desarrollo de nuevos procesadores y el abaratamiento de la memoria RAM que hace más accesible la compra de grandes equipos por parte de pequeños grupos de investigación. A largo plazo existe la posibilidad de que cambie de forma radical los sistemas de computación por ejemplo mediante el desarrollo de una nueva generación de transistores de grafeno de alto rendimiento 72,73con frecuencias mucho mayores que los tradicionales transistores de silicio. ! !! ! Monografía 2- 2014 @3&6*$#-7&' La secuenciación de genomas, lejos de convertirse en un proceso rutinario, es un proceso accesible a cualquier grupo de investigación siempre y cuando posea los medios adecuados y el genoma no sea excepcionalmente grande o polimórfico. El número de genomas eucariotas de tamaño medio se ha multiplicado exponencialmente en los últimos años no solo abriendo la puerta a interesantes estudios evolutivos, sino también generando una importante fuente de recursos para el estudio de enfermedades, la generación de herramientas para la mejora de animales y plantas o la caracterización de la biodiversidad poblacional de cientos de individuos de la misma especie. El desarrollo de las tecnologías de la secuenciación y de análisis de la información están acelerando la generación de conocimiento a límites impensables a principios de siglo. Queda por ver que depara el futuro de la genómica y la bioinformática y cual será el papel que juegue en la ciencia, y a más largo plazo en la historia del ser humano.! AGRADECIMIENTO: El autor quiere agradecer al Dr. Noe Fernández la ayuda prestada en la edición del artículo. 155 Bibliografía citada: 1."Fiers, W., Contreras, R., Duerinck, F. & Haegeman, G. Complete nucleotide sequence of bacteriophage MS2 RNA: primary and secondary structure of the replicase gene. Nature (1976). 2."Mullis, K. B. & Faloona, F. A. Specific synthesis of DNA in vitro via a polymerase-catalyzed chain reaction. Meth. Enzymol. 155, 335–350 (1987). 3."Sutton, G. G., WHITE, O., Adams, M. D. & KERLAVAGE, A. R. TIGR Assembler: A New Tool for Assembling Large Shotgun Sequencing Projects. Genome Science and Technology 1, 9–19 (1995). 4."Fleischmann, R. D., Adams, M. D., White, O. & Clayton, R. A. Whole-genome random sequencing and assembly of Haemophilus. Science 269, 496–512 (1995). 5."Goffeau, A. et al. Life with 6000 genes. Science 274, 546–563–7 (1996). 6."C. elegans Sequencing Consortium. Genome sequence of the nematode C. elegans: a platform for investigating biology. Science 282, 2012– 2018 (1998). 7."Arabidopsis Genome Initiative. Analysis of the genome sequence of the flowering plant Arabidopsis thaliana. Nature 408, 796–815 (2000). 8."Lander, E. S. et al. Initial sequencing and analysis of the human genome. Nature 409, 860–921 (2001). 9."Venter, J. C. et al. The Sequence of the Human Genome. Science Signaling 291, 1304 (2001). 10."Aparicio, S. Whole-Genome Shotgun Assembly and Analysis of the Genome of Fugu rubripes. Science 297, 1301–1310 (2002). 11."Chinwalla, A. T. et al. Initial sequencing and comparative analysis of the mouse genome. Nature 420, 520–562 (2002). 12."Batzoglou, S. ARACHNE: A Whole-Genome Shotgun Assembler. Genome Res 12, 177–189 (2002). 13."Myers, E. W., Sutton, G. G., Delcher, A. L., Dew, I. M. & Fasulo, D. P. A Whole-Genome Assembly of Drosophila. Science (2000). 14."Zhang, Q. et al. The genome of Prunus mume. Nat Commun 3, 1318 (2012). 15."Naim, F. et al. Advanced Engineering of Lipid Metabolism in Nicotiana benthamiana Using a Draft Genome and the V2 Viral Silencing-Suppressor Protein. PLoS ONE 7, e52717 (2012). 16."Tomato Genome Consortium. The tomato genome sequence provides insights into fleshy fruit evolution. Nature 485, 635–641 (2012). 17."Zhang, G. et al. Genome sequence of foxtail millet (Setaria italica) provides insights into grass evolution and biofuel potential. Nat Biotechnol 30, 549–554 (2012). 18."Bennetzen, J. L. et al. Reference genome sequence of the model plant Setaria. Nat Biotechnol 30, 555–561 (2012). 19."Garcia-Mas, J. et al. The genome of melon (Cucumis melo L.). P Natl Acad Sci Usa (2012). doi:10.1073/pnas.1205415109 20."Wang, Z. et al. The genome of flax (Linum usitatissimum) assembled de novo from short shotgun sequence reads. Plant J (2012). doi: 10.1111/j.1365-313X.2012.05093.x 21."Wu, H.-J. et al. Insights into salt tolerance from the genome of Thellungiella salsuginea. P Natl Acad Sci Usa (2012). doi:10.1073/pnas. 1209954109 22."D'Hont, A. et al. The banana (Musa acuminata) genome and the evolution of monocotyledonous plants. Nature (2012). doi:10.1038/nature11241 23."Bombarely, A. et al. A draft genome sequence of Nicotiana benthamiana to enhance molecular plant-microbe biology research. Mol. Plant Microbe Interact. (2012). doi:10.1094/MPMI-06-12-0148-TA 24."Wang, K. et al. The draft genome of a diploid cotton Gossypium raimondii. Nat Genet 44, 1098–1103 (2012). 25."Xu, Q. et al. The draft genome of sweet orange (Citrus sinensis). Nat Genet 45, 59–66 (2012). Vol.7 ¦ Nº 150-Monográfico MONOGRAFÍA CAZADORES DEMonografía GENOMAS! 2- 2014 156 26."Wu, J. et al. The genome of the pear (Pyrus bretschneideri Rehd.). Genome Res (2012). doi:10.1101/gr.144311.112 27."Paterson, A. H. et al. Repeated polyploidization of Gossypium genomes and the evolution of spinnable cotton fibres. Nature 492, 423– 427 (2012). 28."Margulies, M. et al. Genome sequencing in microfabricated high-density picolitre reactors. Nature 437, 376–380 (2005). 29."Bentley, D. R. et al. Accurate whole human genome sequencing using reversible terminator chemistry. Nature 456, 53–59 (2008). 30."Valouev, A. et al. A high-resolution, nucleosome position map of C. elegans reveals a lack of universal sequence-dictated positioning. Genome Res 18, 1051–1063 (2008). 31."Rothberg, J. M. et al. An integrated semiconductor device enabling non-optical genome sequencing. Nature 475, 348–352 (2011). 32."Eid, J. et al. Real-time DNA sequencing from single polymerase molecules. Science 323, 133–138 (2009). 33."Bennett, M. D. & Leitch, I. J. Nuclear DNA amounts in angiosperms: targets, trends and tomorrow. Ann Bot-London (2011). 34."Jiao, Y. et al. Ancestral polyploidy in seed plants and angiosperms. Nature 473, 97–U113 (2011). 35."Bowers, J., Chapman, B., Rong, J. & Paterson, A. Unravelling angiosperm genome evolution by phylogenetic analysis of chromosomal duplication events. Nature 422, 433–438 (2003). 36."Jaillon, O. et al. The grapevine genome sequence suggests ancestral hexaploidization in major angiosperm phyla. Nature 449, 463–467 (2007). 37."Schmutz, J. et al. Genome sequence of the palaeopolyploid soybean. Nature 463, 178–183 (2010). 38."Novak, P., Neumann, P. & Macas, J. Graph-based clustering and characterization of repetitive sequences in next-generation sequencing data. Bmc Bioinformatics 11, 378 (2010). 39."Lim, K., Matyasek, R., Lichtenstein, C. & Leitch, A. Molecular cytogenetic analyses and phylogenetic studies in the Nicotiana section Tomentosae. Chromosoma 109, 245–258 (2000). 40."Ng, P. Multiplex sequencing of paired-end ditags (MS-PET): a strategy for the ultra-high-throughput analysis of transcriptomes and genomes. Nucleic Acids Res 34, e84–e84 (2006). 41."Fullwood, M. J., Wei, C.-L., Liu, E. T. & Ruan, Y. Next-generation DNA sequencing of paired-end tags (PET) for transcriptome and genome analyses. Genome Res 19, 521–532 (2009). 42."Gnerre, S. et al. High-quality draft assemblies of mammalian genomes from massively parallel sequence data. P Natl Acad Sci Usa 108, 1513–1518 (2011). 43."Luo, R. et al. SOAPdenovo2: an empirically improved memory-efficient short-read de novo assembler. Gigascience 1, 18 (2012). 44."Lu, F. et al. Switchgrass genomic diversity, ploidy, and evolution: novel insights from a network-based SNP discovery protocol. PLoS Genet 9, e1003215 (2013). 45."Desjardins, C. A. et al. Fine-scale mapping of the Nasonia genome to chromosomes using a high-density genotyping microarray. G3 (Bethesda) 3, 205–215 (2013). 46."Kapitonov, V. V. & Jurka, J. A universal classification of eukaryotic transposable elements implemented in Repbase. Nat Rev Genet 9, 411–2– author reply 414 (2008). 47."Price, A. L., Jones, N. C. & Pevzner, P. A. De novo identification of repeat families in large genomes. Bioinformatics 21 Suppl 1, i351–8 (2005). 48."Stanke, M. et al. AUGUSTUS: ab initio prediction of alternative transcripts. Nucleic Acids Res 34, W435–W439 (2006). 49."Korf, I. Gene finding in novel genomes. Bmc Bioinformatics 5, 59 (2004). 50."Lukashin, A. V. & Borodovsky, M. GeneMark.hmm: New solutions for gene finding. Nucleic Acids Res (1998). 51."Slater, G. & Birney, E. Automated generation of heuristics for biological sequence comparison. Bmc Bioinformatics 6, 31 (2005). 52."Trapnell, C., Pachter, L. & Salzberg, S. L. TopHat: discovering splice junctions with RNA-Seq. Bioinformatics 25, 1105–1111 (2009). 53."Birney, E. Using GeneWise in the Drosophila Annotation Experiment. Genome Res 10, 547–548 (2000). 54."Cantarel, B. L. et al. MAKER: An easy-to-use annotation pipeline designed for emerging model organism genomes. Genome Res 18, 188–196 (2007). 55."Kuhn, R. M., Haussler, D. & Kent, W. J. The UCSC genome browser and associated tools. Brief. Bioinformatics 14, 144–161 (2013). 56."Stein, L. D. Using GBrowse 2.0 to visualize and share next-generation sequence data. Brief. Bioinformatics 14, 162–171 (2013). 57."Robinson, J. T. et al. Integrative genomics viewer. Nat Biotechnol 29, 24–26 (2011). 58."McGinnis, S. & Madden, T. L. BLAST: at the core of a powerful and diverse set of sequence analysis tools. Nucleic Acids Res (2004). 59."Benson, D. A. et al. GenBank. Nucleic Acids Res 41, D36–42 (2013). 60."Magrane, M. & Consortium, U. UniProt Knowledgebase: a hub of integrated protein data. Database (Oxford) 2011, bar009 (2011). 61."Mulder, N. & Apweiler, R. InterPro and InterProScan: tools for protein sequence classification and comparison. Methods Mol. Biol. 396, 59–70 (2007). 62."Gene Ontology Consortium. Gene Ontology annotations and resources. Nucleic Acids Res 41, D530–5 (2013). 63."Moore, B., Fan, G. & Eilbeck, K. SOBA: sequence ontology bioinformatics analysis. Nucleic Acids Res 38, W161–4 (2010). 64."Li, L. OrthoMCL: Identification of Ortholog Groups for Eukaryotic Genomes. Genome Res 13, 2178–2189 (2003). 65."Subramanian, A. et al. Application of a priori established gene sets to discover biologically important differential expression in microarray data. P Natl Acad Sci Usa 102, 15278–15279 (2005). 66."Soderlund, C., Bomhoff, M. & Nelson, W. M. SyMAP v3.4: a turnkey synteny system with application to plant genomes. Nucleic Acids Res 39, e68 (2011). 67."Wang, Y. et al. MCScanX: a toolkit for detection and evolutionary analysis of gene synteny and collinearity. Nucleic Acids Res 40, e49 (2012). 68."Kaper, F. et al. Whole-genome haplotyping by dilution, amplification, and sequencing. P Natl Acad Sci Usa (2013). doi:10.1073/pnas. 1218696110 69."Wu, C. C., Ye, R., Jasinovica, S., Wagner, M. & Godiska, R. Long-span, mate-pair scaffolding and other methods for faster next-generation sequencing library creation. Nat Meth (2012). 70."Waldbieser, G. Production Of Long (1.5kb – 15.0kb), Accurate, DNA Sequencing Reads Using An Illumina HiSeq2000 To Support De Novo Assembly Of The Blue Catfish Genome. Plant and Animal Genome XXI Conference (2013). 71."Peters, B. A. et al. Accurate whole-genome sequencing and haplotyping from 10 to 20 human cells. Nature 487, 190–195 (2012). 72."Wu, Y. et al. High-frequency, scaled graphene transistors on diamond-like carbon. Nature 472, 74–78 (2011). 73."Nakaharai, S. et al. Electrostatically-reversible polarity of dual-gated graphene transistors with He ion irradiated channel: Toward reconfigurable CMOS applications. in 2012 IEEE International Electron Devices Meeting (IEDM) 4.2.1–4.2.4 (IEEE, 2012). doi:10.1109/IEDM. 2012.6478976 Vol.7 ¦ Nº 150-Monográfico Monografía 2- 2014 Premio Nobel de Medicina o Fisiología 2014 Por segundo año consecutivo, el Nobel en Fisiología o Medicina ha caído del lado de las Neurociencias, un área de investigación muy fructífera que ha cosechado, desde que se instauró en 1901, 16 de los 105 premios en esta categoría (señalar que el primero de ellos, en 1906, fue para Santiago Ramón y Cajal, compartido con Camillo Golgi, por sus estudios sobre la estructura del sistema nervioso). También en esta ocasión, el premio Nobel ha estado compartido, otorgando la mitad a John O'Keefe y la otra mitad en forma conjunta al matrimonio formado por May-Britt Moser y Edvard I. Moser, por sus descubrimientos de las células que constituyen el sistema de posicionamiento en el cerebro, un sistema que nos permite orientarnos en el espacio y conducirnos a través de él. El reconocimiento de las bases neurales de este sistema de orientación, conocido como el “GPS cerebral”, ha tardado muchos años en ver la luz desde que, a principios de los 70, John O'Keefe uno de los investigadores premiados, y actualmente en el University College de Londres, descubriera el primer elemento clave de este sistema de posicionamiento. Haciendo registros electrofisiológicos en neuronas del hipocampo de ratas (el hipocampo es una región cerebral implicada en la formación de las memorias), observó que ciertas neuronas se activaban cuando el animal se encontraba en una localización particular de su entorno, mientras que otras neuronas diferentes se activaban cuando el animal se hallaba en un lugar distinto. Llamó a estas neuronas place cells (células de posición), pues su patrón de actividad estaba codificando para una posición concreta en el espacio. O'Keefe concluía que el hipocampo generaba numerosos mapas, representados por la actividad colectiva de place cells que se activaban en diferentes posiciones del espacio. Por lo tanto, la memoria de un entorno podía ser almacenada como una combinación específica de las actividades de las place cells del hipocampo. Hubo que esperar más de 30 años desde el hallazgo de las place cells por O´Keefe, para el descubrimiento de otro componente clave del sistema de posicionamiento del cerebro. En 2005, el matrimonio formado por May-Britt Moser (en el Centre for Neural Computation, en Trondheim, Noruega) y Edvard Moser (en el Kavli Institute for Systems Neuroscience, Trondheim, Noruega), estudiando las conexiones del hipocampo, observaron que algunas neuronas de la corteza entorrinal (una región cerebral próxima al hipocampo y con el que tiene numerosas conexiones) presentaban un patrón de actividad asombroso. Lo que sorprendió a estos investigadores era que estas neuronas de la corteza entorrinal estaban activas cuando la rata ocupaba varias posiciones dentro del recinto, que en conjunto formaban los vértices de un espacio o rejilla hexagonal. Cada una de estas neuronas, que denominaron grid cells (células de rejilla), se activaba según un patrón espacial específico, constituyendo colectivamente un sistema de coordenadas que permitía la navegación. Estas grid cells, junto con otras neuronas de la corteza entorrinal que reconocen la dirección de la cabeza y los los límites del recinto, formarían circuitos nerviosos con las place cells del hipocampo. Estos circuitos constituirían un sistema de posicionamiento global (GPS) en el cerebro que permitiría al animal, usando determinadas claves contextuales almacenadas en la memoria, saber dónde está y por dónde ir para alcanzar su destino. Los estudios de casos clínicos y mediante técnicas de neuroimagen apoyan la existencia de las place cells y grid cells en los seres humanos, lo que sugiere que este sistema de posicionamiento, descubierto en roedores, también funciona en las personas. El conocimiento del sistema de posicionamiento del cerebro puede ayudar a comprender el mecanismo responsable de la devastadora pérdida de la memoria espacial que afecta a los pacientes con la enfermedad de Alzheimer, cuyo hipocampo y corteza entorrinal se ven afectados en una etapa temprana, y que a menudo no saben encontrar el camino de vuelta a casa porque no pueden reconocer su entorno. El descubrimiento del sistema de posicionamiento global del cerebro constituye un claro ejemplo de cómo grupos de neuronas especializadas trabajan juntas para realizar funciones cognitivas superiores, y apoya la idea de que otros procesos cognitivos como la memoria, el pensamiento o la planificación tiene su base en la actividad de conjuntos de neuronas interconectadas que trabajan de forma coordinada. José Carlos Dávila [email protected] ! ! Vol.7 ¦ Nº 150-Monográfico 157 158 Fuente de la ilustración: Comunicado de prensa de la Asamblea Nobel del Instituto Karolinska informando de la concesión del Premio Nobel de Medicina y Fisiología 2014. ! Vol.7 ¦ Nº 150-Monográfico MONOGRAFÍA CAZADORES DE GENOMAS! ! ! ! Monografía 2- 2014 ! APÉNDICE: PERFIL DE LOS AUTORES QUE HAN COLABORADO EN EL MONOGRÁFICO CAZADORES DE GENOMAS (EN ESPAÑA) Carles Lalueza Fox DOCUMENTACIÓN Web of Science_291014. (de Todas las bases de datos) Autor: (lalueza-fox c) AND Dirección: (barcelona) Período de tiempo: Todos los años Resultados: 85 AFILIACIÓN Instituto de Biología Evolutiva (IBE) CSIC-Universidad Pompeu Fabra. Barcelona, Spain. ! 159 AREAS DE INVESTIGACIÓN ISI (5) Genetics Heredity, Biochemistry Molecular Biology, Zoology, Evolutionary Biology, Cell Biology, Science Technology Other Topics. PUBLICACIÓN MÁS RECIENTE GOMEZ-SANCHEZ D., OLALDE I., PIERINI F. et ál. 2014 Mitochondrial DNA from El Mirador Cave (Atapuerca, Spain) Reveals the Heterogeneity of Chalcolithic Populations. Plos One, vol. 9, no. 8, !"#$ 10.1371/journal.pone.0105105. ISSN 1932-6203. PUBLICACIONES MÁS CITADAS (3) GREEN R.E., KRAUSE J., BRIGGS A.W. et ál. 2010. A Draft Sequence of the Neandertal Genome. Science, vol. 328, no. 5979, pp. 710-722. ISSN 0036-8075 Veces citado: 697 ! COOPER A., LALUEZA-FOX C., ANDERSON S. et ál. 2001. Complete mitochondrial genome sequences of two extinct moas clarify ratite evolution. Nature, vol. 409, no, 6821, pp. 704-707. ISSN 0028-0836 Veces citado: 250 ! ! BRIGGS A.W,. GOOD J.M., GREEN R.E. et ál. 2009. Targeted Retrieval and Analysis of Five Neandertal mtDNA Genomes. Science, vol. 325, no. 5938, pp. 318-321. ISSN 0036-8075 Veces citado: 194 PUBLICACIÓN Cazadores de Genomas (2) GREEN R.E., KRAUSE J., BRIGGS A.W. et ál. 2010. A Draft Sequence of the Neandertal Genome. Science, vol. 328, no. 5979, pp. 710-722. ISSN 0036-8075 Veces citado: 697 ! COOPER A., LALUEZA-FOX C., ANDERSON S. et ál. 2001. Complete mitochondrial genome sequences of two extinct moas clarify ratite evolution. Nature, vol. 409, no, 6821, pp. 704-707. ISSN 0028-0836 Veces citado: 250 !! [http://www.ibe.upf-csic.es/research/research-labs/lalueza-fox.html] [http://www.ibe.upf-csic.es/people/Permanent_Senior_Researchers/lalueza-Foxcarles.html] Vol.7 ¦ Nº 150-Monográfico MONOGRAFÍA CAZADORES DE GENOMAS! Carlos López Otín DOCUMENTACIÓN Web of Science_291014. (de Todas las bases de datos) Busqueda: Autor:(lópez-otín c) AND Dirección: (oviedo) Período de tiempo: Todos los años Resultados: 299 AFILIACIÓN Departamento de Bioquímica, Facultad de Medicina Instituto Universitario de Oncología, Universidad de Oviedo, Spain ! AREAS DE INVESTIGACIÓN ISI (5) Biochemistry Molecular Biology, Genetics Heredity, Cell Biology, Oncology, Pharmacology Pharmacy. PUBLICACIÓN MÁS RECIENTE WORLEY K.C., WARREN W.C., ROGERS J. et ál. 2014. The common marmoset genome provides insight into primate biology and evolution. Nature Genetics, vol. 46, no. 8, pp. 850-857. ISSN 1061-4036. 160 PUBLICACIONES MÁS CITADAS (3) GIBBS R.A., WEINSTOCK G.M., METZKER M.L. et ál. 2004. Genome sequence of the Brown Norway rat yields insights into mammalian evolution. Nature, vol. 428, no. 6982, pp. 493-521. ISSN 0028-0836 Veces citado: 1584$ ! KLIONSKY D.J., ABELIOVICH H., AGOSTINIS, P. et ál. 2008. Guidelines for the use and interpretation of assays for monitoring autophagy in higher eukaryotes. Autophagy, vol. 4, no. 2, pp. 151-175. ISSN 1554-8627 Veces citado: 1300 ! ! MIKKELSEN T.S.,HILLIER L.W., EICHLER E.E. et ál. 2005. Initial sequence of the chimpanzee genome and comparison with the human genome. Nature, vol. 437, no. 7055, pp. 69-87. ISSN 0028-0836 Veces citado: 1034 PUBLICACIÓN Cazadores de Genomas (2) PUENTE X.S., PINYOL M., QUESADA V. et ál. 2011. Whole-genome sequencing identifies recurrent mutations in chronic lymphocytic leukaemia. Nature, vol. 475, no. 7354, pp. 101-105. ISSN 0028-0836 Veces citado: 402 ! HUDSON T.J., ANDERSON W., ARETZ A. et ál. 2010. International network of cancer genome projects%$Nature, vol. 464, no. 7291, pp. 993-998. ISSN 0028-0836 Veces citado: 396 !! [ h t t p : / / w w w. f u n d a c i o n b o t i n . o r g / c a r l o s - l o p e z - o t i n _ d o n d e - e s t a m o s _ p r o g r a m a - t r a n s f e r e n c i a tecnologica_ciencia_areas.htm] [ h t t p : / / w w w . u n i o v i e d o . e s / O n c o l o g i a / i n d e x . p h p ? option=com_content&view=article&id=76&Itemid=120&lang=es] ! ! ! ! Vol.6 ¦ Nº 150-Monográfico MONOGRAFÍA CAZADORES DE GENOMAS! Monografía 2- 2014 ! Pere Puigdomènech i Rosell! DOCUMENTACIÓN Web of Science_291014. (de Todas las bases de datos) Autor: (Puigdomènech P) AND Dirección: (barcelona) Período de tiempo: Todos los años Resultados: 195 AFILIACIÓN Centre for Research in Agricultural Genomics (CRAG) CSIC-IRTA-UAB-UB. Barcelona, Spain. ! AREAS DE INVESTIGACIÓN ISI (5) Plant Sciences, Biochemistry Molecular Biology, Genetics Heredity, Cell Biology, Life Sciences Biomedicine Other Topics. PUBLICACIÓN MÁS RECIENTE LA PAZ J.L., PLA M., CENTENO E. et ál. 2014. The Use of Massive Sequencing to Detect Differences between Immature Embryos of MON810 and a Comparable Non-GM Maize Variety. Plos One, vol. 9, no. 6, DOI: 10.1371/journal.pone.0100895. ISSN 1932-6203 PUBLICACIONES MÁS CITADAS (3) MAYER K., SCHULLER C., WAMBUTT R. et ál. 1999. Sequence and analysis of chromosome 4 of the plant Arabidopsis thaliana. Nature, vol. 402, no. 6763, pp. 769-777. ISSN 0028-0836 Veces citado: 1844 ! SALANOUBAT M., LEMCKE K., RIEGER M. et ál. 2000. Sequence and analysis of chromosome 3 of the plant Arabidopsis thaliana. Nature, vol. 408, no. 6814, pp. 820-822. ISSN 0028-0836 Veces citado: 1404 ! ! BEVAN M., BANCROFT I., BENT E. et ál. 1998. Analysis of 1.9 Mb of contiguous sequence from chromosome 4 of Arabidopsis thaliana. Nature, vol. 391, no. 6666, pp. 485-488. ISSN 0028-0836 Veces citado: 782 PUBLICACIÓN Cazadores de Genomas (1) GARCIA-MAS J., BENJAK, A., SANSEVERINO W. et ál. 2012. The genome of melon (Cucumis melo L.). Proceedings of The National Academy of Sciences of the United States Of America, vol. 109, no. 29, pp. 11872-11877. ISSN 0027-8424 Veces citado: 64 !! [http://www.cragenomica.es/es/personal/detalle/pere-puigdomenech] [ h t t p : / / w w w . c s i c . e s / w e b / g u e s t / b u s c a r ? p_p_state=maximized&p_p_lifecycle=1&_contentviewerservice_WAR_alfresco_packportlet_struts_action= % 2 F c o n t e n t v i e w e r %2Fview&p_p_id=contentviewerservice_WAR_alfresco_packportlet&_contentviewerservice_WAR_alfresco_p ackportlet_nodeRef=workspace%3A%2F%2FSpacesStore%2Ff004c704-753d-40a0-90c4db119932d119&p_p_mode=view&contentType=article] ! ! Vol.7 ¦ Nº 150-Monográfico 161 MONOGRAFÍA CAZADORES DE GENOMAS! ! Antonio Granell Richart! DOCUMENTACIÓN Web of Science_011114. (de Todas las bases de datos) Autor: (Granell A) Refinado por: autores: (GRANELL A OR GRANELL ANTONIO) Período de tiempo: Todos los años. Resultados: 109 AFILIACIÓN Instituto de Biología Molecular de Plantas (IBMCP-CSIC-UPV) Valencia, Spain. 162 ! AREAS DE INVESTIGACIÓN ISI (5) Plant Sciences, Biochemistry Molecular Biology, Genetics Heredity, Chemistry, Biotechnology Applied Microbiology. PUBLICACIÓN MÁS RECIENTE ! RUBIO-MORAGA A., RAMBLA J.L., FERNANDEZ-DE-CARMEN A. et ál. 2014. New target carotenoids for CCD4 enzymes are revealed with the characterization of a novel stress-induced carotenoid cleavage dioxygenase gene from Crocus sativus. Plant molecular biology, vol. 86, no. 4-5, pp. 555-69. ISSN1573-5028 ! PUBLICACIONES MÁS CITADAS (3) SATO S., TABATA S., HIRAKAWA H. et ál. 2012. The tomato genome sequence provides insights into fleshy fruit evolution. Nature, vol. 485, no. 7400, pp. 635-641. ISSN: 0028-0836 Veces citado: 385 ! ORZAEZ D., GRANELL A. 1997. DNA fragmentation is regulated by ethylene during carpel senescence in Pisum sativum. Plant Journal, vol. 11, no. 1, pp. 137-144. ISSN 0960-7412 Veces citado: 135 ! ! FORMENT J., GADEA J., HUERTA L. et ál. 2005. Development of a citrus genome-wide EST collection and cDNA microarray as resources for genomic studies. Plant Molecular Biology, vol. 57, no. 3, pp. 375-391. ISSN 0167-4412 Veces citado: 92 PUBLICACIÓN Cazadores de Genomas (2) SATO S., TABATA S., HIRAKAWA H. et ál. 2012. The tomato genome sequence provides insights into fleshy fruit evolution. Nature, vol. 485, no. 7400, pp. 635-641. ISSN: 0028-0836 Veces citado: 385 ! MUELLER L.A., TANKSLEY S.D., GIOVANNONI J.J.; et ál. 2005. The Tomato Sequencing Project, the first cornerstone of the International Solanaceae Project (SOL). 13th Conference on Plant and Animal Genome. San Diego, C.A. 2004. Comparative And Functional Genomics, vol. 6, no. 3, pp. 153-158 Veces citado: 83 ! ! [http://www.ibmcp.upv.es/FGB/people/toni.html] [http://www.ibmcp.upv.es/index.php?id_grp=32] Vol.6 ¦ Nº 150-Monográfico MONOGRAFÍA CAZADORES DE GENOMAS! Monografía 2- 2014 ! ! Jose Antonio Godoy López! DOCUMENTACIÓN Web of Science_291014. (de Todas las bases de datos) Autor: (godoy j) AND Dirección: (doñana) Período de tiempo: Todos los años Resultados: 56 AFILIACIÓN Estacion Biologica de Doñana (EBD) CSIC-Sevilla, Spain. ! 163 AREAS DE INVESTIGACIÓN ISI (5) Genetics Heredity, Environmental Sciences Ecology,$ Zoology, Biochemistry Molecular Biology, Evolutionary Biology. PUBLICACIÓN MÁS RECIENTE ROQUES S., FURTADO M., JACOMO A.T. et ál. 2014. Monitoring jaguar populations Panthera onca with non-invasive genetics: a pilot study in Brazilian ecosystems. ORYX, vol. 48, no. 3, pp. 361-369. ISSN 0030-6053 !! ! ! PUBLICACIONES MÁS CITADAS (3) JORDANO P., GARCIA C., GODOY J. A. et ál. 2007. Differential contribution of frugivores to complex seed dispersal patterns. Proceedings of the National Academy of Sciences of The United States of America, Vol. 104, no. 9, pp. 3278-3282. ISSN 0027-8424 Veces citado: 215 ! GODOY JA., JORDANO P. 2001. Seed dispersal by animals: exact identification of source trees with endocarp DNA microsatellites. Molecular Ecology, vol.10, no. 9, pp. 2275-2283. ISSN 0962-1083 Veces citado: 165 ! ! PALOMARES F., GODOY J.A. PIRIZ A. et ál. 2002. Faecal genetic analysis to determine the presence and distribution of elusive carnivores: design and feasibility for the Iberian lynx. Molecular Ecology, vol. 11, no. 10, pp. 2171-2182. ISSN 0962-1083 Veces citado: 105 PUBLICACIÓN Cazadores de Genomas (1) CASAS-MARCE M., SORIANO L., LOPEZ-BAO J.V. et ál. 2013. Genetics at the verge of extinction: insights from the Iberian lynx. Molecular Ecology, vol. 22, no. 22, pp. 5503-5515. ISSN: 0962-1083 Veces citado: 1 ! ! [http://es.lynxgenomics.eu/research/523/creacion-genoma-lince-iberico-encara-recta-final-trasidentificarse-20.000-genes] ! ! Vol.7 ¦ Nº 150-Monográfico MONOGRAFÍA CAZADORES DE GENOMAS! ! ! Juan Pascual Anaya! DOCUMENTACIÓN Web of Science_301014. (de Todas las bases de datos) Autor: (Pascual-anaya j) Refinado por: Países/Territorios: (SPAIN OR JAPAN) Período de tiempo: Todos los años Resultados: 16 AFILIACIÓN Center for Developmental Biology (RIKEN) Kobe, Japan. ! 164 AREAS DE INVESTIGACIÓN ISI (5) Genetics Heredity, Environmental Sciences Ecology,$ Zoology, Biochemistry Molecular Biology, Evolutionary Biology. PUBLICACIÓN MÁS RECIENTE ! PASCUAL-ANAYA J., ZADDISSA A., AKEN B. et ál. 2014. Turtle ghrelin. Nature Genetics, vol. 46, no. 6, pp. 526-526. ISSN 1061-4036 ! PUBLICACIONES MÁS CITADAS (3) WANG Z., PASCUAL-ANAYA J., ZADISSA A., et ál. 2013. The draft genomes of soft-shell turtle and green sea turtle yield insights into the development and evolution of the turtle-specific body plan. Nature Genetics, vol. 45. No. 6, pp. 701-706. ISSN 1061-4036 Veces citado: 40 ! D'ANIELLO S., IRIMIA M., MAESO I. et ál.2008. Gene expansion and retention leads to a diverse tyrosine kinase superfamily in amphioxus. Molecular Biology And Evolution, vol. 25, no. 9, pp. 1841-1854. ISSN 0737-4038 Veces citado: 39 ! AMEMIYA C. T., PROHASKA S. J., HILL-FORCE A. et ál. 2008. The amphioxus Hox cluster: Characterization, comparative genomics, and evolution. Journal of Experimental Zoology Part BMolecular And Developmental Evolution, vol. 310B, no. 5, pp. 465-477. ISSN 1552-5007 Veces citado: 37 ! ! PUBLICACIÓN Cazadores de Genomas (1) ! WANG Z., PASCUAL-ANAYA J., ZADISSA A., et ál. 2013. The draft genomes of soft-shell turtle and green sea turtle yield insights into the development and evolution of the turtle-specific body plan. Nature Genetics, vol. 45. No. 6, pp. 701-706. ISSN 1061-4036 Veces citado: 40 [http://www.cdb.riken.jp/emo/japanese/indexj.html] [http://www.riken.jp/en/research/labs/cdb/evol_morphol/] ! Vol.6 ¦ Nº 150-Monográfico MONOGRAFÍA CAZADORES DE GENOMAS! Monografía 2- 2014 ! ! Enrique Viguera Mínguez! DOCUMENTACIÓN Web of Science_011114. (de Todas las bases de datos) Autor: (viguera e) Período de tiempo: Todos los años. Resultados: 29 AFILIACIÓN Universidad de Málaga (UMA) Málaga, Spain. ! 165 AREAS DE INVESTIGACIÓN ISI (5) Biochemistry Molecular Biology, Genetics Heredity, Microbiology, Immunology, Science Technology Other Topics. PUBLICACIÓN MÁS RECIENTE ! DUIGOU S., SILVAIN M., VIGUERA E. et ál. 2014. ssb Gene Duplication Restores the Viability of DeltaholC and DeltaholD Escherichia coli Mutants. PLoS genetics, vol. 10, no. 10. DOI 10.1371/ journal.pgen.1004719. ISSN1553-7404 ! PUBLICACIONES MÁS CITADAS (3) VAN HAM R.C.H.J., KAMERBEEK J., PALACIOS C., et ál. 2003. Reductive genome evolution in Buchnera aphidicola. Proceedings Of The National Academy Of Sciences Of The United States Of America, vol. 100, no. 2, pp. 581-586. ISSN 0027-8424 Veces citado: 785 ! MICHEL B., FLORES M.J., VIGUERA E. et ál. 2001. Rescue of arrested replication forks by homologous recombination. Colloquium on Links Between Recombination and Replication-Vital Roles of Recombination. Irvine, California. 2000. Proceedings Of The National Academy Of Sciences Of The United States Of America, vol. 98, no. 15, pp. 8181-8188. ISSN 0027-8424 Veces citado: 192 ! ! VIGUERA E., CANCEILL D., EHRLICH S.D. 2001. Replication slippage involves DNA polymerase pausing and dissociation. Embo Journal, vol. 20, no. 10, pp. 2587-2595. ISSN 0261-4189 Veces citado: 106 PUBLICACIÓN Cazadores de Genomas (1) !! ! VAN HAM R.C.H.J., KAMERBEEK J., PALACIOS C., et ál. 2003. Reductive genome evolution in Buchnera aphidicola. Proceedings Of The National Academy Of Sciences Of The United States Of America, vol. 100, no. 2, pp. 581-586. ISSN 0027-8424 Veces citado: 785 [http://www.genetica.uma.es/fichapersonal.php?id=53] Vol.7 ¦ Nº 150-Monográfico MONOGRAFÍA CAZADORES DE GENOMAS! Jesús Navas Castillo! DOCUMENTACIÓN Web of Science_021114. (de Todas las bases de datos) Autor:(Navas-Castillo, J) Refinado por: autores: (NAVAS-CASTILLO J OR NAVAS-CASTILLO JESUS) Período de tiempo: Todos los años. Resultados: 96 AFILIACIÓN Instituto de Hortofruticultura Subtropical y Mediterránea. La Mayora (IHSM-CSIC-UMA) Málaga, Spain. ! AREAS DE INVESTIGACIÓN ISI (5) Plant Sciences, Virology, Genetics Heredity, Biochemistry Molecular Biology, Microbiology. 166 PUBLICACIÓN MÁS RECIENTE ! BARBOSA D.F., MARUBAYASHI J.M., DE MARCHI B.R. et ál. 2014. Indigenous American species of the Bemisia tabaci complex are still widespread in the Americas. Pest Management Science, vol. 70, no. 10, pp. 1440-1445. ISSN 1526-498X Veces citado: 1 ! PUBLICACIONES MÁS CITADAS (3) MORIONES E., NAVAS-CASTILLO J. 2000. Tomato yellow leaf curl virus, an emerging virus complex causing epidemics worldwide. 7th International Plant Virus Epidemilolgy Symposium. Almeria, Spain. 1999. Virus Research, vol. 71, no. 1-2, pp. 123-134. ISSN 0168-1702 Veces citado: 187 ! MONCI F., SANCHEZ-CAMPOS S., NAVAS-CASTILLO J. et ál. 2002. A natural recombinant between the geminiviruses Tomato yellow leaf curl Sardinia virus and Tomato yellow leaf curl virus exhibits a novel pathogenic phenotype and is becoming prevalent in Spanish populations. Virology, vol, 303, no. 2, pp. 317-326. ISSN 0042-6822 Veces citado: 138 ! SANCHEZ-CAMPOS S., NAVAS-CASTILLO J., CAMERO R. et ál. 1999. Displacement of tomato yellow leaf curl virus (TYLCV)-Sr by TYLCV-Is in tomato epidemics in spain. Phytopathology, vol. 89, no. 11, pp. 1038-1043. ISSN 0031-949X Veces citado: 101 ! PUBLICACIÓN Cazadores de Genomas (1) !! ! ! VILLANUEV F., SABANADZOVIC S., VALVERDE R.A. et ál. 2012. Complete Genome Sequence of a Double-Stranded RNA Virus from Avocado. Journal Of Virology, vol. 86, no. 2, pp. 1282-1283. ISSN 0022-538X Veces citado: 5 [http://www.ihsm.uma-csic.es/person.php?id=2] Vol.6 ¦ Nº 150-Monográfico MONOGRAFÍA CAZADORES DE GENOMAS! Monografía 2- 2014 Aureliano Bombarely Gómez! DOCUMENTACIÓN Web of Science_021114. (de Todas las bases de datos) Autor: (Bombarely a) Refinado por: autores: (BOMBARELY AURELIANO OR BOMBARELY A) Período de tiempo: Todos los años. Resultados: 23 AFILIACIÓN Boyce Thompson Inst Plant Res. Cornell University NY, USA. ! AREAS DE INVESTIGACIÓN ISI (5) Genetics Heredity, Plant Sciences, Biochemistry Molecular Biology,$ Biotechnology Applied Microbiology, Mathematics. 167 PUBLICACIÓN MÁS RECIENTE SHERMAN-BROYLES S., BOMBARELY A., POWELL A.F. et ál. 2014. The wild side of a major crop: Soybean's perennial cousins from Down Under. American Journal Of Botany, vol. 101, no. 10, pp. 1651-1665. ISSN1537-2197 ! !! PUBLICACIONES MÁS CITADAS (3) SATO S., TABATA S., HIRAKAWA H. et ál. 2012. The tomato genome sequence provides insights into fleshy fruit evolution. Nature, vol. 485, no. 7400, pp. 635-641. ISSN: 0028-0836 Veces citado: 385 ! BOMBARELY A., MENDA N., TECLE I.Y. et ál. 2011. The Sol Genomics Network (solgenomics.net): growing tomatoes using Perl. Nucleic Acids Research, vol. 39, sup: 1, pp. D1149-D1155. ISSN 0305-1048 Veces citado: 79 ! MUELLER L.A., LANKHORST, R.K., TANKSLEY S.D. et ál. 2009. A Snapshot of the Emerging Tomato Genome Sequence. Plant Genome, vol. 2, no. 1, pp. 78-92. ISSN 1940-3372 Veces citado: 51 ! PUBLICACIÓN Cazadores de Genomas (3) SATO S., TABATA S., HIRAKAWA H. et ál. 2012. The tomato genome sequence provides insights into fleshy fruit evolution. Nature, vol. 485, no. 7400, pp. 635-641. ISSN: 0028-0836 Veces citado: 385 ! GUO S., ZHANG J., SUN H. et ál. 2013. The draft genome of watermelon (Citrullus lanatus) and resequencing of 20 diverse accessions. Nature Genetics, vol. 45, no.: 1, pp. 51-U82 ISSN 1061-4036 Veces citado: 44 ! BOMBARELY A., ROSLI H.G., VREBALOV J. et ál. 2012. A Draft Genome Sequence of Nicotiana benthamiana to Enhance Molecular Plant-Microbe Biology Research. Molecular Plant-Microbe Interactions, vol. 25, no. 12, pp. 1523-1530 ISSN 0894-0282 Veces citado: 41 ! [http://doylelab.wordpress.com/members/dr-aureliano-bombarely/] [http://vivo.cornell.edu/display/ ab782} Luis Rodríguez Caso [email protected] Técnico de laboratorio de la Estación Experimental “La Mayora” Vol.7 ¦ Nº 150-Monográfico MONOGRAFÍA CAZADORES DE GENOMAS! ! ! "! #! $! ! ! ! #! %! $! %! #! %! #! $! #! %! #! ! ! ! ! ! $! #! "! %! "! %! #! #! $! #! %! #! $! #! ! "! "! $! "! "! %! #! ! #! ! ! ! ! ! ! ! ! ! ! ! #! #! #! %! $! #! #! "! %! $! #! "! $! %! "! ! $! $! $! #! #! $! %! %! #! $! %! #! %! "! #! Autor de la ilustración: Moisés Donoso Vol.6 ¦ Nº 150-Monográfico