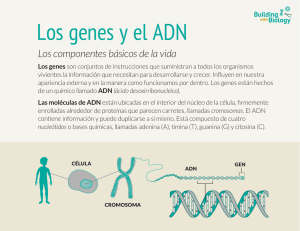
Curso Práctico de Genética - Sección Genética Evolutiva
Anuncio

Sección Genética Evolutiva Departamento de Biología Animal Instituto de Biología Facultad de Ciencias Curso Práctico de Genética 2010 Coordinadores Ruben Pérez y Adriana Parodi Esta guía fue elaborada por los docentes de la Sección Genética Evolutiva. ANÁLISIS INFORMÁTICO DE SECUENCIAS DE ADN El objetivo de este práctico es introducir al estudiante al análisis de secuencias de ADN mediante la utilización de programas informáticos. Para esto utilizaremos bases de datos de secuencias y programas. Lea la información detalladamente y conteste a las preguntas propuestas. Las bases de datos contienen las secuencias que obtienen los investigadores de todas partes del mundo. Estas bases de datos son accesibles a todo el mundo y contienen información sobre secuencias de ácidos nucleicos o secuencias proteicas. Las secuencias de ácidos nucleicos se mantienen en tres grandes bases de datos que sirven a la comunidad científica: EMBL (European Molecular Biology Laboratory), GeneBank (the NIH genetic sequence database) y DDBJ (DNA Database of Japan). Cuando un laboratorio envía una secuencia, se crea una ficha con datos específicos que facilitan su organización. Un investigador puede comparar las secuencias que ha obtenido para establecer si existe similaridad con alguna secuencia ya existente en la base de datos. Ejercicio 1. De una biblioteca genómica humana se obtuvo la siguiente secuencia (Secuencia 1). a) Analice esta secuencia para encontrar homología con alguna secuencia ya descrita utilizando la base de datos del GeneBank: http://www.ncbi.nlm.nih.gov/. Seleccione la opción BLAST, luego Nucleotide blast e introduzca la secuencia 1 (utilice cortar y pegar). Seleccione la base de datos (database): Others Nucleotide collection (nr etc.). Puede limitar su búsqueda a humanos en la opción: Organism. SECUENCIA 1 AGGCCGCGCCCCGGGCTCCGCGCCAGCCAATGAGCGCCGCCCGGCCGGGCGTGCCCCCGCGCCCCAAGCATAAAC CCTGGCGCGCTCGCGGCCCGGCACTCTTCTGGTCCCCACAGACTCAGAGAGAACCCACCATGGTGCTGTCTCCTG CCGACAAGACCAACGTCAAGGCCGCCTGGGGTAAGGTCGGCGCGCACGCTGGCGAGTATGGTGCGGAGGCCCTGG AGAGGTGAGGCTCCCTCCCCTGCTCCGACCCGGGCTCCTCGCCCGCCCGGACCCACAGGCCACCCTCAACCGTCC TGGCCCCGGACCCAAACCCCACCCCTCACTCTGCTTCTCCCCGCAGGATGTTCCTGTCCTTCCCCACCACCAAGA CCTACTTCCCGCACTTCGACCTGAGCCACGGCTCTGCCCAAGTTAAGGGCCACGGCAAGAAGGTGGCCGACGCGC TGACCAACGCCGTGGCGCACGTGGACGACATGCCCAACGCGCTGTCCGCCCTGAGCGACCTGCACGCGCACAAGC TTCGGGTGGACCCGGTCAACTTCAAGGTGAGCGGCGGGCCGGGAGCGATCTGGGTCGAGGGGCGAGATGGCGCCT TCCTCTCAGGGCAGAGGATCACGCGGGTTGCGGGAGGTGTAGCGCAGGCGGCGGCGCGGCTTGGGCCGCACTGAC CCTCTTCTCTGCACAGCTCCTAAGCCACTGCCTGCTGGTGACCCTGGCCGCCCACCTCCCCGCCGAGTTCACCCC TGCGGTGCACGCTTCCCTGGACAAGTTCCTGGCTTCTGTGAGCACCGTGCTGACCTCCAAATACCGTTAAGCTGG AGCCTCGGTAGCCGTTCCTCCTGCCCGCTGGGCCTCCCAACGGGCCCTCCTCCCCTCCTTGCACCGGCCCTTCCT GGTCTTTGAATAAAGTCTGAGTGGGCGGCAGCCTGTGTGTGCCTGGGTTCTCTCTGTCCCGGAATGTGCCAACAA TGGAGGTGTTTACCTGTCTCAGACCAAGGACCTCTCTGCAGCTGCATGGGGCTGGGGAGGGAGAACTGCAGGGAG TATGGGAGGGGAAGCTGAGGTGGGCCTGCTCAAGAGAAGGTGCTGAACCATCCCCTGTCCTGAGAGGTGCCAGCC TGCAGGCAGTGGC b) Obtenga información adicional sobre esta secuencia utilizando el link de Gene info (G). Realice un pequeño resumen de la información obtenida indicando en qué cromosoma se encuentra el gen y cómo está organizado el cluster que lo contiene. c) Analice esta secuencia utilizando la herramienta BLAST como procedió en a) SECUENCIA 2 ACTCTTCTGGTCCCCACAGACTCAGAGAGAACCCACCATGGTGCTGTCTCCTGCCGACAAGACCAACGTCAAGGC CGCCTGGGGTAAGGTCGGCGCGCACGCTGGCGAGTATGGTGCGGAGGCCCTGGAGAGGATGTTCCTGTCCTTCCC CACCACCAAGACCTACTTCCCGCACTTCGACCTGAGCCACGGCTCTGCCCAGGTTAAGGGCCACGGCAAGAAGGT GGCCGACGCGCTGACCAACGCCGTGGCGCACGTGGACGACATGCCCAACGCGCTGTCCGCCCTGAGCGACCTGCA CGCGCACAAGCTTCGGGTGGACCCGGTCAACTTCAAGCTCCTAAGCCACTGCCTGCTGGTGACCCTGGCCGCCCA CCTCCCCGCCGAGTTCACCCCTGCGGTGCACGCCTCCCTGGACAAGTTCCTGGCTTCTGTGAGCACCGTGCTGAC CTCCAAATACCGTTAAGCTGGAGCCTCGGTAGCCGTTCCTCCTGCCCGCTGGGCCTCCCAACGGGCCCTCCTCCC CTCCTTGCACCGGCCCTTCCTGGTCTTTGAATAAAGTCTGAGTGGGCGGC d) Compare (alinear) ambas secuencias utilizando la opción Align two sequences using BLAST (bl2seq) (http://blast.ncbi.nlm.nih.gov/bl2seq/wblast2.cgi) localizada en la página del Blast/ Specialized BLAST. ¿Qué conclusiones puede obtener de su análisis? Realice un esquema comparando ambas secuencias e) Indique los sitios de inicio y finalización de la traducción. Para esto establezca el marco abierto de lectura del gen a partir de la secuencia 2. Utilice la herramienta ORF finder (http://www.ncbi.nlm.nih.gov/gorf/gorf.html). Puede acceder a partir página principal del NCBI: Sequence análisis/Tools/Open Reading Frame Finder (ORF Finder). Indique el tamaño (en aminoácidos) de la proteína codificada. Ejercicio 2 Analice la siguiente secuencia aminoacídica y establezca que dominio conservado presenta. Para hacerlo seleccione la opción Protein blast del BLAST (http://www.ncbi.nlm.nih.gov/BLAST/). La primera ventana que aparece presenta el dominio y su localización en forma gráfica. Haga clic en el recuadro rojo que representa el dominio para obtener información adicional. MTDFFQISQKKCFRLKNPLKHQTQRANTRFRRSHPSSIDTFSNCSDFKSKFYYASMKFQSFLSNRTFSLKVNNTI SPLKHPIPSGVPQGTVSGPLLFILFINDVLLKIPPSVQVSCYADDIKIYGPSASDLQSTIDQIATWSKRNHLPLA PAKTSLLHLGPLNKLHSFTVDNIPVLPSSSVRDLGLLTDDKLTFKSHINRISSLALLRSKQILKSFSSTSPEFYV NLYKLYVSPILEYCSVVFSPPPNSKLAKTLESPLQYYSKRALQRCNIKYNSKSTVNNTSNYSQSYLNRIQILNIQ TARSLRLKAQLLLLYNILTGTAYFPDINDFVVFVSSNRRPMLLINRHPKVRNFFSQVVPIWNSIVHNSPEFLPPS SFSLLIESNICKF Obtenga información sobre las secuencias que presentan este dominio utilizando la base de datos del pubmed: http://www.ncbi.nlm.nih.gov/entrez/query.fcgi?db=PubMed Escriba en español el título o tema de dos trabajos encontrados en la base de datos acerca de este tema. Ejercicio 3 La siguiente secuencia corresponde a una retrotranscriptasa de Mepraia spinolai (Hemiptera-Reduviddae). Realice un BLAST con ella y observe las similitudes que presenta con otras secuencias. Utilice primero la opción nucleotide blast y luego la opción blastx. ¿Por qué existen diferencias en los resultados obtenidos? AGCATATCGTCGACGTAGTGGTTTGAGTTTCCTGTGATTTTTCGTTTCTAAGATATTTTGTACACACA CACATTTATATTTTGCGGTAATTTAGAATCTCAAGAAACCCTTTTAATTTATAATTGTATCACTAACT ACAATGCAGTACCGTACCAGTAACGTGTCAATACAGTCTGTAGAGCTCATATCCCATGCGACTGGAAG AAGTCAGAAATCGCTCCCATACTGAAGAAAGATAAATCCTCAAATATTCCGGAGAGTTATCGACCTAT AGCTCCTACAAGCATGTTCTCTAAGCTTTACGAGAGAATGCTCCTTGATCGCCTTCAGATATACTTAG ACAAAATGGATCTGATTTCAAACAAGCAAGCTGGTTTCAGAAAACACAGAAATACAGTTGAGCAGGCC GCCTTCCTGTCACAGGAAATAAGGAACGGTTTCAATAGGAAGCAAAGTACCCTTGCCGTCTTTATAGA TTTAAAGGCTGCGTTAGACAGAGTTTGGAGGGAGAGGCTGCTGGAAATATAGGCATCATACGTAACTT GTaCAAAAGCATGAACTCGCTCCTAGCGCTAACACTCATCAGAGTAAAGTaCAACAATGTGTTCTCCC CGTGCAAAAAAGCTGTA OTRAS UTILIDADES DE LA BASE DE DATOS DEL NCBI.Buscador taxonómico Esta utilidad permite establecer las secuencias existentes para determinada especie. Diríjase a la página taxonómica del NCBI (http://www.ncbi.nlm.nih.gov/Taxonomy/). Utilice la utilidad para establecer la clasificación correcta de los siguientes organismos y obtener información sobre las secuencias nucleotídicas y aminoacídicas disponibles. a) Caenorhabditis elegans, b) Arabidopsis thaliana, c) Schizosaccharomyces pombe Cuantas secuencias nucleotídicas de Arabidopsis thaliana existen en el GeneBank? VecScreen La secuencia que obtenemos puede presentar contaminación del vector en la que fue clonada. Esta utilidad (special/vecscreen) permite identificar y eliminar secuencias del vector para obtener la secuencia de interés totalmente “limpia”. Puede ingresar a esta utilidad desde la página central del NCBI o utilizando este link: http://www.ncbi.nlm.nih.gov/VecScreen/VecScreen.html. Establezca la presencia de secuencias del vector en la siguiente secuencia. Realice un esquema indicando el tamaño de las regiones de esta secuencia que pertenecen al vector. GTGAGTCGTATTAATTTCGATAAGCCAGCTGCATTAATGAATCGGCCAACGCGCGGGGAGAGGCGGTT TGCGTATTGGGCGCTCTTCCGCTTCCTCGCTCACTGACTCGCTGCGCTCGGTCGTTCGGCTGCGGCGA GCGGATGTCAGGGCGGGGGAAGGGAGGCAAGGGATTGGGAAAGGGAGGCGCCAAGCGTCACCGTAAGG TGCTTCGCGATAACATTCAGGGTATCACAAAGCCAGCAATCCGGCGTTTGGCTCGTAGAGGTGGAGTC AAGCGTATCAGTGGCTTGATCTACGAGGAGACACGTGGCGTCCTGAAGATATTCTTGGAGAACGTCAT CCGTGACGCCGTGACCTACACTGAGCACGCCAGGAGAAAGACCGTGACCGCGATGGACGTCGTTTACG CTCTCAAGAGGCAGGGCAGGACTCTTTATGGATTTGGGGGTATCAGCTCACTCAAAGGCGGTAATACG GTTATCCACAGAATCAGGGGATAACGCAGGAAAGAACATGTGAGCAAAAGGCCAGCAAAAGGCCAGGA ACCGTAAAAAGGCCGCGTTGCTGGCGTTTTTCCATAGGCTCCGC ALGUNAS HERRAMIENTAS PARA EL ANÁLISIS DEL ADN TÉCNICAS DE ADN RECOMBINANTE Enzimas de restricción Las enzimas o endonucleasas de restricción son proteínas que reconocen secuencias particulares del ADN, uniéndose a ellas y cortando en sitios específicos. A partir de su descubrimiento este grupo de enzimas es empleado en el laboratorio para cortar moléculas de ADN. Las secuencias reconocidas por las enzimas de restricción son generalmente de cuatro o seis pares de bases y palindrómicas, es decir que la secuencia de bases leída de 5’ a 3’ en ambas hebras es la misma (fig.1). Las enzimas de restricción de tipo II cortan en una posición específica del ADN dentro de su secuencia de reconocimiento, denominada sitio de restricción. EcoRI 5’ GAATTC 3’ 3’ CTTAAG 5’ HindIII 5’ AAGCTT 3’ 3’ TTCGAA 5’ BamHI 5’ GGATCC 3’ 3’ CCTAGG5’ SmaI 5’ CCCGGG 3’ 3’ GGGCCC 5’ Figura 1. Algunos ejemplos de enzimas de restricción empleadas en el laboratorio. Las flechas indican los sitios de corte. Algunas enzimas de restricción cortan cada cadena del ADN en diferente sitio, dando lugar a extremos “pegajosos”, mientras otras cortan en el mismo sitio ambas cadenas, dando lugar a extremos romos (fig.1). Cada enzima trabaja bajo condiciones apropiadas de concentración salina, pH y temperatura. Una molécula de ADN cortada por una determinada enzima de restricción originará una serie de fragmentos cuyo número y tamaño dependerá de la cantidad y la localización de los sitios de reconocimiento que existan para esa enzima en esa molécula de ADN. Los fragmentos generados por la digestión con enzimas de restricción pueden unirse por la acción de una enzima, denominada ADN ligasa, que forma enlaces fosfodiester entre extremos 5’ y 3’ de los nucleótidos. De esta forma, los extremos romos pueden unirse independientemente de la secuencia que contengan, mientras que los extremos “pegajosos” sólo se unirán si existe complementariedad entre las porciones de simple cadena. Las enzimas de restricción y las ADN ligasas son herramientas claves para la clonación de ADN. Esto significa que cualquier fragmento de ADN (por ejemplo un gen que codifica para una proteína) puede obtenerse tras digestión con enzimas de restricción y agregarse a un plásmido o cualquier otro vector. Este vector es introducido en una célula huésped y dentro de ésta, la molécula de ADN recombinante puede replicarse y expresarse. Mapas de restricción Los fragmentos de ADN, resultantes de una digestión con enzimas de restricción, pueden ser separados por electroforesis en geles de agarosa. Este método consiste en aplicar una corriente eléctrica a través del gel, de modo que el ADN que tiene carga negativa migre hacia el electrodo positivo. La velocidad de migración dependerá del tamaño de cada fragmento. Para un fragmento lineal, esta será inversamente proporcional al log10 de su peso molecular (fig.2). Figura 2. Electroforesis en gel de agarosa. El gel se coloca en una cuba de electroforesis sumergido en el buffer de corrida. Las muestras que contienen el ADN son colocadas en pocillos en uno de los extremos del gel. Al aplicarse una corriente eléctrica, las moléculas de ADN migrarán a través del gel en función de su tamaño, desde el polo negativo al polo positivo. Un factor importante en la electroforesis es la concentración de la agarosa en el gel. Cuanto mayor es la concentración más retrasa el movimiento de todos los fragmentos. Así, se recomiendan concentraciones altas de agarosa para ver y separar fragmentos pequeños de ADN, mientras que será mejor emplear concentraciones bajas de agarosa cuando se trate de separar fragmentos grandes (tabla 1). Tabla 1 % de agarosa en el gel Rango de separación eficiente de moléculas de ADN lineal (kb) 0,3 60-5 0,6 20-1 0,9 7-0,5 1,5 4-0,2 2,0 3-0,1 Tras la corrida electroforética, los distintos fragmentos de ADN así separados son visualizados por tinción. Uno de los métodos de tinción más empleados es el bromuro de etidio el cual se intercala entre las bases del ADN y fluoresce bajo la luz ultravioleta. La combinación de digestión con enzimas de restricción y electroforesis en gel se llama análisis de restricción. La representación de una molécula de ADN, ya sea circular o lineal, donde se indiquen los sitios de restricción que poseen, se denomina mapa de restricción (fig. 3). EcoRI 1/5.541 HindIII 32 PvuII 4.916 EagI 942 YIP5 5.541 ApaI 2.035 PvuII 3.247 SmaI 2.540 Figura 3. Mapa de restricción del plásmido YIP5 de 5.541 pb. Los números indicados después de cada enzima de restricción indican las posiciones de los sitios de corte. Ejercicio 1 Indica los tamaños de los fragmentos que obtendrías tras la digestión del plásmido YIP5 con EcoRI, con EcoRI y EagI, con HindIII y ApaI, con HindIII, ApaI y PvuII. Análisis por hibridación Para conocer si está presente una determinada secuencia de ADN (por ejemplo la correspondiente a un determinado gen) en una muestra se realiza un análisis por hibridación. Este implica separar (desnaturalizar) las moléculas de ADN de la muestra a analizar y mezclarlas con moléculas de ADN (o ARN) de cadena simple con homología con toda o parte de la secuencia que queremos buscar. Esta molécula se denomina sonda y se marca con isótopos radiactivos u otro tipo de marcaje para poder ser detectada. En condiciones apropiadas la sonda formará puentes de hidrógeno (hibridizará) con una secuencia complementaria a ella si se encuentra presente en la muestra, formando una molécula de doble cadena. Si la secuencia complementaria no se encuentra en dicha muestra, la sonda no hibridizará. Tras el período de hibridización, la muestra se lava para remover la sonda no hibridada, y la presencia de la secuencia de interés se pone de manifiesto gracias a la sonda hibridada. La desnaturalización de una molécula de ADN se lleva a cabo por métodos físicos, como el calor, o por métodos químicos, como el tratamiento con una base. Las condiciones dependerán del tamaño y de la composición de bases del ADN. La temperatura necesaria para desnaturalizar en un 50 % una molécula determinada de ADN se denomina temperatura de desnaturalización o “melting”. Si una muestra de ADN se hierve se desnaturalizará, es decir, sus cadenas se separarán. Si la muestra se enfría las cadenas volverán a hibridizar. Las moléculas complementarias cortas tenderán a hibridizar más rápido que las moléculas largas. Las sondas empleadas en experimentos de hibridación son de largo variable, desde cortos oligonucleótidos de 15 a 30 bases de largo, hasta cadenas de miles de bases. Las sondas se marcan por varios métodos. Algunos consisten en sintetizar la sonda en presencia de un nucleótido radiactivo. También existen métodos de marcaje no radiactivos que consisten en nucleótidos con modificaciones químicas que resultan en un producto coloreado o luminiscente luego de una reacción de detección. Southern blotting Para hacer más facil la hibridización y posterior detección de la sonda, el ADN a ser analizado se transfiere a una membrana mediante un método llamado Southern blotting. Este método, junto con el análisis por hibridización, permite detectar los fragmentos de restricción que contienen una determinada secuencia de ADN. Primero la muestra de ADN a analizar se digiere con enzimas de restricción y los productos se separan por electroforesis en gel de agarosa. Una vez separados estos fragmentos son transferidos a membranas de nylon o nitrocelulosa. Para ello el gel se sumerge en una base para desnaturalizar los fragmentos de ADN y luego se coloca sobre una pieza de papel cuyos extremos se suspenden en un reservorio con una solución salina. La membrana se coloca encima del gel y encima de esta se colocan servilletas absorbentes (fig.4). Se crea así un fluido por acción capilar desde el reservorio y que atraviesa el gel arrastrando los fragmentos de ADN que entonces son transferidos a la membrana. La membrana entonces contiene el patrón de fragmentos exacto que se encontraba en el gel. Una vez transferido el ADN a la membrana, éste se fija a la membrana por calor o por exposición a UV. La membrana así preparada está pronta para someterla a hibridación con una sonda. Figura 4. Southern blotting. El ADN es cortado con enzimas de restricción y los fragmentos se separan por electroforesis en gel de agarosa. Tras la corrida, los fragmentos de ADN son transferidos a una membrana de nylon o nitrocelulosa, mediante el proceso denominado Southern blotting. La membrana resultante puede hibridarse con sondas radiactivas específicas para reconocer un ADN homólogo presente en dicha membrana que será revelado posteriormente por autorradiografía (ver más adelante). Ejercicio 2 Se muestran los mapas de restricción para las enzimas EcoRI y BamHI del ADN de un virus X. Los tamaños de los fragmentos están en kilobases (kb). Mapa EcoRI 9 5,5 4 2 6 Mapa BamHI 3 7,5 10,5 5,5 Imagina que has digerido este ADN con estas dos enzimas de restricción por separado y con ambas al mismo tiempo. Realiza el análisis de los productos de digestión tras una corrida de electroforesis y tinción del gel con bromuro de etidio. En el esquema del gel mostrado a continuación (a la izquierda), indica en cada carril las bandas que esperas obtener para cada muestra. Gel de electroforesis teñido EcoRI BamHI Membrana de hibridación EcoRI/BamHI EcoRI BamHI EcoRI/BamHI kb 10 8 6 4 2 1 Dicho gel fue posteriormente transferido a una membrana de nylon y el ADN fue fijado. Esta membrana fue hibridada con una sonda específica que reconoce el ADN. El esquema de la derecha representa el resultado de la hibridación donde se muestran las bandas que son reconocidas por la sonda. A partir de este resultado determina la posición que ocupa el segmento empleado como sonda en los mapas de restricción. Ejercicio 3 Aquí se representan los mapas de restricción del ADN del bacteriófago lambda para tres enzimas. Dibuja las bandas que se obtendrían tras digerir con las enzimas BamHI y HindIII dicho ADN y las bandas que se visualizarían tras la hibridación con la sonda que está señalada en el mapa para EcoRI. Mapa BamHI 5,5 16,8 5,6 6,5 7,2 6,7 Mapa HindIII 23,1 2 2,3 9,4 6,5 4,4 0,6 0,1 Mapa EcoRI Sonda 21,2 4,9 5,6 7,4 5,8 3,5 Gel teñido kb BamHI HindIII Membrana hibridada BamHI HindIII 24 16 8 4 2 CONSTRUCCIÓN DE LIBRERÍAS Vectores y Clonación Los plásmidos son capaces de albergar trozos extras de ADN, por lo que se abre la posibilidad de poner una secuencia de ADN determinada (por ejemplo, un gen) en un plásmido circular, generando un ADN recombinante. En estas circunstancias el plásmido está funcionando como un “vector”: es capaz de llevar el trozo de ADN (que denominamos inserto) manteniéndolo mediante la replicación, ya que posee un origen de replicación. Los plásmidos contienen además genes para la resistencia a antibióticos (fig. 5). Por lo tanto bacterias que contengan un plásmido que confiere resistencia a un determinado antibiótico, serán ellas también resistentes a dicho antibiótico. Esta característica es utilizada para seleccionar bacterias que contengan plásmidos frente a otras que no los contengan. Los plásmidos no son los únicos vectores empleados en clonación. A menudo se requiere clonar trozos de ADN mayores a los soportados por los plásmidos. Así, se emplean también los bacteriófagos (virus que infectan bacterias) y también se han desarrollado otros vectores que son combinaciones de plásmido, de bacteriófago, de cromosoma de levadura, etc. Así surgieron por ejemplo los BACs (“bacterial artificial chromosome”). Figura 5. Clonación de ADN. Se pueden transformar bacterias con plásmidos que llevan un determinado inserto (señalado en rojo). Una vez dentro de la bacteria, el plásmido se replica con ella. Así se consigue que el trozo de ADN además de estar aislado, sea amplificado y se obtienen rápidamente muchas copias idénticas. Las bacterias que contienen el plásmido son seleccionadas por crecer en presencia de un antibiótico, ya que el plásmido lleva un gen que codifica para un producto que confiere resistencia a ese antibiótico (señalado en negro). Ejercicio 4 ¿Cuáles vectores pueden llevar el inserto más grande? ¿Qué ventajas tienen los YACs con respecto a los otros tres? a. Fagos b. Plásmidos c. Cósmidos d. YACs Ejercicio 5 Un fragmento de ADN de 1, 5 kb es clonado en el sitio EcoRI de un vector plasmídico de 5,5 kb de tamaño. Dicho vector es luego usado para transformar bacterias competentes. El ADN plasmídico extraído de una única colonia bacteriana, es digerido con la enzima de restricción EcoRI. a) ¿Qué productos de digestión se producirán si el plásmido contiene el inserto? b) ¿Y si no lo contiene? Construcción y rastreo de librerías Cuando el genoma entero de un organismo es cortado en trozos y clonado en un determinado vector se construye una genoteca o una biblioteca o librería genómica. Esto es posible por ejemplo si se corta dicho genoma con una enzima de restricción y todos los fragmentos resultantes se insertan en plásmidos que han sido previamente digeridos con esta misma enzima de restricción. Como resultado se obtienen una serie de plásmidos que contienen distintos trozos de ADN correspondientes a ese genoma. Esta es una librería genómica (fig. 6). También existen bibliotecas de ADN complementario o copia (ADNc), las cuales son construidas a partir de la población total de ARNm de un organismo, de un tejido o tipo celular particular o de una etapa del desarrollo particular. Representa en este caso al conjunto de genes que están siendo expresados por esas células o por ese estadío. Para construir una librería de ADNc, es necesario extraer el conjunto de ARNm y sintetizar moléculas de ADN complementarias a esos ARNm. Esto se realiza gracias a la acción de una enzima denominada transcriptasa inversa. Una vez sintetizada la cadena de ADN, la molécula híbrida ADN-ARN es tratada con RNasa para degradar las moléculas de ARN y las cadenas simples de ADN son utilizadas como molde para la síntesis de ADN de doble cadena por una polimerasa. Las secuencias resultantes son entonces insertadas en un vector para generar la librería de ADNc. Figura 6. Esquema de la construcción de una librería genómica humana en un vector plasmídico. El ADN genómico humano es digerido con enzima de restricción y los fragmentos resultantes son clonados en un vector plasmídico. Los plásmidos recombinantes son luego introducidos en una bacteria huésped mediante transformación. La librería genómica se puede guardar como un stock bacteriano y plaquearse en medio sólido o crecer en medio líquido cuando va a ser utilizada. Si utilizamos plásmidos que contienen una librería para transformar bacterias, como Escherichia coli, y plaqueamos los transformantes sobre un medio sólido que contenga un antibiótico de selección, obtendremos colonias individuales donde cada una contiene un plásmido recombinante en particular. Las placas conteniendo estas colonias pueden ser transferidas a membranas. Una vez transferidas, las bacterias son lisadas para exponer su ADN y el ADN se desnaturaliza. Tras fijar el ADN a la membrana por calor o por exposición a UV, estas membranas pueden ser hibridizadas con una sonda específica. Si se coloca encima de ellas un film fotográfico que luego es revelado, la colonia que contiene un plásmido con una secuencia de ADN complementaria a la sonda, se evidenciará como una mancha negra en el film. Este proceso de exposición se denomina autorradiografía (fig. 7). El autorradiograma resultante puede ser comparado con la placa de agar que contiene las colonias bacterianas, para localizar la colonia que contiene el plásmido con la secuencia de interés. Esta colonia luego es sometida a un proceso de verificación, es decir se aísla, se replaquea y se vuelve a hibridar con la sonda y/o se secuencia para confirmar la presencia del gen de interés. Hibridización, lavado y autorradiografía Transferencia Colonias sobre una placa de agar Membrana Autorradiograma Figura 7. Rastreo de una librería genómica construida en plásmidos. Para garantizar que la sonda “encuentre” su secuencia complementaria, es necesario plaquear la librería de manera que resulte un número suficiente de colonias individuales, tomando en cuenta que existirán colonias “repetidas”. Ejercicio 6 El plásmido pUC18 lleva el gen que confiere resistencia a ampicilina y lleva un fragmento del gen lacZ que confiere la capacidad de convertir el compuesto X-gal sin color a un compuesto de color azul. Si un fragmento de ADN es clonado interrumpiendo esta última región, a) ¿De qué color serán las colonias que lleven plásmidos con el inserto de ADN si dichas colonias son plaqueadas en un medio conteniendo ampicilina y X-gal? b) ¿De qué color serán las colonias plaqueadas en el mismo medio si contienen plásmidos que no llevan inserto de ADN? c) ¿Por qué es necesario que el medio de cultivo contenga ampicilina? ¿Qué colonias espera que crezcan en ausencia de este antibiótico? Ejercicio 7 Un plásmido resistente a ampicilina y a tetraciclina pBR322, se corta con la enzima de restricción PstI que corta dentro del gen de resistencia a ampicilina. El plásmido cortado se liga con un DNA de Drosophila digerido con PstI para preparar una biblioteca genómica y la mezcla se utiliza para transformar E. coli K12. a) ¿Qué antibióticos deben añadirse al medio de cultivo para obtener colonias con plásmidos que contengan insertos de Drosophila? b) ¿Cómo se puede explicar la presencia de colonias que sean resistentes a ambos antibióticos? Secuenciación del ADN Los métodos más comunes para secuenciar el ADN utilizan compuestos llamados terminadores de cadena (método de Sanger). Se trata de dideoxinucleótidos (ddNTPs) que al incorporarse a una cadena que se está sintetizando, son capaces de detener la elongación llevada a cabo por la ADN polimerasa. Los ddNTPs son moléculas parecidas a los nucleótidos normales excepto que carecen del grupo 3’ hidroxilo (OH). La ADN polimerasa agrega este nucleótido a una cadena de ADN en crecimiento mediante la formación de un enlace entre el grupo 5’ fosfato del nuevo nucleótido y el grupo 3’ OH del nucleótido previo. Seguidamente la enzima no podrá agregar más nucleótidos debido a la ausencia del grupo 3’ OH. Para una reacción de secuenciación se debe mezclar la molécula de ADN molde con cebadores o “primers” requeridos por la ADN polimerasa para iniciar la síntesis y deoxinucleótidos (dNTPs) normales. Esta mezcla es dividida en cuatro tubos y a cada tubo se le agrega un ddNTPs (ddATP, ddTTP, ddGTP, ddCTP) diferente. Por último se agrega la ADN polimerasa que comienza la reacción de síntesis. Durante la reacción de polimerización, la incorporación al azar de un ddNTP en competición con el dNTP normal correspondiente, llevará a la formación de una mezcla de cadenas de distintas longitudes, todas ellas empezando en el extremo 5’ y terminando en todas las diferentes posiciones posibles donde un ddNTP puede incorporarse en lugar de un dNTP. Completada la reacción, en el tubo que contiene por ejemplo ddA, las nuevas moléculas sintetizadas contendrán ddA en cada sitio correspondiente a T en el molde. Como resultado se han generado una serie de moléculas que terminan en las distintas T del molde. La sustitución de uno de los dNTPs por el mismo nucleótido marcado permite la visualización posterior. Esta se hacía clásicamente por electroforesis en geles de poliacrilamida. cargadas en distintos pocillos del gel de Las moléculas sintetizadas se separarán de acuerdo a su tamaño y podrán visualizarse por exposición del gel a un film fotográfico y posterior revelado (fig. 8). Figura 8. Autorradiografía obtenida a partir de un gel de secuencia desnaturalizante de acrilamida-bisacrilamida. Tras la corrida electroforética, los fragmentos de ADN de simple cadena que difieren en un nucleótido de longitud, se separan en el gel. Dichos fragmentos son visualizados luego de secar el gel y exponerlo sobre un film de autorradiografía ya que uno de los dNTPs utilizados en la reacción de secuenciación es radiactivo. G A T C Ejercicio 8 ¿Puedes leer la secuencia de la figura? Al final de la década de 1980 aparecen equipos de secuenciación automática los cuales, basados en el mismo principio de terminación de cadena, emplean dideoxinucleótidos modificados que llevan un grupo fluorescente (distinto para cada ddNTP) o bien a cada una de las cuatro reacciones se le añade el cebador marcado en 5’ con una sonda fluorescente distinta. Los productos de reacción se detectan directamente durante la electroforesis al pasar por delante de un láser que al excitar los fluoróforos permite detectar la fluorescencia emitida (fig. 9). Con estos instrumentos las lecturas de secuencia se transforman en cromatogramas de picos de cuatro colores. Figura 9. Secuenciación automática utilizando terminadores fluorescentes. La reacción se lleva a cabo en un solo tubo. Cada terminador fluorescente emite a una determinada longitud de onda generando un electroferograma. Existen instrumentos de electroforesis capilar como alternativa al sistema basado en geles de poliacrilamida, donde se utiliza un polímero que se inyecta de forma automática en un capilar antes de cargar la mezcla de secuenciación y que va resolviendo los fragmentos de ADN que se diferencian en una única base (fig. 10). Estos instrumentos permiten la total automatización del proceso así como una mayor rapidez. Con estos métodos ha sido posible encarar estrategias de secuenciación de gran escala como han sido los proyectos de secuenciación de genomas completos de organismos. En muchas enfermedades genéticas humanas, una copia cromosómica contiene una o una bases cambiadas en determinada posición dentro del gen. Cuando se obtienen los datos de la secuencia de ese ADN se observan dos bases diferentes en la misma posición. En el contexto de la secuenciación automática se detectan dos picos superpuestos en la misma posición. Figura 10. Secuenciación automática capilar. El equipo funciona de forma automática inyectando las muestras en un capilar previamente cargado con un polímero que funciona como matriz como lo hace la matriz de acrilamidabisacrilamida-urea de los geles de secuencia. Una vez desarrollada la electroforesis de la primera muestra, el capilar se vacía rellenándose nuevamente con polímero fresco y se inyecta una segunda muestra. Ejercicio 9 Escribe la secuencia correspondiente al siguiente cromatograma. El código de colores es: G, negro – C, azul – T, rojo – A, verde A pesar de que el método automático de Sanger fue el método de secuenciación dominante durante casi 2 décadas, en los últimos 4 años las estrategias de secuenciación cambiaron drásticamente, dando lugar a nuevos y revolucionarios métodos referidos como “next generation methods” (NGS). Estos métodos tienen la capacidad de producir un enorme volumen de datos de secuencias. Estas nuevas tecnologías permiten una secuenciación más barata y eficiente, a pesar de obtener fragmentos (reads) de menor tamaño. Las secuencias aisladas obtenidas requieren el empleo de potentes herramientas informáticas para su ensamblaje. Distintas empresas han desarrollado distintos métodos tales como son el método 454 de Roche, Solexa de Illumina y SOLiD de Applied Biosystems. Aunque entre ellos difieren en la forma de preparación del ADN molde a secuenciar, todos se basan en la inmovilización del molde a una superficie sólida o soporte. La mayoría de los métodos utilizan un paso con clonación in vitro para generar muchas copias de cada molécula individual, ya que los métodos de detección molecular frecuentemente no son lo suficientemente sensibles para la secuenciación de una sola molécula. Uno de los métodos es la PCR de emulsión, en la que se aíslan las moléculas individuales de ADN junto con microesferas. Luego, mediante una reacción de PCR se recubre cada microesfera con copias clonales de la biblioteca de moléculas aisladas y seguidamente se inmovilizan ocupando cada microesfera una localización fija para ser más tarde secuenciadas. En algunos de los métodos, la secuenciación de estas moléculas molde se basa en la incorporación, gracias a la ADN polimerasa de nucleótidos fluorescentes, y en la lectura basada en la microscopía de fluorescencia. Durante la polimerización del ADN se incorpora un nucleótido marcado con fluorescencia y que está protegido en la cadena naciente por lo que impide que ésta siga creciendo. Tras detectar la señal fluorescente, se elimina el grupo fluorescente protector, regenerando un extremo 3´OH libre, y se puede incorporar otro nucleótido marcado, con lo que se empieza nuevamente el ciclo. Reacción en cadena de la polimerasa (PCR) Es una técnica muy rápida que permite, a partir de una sola copia de una molécula de ADN, obtener muchas copias de dicho ADN. Por lo tanto resulta ser una técnica muy útil en estrategias de clonación y también de detección, cuando la cantidad de material es limitante, como en el área forense y de identificación humana, así como en genética de poblaciones. Esta técnica aprovecha las características de la replicación del ADN, es decir que a partir de un pequeño cebador la polimerasa puede proseguir la síntesis de una cadena. Se debe contar con dos cebadores adecuados, uno para cada cadena (fig.11). Por la posición de estos cebadores, al cabo de una serie de rondas de replicación, se obtiene la amplificación de una molécula de ADN correspondiente al tramo que va desde uno de los cebadores al otro. Por lo tanto, se obtienen muchas moléculas idénticas. Los cebadores suelen ser cortos de 15-20 bases y en la reacción se mezclan con la muestra de ADN a ser amplificada. Al comenzar la reacción, la muestra de ADN de doble cadena debe ser desnaturalizada calentándola a 95ºC y luego enfriada para permitir la hibridación con los cebadores. La siguiente etapa consiste en la síntesis a partir de los cebadores de cada una de las cadenas de ADN por la polimerasa utilizando nucleótidos agregados a la mezcla de reacción. Este ciclo de desnaturalización, hibridización y síntesis o extensión se repite muchas veces y por tanto se amplifica, puesto que en cada nuevo ciclo se dispone de más cantidad de ADN molde. Como el ADN tiene que ser desnaturalizado por calor para iniciar cada nuevo ciclo, se emplea una polimerasa que resiste el calor (denominada Taq polimerasa, aislada de la bacteria de aguas termales Thermus aquaticus). La reacción de PCR se lleva a cabo en un aparato denominado termociclador, capaz de realizar cambios muy rápidos de temperatura. Así, la mezcla de reacción es colocada en el termociclador estableciéndose las condiciones de incubación. En primer lugar se establece el número de ciclos, que puede variar, oscilando generalmente alrededor de los 30 ciclos. Posteriormente se determinan las condiciones de cada ciclo. Este último se divide en una etapa de desnaturalización, que se lleva a cabo a 95ºC durante 10-60 segundos, una etapa de hibridización de 30-60 segundos a una temperatura que dependerá de la temperatura de desnaturalización de los oligonucleótidos utilizados como cebadores, y por ultimo una etapa de extensión que se realiza también durante un tiempo variable, generalmente a 72ºC o a la temperatura que sea óptima para la polimerasa que se emplea. Figura 11. Reacción en cadena de la polimerasa (PCR). Esta reacción se realiza en un aparato denominado termociclador. Con dicho aparato es posible programar la cantidad de ciclos así como las temperaturas y tiempos deseados para cada etapa Gran parte del éxito de una reacción de PCR depende de la correcta elección de los cebadores que aseguran la amplificación adecuada y al mismo tiempo la especificidad de la reacción. Por esta razón tanto si se diseñan manualmente como con la ayuda de programas adecuados, deben tratar de considerarse varios factores. 1) Los cebadores deben elegirse abarcando el tramo que se desea amplificar 2) Cada uno de ellos deberá unirse a una de las dos hebras de una secuencia de ADN desnaturalizada. Por lo tanto si estamos trabajando sobre una secuencia que representa una de las dos hebras, uno de los cebadores será igual a un tramo de esta secuencia, y el otro será complementario. 3) Se intentará que estos cebadores cumplan con la mayor parte de los siguientes requisitos: a) Longitud: entre 18 y 25 pares de bases b) Contenido en GC. Un porcentaje en el entorno de 50%. Pues esta composición está en relación con la temperatura de hibridación de estos oligonucleótidos con el ADN molde como se observa en la gráfica. c) En relación con lo anterior, debe intentarse que los cebadores tengan una temperatura de desnaturalización (Tm) relativamente alta para asegurar la especificidad de la amplificación, y que las Tms de ambos cebadores del par sean similares, para así definir la temperatura de hibridización que se usará en la reacción. d) Consideraciones sobre las bases en determinadas posiciones, como por ejemplo evitar que el extremo 3´sea A o T, evitar tramos de más de tres bases iguales, etc. e) Evitar que los cebadores diseñados formen estructuras secundarias, homodímeros o heterodímeros, o que éstos, de existir sean lo menos estables posibles. Esto implica por ejemplo que no existan tramos con complementariedad entre dos regiones de un cebador o con el otro o estructuras palindrómicas Ejercicio 10 Dispones del ADN correspondiente a la secuencia que se anota a continuación. Quieres realizar una reacción de amplificación por PCR de una porción de dicho ADN. a) Diseña los cebadores necesarios para dicha reacción. Ten en cuenta que su longitud debe ser de 15-18 nucleótidos. b) Calcula las temperaturas de desnaturalización (Tm) de estos cebadores tomando en cuenta la siguiente fórmula (para oligonucleótidos de hasta 18 nt): (A + T) x 2º + (G + C) x 4º c) Establece las condiciones de amplificación. ACATTTGCTTCTGACACAACTGTGTTCACTAGCAACCTCAAACAGACACCATGGTGCACC 60 TGACTCCTGAGGAGAAGTCTGCCGTTACTGCCCTGTGGGGCAAGGTGAACGTGGATGAAG 120 TTGGTGGTGAGGCCCTGGGCAGGTTGCTGTTGGTCTACCCTTGGACCCAGAGGTTCTTTG 180 AGTCCTTTGGGGATCTGTCCACTCCTGATGCTGTTATGGGCAACCCTAAGGTGAAGGCTC 240 ATGGCAAGAAAGTGCTCGGTGCCTTTAGTGATGGCCTGGCTCACCTGGACAACCTCAAGG 300 GCACCTTTGCCACACTGAGTGAGCTGCACTGTGACAAGCTGCACGTGGATCCTGAGAACT 360 TCAGGGTCCTGGGCAACGTGCTGGTCTGTGTGCTGGCCCATCACTTTGGCAAAGAATTCA 420 CCCCACCAGTGCAGGCTGCCTATCAGAAAGTGGTGGCTGGTGTGGCTAATGCCCTGGCCC 480 ACAAGTATCACTAAGCTCGCTTTCTTGCTGTCCAATTTCTATTAAAGGTTCCTTTGTTCC 540 CTAAGTCCA 549 Ejercicio 11 Te propones obtener la secuencia del gen que codifica para la proteína HP1 de un insecto cuyo genoma no es conocido. a) ¿Cómo procederías si cuentas con una biblioteca de ADNc de ese insecto construida en un vector plasmídico y con un plámido que contiene el gen que codifica para la proteína HP1 de Drosophila? b) ¿Podrías obtenerlo sin tener una biblioteca de ADNc? ¿Qué estrategia emplearías? c) Una vez completada la obtención de este ADNc se establece que consta de 1650 pares de bases. ¿Cómo puedes obtener la secuencia genómica correspondiente? ¿Cómo explicas que una vez obtenida, la misma tenga 19500 pares de bases? IDENTIFICACIÓN CROMOSÓMICA I. INTRODUCCIÓN I.1. GENERALIDADES DEL CROMOSOMA EUCARIOTA Los cromosomas son estructuras discretas que se encuentran en las células ecuariotas, encargadas del almacenamiento y transmisión de la información hereditaria. El término CROMOSOMA se refiere a cromosomas metafásicos en mitosis, cuando la cromatina alcanza su máximo grado de condensación. Cada cromosoma está formado por dos CROMÁTIDAS hermanas, cada una de ellas constituida por una única molécula de ADN. El cromosoma eucariota requiere de ciertas estructuras para llevar a cabo su función: dos telómeros, un centrómero y varios orígenes de replicación por cromátida. Los extremos de las cromátidas se denominan TELÓMEROS y confieren estabilidad a cada unidad hereditaria. La CONSTRICCIÓN PRIMARIA o CENTRÓMERO es el sitio de ensamblaje de una estructura proteica llamada CINETOCORO, a la cual se asocian los microtúbulos del huso metafásico. Según la posición que ocupe el centrómero podemos clasificar a los cromosomas como metacéntricos, submetacéntricos y telocéntricos (algunos autores agregan una cuarta categoría denominada acrocéntricos o subtelocéntricos). En algunos cromosomas aparece otra constricción llamada CONSTRICCIÓN SECUNDARIA. Algunos segmentos cromosómicos localizados entre la constricción secundaria y el telómero se llaman SATÉLITES. Aunque muchas veces el significado funcional de las constricciones secundarias permanece incierto, en algunas de ellas se localiza el cluster 45S de genes ribosomales, a partir del cual se organiza el nucleolo. Por esta razón se denomina REGIÓN ORGANIZADORA DEL NUCLEOLO (NOR), y puede visualizarse al microscopio óptico mediante técnicas de impregnación con plata. Clasificación de los cromosomas según la posición del centrómero; Metacéntrico: Cromosoma cuyo centrómero se encuentra en la mitad del cromosoma, dando lugar a dos brazos de igual longitud (p y q). Submetacéntricos: Cromosoma en el cual el centrómero se ubica de tal manera que un brazo es ligeramente más corto que el otro. Telocéntrico: Cromosoma en el cual el centrómero está localizado en un extremo del mismo (telómero), por lo que el cromosoma posee sólo un brazo. Acrocéntrico o Subtelocéntrico: Cromosoma en el cual el centrómero se encuentra más cercano a uno de los telómeros, dando como resultado un brazo muy corto (p) y el otro largo (q). I.2. CROMOSOMAS POLITÉNICOS DE LAS GLÁNDULAS SALIVALES Las glándulas salivales y otros tejidos blandos de los Dípteros tienen núcleos en interfase permanente. Durante el crecimiento y desarrollo de las larvas, la división celular se suspende en ciertos tejidos pero las células continúan su crecimiento por incremento de tamaño. Este proceso ocurre en los tubos de Malpighi, las células del cuerpo graso, las células nutricias de los ovarios, el epitelio intestinal y en las células de las glándulas salivales. En estos tejidos, los cromosomas sufren rondas de duplicaciones repetidas pero sin separarse, proceso conocido como endomitosis. Esto lleva a la producción de un haz cromatínico de varios cientos o miles de hebras. Durante este proceso de politenización o politenia, los “cromosomas” incrementan su largo y su diámetro. El número de réplicas de ADN sin separación de los cromosomas hijos es de 10, de lo que resultan 1024 (210) hebras cromatínicas alineadas lado a lado. Además los cromosomas politénicos presentan los cromosomas homólogos asociados a lo largo de toda su longitud. Esta condición es un ejemplo extremo de un fenómeno más general denominado “apareamiento somático” el cual ocurre en el ciclo mitótico de la mayoría de los Dípteros. A su vez, los cromosomas muestran un patrón peculiar de bandeo transversal que consiste en zonas cromáticas oscuras (llamadas bandas), y zonas acromáticas claras (interbandas), visibles al microscopio óptico (ver figuras). Este bandeo es reproducible de núcleo a núcleo, formando un patrón específico para cada especie, de tal manera que los cromosomas pueden ser identificados y mapeados en todo su largo, constituyendo un mapa citológico. Hay aproximadamente 5000 bandas y 5000 interbandas en total en el genoma de Drosophila melanogaster. Debido a que el patrón de bandeo que presentan los cromosomas politénicos es un reflejo constante de las secuencias de ADN, las bandas sirven como marcadores para localizar varias características genéticas (áreas con gran concentración de genes, o cambios en el genoma debido a reordenamientos cromosómicos, por ejemplo deleciones, duplicaciones, translocaciones, etc.). En D. melanogaster el patrón de bandeo no está presente en las regiones heterocromáticas centroméricas de todos los cromosomas. Las regiones heterocromáticas están asociadas formando un cromocentro. FIGURAS: Cromosomas politénicos teñidos con orceína (izquierda) y Giemsa (derecha). La imagen ampliada (b) muestra las bandas y las interbandas con mayor detalle. . I.3. CARIOTIPO: CONCEPTO Y REPRESENTACIÓN El conjunto ordenado de todos los cromosomas de una especie es conocido como CARIOTIPO. El análisis del cariotipo es de fundamental importancia para comparar especies o para estudiar la variación dentro de una misma especie. En el hombre además se ha utilizado para correlacionar determinadas patologías con alteraciones del cariotipo normal. Los parámetros utilizados para la elaboración del cariotipo de una especie son: tamaño de los cromosomas; posición del centrómero; patrón de bandas (C, G, Q, T, etc.); posición de las constricciones secundarias u otros marcadores. Izquierda: Metafase mitótica humana (Tinción standard con Giemsa) Derecha: Cariotipo humano. Los cromosomas se ordenan por tamaño y posición del centrómero. I.4. BANDEOS CROMOSÓMICOS A pesar de la aparente homogeneidad estructural de los brazos cromosómicos observable en las preparaciones convencionales, existen técnicas que revelan bandas o regiones con tinción diferencial a lo largo de los brazos cromosómicos. Estas bandas ponen de manifiesto la diferenciación longitudinal de los cromosomas, la cual representa diferencias en su compleja organización a nivel molecular. Una de las aplicaciones más importantes de las técnicas de bandeo es la identificación inequívoca de los cromosomas de un cariotipo. El poder de resolución de estas técnicas permite no sólo la identificación de cromosomas enteros sino también el estudio detallado de reordenamientos cromosómicos. Las técnicas de bandeo cromosómico pueden agruparse en técnicas de bandeo morfológico y de bandeo dinámico. Bandeos morfológicos Los bandeos morfológicos son inherentes a la heterogeneidad de la cromatina, relacionados a proteínas e interacciones ADN-proteínas y a la composición de bases del ADN. Pueden clasificarse, a su vez, en: a. técnicas de tinción diferencial, como las bandas G (Giemsa) y las bandas R (Reverse). Este tipo de bandeo revela un patrón de bandas longitudinales pero sólo en los cromosomas de aves y mamíferos. b. métodos de tinción selectiva, como las bandas C (tiñen la heterocromatina constitutiva), bandas NOR (tiñen los organizadores nucleolares) y bandas T (tiñen los telómeros). c. coloraciones con fluorocromos específicos aislados o combinados con colorantes no fluorescentes (DAPI, Cromomicina A3, etc). Estos fluorocromos pueden teñir regiones ricas en pares de bases AT o CG. d. bandeos con endonucleasas de restricción. Bandeos dinámicos Determinadas regiones cromosómicas inician y terminan la duplicación del ADN durante una pequeña fracción de la fase S constituyendo por lo tanto una unidad de replicación. Los bandeos de replicación involucran la incorporación selectiva de análogos de bases, como por ejemplo la 5bromodeoxiuridina (BrdUrd). El tránsito de la célula a través de la fase S puede ser detenido mediante el empleo de altas concentraciones del mencionado análogo de base. Esto permite identificar las regiones que se replican sincrónicamente en los distintos momentos de la fase S. Metafase mitótica con la técnica de Bandeo G. Esta técnica implica el tratamiento de los cromosomas con una enzima proteolítica (tripsina) y su posterior tinción con el colorante Giemsa. Metafase mitótica humana con técnica de Bandeo C. Está técnica implica el tratamiento con diferentes sustancias y su posterior tinción con el colorante Giemsa. II. OBJETIVOS II.1. Introducir al estudiante en la variabilidad y diversidad cromosómica de los seres vivos mediante la observación de preparaciones de células CHO, Homo sapiens y cromosomas politénicos en D. melanogaster. II. 2. Familiarizar al estudiante con el área de la citogenética mediante la observación al microscopio de preparaciones citológicas con técnicas de tinción clásicas y de bandeo cromosómico. III. ACTIVIDADES III.1. Observación al microscopio de preparaciones citológicas de: células CHO (línea celular de hámster chino). cromosomas politénicos de Drosophila Homo sapiens a. ¿Qué técnica de tinción cree que se utilizó en cada una de las preparaciones que observó y porqué? b. ¿Qué morfología cromosómica puede distinguir en las preparaciones de células CHO? c. Realice un dibujo de lo que observa en las preparaciones de cromosomas politénicos. ¿Cómo explicaría la presencia de 5 brazos emanado del cromocentro? Recuerde que D. melanogaster presenta un 2n= 8 con dos pares cromosómicos metacéntricos (II y III) y dos pares acrocéntricos (X o I y IV) y un cromosoma submetacéntrico (Y) en el caso de los machos. El par cromosómico IV es muy pequeño y totalmente heterocromático. d. ¿Qué diferencias encuentra entre estos cromosomas y los de CHO u Homo sapiens? A qué cree que son debidas? III.2. Observación de láminas Lámina A a. Indiqué número cromosómico de la especie (2n), número de moléculas de ADN y número de cromátidas. b. ¿Se trata de una célula animal masculina o femenina? Justifique. Lámina B ¿Qué particularidad observa en la estructura cromosómica (compare con la lámina B) y que técnica de bandeo se aplicó? III. 3. Observación al microscopio de preparaciones de H. sapiens con distintas técnicas de bandeo. ¿Qué técnicas de bandeo observó y qué parámetros lo llevaron a identificarlas? CICLO CELULAR MITÓTICO I. INTRODUCCIÓN El ciclo celular es el período comprendido entre la formación de una célula, por división de otra precedente, y el momento en que ella misma se divide para originar dos células hijas. Durante el ciclo toda la célula eucariota (núcleo y citoplasma) está sometida a una gran reestructuración. El ciclo celular se puede dividir en dos grandes períodos: interfase y mitosis, cada uno de los cuales se subdivide en varias fases o etapas. La interfase se encuentra subdividida en 3 etapas: a) Período G1: comienza la síntesis de ARN y proteínas, las cuales perduran durante toda la interfase. b) Período S: ocurre la duplicación del ADN dando lugar a la formación de las cromátidas hermanas. c) Período G2: fase post-sintética que va desde el final de S hasta el comienzo de la mitosis o división celular. En la mitosis ocurren 2 procesos altamente sincronizados: la cariocinesis (división del núcleo) y la citocinesis (división del citoplasma). En la cariocinesis se reconocen distintas fases: profase, metafase, anafase y telofase. Algunos autores reconocen a la prometafase como un estadio entre profase y metafase. La mitosis finaliza con la citocinesis, la cual es diferente en células animales y vegetales. (A) INTERFASE: Núcleos en interfase. La cromatina aparece bastante homogénea, a excepción de zonas más claras que corresponden a los nucleolos. (B) PROFASE: La cromatina comienza a condensarse. A medida que avanza este estadio desaparece el nucleolo. Los “cromosomas” aparecen como filamentos delgados. (C) METAFASE: Cada cromosoma, integrado por dos cromátidas hermanas, se dispone con su centrómero en el plano ecuatorial. (D-E) ANAFASE: Las cromátidas hermanas se separan y comienzan a migrar hacia los polos opuestos de la célula. Ahora los cromosomas se observan formados por una sola cromátida, con los centrómeros dispuestos hacia los polos y los telómeros hacia el centro de la célula. (F) TELOFASE: No es posible individualizar los cromosomas. La cromatina comienza a descondensarse en ambos núcleos hijos. TÉCNICAS ESTÁNDAR E INMUNOCITOQUÍMCA UTILIZADAS EN EL ESTUDIO DEL CICLO CELULAR La obtención de preparaciones para el análisis del ciclo celular se realiza a partir de tejidos proliferantes mediante diversas técnicas como el aplastado o la dispersión celular. Estas técnicas generalmente presentan las siguientes etapas: a. Obtención del material y Pretratamiento: muchos tejidos requieren el uso de soluciones que permitan dispersar o separar los cromosomas. En animales se usan soluciones salinas (Cloruro de Potasio, Citrato de Sodio, Cloruro de Sodio) o agua destilada, provocando un choque hipotónico a la célula. Para estudiar las características de los cromosomas de una especie, o para comparar especies distintas, se pueden utilizar agentes antimitóticos (colchicina, colcemida, hidroxiquinoleína, etc.) que actúan como inhibidores de la formación del huso mitótico. De esta manera se incrementa de forma significativa el número de metafases. b. Fijación: tiene por finalidad preservar las estructuras celulares que nos interesan. El líquido fijador varía según la técnica a utilizar. El fijador más utilizado para técnicas con tinción estándar es el llamado 3:1 (metanol o etanol: ácido acético). Para la realización de técnicas inmunocitoquímicas en general se utilizan fijadores del tipo de los glutaraldehidos o metanoles. c. Coloración: en las técnicas estándar se usan varios colorantes tales como: orceína, hematoxilina acética, Feulgen y Giemsa. La elección del colorante depende de los fines perseguidos. En inmunocitoquímica se utilizan fluorocromos con el fin de colorear la cromatina (DAPI, Hoechst, Ioduro de propidio). d. Montaje: esta etapa consiste en preservar el preparado colocando un cubreobjeto y sellándolo con parafina líquida, esmalte de uñas, bálsamo de Canadá o resinas sintéticas. II. OBJETIVOS Reconocer las diferentes etapas del ciclo celular mitótico. Realizar preparaciones citológicas de Allium cepa (cebolla). III. ACTIVIDADES III.1. Observación al microscopio de preparaciones citológicas de A. cepa fijadas en 3:1 y coloreadas con Feulgen/verde luz. a. Dibuje e identifique las principales etapas del ciclo celular. ¿Qué parámetros utilizó para identificarlas? b. El número cromosómico de A. cepa es 2n=16. ¿Cuántos cromosomas, cromátidas y moléculas de ADN encuentra en la placa metafásica? ¿Cual es el valor C en cada una de las etapas del ciclo celular? III.2. Observación al microscopio de preparaciones citológicas de A. cepa con tinción argéntica. a. ¿Qué estructura se observa con esta metodología? b. Analice el comportamiento de esta estructura durante el ciclo celular. III.3. Observación de una lámina de células en cultivo de mamíferos tratadas con la técnica de inmunocitoquímica. a. ¿Qué estructura observa en color verde y cuál en azul? b. Identifique y ordene las principales etapas del ciclo celular. ¿Qué parámetros utilizó para ello? III.4. Realización de preparaciones de meristemo de A. cepa y observación de las mismas. PROTOCOLO PARA LA REALIZACIÓN DE LAS PREPARACIONES DE ALLIUM CEPA Obtención del material: Cinco o seis días antes de la realización de las preparaciones, se escoge una cebolla fresca y se coloca en un recipiente con agua, con el bulbo sumergido. Se cambia el agua diariamente. Fijación del material: Cuando las raíces nuevas alcanzan 3 cm de longitud, se extrae la cebolla del recipiente y se corta el último centímetro de la punta. Se depositan estas raíces en la solución fijadora denominada 3:1 (3 partes de etanol absoluto: 1 parte de ácido acético glacial) durante 2 o tres días. Realización de las preparaciones por el método de aplastado y coloración. En células vegetales, después de la fijación, se requiere de un tratamiento para romper la pared celular. Traslade las raíces fijadas a un recipiente que contiene ácido clorhídrico 5 N durante 15 minutos. Coloque las raíces en un recipiente con agua y lávelas por cinco minutos. Corte el extremo del meristemo y póngalo en un portaobjetos. Triture levemente el material. Deje caer sobre el material una gota de orceína acético-láctica y espere 5-10 minutos para que coloree. Luego coloque un cubre objeto y con un lápiz disperse y aplaste el material. Observe al microscopio si el aplastado es suficiente y en tal caso selle con esmalte la preparación. MEIOSIS INTRODUCCIÓN La MITOSIS es el único tipo de división celular existente en algunas especies de protozoarios, algas y hongos. Pero muchos organismos simples y casi todos los complejos, pueden también dividir sus células por MEIOSIS. Este tipo de división genera células esencialmente diferentes de las progenitoras en cuanto a las combinaciones de su material hereditario, su número cromosómico y su cantidad de ADN. Esquemas comparativo entre los ciclos celulares meiótico y mitótico. La MEIOSIS consta de dos divisiones precedidas por un único período S de duplicación del ADN. Como consecuencia, a partir de una única célula, se originan cuatro células distintas con un solo set o conjunto cromosómico (denominado haploide o “n”) y con una carga de ADN equivalente a “C”. El estado diploide (2n) se restaura mediante la fusión de dos células haploides, proceso conocido como fertilización. La combinación de la meiosis y la fertilización en el ciclo vital de un organismo es lo que se conoce como reproducción sexual. Esquemas en los que se comparan el ciclo celular en células somáticas y la meiosis en células de la línea germinal. Se han relacionado la cantidad de ADN de las células (C) y el grado de ploidía celular (n = haploide, 2n = diploide) para las distintas etapas. En animales superiores, la meiosis tiene lugar en los órganos sexuales, tanto masculinos como femeninos, dentro de un proceso general que se denomina respectivamente espermatogénesis y ovogénesis. Estos procesos producen células genéticamente diferentes y equilibradas con una reducción a la mitad del número de cromosomas. Estas células presentan además las modificaciones necesarias para la fecundación. ESPERMATOGÉNESIS Definición de Espermatogénesis: Conjunto de cambios que experimenta una célula prácticamente indiferenciada: la ESPERMATOGONIA, para originar células altamente especializadas, con un complemento haploide de cromosomas recombinados y capaz de fecundar: el ESPERMATOZOIDE. Teniendo en cuenta los cambios que se producen en la espermatogonia, y por tanto los nuevos tipos celulares y los procesos en los que participan, podemos dividir a la espermatogénesis en las siguientes etapas: PROLIFERACIÓN MEIOSIS ESPERMIOGÉNESIS O HISTODIFERENCIACIÓN A) PROLIFERACIÓN. Este período comprende el desarrollo de las espermatogonias, las cuales se dividen mitóticamente para aumentar la población celular. En esta etapa de divisiones rápidas y continuas se puede observar el número y morfología cromosómica en las metafases mitóticas. ESPERMATOGONIAS Fotografía (A) y esquema (B) de una sección de un túbulo seminífero de saltamontes en los que se observa la disposición secuencial de las células que cursan la espermatogénesis. B) MEIOSIS. La profase de la primera división meiótica es extremadamente larga pudiendo durar desde días (en machos) hasta años (generalmente en hembras). Durante la profase I se produce el apareamiento de los cromosomas homólogos y la recombinación entre cromátidas homólogas. Para su estudio, se ha dividido esta profase I en varias etapas: LEPTOTENO, ZIGOTENO, PAQUITENO, DIPLOTENO Y DIACINESIS. En la metafase I los cromosomas homólogos apareados (bivalentes) se disponen en el plano ecuatorial. En la primera anafase meiótica los cromosomas homólogos, previamente recombinados, migran a polos opuestos. Tras una interfase muy corta (intercinesis), y a veces inexistente, se efectúa la segunda división meiótica. En esta división cada célula posee solamente un cromosoma del par homólogo ya recombinado. Además los cromosomas en metafase II poseen sus cromátidas unidas únicamente a nivel del centrómero, ya que la adhesividad a nivel de brazos se perdió en la anafase I. Por cada célula que entra en meiosis se obtienen cuatro células haploides y con una carga "C" de ADN: las ESPERMÁTIDAS. C) ESPERMIOGÉNESIS. Se conoce con este nombre a toda la serie de cambios tanto citoplásmicos como nucleares que experimentan las espermátidas hasta transformarse en espermatozoides. Estos cambios son muy variables y dependen de la especie estudiada. No obstante, y como rasgos generales, podemos decir que se centran en la compactación de la cromatina en el núcleo, la pérdida de casi la totalidad del citoplasma y la adquisición de un aparato locomotor por parte de la célula. II) OBJETIVOS DEL PRÁCTICO a) Analizar la meiosis y la espermatogénesis en preparaciones de una especie de ortóptero (Locusta migratoria). III) CARACTERÍSTICAS DEL MATERIAL Y METODOLOGÍA Los ortópteros suelen emplearse para los estudios cromosómicos por su fácil obtención y manejo en el laboratorio. Presentan además un número reducido de cromosomas de gran tamaño y una meiosis fácilmente observable en su totalidad. En el túbulo seminífero de ortópteros las células que cursan la espermatogénesis se encuentran en grupos denominados CISTOS. Todas las células que componen un mismo cisto son sincrónicas, es decir, están en el mismo estadio de la meiosis por lo que resulta relativamente fácil visualizar las distintas etapas meióticas en una misma preparación. TINCIÓN CON FEULGEN Y APLASTADO Los testículos de langosta se fijan en una mezcla de ácido acético y etanol en proporción 3:1 al menos una semana antes. Para realizar la tinción de Feulgen este material es tratado con HCl 5N durante 1 hora y teñido con reactivo de Schiff durante 3 horas. Posteriormente se coloca sobre una porción del testículo (1 o 2 túbulos) un cubreobjetos y se dispersa y aplasta el material. ACTIVIDADES A REALIZAR b) Observar las preparaciones de Locusta migratoria y determinar el número diploide y las características de su cariotipo (morfología de los cromosomas y sistema de determinación sexual). Realizar un esquema de las diferentes etapas de la meiosis. c) Observar los distintos estadios de la espermatogénesis. d) Comparar el cariotipo de L. migratoria con el de Chorthippus jucundus (especie de la cual se obtuvieron las planchas de este repartido). e) Realizar un esquema de la meiosis de un individuo 2n=4 con cromosomas submetacéntricos y telocéntricos. IMÁGENES DE LA ESPERMATOGÉNESIS EN Chorthippus jucundus Células del testículo de Chorthippus jucundus obtenidas mediante la técnica de aplastado y teñidas con orceína acético-láctica. El cromosoma sexual X ha sido señalado con una X. A.- Núcleo de espermatogonia en interfase (ciclo mitótico). B.- Metafase mitótica (espermatogonial). Cada cromosoma está integrado por dos (2) cromátidas. Vista polar. C.-Comienzo de la Meiosis. Núcleo prepaquiténico, Lepto/Zigoteno. En leptoteno los cromosomas homólogos no se encuentran apareados y se observan como fibras simples. Zigoteno, comienza el apareamiento de homólogos, se observan fibras dobles (cromosomas apareados) y fibras simples (sin aparear) D.- Paquiteno medio. E.- Paquiteno tardío. Los cromosomas homólogos se encuentran totalmente apareados F.- Diploteno. Con flechas se señala la posición de los quiasmas en los bivalentes (constituidos por 4 cromátidas). M7 = bivalente monoquiasmático. M4= bivalente con 2 quiasmas. L1= Bivalente con 4 quiasmas. El cromosoma X, telocéntrico, aparece claramente formado por 2 cromátidas. Células del testículo de Chorthippus jucundus obtenidas mediante la técnica de aplastado y teñidas con orceína acético-láctica. A. Diploteno tardío-diacinesis. Aumenta la condensación de la cromatina. B. Metafase I. Vista lateral. Se aprecian los bivalentes con quiasmas, co-orientados en el eje ecuatorial de la célula. C. Anafase I. Segregan los cromosomas homólogos. El cromosoma sexual X migra completo (con sus dos cromátidas) al polo superior de la célula. El polo inferior carecerá de cromosoma X. D. Telofase I. Finaliza con la formación de dos células haploides pero con 2C de contenido de ADN por célula. E. Intercinesis/Profase-II (dos células). La célula de la parte superior de la fotografía posee el cromosoma X, mientras que la de la parte inferior carece de él. Células del testículo de Chorthippus jucundus obtenidas mediante la técnica de aplastado y teñidas con orceína acético-láctica. A. Metafase-II. Se observa la disposición radial de los cromosomas característica de una vista polar. Cada cromosoma (o diada) está integrado por 2 cromátidas. B. Anafase-II temprana. Las 2 cromátidas de cada cromosoma comienzan a segregar. C. Anafase-II tardía. Continúa la migración de las cromátidas a polos opuestos. D. Telofase-II. E. Espermátidas tempranas. Dos de las que aparecen en la fotografía poseen el cromosoma sexual (X), mientras que la situada en parte central carece de él. F-G. Espermátidas en diferentes estados de maduración (redondeadas y fusiformes). PROBLEMAS SOBRE MECANISMOS DE LA HERENCIA PROBLEMAS RELACIONADOS CON LAS LEYES DE MENDEL 1) La descendencia (F1) de un cruzamiento entre dos cerdos, una hembra de color blanco y un macho de color negro, fue toda de color negro. a) Diagramar un cruzamiento simple mostrando los posibles genotipos y fenotipos de los parentales y su descendencia. b) Si se realizan cruzamientos entre individuos de la F1. En cada uno de ellos se obtiene aproximadamente un 25% de individuos blancos y un 75% negros. Indique los genotipos de los parentales y descendientes. c) Dos diferentes cruzamientos fueron hechos entre individuos negros de la F2 con los resultados que se muestran en la tabla. Diagrame cada uno de los cruzamientos. Cruzamientos Cruz. 1 Cruz. 2 Fenotipos de la Progenie Todos negros ¾ negros; ¼ blancos 2) Si se conoce una serie de 4 alelos en el locus para color de ojos en Drosophila: Cuántos alelos a) hay en un cromosoma para este locus? b) podrían haber en un par de cromosomas? c) Podrían haber una célula somática de un individuo miembro de esta especie? d) Sobre esta misma base, cuántas combinaciones diferentes se esperaría encontrar en toda la población? 3) La talasemia es una enfermedad hereditaria de la sangre en los seres humanos, que produce anemia. La anemia severa (talasemia mayor) es encontrada en los homocigotas (TN TN) y un tipo más benigno de anemia (talasemia menor) en los heterocigotas (TM TN). Los individuos normales son homocigotas (TM TM). Si todos los individuos con talasemia mayor mueren antes de la madurez sexual: a) ¿Qué proporción de F1 adultos, producidos de matrimonios entre talasémicos menores con normales puede esperarse que sea normal? b) ¿Qué fracción de adultos F1 descendientes de matrimonios entre talasémicos menores podemos esperar que sean anémicos? c) ¿Qué probabilidad hay que de un cruzamiento entre dos talasémicos menores se obtenga primero un hijo talasémico menor, después un talasémico mayor y por último uno normal? d) ¿Qué probabilidad hay que de un cruzamiento como el anterior nazcan dos hijos normales y un talasémico menor, sin importar el orden? 4) El color del pelaje de los conejos está determinado genéticamente por una serie de alelos múltiples con la siguiente jerarquía de dominancia: C (gris típico) > cch (chinchilla) > ch (himalayo) > c (albino) Se cruza una hembra gris con un macho chinchilla y se obtiene una progenie que consta de conejos grises, chinchilla e himalayos. Al año siguiente la hembra se aparea con un macho himalayo y produce una progenie gris, himalaya y albina. a) Determinar los genotipos de todos los animales mencionados. b) ¿Cuál es la probabilidad de que la primera cruza origine dos hembras, una chinchilla y una himalaya y un macho gris en un orden dado? 5) En la tabla que se ilustra a continuación se detallan los fenotipos de cinco madres (A-E). Cada madre tiene un hijo cuyo fenotipo también se describe. De los cinco hombres cuyo genotipo está determinado seleccione al padre que corresponde a cada uno de los hijos. Madre A B C D E fenotipo A M Rh+ B N RhO M RhA N Rh+ AB MN Rh- fenotipo del hijo O M Rh+ O N RhA MN Rh+ AB MN Rh+ AB M Rh- genotipo de posibles padres IAi LMLM rr IBi LMLN RR ii LNLN rr ii LMLM rr IAIA LMLN RR 6) En Drosophila el color ébano del cuerpo se debe a un gen recesivo e y el tipo silvestre + (gris), a su alelo dominante e . Las alas vestigiales se producen por un gen recesivo (vg); + las alas de tamaño normal (tipo silvestre) las determina el alelo dominante vg . a) Si se cruzan moscas dihíbridas tipo silvestre y producen una progenie de 256 individuos, ¿cuántas moscas de éstas se espera que haya para cada clase fenotípica? b) ¿Qué cruza realizaría para conocer el genotipo de una mosca de fenotipo salvaje de la F1? c) Si obtuviera 139 moscas de fenotipo salvaje, 50 de color ébano, 45 de alas vestigiales y 22 ébano de alas vestigiales, ¿podría considerar de todas formas que el mecanismo de herencia es el propuesto? Contrastación de hipótesis (Test de Χ2) 7) La condición heterocigótica llamada “creeper” en las gallinas, produce patas y alas deformadas. Cruzamientos entre “creeper” produjeron 785 gallinas “creeper” y 378 normales. a) ¿Es aceptable la hipótesis de una proporción 3:1? b) ¿Se ajustará mejor la de 2:1? c) ¿Qué fenotipo producirá el gen “creeper” cuando está en la condición homocigótica? 8) Las flores de ciertas plantas pueden ser rojas, rosas o blancas. Las flores rojas cruzadas con las blancas producen solo flores rosas. Cuando plantas con flores rosas fueron cruzadas, produjeron 113 rojas, 129 blancas y 242 rosas. a) Proponga una hipótesis b) Aplique el test de chi cuadrado para ver si esta hipótesis es aceptable. Deducción de genotipo 9) En los perros el color oscuro del pelo es dominante sobre el albino y el pelo corto es dominante sobre el largo. Si estos efectos son causados por dos pares de genes que segregan independientemente, escriba los genotipos más probables de los progenitores de cada uno de los siguientes cruzamientos, utilizando los símbolos A y a para los alelos para el color oscuro y albino del pelo, y L y l para los alelos que rigen el pelo corto y largo respectivamente. oscuro corto Fenotipos de la descendencia oscuro largo albino corto albino largo Fenotipos paternos a) oscuro corto x oscuro corto 89 31 29 11 b) oscuro corto x oscuro largo 18 19 0 0 c) oscuro corto x albino corto 20 0 21 0 d) albino corto x albino corto 0 0 28 9 e) oscuro largo x oscuro largo 0 32 0 10 f) oscuro corto x oscuro corto 46 16 0 0 g) oscuro corto x oscuro largo 29 31 9 11 Genética del sexo 10) En Drosophila, se identifica una mutación que produce márgenes irregulares en las alas (scalloped, sc). a) Cuando se cruza una hembra normal con un macho mutante de cepa pura, toda la descendencia es de fenotipo salvaje. ¿Qué puede deducir acerca de la mutación? b) Cuando se realiza la cruza recíproca a la anterior, se obtienen hembras salvajes y machos con alas de márgenes irregulares. ¿Qué más deduciría ahora acerca de la ubicación del locus mutante? Describa los genotipos y los cruzamientos descritos en las partes a) y b) 11) Se realizó un cruzamiento entre una hembra de Drosophila heterocigótica respecto a los genes recesivos c (que determina alas cortadas) y s (que determina ojos color sepia) y un macho de alas normales y ojos color sepia, obteniéndose la siguiente progenie: hembras 1/2 alas largas, ojos rojos 1/2 alas largas, ojos sepia machos 1/4 alas largas, ojos rojos 1/4 alas cortas, ojos rojos 1/4 alas largas, ojos sepia 1/4 alas cortas, ojos sepia Explique el modo de herencia de estos rasgos. Indique el genotipo de los padres y de los descendientes.* *Considere que del cruzamiento de machos con ojos color rojo y hembras con ojos color sepia (ambas cepas puras) toda la descendencia obtenida tiene ojos rojos. 12) La calvicie es un carácter hereditario influido por el sexo, dominante en los hombres y recesivo en las mujeres. Si C1 es el alelo determinante de la calvicie y C2 el de la no calvicie, determine el genotipo de un hombre calvo cuyo padre no lo era, el de su esposa, que no es calva, pero su madre sí lo era, y el de sus futuros hijos. PROBLEMAS RELACIONADOS CON LIGAMIENTO Y MAPEO 13) Un individuo homocigota para los genes recesivos a y b se cruza con el tipo salvaje AABB. Con los individuos de la F1 se hace una retrocruza con el doble recesivo. El aspecto de la descendencia es el siguiente: AB 903 Ab 98 aB 102 ab 897 a) Explique estos resultados, dando el porcentaje de recombinación entre los genes A y B. b) Si la transmisión de A y B fuese de forma independiente, cuáles serían los resultados aproximados de este cruzamiento? 14) En el tomate, la forma del fruto depende de los loci P, p (P, liso p, rugoso) y R, r (R, redondo r, alargado). La F1 de un cruzamiento entre homocigotos lisos y alargados por rugosos y redondos se cruzó por el doble recesivo, obteniéndose los siguientes resultados: liso y redondo 45 rugoso y redondo 91 liso y alargado 86 rugoso y alargado 39 a) Describa los genotipos de los individuos indicando la posición de ambos loci. b) Determine el porcentaje de recombinación y la distancia genética entre estos loci. c) Si analizásemos 3000 células madres del polen, ¿En cuántas se esperaría observar al menos un quiasma entre los loci considerados? 15) En una determinada planta diploide, tres loci determinan los siguientes caracteres de las hojas: L,l hojas opacas, hojas lustrosas R,r hojas con bordes lisos, hojas con bordes rugosos A,a hojas amplias, hojas angostas Estos loci están ligados del modo siguiente: L,l R,r A,a ³------10 cM ---------³---------20 cM --------³ a) ¿Qué gametos formaría una planta trihíbrida de genotipo LrA/lRa? b) Si esta planta trihíbrida se cruza con una planta homocigota recesiva, ¿cuáles serán las proporciones fenotípicas esperadas? 16) A los ojos en forma de riñón los produce un gen recesivo k en el tercer cromosoma de Drosophila. Los ojos color naranja, llamados cardenales son producidos por el gen recesivo cd en el mismo cromosoma. Entre estos dos loci, hay un tercer locus con un alelo recesivo e que produce color de cuerpo ébano. Hembras homocigotas con ojos arriñonados y de color cardenal se cruzan con machos homocigotas con cuerpo color ébano. Se hace luego una cruza de prueba con las hembras F1 trihíbridas para producir la F2. Entre la progenie F2 de 4000 se encontró lo siguiente: 1761 1773 97 89 128 138 6 8 arriñonado, cardenal ébano arriñonado ébano, cardenal arriñonado, ébano cardenal arriñonado, ébano,cardenal tipo silvestre a) Determine las relaciones de ligamiento en los progenitores y de la F1 b) Estime las distancias de mapa c) Determine el coeficiente de coincidencia 17) El trihíbrido AaBbCc es cruzado con el homocigota aabbcc, obteniéndose los siguientes resultados: ABc aBC Abc abC 1060 1050 1060 1055 AbC abc aBc ABC 128 130 130 128 a) ¿Cuál es la relación de ligamiento en el trihíbrido? b) Construya un mapa cromosómico para estos tres loci c) ¿Cuál es el porcentaje de recombinación entre los genes? d) ¿Para cuál o cuáles de estos genes se cumplen las leyes de Mendel? 18) En la especie humana el alelo autosómico N provoca anormalidades en uñas y rótula, rasgos conocidos como síndrome uña-rótula. Considere los matrimonios en los que uno de los individuos padece el síndrome uña-rótula y es de grupo sanguíneo A y el otro individuo es de grupo sanguíneo O y no padece el síndrome. Estos matrimonios tienen algunos hijos que son de grupo sanguíneo A y padecen el síndrome uña rótula. Suponga que hijos de ese grupo fenotípico, se cruzan con individuos de grupo sanguíneo O y sin el síndrome. Entre los descendientes se observan cuatro fenotipos distintos en las proporciones siguientes: síndrome uña-rótula, grupo sanguíneo A sin síndrome uña-rótula, grupo sanguíneo A síndrome uña-rótula, grupo sanguíneo O sin síndrome uña-rótula, grupo sanguíneo O 42% 8% 10% 40% Dado que el locus que define el grupo sanguíneo ABO ya ha sido localizado en el genoma humano en el cromosoma 9 ¿qué puede decir de la localización del locus responsable del síndrome uña-rótula? PROBLEMAS RELACIONADOS CON INTERACCIÓN GÉNICA 19) El pigmento de los ratones es producido sólo cuando el alelo C está presente. Individuos del genotipo cc no tienen color. Si el color está presente, éste puede ser determinado por los alelos A, a. Los genotipos AA o Aa dan lugar al color gris (agoutí) mientras que aa da lugar al pelaje negro. a) ¿Cuáles son las proporciones fenotípicas y genotípicas de la F1 y la F2 del cruzamiento entre ratones AACC x aacc? b) Las proporciones fenotípicas obtenidas de tres cruzamientos entre hembras grises de genotipo desconocido con machos de genotipo aacc, son las siguientes: (1) 8 grises 8 sin color (2) 9 grises 10 negros (3) 4 grises 5 negros 10 sin color ¿Cuál es el genotipo de cada una de esas tres hembras? 20) Al cruzar entre sí varias cepas de la calabaza de verano, Sinnott y Dunn encontraron que las líneas de plantas de frutos blancos podían dar lugar ocasionalmente a plantas verdes o amarillas y que las líneas de plantas amarillas producen ocasionalmente plantas verdes. Después de realizar cruzamientos consanguíneos en las distintas líneas hasta que fuesen completamente homocigóticas y constituyesen líneas puras, se realizaron cruzamientos entre las distintas líneas y entonces se cruzaron entre sí los productos de la F1 (F1 x F1) dando los siguientes resultados: Cruzamientos Progenitores F1 F2 a) verde x amarillo amarillo 81 amarillo 29 verde b) blanco x amarillo blanco 155 blanco 40 amarillo 10 verde Dé símbolos a los genes implicados y explique dichos resultados. 21) En Drosophila el gen dominante S produce una condición peculiar del ojo llamado estrella (Star). Su alelo recesivo s origina el ojo normal. La expresión de S puede ser suprimida por el alelo dominante Su (supresor de S) en otro locus. El alelo recesivo de este locus (su) no tiene efecto sobre s. a) ¿Qué tipo de mecanismo está actuando? b) Cuando un macho con ojos normales de genotipo SuSuSS es cruzado con una hembra con ojos normales de genotipo sususs, ¿qué proporción fenotípica se puede esperar en F1 y F2? c) ¿Qué porcentaje de F2 de tipo normal es probable que sea portadora del gen dominante para el tipo Star? PROBLEMAS RELACIONADOS CON HERENCIA CUANTITATIVA 22) En el estudio de la herencia del carácter altura de la planta del tomate, se construyó el siguiente cuadro con la información obtenida de los siguientes cruzamientos: Cruzas rango de altura (cm) Media varianza P1 (línea pura) 20-30 25 6,5 P2 (línea pura) 60-80 75 6,8 F1 (P1 X P2) 30-60 50 6,2 F2 (F1 X F1) 20-76 50 10,6 a) ¿A qué atribuye el valor de la varianza observado en P1 y P2? b) ¿Cómo explica el valor de la varianza en la F2? c) ¿Cuál es la varianza genética de F1? d) Teniendo en cuenta que los individuos de 20 cm de altura aparecen en la F2 con una frecuencia de 0,0156, indique cuántos alelos como mínimo están determinando esta característica. e) ¿Cuál es la contribución que realiza cada alelo a la altura final? 23) La producción anual de leche de las vacas de un tambo es de 18.000 lts. La producción promedio de leche de los individuos seleccionados para ser los progenitores de la siguiente generación es de 20.000 lts. La producción de leche promedio de la primera generación es de 18.440 lts. a) calcule la heredabilidad de la producción de leche de esa población. b) si la varianza fenotípica de esa población es de 4.000.000 lts2, calcule la varianza genotípica. c) ¿entre qué valores se encontraría el 68% de la población original? PROBLEMAS RELACIONADOS HEREDITARIOS CON DIVERSOS MECANISMOS 24) En una familia, cierta afección se transmite de la forma representada en la siguiente genealogía: ? ? a) Tras el análisis, ¿qué conclusiones puede sacar acerca del modo de herencia de esta afección? b) ¿Qué fenotipo presentarán los dos posibles hijos (representados por el símbolo ?) de la pareja II4 y II5 si nacen una mujer y un varón? c) ¿Qué explicación puede proporcionar en el caso de que nazca de dicha pareja una mujer afectada? 25) Los gatos caseros machos pueden ser negros o amarillos. Las hembras pueden ser negras, moriscas o amarillas. a) ¿Cómo pueden explicarse estos resultados? b) Utilizando símbolos apropiados determine los fenotipos esperados en la descendencia de la cruza de una hembra amarilla con un macho negro. c) Hágase lo mismo para la cruza recíproca de la parte b) d) Cierto tipo de combinación produce hembras, la mitad moriscas y la otra mitad negras; la mitad de los machos son amarillos y la otra mitad son negros. ¿Cuáles son los colores de los precursores en esta cruza? e) Otro tipo de combinación produce descendencia, la cuarta parte son machos amarillos, otra cuarta parte hembras amarillas, otra cuarta parte machos negros y otra cuarta parte hembras moriscas. ¿Cuáles son los colores de los precursores? 26) Una condición mutante ligada al sexo denominada "muesca" (M) es letal en Drosophila cuando se presenta en los machos hemicigóticos y en las hembras homocigóticas. Las hembras heterocigóticas (XMXm) tienen pequeñas muescas en las puntas de sus alas. Las hembras homocigóticas recesivas (XmXm) y los machos hemicigóticos (XmY) tienen alas normales (tipo común). a) Calcule las proporciones fenotípicas viables esperadas en F1 sin considerar el sexo, cuando se cruzan machos de tipo común con hembras con muescas. b) ¿Cuál es la proporción de machos viables: hembras viables en F1? c) ¿Cuál es la proporción de animales viables con muesca: tipo común en F1? 27) Un investigador posee 6 plantas de una especie en la que quiere estudiar la herencia del tipo de inflorescencia. Para ello realizó algunos cruzamientos entre ellas, cuyos resultados se dan a continuación: a) planta inflor. sencilla x planta inflor. compuesta Progenie: 27 plantas inflor. sencilla; 24 plantas inflor. compuesta b) planta inflor. sencilla x planta inflor. sencilla Progenie: 53 plantas inflor. sencilla c) planta inflor. compuesta x planta inflor. compuesta Progenie: 37 plantas inflor. compuesta I) II) III) ¿Qué conclusiones y/o suposiciones le permiten sacar los resultados de estos cruzamientos? En base a esas suposiciones elabore dos hipótesis que puedan explicar estos resultados. Para cada hipótesis indique los genotipos de todas las plantas y sus descendientes posibles. Plantee un cruzamiento entre dos plantas de la descendencia del cruzamiento a) de manera que sus resultados le permitan descartar una de las dos hipótesis elaboradas. 28) El árbol genealógico siguiente corresponde a una familia en que existe la afección “albinismo” causada por un alelo recesivo autosómico. Los individuos II1 y II5 son albinos. Se admitirá que los sujetos II2, III1 y III4 son homocigotas para el alelo normal. I II III IV a) sea “a” el alelo para albinismo y “A" su alelo normal, dar los genotipos de los individuos hasta donde sea posible. b) ¿Cuál es la probabilidad de que II3 sea heterocigota para ese gen? c) IV1 y IV2 desean tener un hijo. ¿Cuál es la probabilidad de que se presente la afección en la descendencia? 29) En un centro de investigación que trabaja con Drosophila melanogaster se detecta y aísla un mutante recesivo (lob) que modifica la forma de los ojos del insecto, que aparecen con un contorno lobulado. Posteriormente se aísla otro mutante recesivo (es) que también afecta a la forma del ojo, teniendo ahora un contorno estrellado. ¿Cómo se puede saber si los mutantes lob y es son alelos de una serie alélica? 30) En Drosophila se identificaron dos cepas puras que difieren de la cepa salvaje por el color de los ojos. Una es bermellón claro "ber", la otra es rubí "rub". a) Si el cruzamiento de hembras "rub" x machos "ber" da una F1 toda salvaje, ¿cómo explicaría Ud. que ninguno de los colores mutantes aparezca en la descendencia? b) El cruzamiento hembras "ber" x machos "rub" da en la F1 hembras salvajes y machos "ber". ¿Cómo explica la aparición del fenotipo "ber" en los machos? c) ¿Están estos genes implicados en el mismo cromosoma? d) F1 x F1 del cruzamiento b) da una descendencia con cuatro fenotipos diferentes: "+", "ber", "rub" y "orange". ¿Qué hipótesis simple explica la aparición del fenotipo "orange"? e) Según esta hipótesis, cuáles son las proporciones esperadas para cada fenotipo? MARCADORES CITOGENÉTICOS Y MOLECULARES 31) Hembras de Drosophila homocigotas para el gen ligado al X carnation (ojos rubí, recesivo) se cruzan con machos salvajes que tienen cromosomas X de tamaño mayor al normal como consecuencia de la adición de un fragmento Marcador del cromosoma Y. Las hembras descendientes de este cromosómico cruzamiento se cruzan con machos carnation. De los Locus individuos que llevan el marcador cromosómico, 1% son carnation carnation. Indique la distancia genética del locus carnation con respecto al marcador cromosómico. 32) La siguiente genealogía corresponde a una familia que presenta una patología conocida como eliptocitosis u ovalocitosis. El gen causante de esta enfermedad se halla ligado al gen que determina el sistema de grupos sanguíneo Rh. El porcentaje de recombinación entre ambos genes es del 3%. Si el individuo IV8 tiene un hijo del grupo sanguíneo R1r, ¿cuál es la probabilidad de que éste tenga eliptocitosis? 33) De la siguiente genealogía el individuo I3 y su hijo II2 desarrollaron, después de los 50 años, la enfermedad de Huntington. Esta enfermedad, de herencia monogénica y dominante, ha sido diagnosticada gracias a la presencia de un marcador de tipo VNTR que se comporta ligado al locus responsable de la enfermedad. Con estos antecedentes, la mujer III 7 consulta por la posibilidad de tener un hijo que lleve el alelo afectado, por lo cual se analiza esta familia en cuanto a su genotipo para el marcador molecular. Este marcador, en la familia en cuestión, presenta 4 alelos identificables por su migración diferencial en gel, como se observa en el southern blot de la figura. En base a la genealogía y el southern blot, ¿qué probabilidad tiene esta mujer, casada con un hombre sin antecedentes de enfermedad de Huntington, de tener un hijo afectado? Drosophila melanogaster UN MODELO BIOLÓGICO PARA EL ESTUDIO DE LOS CARACTERES HEREDITARIOS Cronograma 23/09 Clase 1 Introducción a la biología y genética de D. melanogaster. Observación del ciclo de vida y dimorfismo sexual. Identificación del fenotipo salvaje y de las mutaciones incógnitas. Planteo de hipótesis para investigar el modo de herencia de las mutaciones. 28/09 Clase 2 Discusión de las hipótesis planteadas con los estudiantes. Realización de los cruzamientos. 12/10 Clase 3 Análisis de la progenie F1. Planteo de hipótesis para determinar el grupo de ligamiento de las mutaciones, empleo de los “cromosomas balanceadores”. Planteo del test de alelismo. 14/10 Clase 4 Discusión de las hipótesis planteadas. Realización de cruzamientos para el análisis de ligamiento. Realización de cruzamientos para el test de alelismo. 28/10 Clase 5 Continuación de los cruzamientos realizados en la clase anterior. Análisis de ligamiento: análisis de la progenie F1 y segundo cruzamiento. Test de alelismo: análisis de la progenie F1. Discusión de los resultados observados. 11/11 Clase 6 Análisis de la progenie F2 y determinación del grupo de ligamiento. Discusión de los cruzamientos para realizar el análisis de las frecuencias de recombinación entre dos loci (uno de ellos incógnita). 16/11 Clase 7 Discusión de las hipótesis planteadas. Análisis de la progenie y análisis de la frecuencia de recombinación. Cálculo de las distancias génicas y discusión de los resultados. La mosca del vinagre, Drosophila melanogaster, es un organismo eucariota empleado como modelo de experimentación en Genética. Tiene las siguientes ventajas: 1) un ciclo vital relativamente corto a temperatura ambiente, entre 10-14 días; 2) es fácil de criar en botellas o tubos de vidrio con un medio de cultivo barato y sencillo de preparar; 3) una gran productividad, una pareja produce varios cientos de descendientes; 4) un número cromosómico bajo, 4 pares de cromosomas; y 5) un gran número de caracteres heredables que afectan la morfología del adulto. Como resultado de la larga trayectoria en la investigación en genética, se han descubierto un gran número de mutaciones y se ha logrado un vasto conocimiento de su genoma. Objetivos • Introducir al estudiante en el ciclo de vida de la mosca Drosophila, el reconocimiento de los sexos y de los fenotipos mutantes, y la nomenclatura. • Estimular el planteo de hipótesis y su contrastación mediante el desarrollo de cruzamientos experimentales. • Determinar el modo de herencia y el grupo de ligamiento de tres mutaciones incógnita empleadas en el práctico, incluyendo la prueba de alelismo. • Calcular la distancia genética de las mutaciones incógnita respecto a un locus conocido. Determinar la posición e identidad de la mutación estudiada. Clase 1 Introducción a la biología y genética de D. melanogaster. Observación del ciclo de vida y dimorfismo sexual. Identificación del fenotipo salvaje y de las mutaciones incógnita. Planteo de hipótesis para investigar el modo de herencia de las mutaciones. Materiales: Lupa, Lámpara, Tablilla, Paletita, Tubo anestesiador, Almohadilla Cepas: salvaje y cepas mutantes: m1, m2 y m3 Ciclo de vida: placas de petri con huevos. Tubos de cultivo con diferentes estadios de larva y pupa. D. melanogaster (Clase: Insecta; Orden: Diptera) es un insecto holometábolo, cuyo ciclo vital consta de cuatro estadios: huevo, larva, pupa y adulto (o imago) (Figura 1). Las hembras comienzan a depositar los huevos alrededor del tercer día de vida del imago y continúan hasta su muerte. A simple vista los huevos se ven como un objeto pequeño, blanco y oblongo, con un par de filamentos anteriores. El desarrollo del huevo comienza con la fecundación y consta principalmente de la formación de los tejidos larvales. Después de un día o dos, las larvas emergen de los huevos. Como la cutícula de los insectos no es elástica, la larva muda periódicamente. Existen tres estadios larvales, separados por las mudas correspondientes. Durante el tercer estadio larval, la larva se alimenta hasta estar pronta para pupar. Durante el estadio pupal ocurre la metamorfosis y a los 4 días emerge el adulto de la cubierta pupal. Las moscas se pueden cultivar en un medio compuesto por agar, levadura, harina de maíz, glucosa, un antimicótico y un bactericida. Este medio se dosifica en tubos o botellas de vidrio o plástico. En buenas condiciones de cultivo y a 25°C transcurren alrededor de 10 días desde la puesta de los huevos hasta la emergencia del imago. Si la temperatura permanece entre 22°C y 26°C, se producirá una nueva generación de moscas en aproximadamente 2 semanas, por ello el práctico se realiza cada 14 días. Los huevos son puestos en la superficie del alimento (o medio de cultivo). Cuando la larva 1 emerge del huevo, comienza a alimentarse e introducirse en el medio de cultivo. Las larvas en movimiento se detectan por el movimiento de las mandíbulas quitinosas de color oscuro. La larva 3 se mueve fuera del medio hacia un lugar seco donde se detiene a pupar. EL GENOMA de D. melanogaster D. melanogaster presenta un número cromosómico 2n=8. Los pares cromosómicos se numeran del I al IV, siendo el I el cromosoma X, y del II al IV los pares autosómicos. El par sexual en las hembras es XX y en el macho es XY. El cromosoma IV (o”dot”) es el más pequeño. El genoma de D. melanogaster ha sido completamente secuenciado. Mide alrededor de 165 millones de bases y se estima que contiene 14.000 genes. La posición de muchos genes a lo largo de los cromosomas ha sido identificada. Similitud con los humanos: a nivel genético, la gente y las moscas somos muy similares. Cerca del 61% de las enfermedades conocidas en los humanos tienen un reflejo reconocible en el genoma de las moscas y el 50% de las secuencia de proteínas de las moscas tienen un análogo en los mamíferos. Es por ello que Drosophila es utilizada como modelo genético en varias enfermedades de los humanos, incluyendo las enfermedades denominadas Parkinson y Huntington. NOMENCLATURA ¿Cómo designar el genotipo? Los nombres de los genes son designados en base a los alelos recesivos, los cuales se designan con letra minúscula y los alelos dominantes con letra mayúscula. La convención para escribir un genotipo es la siguiente: X/Y; 2nd/2nd; 3rd/3rd. La barra “/” se usa para : separar los cromosomas homólogos. El punto y coma “;” se usa para separar diferentes pares de cromosomas. El símbolo + es usado para describir el fenotipo tipo salvaje y los alelos que dan el fenotipo normal, y también al genoma entero o un gen en particular. Para designar el alelo salvaje (es decir el más frecuente) de un determinado gen, se utiliza este símbolo (como un superíndice). Si un individuo (o cepa) se designa solamente por símbolos mutantes, ej.: dp, ec, ey, se asume que es cepa pura, homocigota para los alelos mutantes que porta. Si el individuo (o cepa) es heterocigota para uno o más genes, el genotipo puede describirse así: Genes ubicados en el mismo cromosoma: dp + bwV _______________ o así: dp + bwV/+ cn + + cn + También es válido: dp cn+ bwV/dp+ cn bwV+ Actividad 1. Observación del ciclo de vida Se le proporcionarán tubos de cultivo con los estadios larvales, pupas, y placas de Petri con huevos. Actividad 2. Anestesiado de las moscas Proceda de la siguiente manera: 1) Transfiera las moscas de cepa salvaje a un tubo anestesiador, tape el mismo con un tapón de polifom y dosifique vapores de trietilamina dentro de dicho tubo por el orificio del tapón. 2) Una vez que todas las moscas estén inmovilizadas, deposítelas sobre una tablilla. Las moscas permanecerán anestesiadas por 45 minutos. La exposición prolongada a la trietilamina puede matar a las moscas, presentándose con alas y patas extendidas en ángulo recto al cuerpo y con ojos oscurecidos y deformados. En tal caso descarte las moscas muertas. 3) Observe los caracteres de la mosca salvaje. Ajuste la lupa al MENOR aumento y haga foco. Si es necesario, observe a mayor aumento. No coloque la luz muy cerca de las moscas, o el calor excesivo las deshidratará y acabará matándolas. Actividad 3. Identificación de los sexos (Figuras 2 y 3) 1. Tamaño del adulto. La hembra es generalmente más grande que el macho. 2. Forma del abdomen. El abdomen de la hembra se curva y termina en punta; el abdomen del macho es redondeado y más corto. 3. Marcas en el abdomen. Bandas claras y oscuras se alternan en la porción posterior de la hembra; mientras que en el macho están fusionadas y forman una banda oscura. 4. Presencia de peine sexual. En los machos existe un pequeño penacho de setas en el segmento basal del tarso en el primer par de patas llamado “peine sexual”. Este es el único carácter sexual secundario que diferencia los machos jóvenes de las hembras. 5. Genitalia externa. La genitalia es un carácter sexual primario. En las hembras se encuentra el ovipositor en la punta del abdomen, mientras que en el macho existen ganchos pigmentados, ordenados en forma circular y localizados en el extremo caudal. Actividad 4. Observación de los mutantes Recibirá tres cepas, cada una con una mutación diferente que afecta solamente un carácter. Determine el fenotipo mutante comparándolo con el fenotipo salvaje. Describa el fenotipo de cada mutación incógnita y el número correspondiente en sus apuntes, designe un “nombre” que sea representativo del carácter mutante, si lo desea. Actividad 5 (domiciliaria). Planteo de hipótesis Diseñe los cruzamientos y plantee los resultados esperados que le permitan determinar: a) el modo de herencia de cada mutación incógnita (tres en total) (autosómica vs ligada al sexo). b) la naturaleza del alelo mutante (recesivo vs dominante respecto al salvaje). Los cruzamientos e hipótesis serán puestos en común y discutidos en la Clase 2. Clase 2 Discusión de las hipótesis planteadas con los estudiantes. Realización de los cruzamientos. Materiales: Lupas,etc. Tubos con medio de cultivo para los cruzamientos. Cepas de las mutaciones m1, m2 y m3 y de la cepa salvaje Vírgenes de la(s) cepa(s).... Actividad 1. Discusión de las hipótesis. Propuesta de cruzamientos y discusión de los resultados esperados Los estudiantes integrantes de cada grupo llevarán a cabo en forma conjunta todas las actividades del práctico de Drosophila. Deberán elaborar hipótesis de los cruzamientos indicados para investigar la naturaleza y herencia de las mutaciones. Dicho planteo será discutido con el docente. Describa los cruzamientos propuestos en sus notas. Actividad 2. Realización de cruzamientos. Metodología utilizada a lo largo del práctico . En cada cruzamiento utilice alrededor de 10-12 hembras vírgenes y de 5 a 8 machos. El docente le proveerá de las hembras vírgenes. Ud. deberá seleccionar los machos, previa anestesia de la cepa correspondiente. Previo a la realización del cruzamiento confirme con el docente el sexo y fenotipo de las moscas seleccionadas. Coloque los tubos con las moscas anestesiadas en forma horizontal. Señale en cada tubo el TIPO DE CRUZAMIENTO (genotipos de machos y de hembras), el NÚMERO DE LA MUTACIÓN, la FECHA y el NOMBRE DE SU GRUPO para luego identificar los tubos en la próxima clase. Actividad 3 (domiciliaria). Planteo de los resultados esperados Plantee los resultados esperados de cada cruzamiento según cada hipótesis. Plantee los genotipos y fenotipos esperados. Si lo desea, puede utilizar la tabla que se ejemplifica a continuación: Tabla de los fenotipos esperados de cada cruzamiento (complete las proporciones esperadas en cada cuadrado) Hipótesis # .: Cruzamiento: [m] [+] ♀♀ ♂♂ Utilice una Tabla similar para indicar el número de individuos observados (progenie) de cada cruzamiento que realice en el práctico. Indique también el porcentaje o fracción en cada clase fenotípica y los totales. Clase 3 Análisis de la progenie F1. Planteo de hipótesis para determinar el grupo de ligamiento de las mutaciones, introducción al empleo de los “cromosomas balanceadores”. Test de alelismo. Materiales: Lupas,etc. Cruzamientos realizados en clase anterior. Cepas balanceadoras: Cy/bwv, y Ly Sb/In(3)LVM Actividad 1. Análisis de la progenie Observe la progenie (F1) de cada cruzamiento realizado en la clase anterior. Trabaje de forma ordenada, analice un tubo por vez. Describa los resultados obtenidos en tablas. Compare los datos obtenidos con los esperados según cada hipótesis. ¿A qué conclusiones ha llegado? Consulte con el docente sus resultados y conclusiones. Actividad 2. Planteo de nuevas hipótesis para la determinación del grupo de ligamiento de las mutaciones autosómicas. Empleo de cromosomas balanceadores. Si alguna de las mutaciones presenta herencia autosómica deberá investigar a qué cromosoma está ligada (consideraremos sólo los cromosoma 2 ó 3). Para determinar el grupo de ligamiento, se utilizarán cepas que portan cromosomas balanceadores. Ello permitirá determinar, mediante cruzamientos, si su mutación se segrega o no de forma independiente del cromosoma balanceador. ¿Qué son los “cromosomas balanceadores”? H J Müller (1918) inventó la idea de los balanceadores cuando primero identificó al cromosoma ClB por su propiedad como supresor de entrecruzamiento en el X y lo utilizó para aislar nuevas mutaciones letales ligadas a dicho cromosoma. Desde entonces, se han elaborado otros cromosomas conteniendo múltiples inversiones que también tienen la propiedad de inhibir la ocurrencia de entrecruzamiento con su cromosoma homólogo. Cuando estos cromosomas llevan además mutaciones dominantes (y recesivas) se vuelven una herramienta muy útil para el análisis de la segregación y la síntesis de genotipos deseados. Las condiciones que hacen a un cromosoma balanceador son: • Portar inversiones (múltiples) del tipo paracéntricas y pericéntricas, las cuales suprimen el intercambio genético en individuos heterocigotas para dichos reordenamientos cromosómicos (Ver esquema) • Portar mutaciones dominantes que sirven para “marcar” fenotípicamente la presencia de dicho cromosoma (en la progenie) • Tienen la habilidad, en condición heterocigota, de poder determinar los genotipos (invisibles) y los gametos esperados con una seguridad del 100%. • Estos cromosomas (y las cepas que los portan) se denominan “balanceadores” pues se mantienen en cultivo en condición heterocigota y segregan solamente gametos no recombinantes. • Existen cromosomas balanceadores para el cromosoma X (denominados F por “First”), el 2 (S por “Second”) y el 3 (T por “Third). Consecuencia genética de las inversiones heterocigotas sobre el crossingover Aunque las inversiones por sí mismas no tienen efecto directo sobre el fenotipo, pueden tener consecuencias genéticas en individuos heterocigotas. En el siguiente esquema se muestra la ocurrencia de inversiones (paracéntricas y pericéntricas) en un individuo heterocigota, el apareamiento, la ocurrencia de crossingover y la segregación de gametos viables e inviables (que no son integrados en el gameto femenino) en la meiosis (ver esquema). Utilizaremos dos cepas balanceadoras: Balanceador del cromosoma 2: Cy/bwV (Curly sobre brown variegado): Porta el cromosoma balanceador “SM6” (cromosoma 2) caracterizado por la In(2LR)SM6, y las mutaciones al Cy dp cn sp. • In (2LR) = inversión pericéntrica que ocupa el brazo izquierdo y derecho del cromosoma 2. La inversión In(2LR) previene la recombinación entre los homólogos del cromosoma 2. • Cy (Curly) es una mutación dominante letal en homocigosis y los genes recesivos al dp cn sp =: aristaless (al), dumpy (dp), cinnabar y speck (sp). • El cromosoma SM6 está balanceado con un homólogo “bwv”, que porta la mutación brown variegated y un gen letal. Cy (2-6.1) (Curly; dominante) Alas curvadas hacia arriba. Rara vez se solapa con el fenotipo salvaje a 25 C pero sí si se cultiva a 19 C. Generalmente es letal en homocigotas, pero pueden emerger moscas homocigotas enanas mostrando el carácter de las alas de forma más extrema. La mutación está asociada con una inversión en el segundo cromosoma de la cual no se puede separar. bwV (2-104.5) (Brown-Variegated; dominante). El hecho de que el símbolo bw esté en minúscula es una excepción. Color de ojos al emerger marrón borra de vino claro, se oscurece a granate, es manchado con máculas más oscuras que profundizan su color con la edad. Letal en homocigotas, fértil en heterocigotas. Asociado a una inversión en el segundo cromosoma. Balanceador del cromosoma 3: Ly Sb/In(3)LVM (Lyra Stubble sobre la inversión 3 LVM): Cepa que porta las mutaciones Ly (Lyra) y Sb (Stuble) en el (mismo) cromosoma 3, y la In(3)LVM en el cromosoma homólogo. Sb, como In(3)LVM, son letales en homocigosis, por lo que esta cepa está balanceada. La inversión In(3)LVM previene la recombinación entre los homólogos del cromosoma 3. Ly (3-40.5) (Lyra; dominante) Márgenes laterales de las alas recortadas de tal manera que resultan con una forma angosta; ángulo entre las venas L2 y L5 reducido. Las setas son cortas y retaconas, las postescutelares faltan a menudo. Ojos algo deformados con salientes. El abdomen oscuro y angosto con los bordes de los tergitos posteriores levantados. Sb (3-58.2) (Stubble; dominante) Las setas del heterocigota (Sb/+) tienen menos de 1/2 de la longitud normal y son algo más gruesas que el tipo salvaje. Homocigotas letales. In(3)LVM: cromosoma balanceador, porta una inversión. Posee dos mutaciones que son recesivas letales en la región invertida. Actividad 3. Observación de cepas balanceadoras Observe el fenotipo de cada cepa para luego reconocer las marcas (mutaciones) en la progenie de los cruzamientos que Ud realice. Clase 4 Discusión de las hipótesis planteadas para determinar: (a) El grupo de ligamiento de las mutaciones autosómicas. (b) El posible alelismo. Materiales: Lupas,etc. Tubos con medio de cultivo para realizar cruzamientos. Cepas de las mutaciones m1, m2 y m3 Cepas balanceadoras: Cy/bwv, y Ly Sb/In(3)LVM Vírgenes de la(s) cepa(s).... Actividad 1. Ligamiento autosómico. Discusión de hipótesis Discuta con su grupo la serie de cruzamientos y generaciones necesarias para determinar si la/s mutacion/es están ligadas al cromosoma 2 o al cromosoma 3. Elabore los cruzamientos y fenotipos esperados según cada hipótesis. Elabore con su grupo el planteo de cruzamientos necesarios a fin de poner en común con el docente previo a la puesta en práctica de los mismos. Actividad 2. Ligamiento autosómico. Realización de cruzamientos Describa los cruzamientos propuestos en sus notas. Confirme con el docente el sexo y el fenotipo de las moscas seleccionadas. Utilice la misma metodología realizada a lo largo del práctico de Drosophila. Actividad 3. Test de alelismo. Realización de cruzamientos Plantee en el grupo las siguientes preguntas: ¿En qué consiste el Test de Alelismo? En base a los resultados obtenidos en la clase anterior, ¿qué cruzamientos debería realizar para determinar si dos mutaciones pertenecen (o no) a la serie alélica de un mismo gen? El docente le brindará hembras vírgenes y Ud deberá seleccionar los machos. Utilice la misma metodología realizada a lo largo del práctico de Drosophila. Describa todos los cruzamientos realizados en esta clase y las Tablas fenotípicas que espera llenar en la próxima clase. Clase 5 Continuación de los cruzamientos realizados en la clase anterior. (a) Análisis de ligamiento. Análisis de la progenie F1 y segundo cruzamiento. (b) Test de alelismo. Análisis de la progenie F1. Discusión de los resultados observados. Materiales: Lupas,etc. Cruzamientos realizdos en la clase anterior. Tubos con medio de cultivo para realizar nuevos cruzamientos. Vírgenes de la(s) cepa(s).... Actividad 1. Ligamiento cromosómico. Observación de la progenie F1. Realización de cruzamientos. Observe la progenie F1 de los cruzamientos realizados en la clase anterior. Analice un tubo por vez. Cuente los machos y las hembras, anote el fenotipo y la frecuencia de cada tipo en la Tabla correspondiente. Trabaje de forma ordenada. No tire las moscas de la progenie hasta que realice nuevos cruzamientos que le permitan determinar el grupo de ligamiento de su mutación. El docente le brindará hembras vírgenes y Ud deberá seleccionar los machos. Siga la metodología utilizada hasta ahora. Describa TODOS los cruzamientos realizados en esta clase y las Tablas fenotípicas que espera llenar en la próxima clase. Actividad 2. Test de alelismo. Observación de la progenie y discusión de los resultados. ¿Qué evidencias tiene para rechazar o confirmar si las mutantes seleccionadas son alelos de un mismo gen? Clase 6 Análisis de la progenie F2 y determinación del grupo de ligamiento. Planteo de hipótesis para la determinación de las distancias génicas en el mapa genético. Discusión de los cruzamientos genéticos para realizar el análisis de las frecuencias de recombinación. Materiales: Lupas,etc. Cruzamientos realizados en la clase anterior. Actividad 1. Ligamiento cromosómico. Observación de la progenie F2 y discusión de los resultados. Observe la progenie F2 de los cruzamientos realizados en la clase anterior. Analice un tubo por vez. Describa los resultados obtenidos en Tablas. Cuente los machos y las hembras, anote el fenotipo y la frecuencia de cada tipo en la Tabla correspondiente. Trabaje de forma ordenada. Contraste los resultados obtenidos con los esperados según cada hipótesis. ¿Qué evidencias tiene que apoyen o no que la/s mutación/es están ligadas a determinado cromosoma? ¿y qué evidencias tiene que excluyan su ubicación en un determinado cromosoma? Actividad 2. Análisis de las frecuencia de recombinación. Observación de cepas mutantes (marcadoras). Para genes ligados al cromosoma X, utilizaremos la mutación cv ( crossveinless). Para genes ubicados en los autosomas (cromosomas 2 ó 3) utilizaremos una de las mutaciones dominantes empleadas anteriormente (en el análisis de ligamiento). cv (X-13.7) (crossveinless; recesivo) Ausencia de la vena transversal del ala presente en moscas salvajes entre las venas longitudinales 4 y 5 (Fig. 3). Actividad 3. Análisis de las frecuencia de recombinación. Planificación de cruzamientos. ¿Qué fenómenos genéticos le permiten determinar la distancia entre dos genes ligados ? Discuta con su grupo el o los cruzamiento(s) necesarios para determinar la distancia entre dos genes. Se le proporcionará, como marcador, un gen conocido (ver actividad 2) ¿Qué condiciones genéticas son necesarias para observar crossing over? ¿Cuántas generaciones lleva dicho análisis? Elabore la Tabla fenotípica (y genotípica) de resultados esperados de los cruzamientos planteados. Clase 7 Análisis de la progenie (proporcionada por los docentes) y análisis de la frecuencia de recombinación. Cálculo de las distancias génicas y discusión de los resultados. Materiales: Lupas, etc. Cruzamientos realizados para análisis de la frecuencia de recombinación. Actividad 1. Análisis de la progenie Si la mutación está ligada a un autosoma, cuente los machos y las hembras; si está en el cromosoma X cuente sólo los machos de la progenie. ¿A qué se debe esta distinción? Determine el número de moscas de cada fenotipo. Anote el número de individuos de cada fenotipo en una Tabla. Para facilitar este trabajo, separe las moscas por la presencia vs ausencia del FENOTIPO (mutante) MÁS FACIL DE RECONOCER. Cuente y clasifique la mayor cantidad de progenie posible a fin de obtener resultados más confiables. Describa los resultados obtenidos en Tablas. Actividad 2. Cálculo de las distancias génicas entre loci utilizados y puesta en común de los resultados obtenidos. Uso del mapa genético de la especie. Calcule la distancia genética entre el marcador de posición conocida y cada mutación incógnita. ¿Para qué es importante este dato? De acuerdo con sus resultados determine en el mapa genético qué gen candidato podría identificar como su mutación incógnita (Figura 4). Discuta la propuesta con el docente. Se evaluarán los datos de los otros grupos en conjunto. Figura 4. Mapa genético de D. melanogaster VARIACIONES CROMOSÓMICAS Introducción Como regla general la constitución cromosómica de los individuos de una especie es constante en cuanto a la morfología y número de los cromosomas. Sin embargo, pueden producirse variaciones cromosómicas espontáneas o inducidas que afectan a su estructura u ordenación lineal de genes (variaciones cromosómicas estructurales) o al número cromosómico (variaciones cromosómicas númericas). Los cambios cromosómicos constituyen un importante mecanismo en la evolución de las especies. Sin embargo, en la mayor parte de los casos su aparición provoca severas repercusiones fenotípicas en el organismo o en su descendencia. Es por este motivo algunos autores las denominan aberraciones cromosómicas. Las variaciones cromosómicas observables al microscopio óptico son el producto final de una larga cadena de acontecimientos. Las lesiones primarias ocurren a nivel molecular y se localizan en el ADN nuclear. Se requieren una serie de procesos celulares activos para convertirlas en cambios que continúen presentes en las células descendientes de aquellas que recibieron el daño inicial. Las variaciones pueden ser espontáneas o inducidas por diferentes agentes, que pueden ser de carácter físico o químico, ya sea enzimático o no, a los cuales se denomina agentes clastogénicos. Los tipos más comunes de agentes clastogénicos son las radiaciones ionizantes y la radiación ultravioleta, las endonucleasas de restricción, los agentes químicos antitopoisomerasa I y II, que interactuán con dichas enzimas evitando que actúen durante la reparación del ADN, y los agentes alquilantes. Reordenamientos cromosómicos estructurales Las variaciones cromosómicas estructurales generalmente provocan una reestructura de uno o más de los cromosomas del complemento, y pueden implicar pérdida de material genético. Los tipos más comunes de alteraciones estructurales son: duplicaciones, deleciones, inversiones, translocaciones recíprocas, y fusiones/fisiones robertsonianas. Reordenamientos cromosómicos numéricos Las variaciones numéricas son aquellas que no afectan la estructura de los cromosomas ni el ordenamiento de los genes, pero hacen que el número cromosómico de la célula que los porta difiera del número cromosómico normal de la especie. Existen dos tipos de variaciones numéricas: la EUPLOIDÍA, en que hay cambios en el número de juegos completos de cromosomas, y la ANEUPLOIDÍA, en que solo varía el número de uno o alguno de los cromosomas del complemento. Las aneuploidías se generan por no disyunción en meiosis, proceso por el cual se gana o pierde un cromosoma (por ejemplo en la trisomía 21 que provoca el síndrome de Down y el sindrome de Turner en el que se pierde un cromosoma X). Las euploidías más comunes son las poliploidías, en que las células portan más de dos juegos haploides de cromosomas. Aunque se conocen algunos poliploides animales, este fenómeno es mucho más común en plantas. Esto se debe a que los animales suelen tener mecanismos cromosómicos de determinación del sexo, y a que las plantas se pueden reproducir vegetativamente (con lo que se reducen los riesgos de una incorrecta segregación durante la meiosis). Existen dos tipos de poliploidía: la autopoliploidía, en que todos los cromosomas provienen de la misma especie, y la alopoliploidía, que se origina con la fecundación entre dos especies diferentes. Objetivos: Reconocer distintos tipos de variaciones cromosómicas estructurales (reordenamientos), proponer métodos de análisis para conocer su origen y plantear las posibles consecuencias en la meiosis. 1- Mencione y explique brevemente las técnicas citogenéticas que utilizaría para diagnosticar cada uno de los siguientes reordenamientos cromosómicos: a. Deleción b. Duplicación c. Inversión d. Translocación recíproca 2- Dos especies de mamíferos cercanamente emparentadas tienen cariotipos idénticos, excepto por una diferencia en el número cromosómico. La especie A tiene un par menos que la B. Los cromosomas que difieren entre una especie y otra se muestran a continuación. ¿Qué tipo de reordenamiento ha ocurrido durante el proceso de divergencia de estas especies? Especie A Especie B 3- A continuación se muestra una representación de dos cromosomas homólogos. Uno de ellos ha sufrido un proceso de inversión. a- Realice un esquema del apareamiento entre estos cromosomas durante el paquiteno. b- Suponga que ocurre recombinación entre estos dos cromosomas en la región comprendida entre los genes b y d. Esquematice los cromosomas resultantes que serán portados por los gametos de este individuo. c- Discuta las implicancias evolutivas de esta transformación para la especie que la porta. 4- A continuación se presenta un cariotipo humano. a- ¿Qué técnica se utilizó para teñir estos cromosomas? b- ¿Qué alteraciones presenta este cariotipo? Fundamente su respuesta. 5La leucemia crónica mielogénica (CML) está asociada en un 90% de los casos con una translocación recíproca entre el cromosoma 9 y el 22, como se explica en la figura adjunta. Los puntos de rotura de los cromosomas están ubicados en la Región del Cluster de Rotura (BCR) en el cromosoma 22, y el gen Abl en el cromosoma 9. A continuación se muestra una metafase de una célula normal y una metafase de un individuo con CML, y varias células en interfase. Para obtenerlas se realizó la técnica de FISH, en la cual una sonda marcada con un fluorocromo rojo marca el gen abl y otra sonda marcada con fluorocromo verde marca el cluster BCR. a- ¿Cuál de las metafases - A o B- corresponde al individuo normal y cuál al enfermo? b- ¿A qué genotipo corresponde la imagen de interfase? c- Fundamente su respuesta explicando las características de la técnica utilizada que le permitieron llegar a esa conclusión. Metafase A Metafase B Interfases GENÉTICA DE POBLACIONES: RELEVAMIENTO DE RASGOS GENÉTICOS EN POBLACIONES HUMANAS Ciertos rasgos genéticos, apreciables a simple vista, pueden ser analizados como si estuvieran determinados por un solo gen que presenta dos formas alternativas. Veamos en detalle algunos de estos rasgos: 1. Lengua enrollada o no: Algunas personas pueden enrollar la lengua formando una U mientras que otras no pueden hacerlo. 2. Entrecruzamiento de los dedos de ambas manos: al entrecruzar los dedos, puede quedar arriba el pulgar izquierdo o el derecho. 3. Presencia o ausencia de hoyuelo en la barbilla. 4. Lóbulo de la oreja suelto o adherido. Pueden verse las figuras de estos rasgos en la última página. Proponemos realizar dos actividades que contribuirán al conocimiento de la genética en el marco del curso: 1) Realizar un relevamiento para los rasgos antes expuestos dentro de la familia y construir una genealogía a partir de los fenotipos. Recuerda la nomenclatura utilizada en genealogías. Extrae conclusiones acerca de la forma de herencia de dichos caracteres: para cada caso encuentra la relación de dominancia entre los dos alelos existentes. Intenta asignar genotipos hasta donde sea posible en la genealogía. GENEALOGÍA: 2) Realizar un relevamiento poblacional de uno de los rasgos antes expuestos (número mínimo de la muestra: 20). Una vez relevados los datos, en clase trabajaremos para obtener las frecuencias génicas y genotípicas para dicho rasgo asumiendo que la población se encuentra en equilibrio. A partir de sus resultados ¿cuántas personas posiblemente sean heterocigotas en la muestra? DESCRIPCIÓN FENOTIPO: FENOTIPOS [ ] NUMEROS FRECUENCIAS GÉNICAS Y GENOTÍPICAS: [ ] 1) Capacidad de enrollar la lengua en U 2) Entrecruzamiento de los dedos de ambas manos 1) Barbilla con hoyuelo 2) Lóbulo suelto (A) o adherido (B) GENÉTICA DE POBLACIONES: MARCADORES MOLECULARES Y EQUILIBRIO HARDY-WEINBERG MARCADORES MOLECULARES Y FACTORES DE MICROEVOLUCIÓN Tanto la genética clásica como la genética molecular ofrecen en la actualidad una diversidad de técnicas y aproximaciones para acceder al estudio de distintos procesos biológicos a nivel poblacional. Estas herramientas pueden ser utilizadas para la identificación de un individuo o para determinar su éxito reproductivo, permiten también la exclusión o asignación de paternidad, el análisis de la estructura poblacional a diferentes niveles o de las tasas de divergencia genética entre poblaciones. La técnica más apropiada para responder una pregunta concreta depende de: (1) el grado de polimorfismo genético requerido para contestar mejor la cuestión, (2) la disponibilidad de métodos analíticos o estadísticos para la aplicación de cada una de las técnicas y (3) cuestiones pragmáticas como tiempo y costo. Antes del desarrollo de las técnicas de electroforesis en la década del 50, los marcadores genéticos incluían rasgos mendelianos como el color de la flor o fruto de una planta. Es posible hacer estudios sobre genética de las poblaciones a partir del análisis de las frecuencias génicas y genotípicas en base a las características fenotípicas de los individuos que comprenden dichas poblaciones. MARCADORES FENOTÍPICOS PARA EL CÁLCULO DE FRECUENCIAS GÉNICAS Y GENOTÍPICAS 1) El color de cierto roedor se encuentra determinado por un único gen, siendo el color negro determinado por el genotipo AA, el gris por Aa y el blanco por aa. Una población de estos ratones presenta las siguientes frecuencias fenotípicas: color negro = 0.9, color blanco =0.09 y color gris = 0.01. a) ¿Cuáles son las frecuencias de los alelos A y a? b) ¿Cuáles son las frecuencias genotípicas esperadas con apareamiento al azar? 2) Una variación genética en el hombre (no deletérea) se manifiesta en los homocigotas recesivos. Los individuos heterocigotas presentan el fenotipo normal. En una población humana, 1 de cada 10.000 individuos presentan dicha variación. Una mujer fenotípicamente normal, que es hija de un individuo que presenta la variación, se casa con una persona fenotípicamente normal. ¿Cuál es la probabilidad de que su primer hijo presente la variación en cuestión?. 3) Un entomólogo realiza una amplia captura de mariposas y las clasifica por la coloración que viene determinada por la pareja alélica A,a. color negro (AA) Nº 400 color marrón (Aa) color amarillo (aa) 400 200 a) ¿Cuáles son las frecuencias génicas y genotípicas en esa población? b) ¿Está en equilibrio la población? 4) El condor de California presenta condrodisplasia, una condición que resulta en una malformación severa en los huesos largos que determina la muerte cerca del momento de eclosión. Esta condición se debe a la presencia en homocigosis de un alelo recesivo. De 169 huevos analizados en una población de esta especie, cinco exhibieron condrodisplasia. ¿Cuáles son las frecuencias génicas y genotípicas en esa población? MARCADORES MOLECULARES POLIMORFISMOS PARA EL RELEVAMIENTO DE A continuación vamos a hacer una breve descripción de las técnicas de genética molecular más utilizadas para el estudio de poblaciones: Métodos basados en aloenzimas La electroforesis de proteínas desarrollada en la década del 50, suministró una nueva fuente de marcadores genéticos, permitiendo identificar individuos homocigotas o heterocigotas para un locus dado. Las isoenzimas son distintas formas moleculares de una misma enzima que presentan o muestran especificidad por el mismo sustrato. El término “aloenzima” se refiere a diferentes formas alélicas de la codificación nuclear de una enzima. A partir de 1966 hubo una explosión de estudios de aloenzimas. Por más de cuarenta años se ha generado una rica y basta literatura donde se han utilizado las aloenzimas para contestar cuestiones de genética poblacional. La técnica se basa en la purificación de la enzima activa sin desnaturalizar, utilizando tampones específicos. Posteriormente la muestra es homogenizada y cargada en un gel (de almidón o poliacrilamida) y separadas por tamaño, forma y/o carga a lo largo de un gradiente eléctrico. Se utilizan tinciones histoquímicas específicas sobre el gel revelando así bandas coloreadas que determinan las posiciones de las diferentes aloenzimas. De tal modo que visualizando los fenogramas, es posible asignar los genotipos a cada individuo. Las aloenzimas se comportan como marcadores co-dominantes, en la medida en que alelos con diferentes movilidades electroforéticas pueden ser visualizados en el genotipo heterocigoto. Métodos basados en ADN Con el desarrollo de diversas técnicas moleculares, los biólogos de poblaciones tienen la opción de analizar la variación en las secuencias nucleotídicas. Las diferentes regiones del genoma experimentan distintas presiones de selección, dependiendo del producto genético y/o la tendencia del ADN a sufrir cambios en su secuencia nucleotídica. El segmento óptimo de ADN a utilizar en un estudio particular dependerá no solamente del grado de relacionamiento entre los individuos estudiados, sino también por el grado de selección impuesta en las distintas regiones del genoma. Técnicas básicas En primer lugar es necesario realizar la extracción de ADN. Existen distintas técnicas para obtener este material de distintos tipos y estados de tejidos. Es posible también aislar ADN de origen nuclear y de organelos. RFLPs (del inglés: Restriction Fragment Length Polymorphisms, polimorfismo en el largo de los fragmentos de restricción): Las enzimas de restricción cortan el ADN en una secuencia específica llamado sitio de reconocimiento. La exposición del material genético a enzimas de restricción genera fragmentos de ADN, éstos difieren en su tamaño cuando una mutación crea o elimina un sitio de restricción. La determinación de variaciones en el tamaño de los fragmentos es conocida como RFLPs. La digestión enzimática de una pequeña molécula como la de ADN mitocondrial genera un número de fragmentos de ADN suficientemente pequeño cuyo patrón de bandeo puede ser resuelto de manera consistente luego de correrlo en una electroforesis en gel de agarosa. Las frecuencias haplotípicas pueden ser cuantificadas por la presencia o ausencia de sitios de restricción entre los individuos (PLANCHA Nº1). El ADN nuclear digerido por enzimas de restricción genera un patrón en la electroforesis tipo “chorrete” (smear). En este caso pueden reconocerse fragmentos de interés particular luego de la electroforesis, por medio de hibridización con una sonda determinada. La presencia de la secuencia complementaria en el ADN molde a la sonda de ADN, es detectada mediante Southern blot y autorradiografía (PLANCHA Nº2 Y Nº3). 5) La siguiente figura muestra el diagrama de bandas con patrones de RFLPs (fragmentos de ADN homólogos que difieren en la ubicación de los sitios de restricción). Ésta fue generada por medio de una electroforesis del ADN, previamente expuesto a una enzima de restricción, e hibridización con una sonda de ADN. En la parte superior se indica el número de individuos presentando un mismo patrón de bandas. a) b) c) Realice un esquema del patrón de restricción y del sitio de unión de la sonda para ambos alelos Estime las frecuencias alélicas y coloque los genotipos correspondientes debajo de cada carril. ¿Se encuentra este “locus” en equilibrio Hardy-Weinberg? Reacción en Cadena de la Polimerasa (PCR): Esta técnica permite la amplificación de pequeños fragmentos de ADN. En la reacción de PCR se incluye el ADN molde, la enzima Taq polimerasa y buffer Mg 10 x así como la mezcla de los 4 nucleótidos (dNTP). La región blanco a amplificar debe estar flanqueada por regiones de secuencia conocida a la cual se unirán los cebadores. El producto obtenido por PCR puede ser visualizado en una electroforesis de agarosa y tinción con bromuro de etidio. PCR-RFLPs: Muchos estudios en poblaciones naturales se limitan a analizar los patrones de digestión con enzimas de restricción sobre una región específica de ADN, obtenida por medio de un PCR previo. De esta manera se pueden establecer distintos alelos en función de la presencia o ausencia de sitios de restricción (PLANCHA Nº4). 6) Para una población de camarones Peneaus paulensis de la costa Atlántica de América del sur se encontraron los siguientes patrones de bandas en un locus RFLP con la enzima HaeI. En una muestra poblacional se encontraron los siguientes patrones: a) b) c) Describa en cada caso los alelos encontrados, codifíquelos según su tamaño en pares de bases e indique la estructura genotípica de cada grupo de individuos Estime las frecuencias alélicas Calcule las frecuencias genotípicas esperadas en el equilibrio Hardy-Weinberg. Amplificación al azar de ADN polimórfico: Los RAPDs (de Random Amplified Polymorphic DNA) son marcadores producidos por PCR utilizando cebadores de secuencias al azar. Los patrones diferenciales surgen cuando una región del genoma varía en la presencia/ ausencia de sitios complementarios de unión con los cebadores. Los cebadores son típicamente de unas 10pb y no se necesita un conocimiento específico de la secuencia particular de ADN que se amplificará para elegir o producir un cebador. La variación genotípica consiste en la presencia o ausencia de productos particulares amplificados, que luego son separados por una corrida en gel de agarosa. En ese sentido es un marcador dominante ya que uno de los homocigotos no se distingue del heterocigoto. Esta técnica ha sufrido fuertes críticas ya que diversos autores consideran que sus resultados no son reproducibles, de manera que la naturaleza de la variación genética observable por esta técnica no es absolutamente clara y por tanto la inferencia a partir de sus resultados debe ser sumamente prudente. Esta técnica ha resultado muy útil en ausencia de informaciones genómicas previas referidas a genomas de especies silvestres. DNA Fingerprinting: El término (huella digital de ADN) se refiere a una serie de técnicas donde se analizan patrones de bandas generados por electroforésis sobre marcadores genéticos muy variables. El común denominador es que el patrón generado por el marcador elegido, presente un grado de variabilidad tal, que permita la identificación a nivel de individuo. Estas técnicas son de gran utilidad para determinación de paternidad, estudios forenses, asignación de muestras a un sospechoso, etc. Los patrones de bandas que conforman el fingerprinting pueden obtenerse por el análisis de un único locus o ser originado a partir de un estudio de varios loci simultáneamente. Si bien puede obtenerse un fingerprinting por medio de análisis de bandas de RFLPs y RAPDs, los más comúnmente utilizados son los que se basan en análisis de marcadores del tipo VNTRs, ya que se caracterizan por un elevado nivel de polimorfismo. Número variable de repetidos en tandem (VNTRs): Los satélites de ADN fueron identificados aproximadamente hacia 1969 existiendo dos tipos de secuencias satélites –microsatélites y minisatélites. Los microsatélites son también conocidos como secuencias repetidas simples (SSRs Simple Secuence Repeat) y están formados por unidades repetidas. Cada repetido tiene un largo de entre dos y seis pares de bases. Los minisatélites en cambio, son unidades repetidas que van desde diez a 100 pares de base de largo. Tanto los microsatélites como los minisatélites presentan un altísimo grado de polimorfismo, lo que los convierte en una muy buena herramienta para el análisis de poblaciones. a) Microsatélites de ADN: El análisis de microsatélites es extremadamente útil para el estudio de poblaciones ya que se puede analizar un locus simple con más de 10 alelos. Estos marcadores hipervariables se componen de repetidos en tandem de una unidad o “motivo” compuesto por entre 2 a 6 pb (ej. CA, CAAC, o GGAACC). Los loci de microsatélite son analizados por amplificación por PCR de una región blanco del ADN que contiene repetidos en tandem flanqueadas por secuencias en dónde se unen los cebadores diseñados a tales efectos. Los productos amplificados se visualizan en una electroforesis en gel de acrilamida. Este tipo de gel permite la resolución de los alelos ya que se pueden diferenciar fragmentos que difieren hasta tan sólo en dos pares de bases. Actualmente el tamaño de los microsatélites también puede ser determinado utilizando la misma infraestructura que la utilizada en la secuenciación automática. En este caso por ejemplo, puede emplearse uno de los cebadores en el PCR el que se encuentra marcado con un determinado fluorocromo. Durante la electroforesis en microcapilares, los fluorocromos emiten una señal lumínica (al pasar delante de una fuente de emisión de luz láser) que sirve para determinar el tamaño exacto del fragmento en relación con un marcador de peso molecular de referencia. (PLANCHA Nº5 Nº6 Nº7 y Nº8) b) Minisatélites: Los minisatélites de ADN se componen de unidades repetidas en tandem 10100 bp de largo, con una extensión total que típicamente va desde 0.5-50 kb. Los polimorfismos están dados tanto por variaciones en la cantidad de repetidos como por cambios en la secuencia del repetido. El genotipado del minisatélite se puede establecer de diferentes maneras: a) por medio de reacciones de PCR con cebadores universales que hibridizan con regiones externas al minisatélite y cebadores que se unen a variantes específicas dentro del minisatélite; b) por el reconocimiento de los minisatélites por medio de electroforesis y exposición a una sonda de ADN con la secuencia del minisatélite (que será detectada por hibridización en un Southern blot y autorradiografía). (PLANCHA Nº9). Polimorfismos de un nucléotido SNP: este tipo de polimorfismo se caracteriza por mutaciones puntuales en la secuencia de un fragmento particular de ADN. Por ejemplo, algunas moléculas presentan el par A-T en un sitio particular y otras moléculas en la misma población presentan el par C-G. Esta diferencia constituye un SNP. El 99 % del ADN humano no difiere entre poblaciones, en el 1% restante se encuentran gran cantidad de SNP. Se considera que esta variabilidad determina por ejemplo susceptibilidades a enfermedades y tienen por tanto una gran importancia en la investigación biomédica. Secuenciación: Incluso entre las poblaciones más homogéneas existen diferencias en la secuencia nucleotídica entre individuos. La secuenciación se ha vuelto un procedimiento de rutina con el desarrollo de los secuenciadores automáticos. En combinación con el PCR es posible acceder a datos precisos sobre cortas secuencias de ADN. La comparación de distintas secuencias dentro o entre poblaciones permite hacer inferencias sobre los procesos genéticos de las poblaciones (PLANCHA Nº10) TABLA1. Esquema simplificado de los patrones de bandeo para un locus (dos alelos) y los niveles de polimorfismo que pueden detectarse con los distintos tipos de marcadores genéticos. Pocillos de gel 2 3 Genotipo A1,A1 A1,A2 A2,A2 1 Aloenzima PCR-RFLP VNTR Micro o minisatélites de locus simple RAPDs (-/+ sitio de restricción) (-/+ sitio de unión con el cebador) Tomado de Parker PG, Snow AA, Schug MD, Booton GC & Fuerst PA (1998) What molecules can tell us about populations: choosing and using a molecular marker. Ecology 79(2), 361–382 Cambios en las frecuencias de equilibrio 7) En los ratones, el alelo recesivo e, produce esterilidad total en estado homocigota. En una población de ratones, la frecuencia de individuos estériles es igual a 1/10. ¿Cuál será la frecuencia de individuos estériles 10 generaciones después? 8) En una población de afroamericanos, el 91% son Rh positivos (locus autosómico: Rh dominante sobre rh). En otra población de orientales, el 100% son Rh positivos. A la población afroamericana llega un grupo de la población oriental constituyendo ahora el 10% de la población receptora. a) ¿Cuáles serán las frecuencias génicas en la F1? b) ¿Cuáles serán las frecuencias genotípicas de equilibrio? PRÁCTICO DE GENÉTICA DE POBLACIONES PROCESOS MICROEVOLUTIVOS EN Drosophila melanogaster Objetivo Interpretar los factores relacionados con la variación en frecuencias génicas y genotípicas en dos cepas de Drosophila melanogaster en cajas de cultivo. ACTIVIDADES A DESARROLLAR En este práctico se emplean moscas D. melanogaster de dos fenotipos distintos en el tamaño de las alas de la mosca y que están definidos por la existencia de dos alelos en un gen autosómico: Alas normales [+] y alas vestigiales [vg], este último constituye una mutación recesiva en este locus. Durante este práctico, cada mesa recibirá un tubo de moscas que han sido previamente cultivadas conteniendo ambos fenotipos. Se partió de cepas puras: 10 machos y 10 hembras vírgenes de cada fenotipo (generación parental) que se aparearon al azar. 1) Dados estos datos, calcular: a) las frecuencias génicas y genotípicas de la generación parental; b) las frecuencias génicas y genotípicas esperadas en la generación actual (F1). 2) Para contrastar las expectativas teóricas con los datos reales, se contabilizará la F1: a) Anestesiar las moscas. b) Contabilizar los individuos de cada fenotipo. c) Constatar si la población se encuentra en equilibrio de Hardy-Weinberg. d) Llenar la tabla 1 con los resultados del tubo contabilizado, más los tubos contabilizados por el resto del grupo. e) Calcular los parámetros de la tabla 1 (abajo). 3) Discutir: a) ¿Cuál es la diferencia entre las frecuencias fenotípicas observadas y las esperadas en cada tubo? b) ¿Cuál es la variación en frecuencias fenotípicas entre tubo y tubo? 4) Sobre la base de la discusión y lo concluido sobre el mecanismo evolutivo predominante en este experimento, conteste las siguientes preguntas: SELECCIÓN NATURAL a) Calcule la eficacia biológica relativa (W) de cada uno de los fenotipos, empleando la suma de los valores de los tubos. b) ¿Cuáles serán las frecuencias alélicas y genotípicas esperadas después de una generación de apareamiento al azar? DERIVA GÉNICA a) Calcule el desvío estándar de las frecuencias génicas entre la generación parental y la F1. b) En el caso que se mantuviera el tamaño poblacional, ¿en el correr de cuántas generaciones observaría la pérdida aleatoria de uno de los alelos? Tabla 1: Conteo de fenotipos de la F1 TUBO 1 2 3 4 Total Media Desv. estándar [+] (vg+ / vg+ y vg+ / vg) conteo proporción [vg] (vg / vg) conteo proporción Total FÓRMULAS ÚTILES: Media ( X ): Desvío estándar (s): n n ∑x X = ∑(x − X ) i 2 i i s= n i n Supervivencia Para cada fenotipo Frecuencia fenotípica observada en la F1/ Frecuencia fenotípica esperada en la F1 Eficacia biológica relativa (W) Supervivencia del fenotipo menos apto/Supervivencia del fenotipo más apto Varianza en las frecuencias de dos alelos por efecto de muestreo s 2 = pq 2N (Recuérdese que s = s 2 ) ACTUALIZACIÓN EN GENÉTICA DESARROLLO DE LA GENÉTICA MOLECULAR Y SU IMPACTO EN LA BIOTECNOLOGÍA La tecnología del ADN recombinante no sólo ha proporcionado información acerca de la estructura y función de los genes, sino que ha permitido desarrollar numerosas técnicas de análisis del genoma y su expresión. Las técnicas básicas que implican el uso de enzimas de restricción, ADN recombinante, Northern y Southern Blot, PCR y secuenciación han dado pie al desarrollo de una amplia batería de nuevas técnicas y procesos biotecnológicos. Paralelamente dispararon la capacidad de crear o modificar desde productos hasta organismos con novedades genéticas y amplió las posibilidades de diagnosticar y tratar enfermedades. Como ejemplos del impacto actual de estas tecnologías podemos citar el desarrollo de productos farmacéuticos, que tiene su precedente en 1979 cuando, con la utilización de tecnología de ADN recombinante, se sintetiza en el laboratorio la molécula de insulina. A partir de ese momento gran número de fármacos son desarrollados de este modo. La creación de organismos genéticamente modificados (OGM) o transgénicos ha tenido un impacto enorme en la economía y la sociedad. En el diagnóstico médico, la identificación y clonación de muchos genes permite detectar mutaciones causantes de enfermedades. Se logra así el diagnóstico pre‐sintomático, consejo genético y diagnóstico temprano de enfermedades. Finalmente podríamos citar la terapia génica, que implica la transferencia directa de genes para tratar enfermedades. En este práctico nos proponemos discutir someramente dos ejemplos: I) El uso de una herramienta con múltiples aplicaciones: los microarreglos (microarrays) de ADN. II) La utilización de tecnología de ADN recombinante para la producción de organismos genéticamente modificados (OGM). I) MICROARREGLOS DE ADN Los microarreglos de ADN son un soporte sólido que puede ser una lámina de vidrio, plástico o silicio en el cual se fijan en localizaciones precisas secuencias correspondientes a miles de genes diferentes. Estas secuencias pueden ser ADN, ADNc u oligonucleótidos. Estos últimos son fragmentos cortos de ADN de simple cadena de de 5 a 50 nucleótidos. La técnica consiste en la hibridización de este microarreglo con una muestra de ADN genómico o ADNc (que incorpora algún precursor luminiscente que permitirá su detección). La hibridación de la muestra estudiada es detectada por la presencia e intensidad de esta señal luminscente y cuantificada para determinar la abundancia relativa de un ARN mensajero o una variante del genoma en la muestra. Dos de los usos fundamentales de la tecnología de microarreglos de ADN son el estudio de perfiles de expresión génica y el genotipado por polimorfismos de base simple (Single Nucleotide Polymorphisms o SNPs) en el genoma completo de un individuo. I.A. El uso de microarreglos en el análisis de expresión génica Prácticamente todas las células de nuestro cuerpo contienen los mismos genes, pero no todos los genes se expresan ni lo hacen al mismo nivel en todas las células. La expresión génica diferencial está en la base de la identidad y especialización celular. Por ejemplo, las células del páncreas expresan genes relacionados con la síntesis de insulina, mientras que las neuronas expresan genes relacionados con la neurotransmisión. Los investigadores estudian la expresión génica para entender las funciones celulares y se interesan por los cambios que ocurren en dicha expresión en respuesta a una variedad de situaciones: durante el desarrollo y la diferenciación, en respuesta a estímulos concretos, en enfermedades, etc. La técnica de microarreglos de ADN permite evaluar la cantidad relativa de transcripción de los genes de un genoma en un único experimento. No permite cuantificar niveles absolutos de expresión génica, medida por ejemplo en cantidad de moléculas de ARNm producidas por célula, sino que los microarreglos de ADN permiten determinar cuánto ARNm se produce en una muestra problema en relación a la cantidad producida en otra muestra o en una muestra control. Podemos entonces comparar los ARNm sintetizados a partir de un tejido de cáncer de pulmón con respecto a los sintetizados por tejido de pulmón sano, para poder determinar si hay incremento (inducción) o disminución (represión) de la expresión génica y cuantificar esos cambios con respecto al tejido sano. Las cantidades relativas de ARNm producido por un gen particular en dos muestras, pueden expresarse como una relación o ratio que indica las diferencias en los niveles de transcripción. La tecnología de microarreglos aplicada a la expresión génica ha sido utilizada para abordar numerosos aspectos tanto del crecimiento como del desarrollo y también se ha empleado para tratar de comprender las causas genéticas de muchas enfermedades humanas. En el caso de cáncer, ha permitido categorizar los distintos tipos para alcanzar el mejor tratamiento. La metodología asociada a microarreglos de ADN requiere de varias etapas. 1. Se colocan moléculas de ADN que representan cada gen del genoma en un “spot” de un portaobjeto de vidrio o de una membrana: éste constituye el microarreglo. El microarreglo puede construirse con oligonucleótidos por ej. de 50 nucleótidos cada uno representando a un único gen. Cada “spot” conteniendo únicamente uno de estos ADN, tiene aproximadamente 100 micras de diámetro. Un conjunto de éstos son ordenados en un patrón regular. De esa manera se conoce la posición que ocupa en la matriz (portaobjeto o membrana) cada gen. La localización precisa de cada gen analizado en el microarreglo o chip es registrada por una computadora. A modo de ejemplo, un microarreglo que contenga ADNs que representen todos los genes del genoma humano (aproximadamente 25.000) constaría de 25.000 spots. 2. Se aísla el total de los ARNm de las muestras a analizar. 3. Se sintetiza el ADNc usando como molde los ARNm aislados en presencia de precursores (dNTPs) marcados con un colorante fluorescente. Se emplea un fluoróforo diferente para cada muestra (por ej. verde y rojo). 4. Se incuba el portaobjeto conteniendo el microarreglo con los ADNc marcados fluorescentemente. Aquellos ADNc que encuentran moléculas de ADN complementarias en el chip hibridizarán. Supongamos que las dos muestras de ADNc marcados corresponden a: tejido normal (rojo) y tejido canceroso (verde). Estas dos muestras las utilizamos para hibridizar un microarreglo de ADN genómico humano. Si un gen del microarreglo se expresa en tejido normal, el “spot” correspondiente a dicho gen se “teñirá” o emitirá en rojo. Si se expresa en tejido canceroso, emitirá en verde. En el caso de que este gen se encuentre expresado a iguales niveles en ambos tipos de tejidos, ambos ADNc podrán hibridizar con el spot y en este caso el “spot” emitirá en ambos colores (amarillo). Si dicho está siendo expresado en ambos tejidos pero a diferentes niveles encontraremos que el spot correspondiente presenta un color intermedio entre el verde y el rojo. 5. Por último, se analizan los datos cuantificando ambas emisiones para determinar cuáles genes se expresan en cada muestra y se obtienen valores relativos o “ratios”. La pregunta Para emprender un experimento de hibridización de microarreglos de ADN, debemos formular claramente la pregunta que queremos contestar mediante esta tecnología, por ejemplo: ¿Cómo cambia la expresión génica cuando las células son irradiadas con luz ultravioleta o expuestas a un compuesto químico tóxico? ¿Qué sucede con la actividad de varios genes de levaduras cuando éstas pasan a cultivarse de 30ºC a 42ºC? ¿Qué genes son expresados únicamente en un embrión de pez? ¿Qué genes presentan una actividad diferente en células de cáncer cuando son comparadas con células sanas? Ejercicio 1 Un investigador está interesado en estudiar los efectos de altos niveles de ozono sobre la soja. Cultiva entonces un grupo de plantas en condiciones de aire normal y otro grupo en presencia de altos niveles de ozono. Realiza el marcaje del ADNc de la soja crecida en ozono con un fluoróforo rojo y la crecida en condiciones normales con un fluoróforo verde. Los resultados obtenidos para seis genes del microarreglo son los siguientes: ¿Qué genes no muestran diferencias de expresión entre ambas condiciones de crecimiento? ¿Qué genes se elegirían para continuar estos estudios? Explique. Ejercicio 2 Coloque en orden las siguientes etapas de la tecnología de microarreglos aplicada al ejemplo previamente analizado: ___ ___ ___ ___ ___ ___ ___ 1. Analizar los resultados comparando los colores de los spots del microarreglo 2. Identificar genes que están expresados o reprimidos en condiciones de altos niveles de ozono. 3. Aislar ARNm de cultivos de soja crecida en condiciones normales y en altos niveles de ozono. 4. Depositar secuencias génicas de soja en el portaobjeto de vidrio 5. Sintetizar ADNc marcado fluorescentemente por transcripción reversa. 6. Crecer soja en condiciones atmosféricas normales y con altos niveles de ozono durante un mes 7. Hibridizar ADNc a secuencias génicas complementarias en el portaobjeto de vidrio. Ejercicio 3 Se dispone de un chip conteniendo ADNs que representan los genes del genoma humano. Se han extraído muestras de ARN de 5 pacientes con cáncer, las cuales se emplean para hibridizar el microarreglo. Aquí se muestra el resultado obtenido para 10 genes: En negro se representan los spots donde hubo hibridización y en blanco aquellos donde no hubo hibridización. ¿Cuáles genes se expresan siempre? ¿Cuál podría ser su función? ¿Cómo podría estudiarlos? ¿Cuáles genes nunca se expresan? ¿Cómo podría explicarlo? ¿Cuál podría ser su función? ¿De los 10 genes estudiados cuáles podrían potencialmente tener una función directa en el cáncer? ¿Cómo los estudiaría? ¿Qué similitudes ve entre pacientes? Construya una nueva tabla agrupando los genes según su patrón de expresión en los distintos pacientes. En base a los resultados obtenidos ¿Cuál puede ser la función del gen 4 en relación al cáncer? ¿Y la del gen 9? ¿Son relevantes los patrones de expresión de los genes 3, 5 y 10? ¿Qué información nueva le aportaría este análisis si incluyera los resultados de hibridización de estos 10 genes con ADNc proveniente de personas sanas? I B – El uso de microarreglos en genotipado – El uso de microarreglos en la determinación de polimorfismos de nucleótido simple (SNPs) Para caracterizar a un individuo o a numerosos individuos de una población, los estudios genéticos determinan su genotipo para distintos loci. Tradicionalmente se utilizaron loci tales como grupos sanguíneos, antígenos de histocompatibilidad, etc. El desarrollo de los denominados “marcadores moleculares”, permitió de forma relativamente rápida determinar el genotipo de individuos de forma precisa y masiva. En el laboratorio, el genotipado tradicional puede limitarse en el mejor de los casos a unos cientos de marcadores, con lo cual se tiene una cobertura de resolución relativamente baja del genoma completo. Un tipo de estos marcadores son los polimorfismos de nucleótido simple (SNPs), de los cuales hay aproximadamente 10 millones en el genoma humano. La presencia de uno u otro alelo para un SNP puede rastrearse por digestión diferencial con una enzima de restricción, o por PCR. Sin embargo, el genotipado empleando microarreglos permite un aumento en la resolución, valiéndose de SNPs, y analizando un gran número de ellos simultáneamente. Utilizando segmentos del genoma, portando los sitios polimórficos, depositados en un microarreglo, se podría genotipar un individuo para todos y cada uno de los marcadores existentes. Tal resolución no se ha alcanzado aún, pero los microarreglos más utilizados son actualmente capaces de establecer el genotipo de un individuo para 500.000 marcadores, esto es en promedio un marcador cada 7 Kb en el genoma humano. Estos marcadores de tipo SNPs también pueden ser utilizados para mapeo analizando si se heredan ligados a un rasgo en estudio. En estudios en los cuales se busca la asociación de alelos específicos con rasgos complejos, esta resolución es más que suficiente considerando que 1 centimorgan en el genoma humano equivale aproximadamente a 750 Kb. Los pasos necesarios para el genotipado usando un microarreglo son los siguientes (Figura 2): 1) Digestión del genoma con una o más enzimas de restricción, generando fragmentos de tamaño diverso con extremos "pegajosos". 2) Ligado de los fragmentos con un "adaptador" de secuencia única. Esta secuencia única es complementaria con un cebador universal que se empleará en el paso siguiente. 3) Amplificación por PCR con cebador universal. Por las condiciones elegidas para la reacción, la PCR amplificará fragmentos de hasta aproximadamente 1 Kb, portando sitios polimórficos del genoma incluidos en el diseño del microarreglo. Los fragmentos de mayor tamaño no amplifican, con lo cual se reduce la complejidad de la muestra de los 10 millones de SNPs existentes a los 500.000 incluidos en el microarreglo. 4) Reducción del tamaño de los fragmentos amplificados: para aumentar la eficiencia de la hibridación, se digieren los fragmentos amplificados a aproximadamente 100 pares de bases empleando DNAsa I. 5) Se realiza la hibridización de los fragmentos portadores de SNPs, que llevan una señal luminiscente, al microarreglo. Para cada sitio polimórfico, hay cuatro oligonucleótidos presentes en el microarreglo: Dos con complementariedad perfecta (perfect match) con los alelos A y B, y dos portando diferencias de bases (mismatches) con ambos alelos, que sirven como control de hibridación inespecífica para calibrar la señal de hibridación con las sondas correctas: 6) Lectura de la señal luminiscente en cada uno de los conjuntos de oligonucleótidos y determinación del genotipo del individuo para cada SNP. Figura 2: Pasos en el genotipado usando microarreglos. Ejercicio 4 Suponga que el panel mostrado a continuación representa la lectura de un sector del microarreglo hibridado con fragmentos de ADN obtenido de un individuo para caracterizar su genotipo para numerosos SNPs. Indique el genotipo del individuo analizado para los genes que se leen en la figura. Estudios de asociación a nivel genómico Uno de los usos actuales más importantes de las plataformas de genotipado masivo es el de estudios de asociación a nivel de genoma (Genome‐Wide Association Studies o GWAS). En estos estudios, se busca la asociación positiva de ciertos alelos o genotipos con enfermedades, a través de estudios caso‐control. El o los alelos con los cuales se observa una asociación positiva pueden ser variantes que se encuentran dentro de genes, o variantes ligadas a alelos de genes candidatos a tener algún rol en el desarrollo de la enfermedad. El GWAS se basa en el genotipado masivo y comparado de grandes números de casos y controles, y al trabajar con el genoma completo, constituye un análisis exploratorio, libre de hipótesis, a partir de cuyos resultados se pueden hacer análisis más específicos. Hasta 2008 se habían identificado 100 loci asociados a 40 enfermedades comunes de características complejas. El riesgo relativo de contraer una enfermedad en presencia de una variante dada se mide empleando la relación de chances u odds ratio (OR), que se define como: OR = p/q p⋅s ⇒ OR = r/s r ⋅q Donde: p = frecuencia de casos que tienen el factor (en este caso, el alelo) estudiado q = frecuencia de controles con el factor r = frecuencia de casos que no tienen el factor s = frecuencia de controles sin el factor Un OR de 1 implica que no hay asociación del factor con la enfermedad. Un OR mayor que 1 indica una asociación positiva, y establece una cuantificación relativa de la asociación. Por ejemplo, en 2007 un análisis en busca de polimorfismos asociados a diabetes tipo 2 halló asociación significativa entre dicha enfermedad y uno de los alelos de un SNP. Este marcador se encuentra ubicado en el cromosoma 10 y cercano al gen TCFL2 Genotipo Fenotipo CC TC TT Diabéticos 876 (35,1%) 1215 (48,6%) 408 (16.3%) No diabéticos 1417 (49,7%) 1194 (41,9%) 238 (8,4%) Puede observarse que la proporción de diabéticos que portan el alelo T en el SNP asociado a TCFL2 es mayor que la proporción de controles, por lo que el alelo T estaría asociado a la enfermedad. Ahora bien, para cuantificar hasta qué punto portar el alelo T aumenta la propensión a la diabetes, se calcula el OR de cada tipo de portador respecto a los homocigotas CC: Riesgo relativo de los heterocigotas: OR = 0,486 / 0,419 1,16 = = 1,64 0,351 / 0,497 0,706 Riesgo relativo de los homocigotas TT: OR = 0,163 / 0,084 1,94 = = 2,75 0,351 / 0,497 0,706 Esto implica que un heterocigota tiene una probabilidad 64% mayor de desarrollar diabetes tipo 2 que un homocigota CC. El homocigota TT tiene 175% más de probabilidad, es decir, más del doble que la probabilidad del homocigota CC. Ahora bien, en términos generales, la probabilidad que tiene el homocigota CC de volverse diabético es aproximadamente equivalente a la prevalencia de la enfermedad en la población general. Por ejemplo, en Estados Unidos se calcula que el 7,8% de la población adulta tiene diabetes tipo 2. Pero si un individuo dado porta el alelo asociado, esa probabilidad aumenta a 1,64 * 7,8 = 12.79% si es heterocigota, y 2.75 * 7,8 = 21,45% si es homocigota TT. Esta es una aproximación simplificada de los cálculos precisos, ya que en el 7,8% de individuos enfermos están presentes los tres genotipos. No obstante, sirve para dar una idea de la interpretación del Odds‐Ratio. Ha de señalarse, sin embargo, que la mayor parte de los OR de SNPs asociados a enfermedades son bastante más modestos. Ejercicio 5 Los siguientes datos relacionan, en forma estadísticamente significativa, un SNP ubicado en el cromosoma 8 con cáncer de colon. Genotipos Alelos C T Casos 875 675 Casos 1940 Controles 1860 CC CT TT 250 375 150 Controles 460 940 500 a) ¿Cuál de los alelos está positivamente asociado con la enfermedad? b) Calcule el OR de los homocigotas para el alelo contra los homocigotas para el alelo alternativo, y el OR de los heterocigotas contra los homocigotas para el alelo alternativo. ¿Cuál es el aumento en las probabilidades en cada caso? II. ORGANISMOS GENETICAMENTE MODIFICADOS Los Organismos Genéticamente Modificados (OGM) son organismos transgénicos. Esto quiere decir que mediante procedimientos de biología molecular, se ha adicionado o introducido a su genoma uno o varios genes de una especie diferente. Normalmente estos genes son clonados en plásmidos u otros vectores de ADN y se los liga a promotores que aseguran altos niveles de expresión. En el caso de las plantas transgénicas, los intermediarios más utilizados son bacterias del género Agrobacterium, debido a que son muy eficientes introduciendo nuevos genes en un amplio rango de especies vegetales de la clase de las dicotiledóneas, aunque se utilizan también otras bacterias y virus. En la naturaleza Agrobacterium tumefaciens se adsorbe a las células de la planta e introduce un plásmido inductor tumoral (Ti). Este plásmido de ADN recombina entonces con el ADN nuclear de la célula vegetal hospedadora, generando en última instancia la formación tumoral. Los plásmidos Ti son manipulados para incorporar nuevos genes, esta metodología es la base de la mayoría de los trabajos con plantas genéticamente modificadas (ver figura). En la figura se esquematiza el proceso de generación del plásmido recombinante y posterior transformación genética de cultivos celulares vegetales, en este caso con un gen de resistencia al herbicida glifosato. Tomado de Beebee T, Rowe G (2008) An Introduction to Molecular Ecology Oxford University Press, Oxford. Los primeros organismos genéticamente modificados que se desarrollaron fueron bacterias. Así pueden crearse bacterias genéticamente modificadas para degradar sustancias contaminantes como derrames de petróleo en el mar o prevenir la acumulación de pesticidas en los suelos. En las plantas los genes introducidos son expresados en una variedad de tejidos dependiendo del objetivo del experimento. Es así como se ha desarrollado resistencia a herbicidas e insectos, aumento o alteración en la productividad de los cultivos o tolerancia a factores ambientales como puede ser la helada. En algunos casos la modificación persiste solamente por una generación ya que se incluye un factor de esterilidad que previene la reproducción, pero frecuentemente la novedad genética es heredable de la manera usual. Una gran variedad de microbios, plantas (incluyendo casi todos los cultivos) y animales han sido sujetos de modificaciones genéticas. Cada vez son más importantes los debates sobre los OGM, especialmente en plantas, y no hay duda de que esta discusión continuará en el futuro. Si bien esta discusión escapa a los cometidos del curso, los avances tecnológicos recientes han determinado que los OGM tengan un gran atractivo como un método de generar nuevas variedades de plantas económicamente más rentables. Sin embargo existen potenciales amenazas: ‐ Los OGM podrían dispersarse más allá de sus regiones de cultivo y competir con las especies silvestres no modificadas. ‐ Los nuevos genes podrían transferirse a otras especies y preocupa los efectos directos que puedan tener sobre éstas. ‐ La actividad de los genes introducidos podría afectar a especies que interaccionan con los OGM (por ej. predadores y consumidores) El hecho de que los OGM difieran de las variedades parentales solamente en uno o unos pocos genes no significa que monitorear los OGM sea algo sencillo. Es por ello que está teniendo un rol clave el desarrollo de marcadores genéticos para los estudios sobre OGM y su interacción con las comunidades naturales. Un aspecto muy relevante en relación a los OGM y su interacción con las comunidades naturales son los aspectos relacionados con el flujo génico de un OGM en relación a otros organismos. Los genes pueden moverse por transmisión normal (vertical) por hibridización de un cultivo genéticamente modificado con una planta silvestre o por transmisión horizontal. La transmisión vertical implica el proceso de división celular (en procariotas) o reproducción sexual (en eucariotas), estos mecanismos son bien conocidos y no es necesario profundizar en ellos. La transmisión horizontal es menos conocida pero potencialmente muy importante. La Transferencia Genética Horizontal (TGH) es la transmisión de información genética entre generaciones contemporáneas de organismos y puede ser intra o interespecífica. Como la TGH no requiere de un tiempo de generación puede diseminar genes muy rápidamente en el medio ambiente. Una línea de evidencia sobre la existencia de la TGH viene de la filogenética molecular, como es el hallazgo de secuencias de ADN que parecen estar fuera de lugar, por ejemplo un típico gen bacteriano que es encontrado en un eucariota o vice‐versa. El gen eucariota de la gliceraldehído 3‐fosfato deshidrogenasa (Gapdh) aparece en algunas cepas de E. coli que también hospeda a un gen reconocible como procariota para la Gapdh. El análisis genómico de E. coli sugiere que al menos el 17 por ciento de sus genes han sido adquiridos por THG en más de 200 eventos independientes. Entonces, si bien la frecuencia de la THG difiere entre distintas clases de organismos, la evidencia actual sugiere un patrón complejo donde las bacterias tienen un rol protagónico. Sin embargo, hasta el momento, el análisis del genoma humano sugiere que por lo menos para esta clase de organismos eucariotas superiores la transferencia de genes por medio de la THG es probablemente muy rara. La existencia de OGM mediante técnicas de ADN recombinante plantea el riesgo de la dispersión de la cepa modificada más allá del control humano, mediante alguna de estas formas de transferencia genética. Ejercicio 6 Usted es designado por un agricultor orgánico para determinar si un cultivo de frutillas está sufriendo contaminación genética. La preocupación surge porque en el área circundante al agricultor existen establecimientos donde crecen frutillas modificadas por la adición de un gen único, que produce un aumento en la tolerancia a la helada. Esquematice los pasos a seguir para investigar este problema, asumiendo la cooperación del productor de frutillas genéticamente modificadas. Ejercicio 7 A partir de la lectura de ”Maíz transgénico en Uruguay” páginas 26‐36, responda grupalmente las siguientes preguntas: ¿Qué eventos de maíz transgénico se autorizaron en Uruguay y qué genes contienen? ¿Cuáles son las condiciones para su uso y por qué éstas son difíciles de cumplir por los productores hortícolas? ¿Qué se propone la nueva Ley de Bioseguridad de OGM? ¿Qué es la contaminación genética y cómo se intenta evitarla? Bibliografía consultada y material complementario Beebee T, Rowe G (2008) An Introduction to Molecular Ecology. Oxford University Press, Oxford Campbell AM, Zanta CA, Heyer LJ, Kittinger B, Gabric KM, Adler L, Schulz B (2006) DNA microarray wet lab simulation brings genomics into the high school curriculum. CBE Life Sci Educ 5(4):332‐339 Material de apoyo a organismos genéticamente modificados: http://cls.casa.colostate.edu/CultivosTransgenicos