Un operón es un conjunto de genes bacterianos que se co
Anuncio

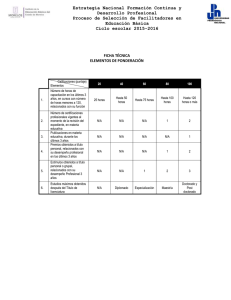
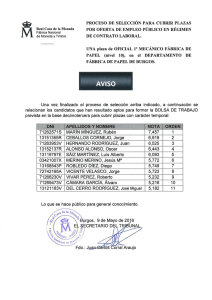
Tit PREDICCION DE OPERONES BACTERIANOS Y REDES DE REGULACIÓN Enrique Merino En años recientes hemos sido testigos del crecimiento vertiginoso de información proveniente del análisis de metodologías genómicas. En la presentación de grupo incluiremos como ejemplo de nuestro trabajo, una breve descripción de dos líneas de investigación referentes a una nueva estrategia que hemos desarrollado para predecir operones bacterianos, así como un análisis de redes de regulación en dos organismos modelo. Predicción de operones bacterianos de forma sencilla y precisa. Un operón es un conjunto de genes bacterianos que se co-transcriben en una misma molécula de RNA. Debido a la importancia biológica de los operones en coordinar la expresión de genes que se encuentran metabólica o funcionalmente relacionados, distintos protocolos de cómputo han sido ideados para su identificación in silico. En principio, los genes que pertenecen a un operón podrían ser definidos si los elementos de regulación que delimitan el inicio (promotor) y el final de la transcripción (terminator) de las unidades transcripcionales pudieran ser identificados. No obstante, la capacidad actual para determinar computacionalmente promotores y terminadores transcipcionales de manera precisa está restringida a elementos canónicos, por lo que otras características genómicas han tenido que ser consideradas para la identificación in silico de operones, entre las que se encuentran: i) la dirección de transcripción de los genes, ii) las distancias intergénica de genes contiguos, iii) el patrón de expresión génica evaluados a partir del análisis de microarreglos, iv) relaciones funcionales de las proteínas codificadas por los genes del operón, v) conservación de vecindad genética y vi) perfiles filogenéticos. A pesar de este gran conjunto de variables utilizadas en la predicción in silico de operones y a las diferentes mejoras en los métodos matemáticos empleados en dichos análisis, la capacidad predictiva de operones en E. coli, el organismo bacteriano mejor caracterizado, es del orden de 93% y decrece entre 10% y 30% en la predicción de operones de otros organismos. En nuestro grupo hemos desarrollado una metodología de sencilla aplicación que solamente considera dos parámetros, la distancia intergénica de los genes y el valor de la relación funcional entre grupos de proteínas ortólogas definidas en la base de datos STRING (Jensen et al., 2009) para determinar con una precisión la estructura de operones en genomas bacterianos. La precisión alcanzada por nuestro método es del 95% para operones de Escherichia coli y 93% para operones de Bacillius subtilis. Hasta donde sabemos, esta es la precisión más grande lograda en la predicción de operones por métodos bioinformáticos. Estudiando la regulación de la transcripción de una manera global Una de las líneas de interés en las que nuestro ha trabajado recientemente versa en la construcción de modelos de regulación transcripcional en diferentes organismos modelo. Para tal fin, hemos empleado la llamada Teoría de Redes que nos permite entender a las diferentes relaciones entre los factores transcripcionales y sus genes regulados, como una compleja red de interacciones cuya estructura topológica nos permite elucidar algunas de las propiedades de la fisiología del organismo de estudio. En una primera instancia, nuestros trabajo se ha enfocado al estudio de las redes de regulación de Escherichia coli y Bacillus subtilis, organismos modelo representantes de las bacterias Gram negativas y Gram positivas, respectivamente. Nuestro estudio realizado en Bacillus subtilis, consideró una sección de la red de regulación transcripcional que responde a cambios en la fuente de carbono, tomando como base los resultados de la expresión de los genes en medio LB enriquecido con glucosa, cuantificados mediante microarreglos. Desde el punto de vista de la Teoría de Redes, el análisis de la subred construida mostró que está posee propiedades libres de escala, presentando una organización jerárquico-modular, compuesta por 9 módulos discretos funcionalmente relacionados con procesos celulares tales como la represión catabólica, esporulación, reparación del DNA, sistema SOS y competencia, entre otros. Los resultados de B. subtilis, fueron comparados con nuestro trabajo previo en Escherichia coli, en donde encontramos 8 módulos también funcionalmente relacionados. La comparación demostró que la respuesta regulatoria a glucosa está parcialmente conservada en funciones generales como transcripción, traducción y replicación, así como en genes relacionados con el metabolismo central (Vázquez-Hernández C, 2009). Siguiendo esta misma línea de trabajo, y en base a los datos reportados en la literatura, nos dimos a la tarea estudiar la red de factores trancripcionales de Bacillus subtilis y definir sus propiedades topológicas. Los resultados mostraron una red jerárquico modular con 9 módulos funcionalmente relacionados cuyos elementos pudieran estar regulados de manera redundante. Los módulos mostraron además no ser totalmente independientes ni completamente homogéneos, lo que es el reflejo de la manera en que los componentes de la célula están conectados y de cómo una función tiene influencia sobre otra (Manjarrez-Casas A. 2009). Empleando el enfoque de descomposición natural recientemente propuesto por Freyre-González (2008) se hizo un análisis de la red completa conocida para Bacillus subtilis. Nuestros resultados muestran que a pesar de su distancia filogenética, Bacillus subtilis posee la misma arquitectura jerárquico-modular no piramidal revelada para Escherichia coli, compuesta por 19 factores de transcripción globales gobernando a 90 módulos independientes cuyas respuestas se integran a nivel promotor por 42 genes intermodulares. Al igual que en el caso de Escherichia coli, mediante una metodología matemática conocida como valor kappa, se identificó a los factores de transcripción globales, recuperando así 6 previamente descritos en la literatura, 8 de 14 factores sigma, más 5 predicciones. Además, se identificó y clasificó a los factores de transcripción de acuerdo a su jerarquía dentro de la red. Finalmente, se ha iniciado el análisis de la red de regulación transcripcional de levadura. Los resultados de análisis topológicos sugieren que esta red exhibe propiedades que aparentemente permiten catalogarla como jerárquico-modular. Sin embargo, la presencia de un bajo valor de agrupamiento en nodos participando en pocas interacciones regulatorias indica que esta red puede seguir principios de organización diferentes a aquellos gobernando a las redes de regulación de procariontes. Referencias.Jensen, L.J. et al. (2009) Nucleic Acids Res., 37, D412-D416 Freyre-González JA, et al., (2008) Genome Biol. 9:R154. Vázquez CD, et al., (2009) . BMC Microbiol. 9:176. Manjarrez Casas A. Tesis de licenciatura 24 de Agosto de 2009. A. Integrantes del Grupo Personal Académico Dr. Enrique Merino Pérez Dra. Rosa Ma. Gutiérrez Ríos Dr. Alejandro Garciarubio Granados M.B. Ma. Luisa Tabche Barrera MC. José Ricardo Ciria L.I. Nancy Mena Ocampo M.C. José Antonio Loza Román Lic. Karel Estrada Guerra. Biol. Tobías Portillo Bobadilla Dr. Fidel Alejandro Sánchez Flores Investigador Titular Investigador Asociado Investigador Asociado Técnico Académico Técnico Académico Técnico Académico Técnico Académico Técnico Académico Técnico Académico Técnico Académico Estancias postdoctorales Dr. Julio Augusto Freyre González y Dr. Raúl Noguez Moreno Estudiantes Lic. Ana Lucia Gutiérrez Preciado Lic. Zuemy Rodríguez Escamilla Lic. Viridiana Ávila Magaña M.C. Blanca Itzel Taboada Ramírez M.C. Mario Alberto Martínez Núñez M.C. José Alfredo Morales Pablos MC. Patricia Oliver Ocaño M.C. Eugenio López M.C. José Luis Rodríguez Mejía MC Juan Manuel Hurtado Ramírez Ing. Christian Eduardo Martínez Guerrero L.I. Alma lidia Martínez Valle Lic. Carlos Daniel Vázquez Hernández Lic. Alejandra Mayela Manjarrez Casas Javier Morales Barrera Alejandro Granados Ilse Ariadna Valtierra Gutierrez Doctorado Doctorado Doctorado Doctorado Doctorado Doctorado. Doctorado Doctorado Doctorado Doctorado Maestría Maestría Maestría Licenciatura Licenciatura Licenciatura Licenciatura Personal administrativo Rosalva González Apoyo Administrativo B. Productividad primaria 1.- Martinez-Nunez,M.A. Pérez-Rueda,E. Gutierrez-Rios,R.M. Merino,E. 2009. New insights into the regulatory networks of paralogous genes Microbiology Oct 22. [Epub ahead of print] . 2.- Vazquez,C.D. Freyre-Gonzalez,J.A. Gosset,G. Loza,J.A. Gutierrez-Rios,R.M. 2009. Identification of network topological units coordinating the global expression response to glucose in Bacillus subtilis and its comparison to Escherichia coli. BMC Microbiol 9: 176. 3.- Qu,Y. Brown,P. Barbe,J.F. Puljic,M. Merino,E. Adkins,R.M. Lovley,D.R. Krushkal,J. 2009. GSEL version 2, an online genome-wide query system of operon organization and regulatory sequence elements of Geobacter sulfurreducens. OMICS 13: 439-449. 4.- De la Cruz,M.A. Merino,E. Oropeza,R. Tellez,J. Calva,E. 2009. The DNA static curvature has a role in the regulation of the ompS1 porin gene in Salmonella enterica serovar Typhi Microbiology. 155: 2127-2136. 5.- Romero-Garcia,S. Hernandez-Bustos,C. Merino,E. Gosset,G. Martinez,A. 2009. Homolactic fermentation from glucose and cellobiose using Bacillus subtilis. Microb Cell Fact 8: 23 6.- Verleyen,J. Hurtado-Ramirez,J.M. Merino-Perez,E. 2009. Meta-Dock, a gridification of a docking application Proceedings of the First EELA-2 147-153. 7.- Gutierrez-Preciado,A. Henkin,T.M. Grundy,F.J. Yanofsky,C. Merino,E. 2009. Biochemical Features and Functional Implications of the RNA-Based T-Box Regulatory Mechanism. Microbiol. Mol. Biol .Rev. 73: 36-61. 8.- Cevallos,M.A. Cervantes-Rivera,R. Gutierrez-Rios,R.M. 2008. The repABC plasmid family. Plasmid 60: 19-37. 9.- Martinez-Guerrero,C.E. Ciria,R. Abreu-Goodger,C. Moreno-Hagelsieb,G. Merino,E. 2008. GeConT 2: gene context analysis for orthologous proteins, conserved domains and metabolic pathways. Nucleic Acids Res. 36 (Web Server issue) W176W180. 10.- Merino,E. Jensen,R.A. Yanofsky,C. 2008. Evolution of bacterial trp operons and their regulation. Curr .Opin. Microbiol. 11: 78-86. 11.- Gama-Castro,S. Jimenez-Jacinto,V. Peralta-Gil,M. Santos-Zavaleta,A. PenalozaSpinola,M.I. Contreras-Moreira,B. Segura-Salazar,J. Muniz-Rascado,L. MartinezFlores,I. Salgado,H. Bonavides-Martinez,C. Abreu-Goodger,C. Rodriguez-Penagos,C. Miranda-Rios,J. Morett,E. Merino,E. Huerta,A.M. Trevino-Quintanilla,L. ColladoVides,J. 2008. RegulonDB (version 6.0): gene regulation model of Escherichia coli K12 beyond transcription, active (experimental) annotated promoters and Textpresso navigation. Nucleic Acids Res 36: (Database issue) D120-D124. 12.- Rodríguez-Magadan,H. Merino,E. Schnabel,D. Ramirez,L. Lomeli,H. 2008. Spatial and temporal expression of Zimp7 and Zimp10 PIAS-like proteins in the developing mouse embryo Gene Expr.Patterns 8 206-213. 13.- Flores,N. Escalante,A. de Anda R. Baez-Viveros,J.L. Merino,E. Franco,B. Georgellis,D. Gosset,G. Bolivar,F. 2008. New Insights into the Role of Sigma Factor RpoS as Revealed in Escherichia coli Strains Lacking the Phosphoenolpyruvate: Carbohydrate Phosphotransferase System. J. Mol. Microbiol Biotechnol. 14: 176-192. Alumnos recibidos Patricia Oliver Ocaño. Tesis de Maestría en Ciencias Bioquímicas. UNAM. Análisis de operones divergentes conservados en procariontes para la identificación de potenciales sitios de unión de a factores transcripcioneles. Fecha de titulación: 22 de enero 2008. Viridiana Ávila Magaña. Tesis de licenciatura. Facultad de Ciencias. UNAM. Termoriboswitches: Moléculas de RNA regulatorias responsivas a temperatura. Fecha de titulación: 27 de Agosto 2009. Alejandra Mayela Manjarrez Casas. Tesis de licenciatura. Facultad de Ciencias. UNAM. Análisis topológico de la red de Regulación transcripcional de Bacillus subtilis Fecha de titulación: 20 de Agosto 2009. C. Actividades Docentes Tópico Selecto. Doctorado en Ciencias Bioquímicas. Responsables: Pérez Rueda E. Gutierre-Rios RM y Merino Pérez E. Métodos y Estrategias en Bioinformática.. 6 de Febrero 2008 – 23 Mayo 2008 Tópico Selecto. Doctorado en Ciencias Bioquímicas. Responsable. Merino Pérez E. Lenguaje Perl para aplicaciones en bioinformática. 13 de Agosto al 25 de Noviembre de 2009 Tópico Selecto. Doctorado en Ciencias Bioquímicas. Responsables. Rueda E. Gutierre-Ríos RM y Merino Pérez E. Métodos y Estrategias en Bioinformática. 6 de Febrero 2009 – 22 de Mayo 2009. Tópico Selecto. Doctorado en Ciencias Bioquímicas. Responsable. Gutierre-Rios RM. Lenguaje Perl para aplicaciones en bioinformática. 13 de Agosto al 25 de Noviembre de 2009. D. Fuentes de Financiamiento -CONACyT: 60127 Proyecto Dr. Enrique Merino "Identificación in silico y caracterización molecular, estructural y cinética de elementos de regulación de la expresión genética basada en riboswitches". -CONACyT: 58840 Proyecto Dra. Rosa Ma. Gutierrez "Generación y comparación de modelos de regulación transcripcional para la red de Escherichia coli y Bacillus subtilis y su consistencia con análisis de datos de expresión global y experimentos de PCR en tiempo real". -CONACyT Salud : 68992Proyecto Dr. Enrique Merino "Riboswitches como blancos de nuevos agentes antimicrobianos" -DGAPA: IN215808 Proyecto Dra. Rosa Ma. Gutiérrez "Generación de modelos de regulación de la transcripción en Bacillus subtilis y Escherichia coli, análisis comparativo y su corroboración experimental". -DGAPA: IN212708 Proyecto Dr. Enrique Merino "Análisis de curvatura estática del DNA genomas y metagenomas. E. Distinciones. Merino Pérez Enrique. Reingreso vigente al Sistema Nacional de Investigadores con el nombramiento de SNI nivel III para el periodo de enero del 2010 al 31 de diciembre del 2013. Otorgado el 1 de Septiembre de 2009. Merino Pérez Enrique. Programa de Primas al Desempeño del Personal Académico de Tiempo Completo. Con nivel D. Gutiérrez Ríos Rosa María. Reingreso vigente al Sistema Nacional de Investigadores con el nombramiento de Candidato a Investigador Nacional, para el periodo de enero del 2008 al 31 de diciembre del 2009. Otorgado el 1 de Septiembre de 2007. Gutiérrez Ríos Rosa María. Reingreso vigente al Sistema Nacional de Investigadores con el nombramiento de SNI nivel 1 para el periodo de enero del 2009 al 31 de diciembre del 2011. Otorgado el 1 de Septiembre de 2008. Gutiérrez Ríos Rosa María. Programa de Primas al Desempeño del Personal Académico de Tiempo Completo. Con nivel B Junio del 2009. Noguez Moreno Raúl. Ingreso al Sistema Nacional de Investigadores con el nombramiento de Candidato a Investigador Nacional para el periodo de enero del 2010 al 31 de diciembre del 2012. Otorgado el 1 de Septiembre de 2009. Freyre González Julio Augusto. Ingreso al Sistema Nacional de Investigadores con el nombramiento de Candidato a Investigador Nacional para el periodo de enero del 2010 al 31 de diciembre del 2012. Otorgado el 1 de Septiembre de 2009.